peptides
spectra
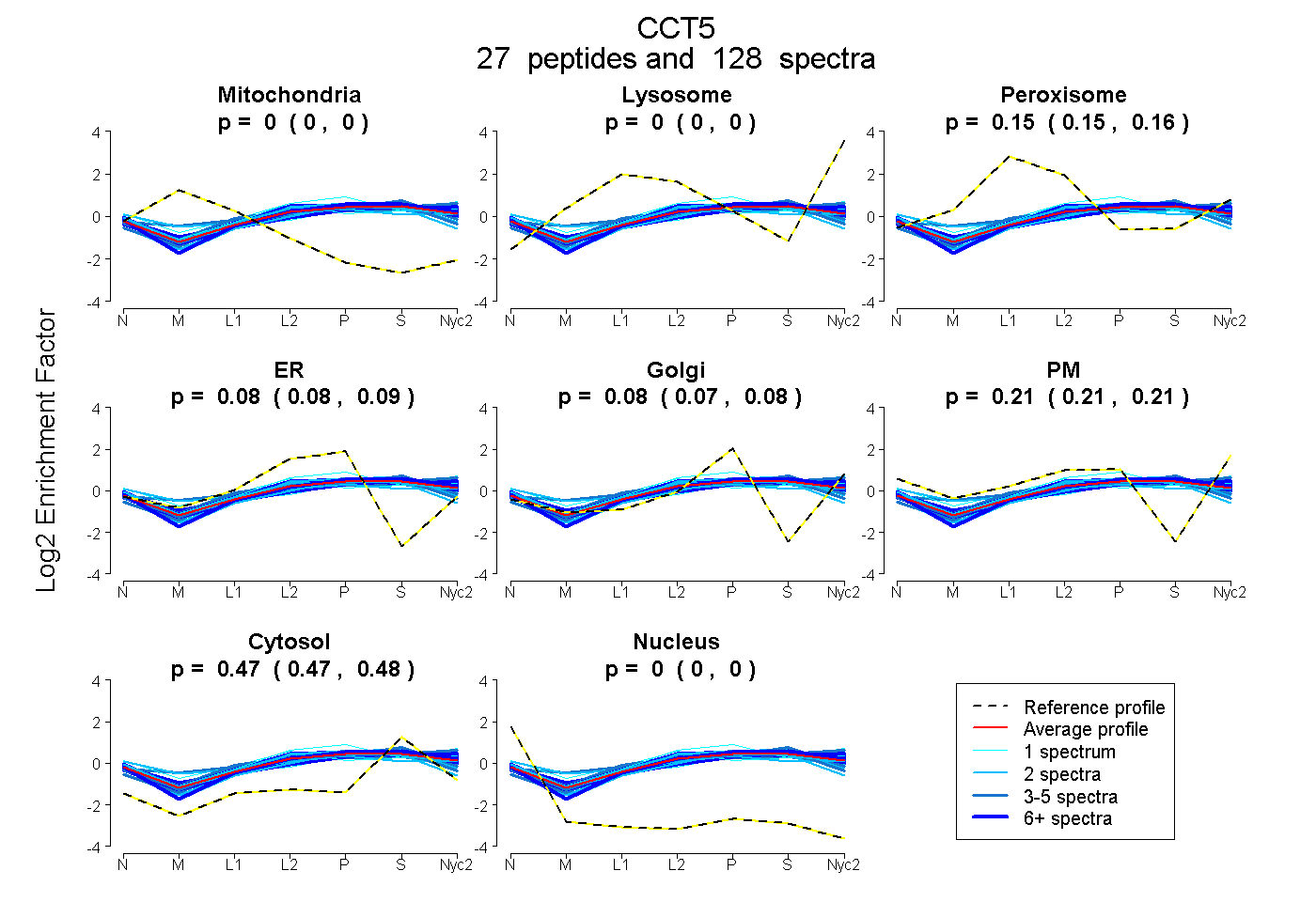
0.000 | 0.000
0.000 | 0.000
0.152 | 0.156
0.078 | 0.086
0.074 | 0.083
0.207 | 0.214
0.473 | 0.476
0.000 | 0.000
peptides
spectra
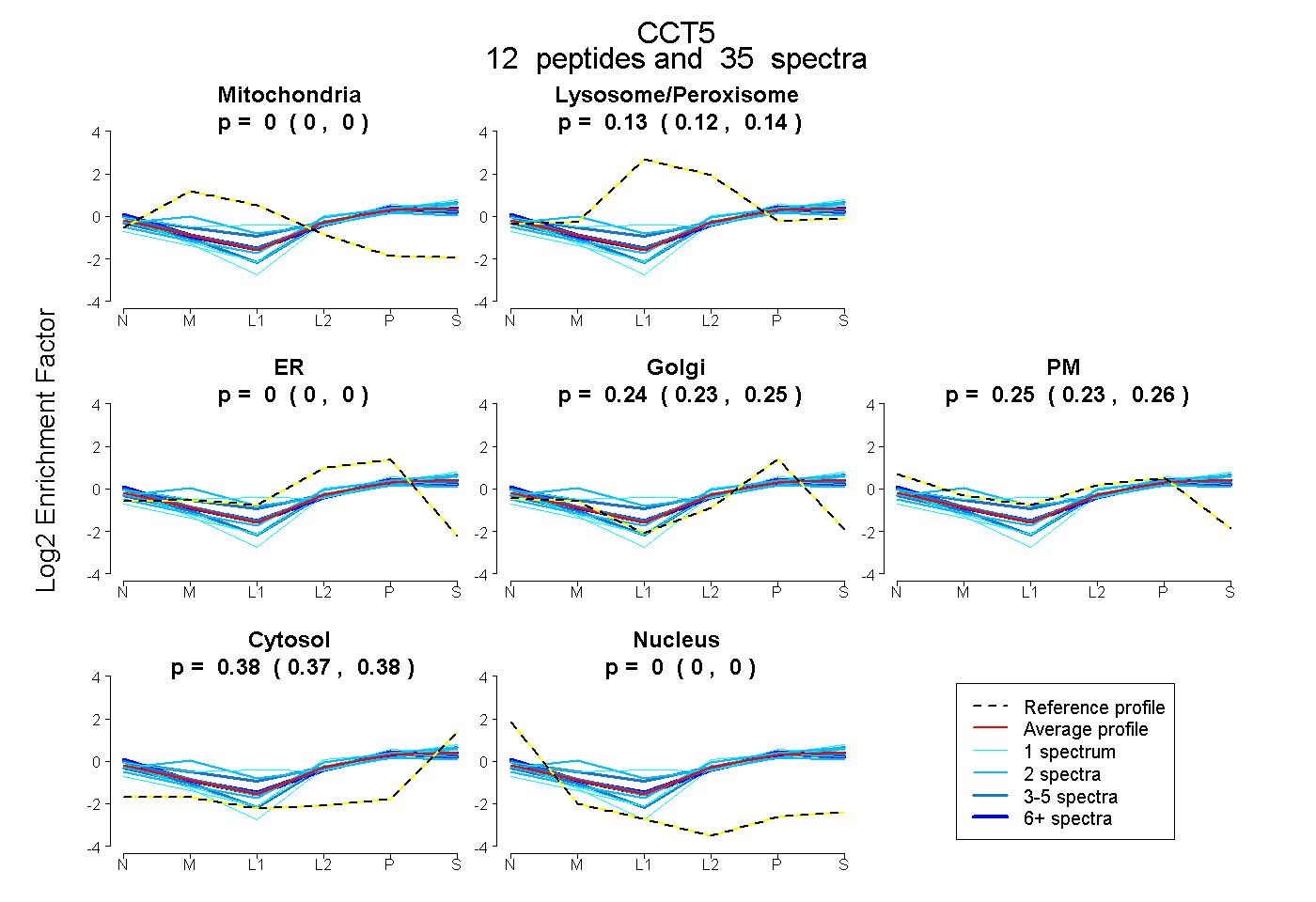
0.000 | 0.000
0.122 | 0.141
0.000 | 0.000
0.230 | 0.251
0.230 | 0.262
0.375 | 0.383
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
128 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.154 0.152 | 0.156 |
0.082 0.078 | 0.086 |
0.079 0.074 | 0.083 |
0.210 0.207 | 0.214 |
0.475 0.473 | 0.476 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.000 0.000 | 0.000 |
0.132 0.122 | 0.141 |
0.000 0.000 | 0.000 |
0.241 0.230 | 0.251 |
0.247 0.230 | 0.262 |
0.379 0.375 | 0.383 |
0.000 0.000 | 0.000 |
| 1 spectrum, FEEMIAQIK | 0.000 | 0.000 | 0.460 | 0.000 | 0.000 | 0.540 | 0.000 | |||
| 1 spectrum, DVDFELIK | 0.000 | 0.000 | 0.116 | 0.110 | 0.322 | 0.453 | 0.000 | |||
| 1 spectrum, TSLGPNGLDK | 0.000 | 0.289 | 0.000 | 0.208 | 0.215 | 0.288 | 0.000 | |||
| 5 spectra, AVANTMR | 0.000 | 0.000 | 0.190 | 0.069 | 0.236 | 0.506 | 0.000 | |||
| 4 spectra, LGFAGVVR | 0.000 | 0.101 | 0.000 | 0.163 | 0.364 | 0.372 | 0.000 | |||
| 6 spectra, AVTIFIR | 0.000 | 0.090 | 0.000 | 0.157 | 0.367 | 0.386 | 0.000 | |||
| 2 spectra, LMGLEALK | 0.000 | 0.095 | 0.310 | 0.103 | 0.026 | 0.466 | 0.000 | |||
| 1 spectrum, LDVTSVEDYK | 0.000 | 0.000 | 0.039 | 0.405 | 0.151 | 0.405 | 0.000 | |||
| 2 spectra, MLVIEQCK | 0.000 | 0.142 | 0.016 | 0.181 | 0.236 | 0.425 | 0.000 | |||
| 7 spectra, IADGYEQAAR | 0.000 | 0.094 | 0.000 | 0.195 | 0.372 | 0.339 | 0.000 | |||
| 2 spectra, QQISLATQMVR | 0.017 | 0.239 | 0.000 | 0.243 | 0.213 | 0.288 | 0.000 | |||
| 3 spectra, GLHPIR | 0.000 | 0.203 | 0.000 | 0.182 | 0.311 | 0.304 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
218 spectra |
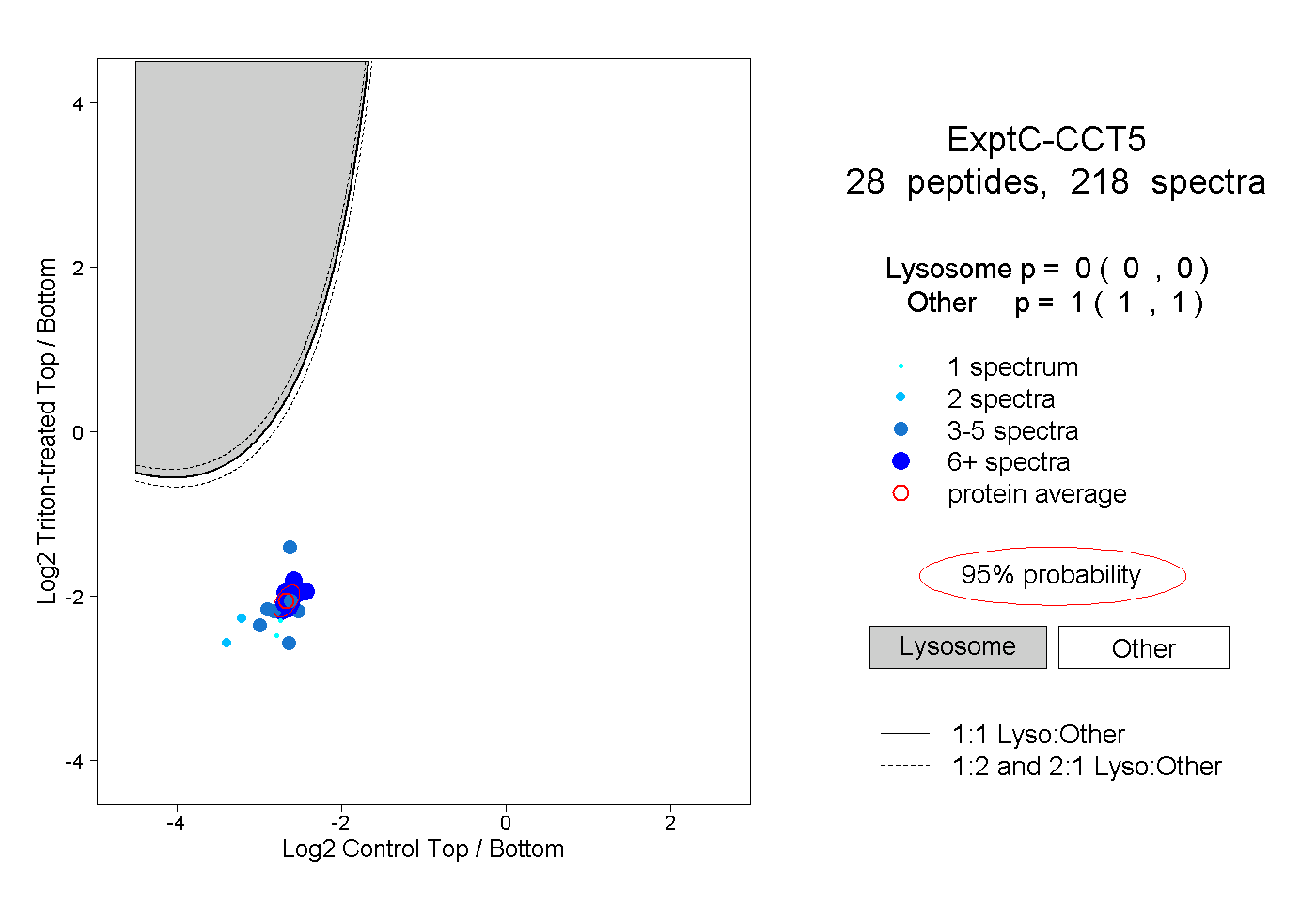 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
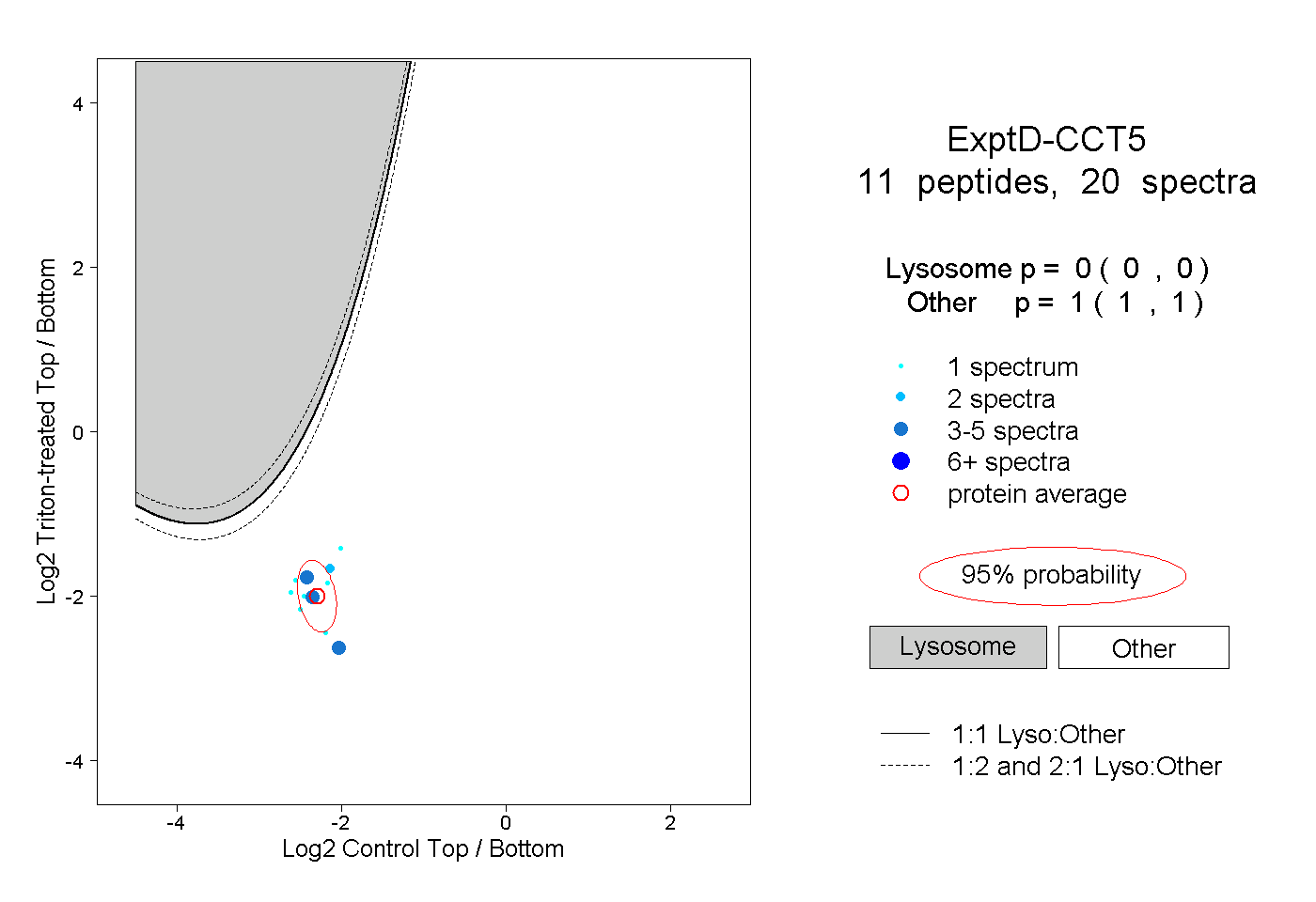 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |