peptides
spectra
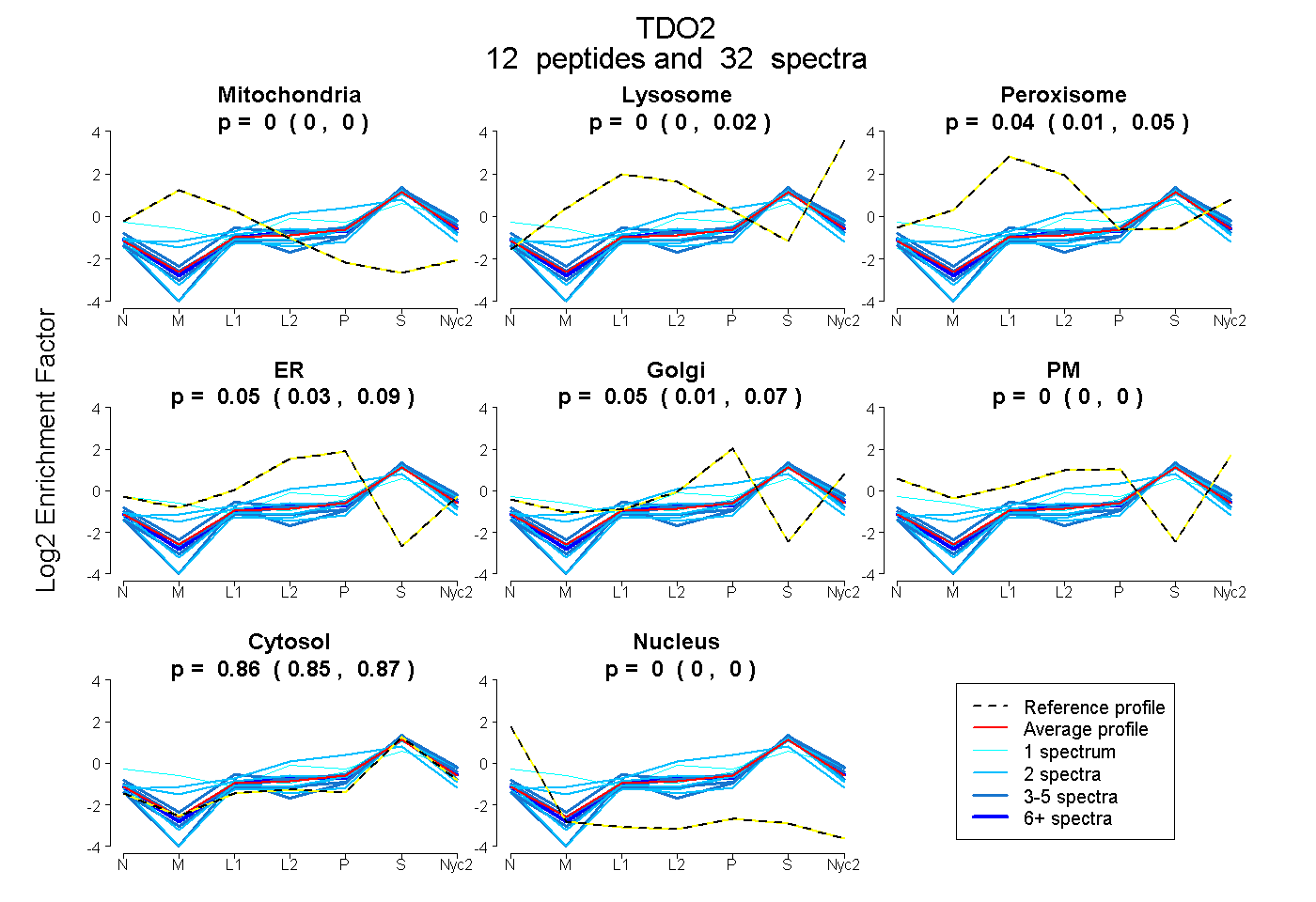
0.000 | 0.000
0.000 | 0.016
0.011 | 0.048
0.029 | 0.091
0.007 | 0.070
0.000 | 0.000
0.846 | 0.866
0.000 | 0.000
peptides
spectra
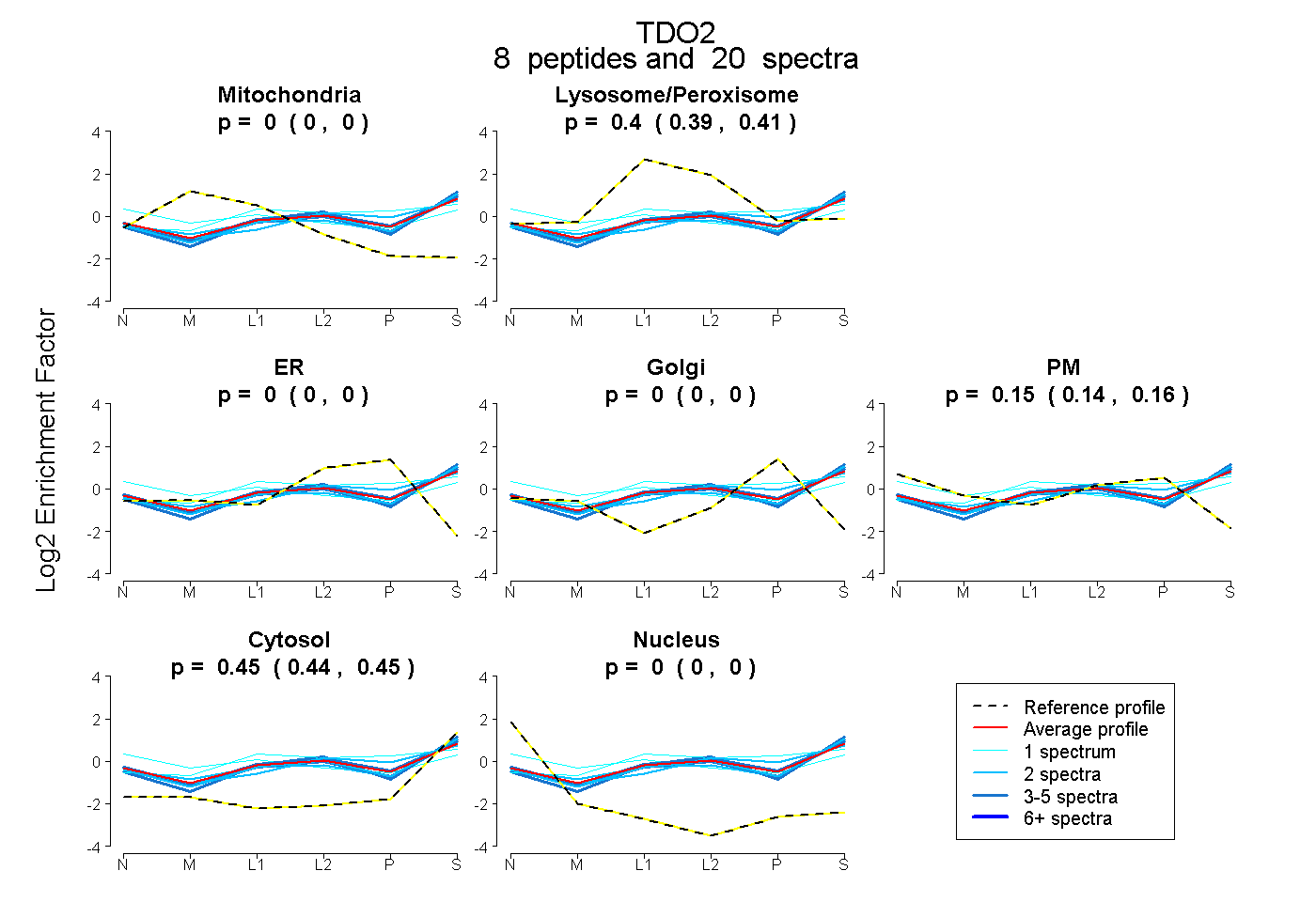
0.000 | 0.000
0.394 | 0.408
0.000 | 0.000
0.000 | 0.000
0.140 | 0.162
0.438 | 0.452
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
32 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.016 |
0.039 0.011 | 0.048 |
0.053 0.029 | 0.091 |
0.052 0.007 | 0.070 |
0.000 0.000 | 0.000 |
0.855 0.846 | 0.866 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.402 0.394 | 0.408 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.153 0.140 | 0.162 |
0.446 0.438 | 0.452 |
0.000 0.000 | 0.000 |
| 1 spectrum, EYLSPASGFQSLQFR | 0.000 | 0.517 | 0.000 | 0.207 | 0.000 | 0.276 | 0.000 | |||
| 2 spectra, ILNAQELQSEIK | 0.000 | 0.353 | 0.013 | 0.115 | 0.122 | 0.396 | 0.000 | |||
| 1 spectrum, EIFQNGHVR | 0.000 | 0.402 | 0.000 | 0.000 | 0.231 | 0.280 | 0.087 | |||
| 2 spectra, GGLIYGDYLQLEK | 0.000 | 0.388 | 0.000 | 0.000 | 0.120 | 0.492 | 0.000 | |||
| 3 spectra, EVLLCLFDEK | 0.000 | 0.462 | 0.000 | 0.000 | 0.018 | 0.521 | 0.000 | |||
| 2 spectra, QILWELDSVR | 0.000 | 0.415 | 0.000 | 0.000 | 0.080 | 0.505 | 0.000 | |||
| 5 spectra, GLEEEFLK | 0.000 | 0.419 | 0.000 | 0.000 | 0.136 | 0.445 | 0.000 | |||
| 4 spectra, IGVLQSLR | 0.000 | 0.402 | 0.000 | 0.000 | 0.103 | 0.494 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
34 spectra |
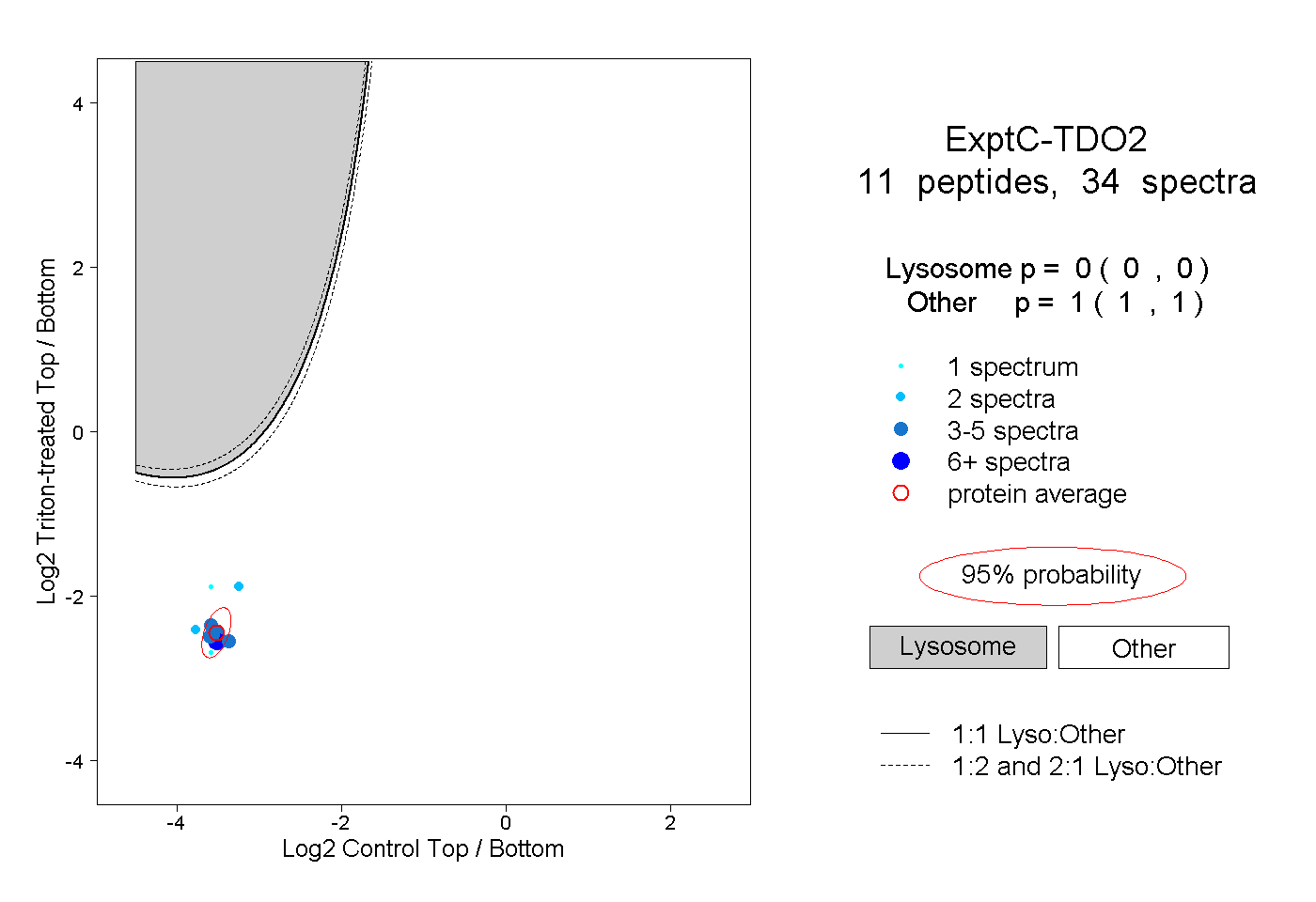 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
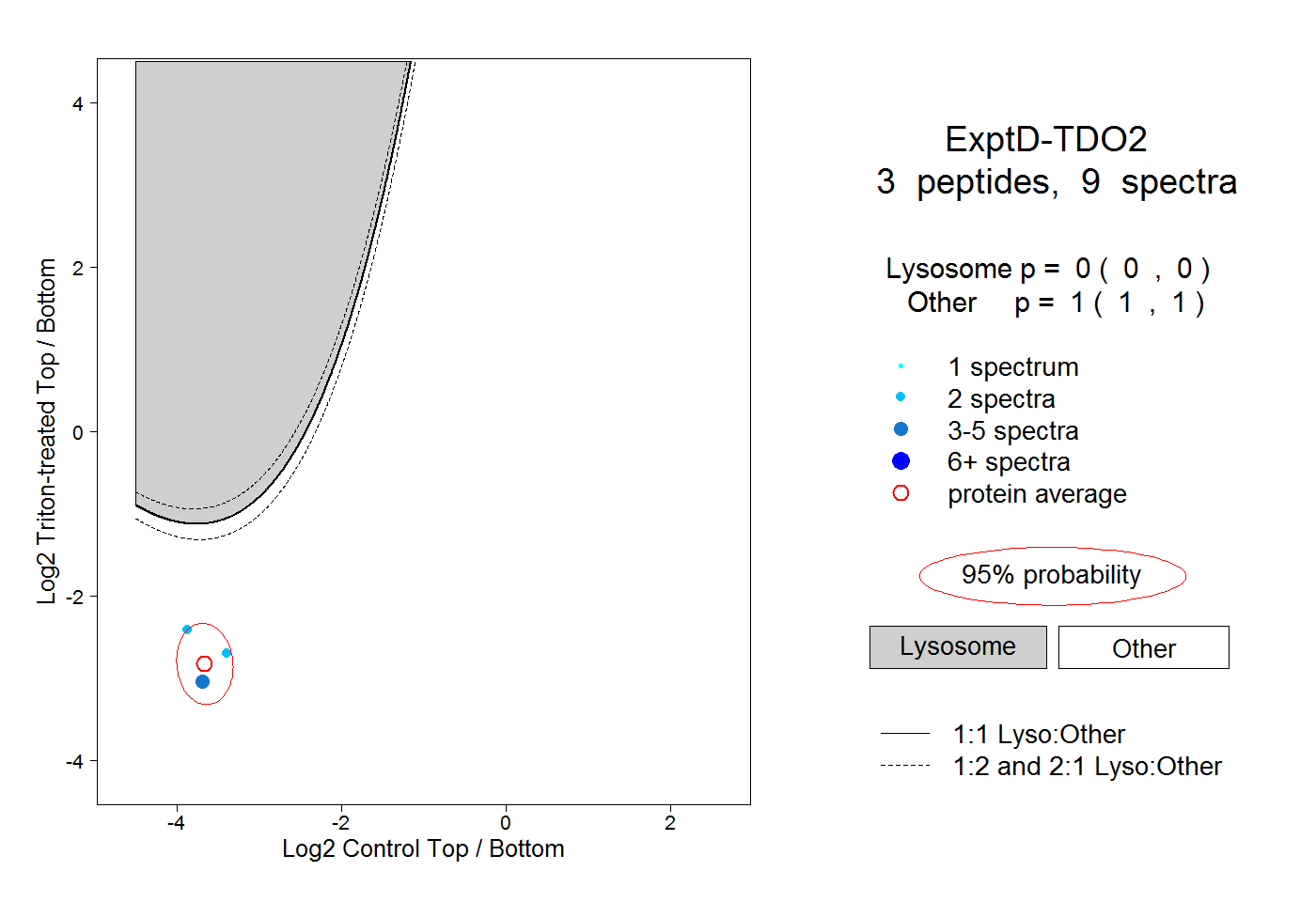 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |