peptides
spectra
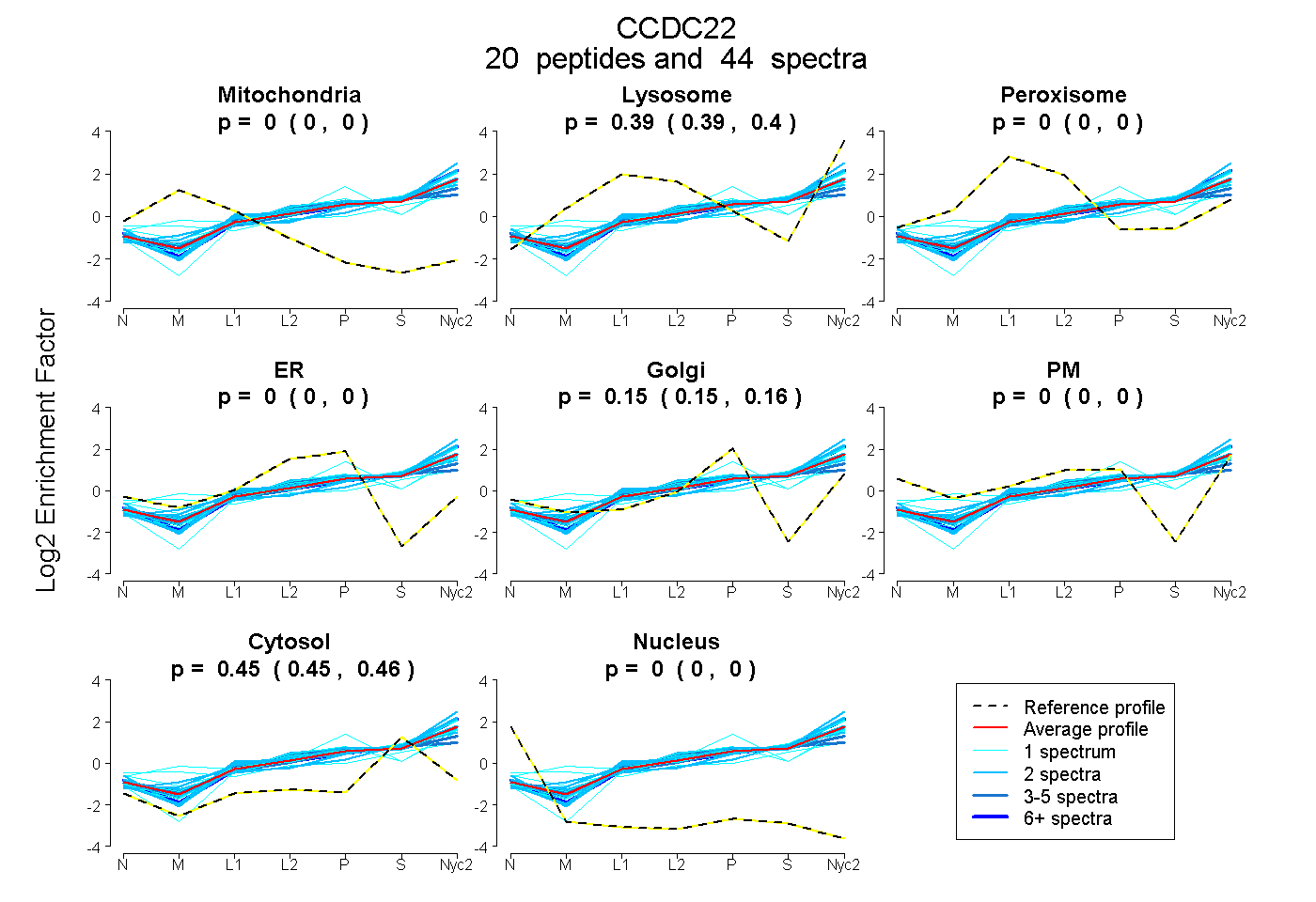
0.000 | 0.000
0.389 | 0.396
0.000 | 0.000
0.000 | 0.000
0.149 | 0.156
0.000 | 0.000
0.451 | 0.457
0.000 | 0.000
peptides
spectra
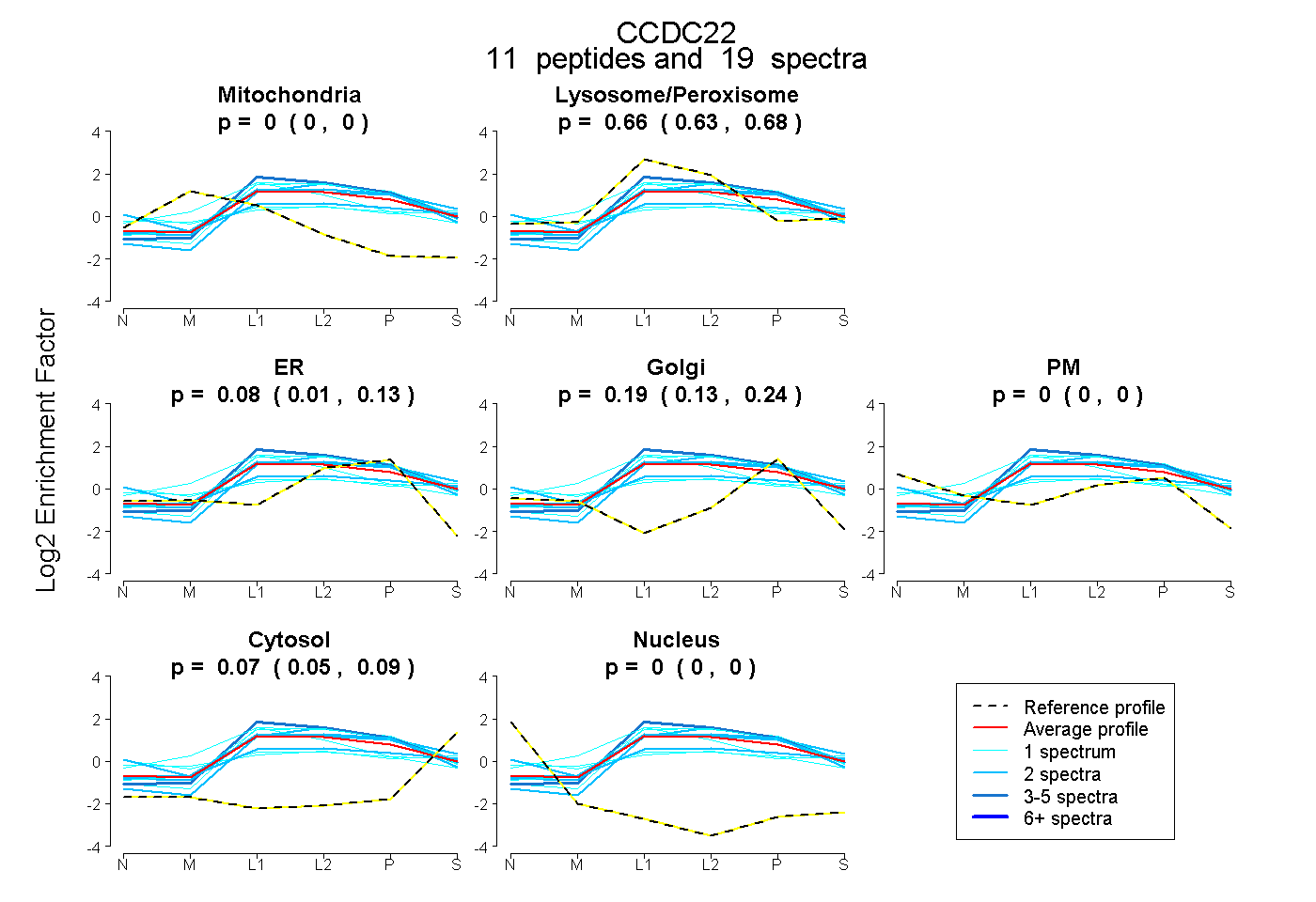
0.000 | 0.000
0.634 | 0.682
0.009 | 0.133
0.131 | 0.243
0.000 | 0.000
0.051 | 0.087
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
44 spectra |
 |
0.000 0.000 | 0.000 |
0.393 0.389 | 0.396 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.153 0.149 | 0.156 |
0.000 0.000 | 0.000 |
0.455 0.451 | 0.457 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
19 spectra |
 |
0.000 0.000 | 0.000 |
0.659 0.634 | 0.682 |
0.077 0.009 | 0.133 |
0.192 0.131 | 0.243 |
0.000 0.000 | 0.000 |
0.071 0.051 | 0.087 |
0.000 0.000 | 0.000 |
| 1 spectrum, LQLVVESSAQR | 0.085 | 0.717 | 0.000 | 0.198 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EINSLSGK | 0.000 | 0.471 | 0.000 | 0.086 | 0.259 | 0.183 | 0.000 | |||
| 1 spectrum, FTHSEK | 0.000 | 0.635 | 0.141 | 0.186 | 0.000 | 0.038 | 0.000 | |||
| 2 spectra, TVELLPDGAANLTK | 0.000 | 0.632 | 0.181 | 0.178 | 0.000 | 0.009 | 0.000 | |||
| 1 spectrum, SLGMNLVQVETECR | 0.000 | 0.496 | 0.000 | 0.140 | 0.153 | 0.211 | 0.000 | |||
| 1 spectrum, ILEIVGNIR | 0.000 | 0.650 | 0.284 | 0.000 | 0.000 | 0.066 | 0.000 | |||
| 5 spectra, ILIHSLR | 0.000 | 0.712 | 0.254 | 0.000 | 0.000 | 0.034 | 0.000 | |||
| 2 spectra, TFAVTDELVFK | 0.000 | 0.520 | 0.000 | 0.147 | 0.180 | 0.153 | 0.000 | |||
| 1 spectrum, QENAGLLGR | 0.000 | 0.652 | 0.306 | 0.000 | 0.000 | 0.042 | 0.000 | |||
| 2 spectra, LAYTQR | 0.000 | 0.648 | 0.135 | 0.151 | 0.000 | 0.066 | 0.000 | |||
| 2 spectra, DLLLFLAER | 0.000 | 0.606 | 0.251 | 0.000 | 0.000 | 0.143 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
85 spectra |
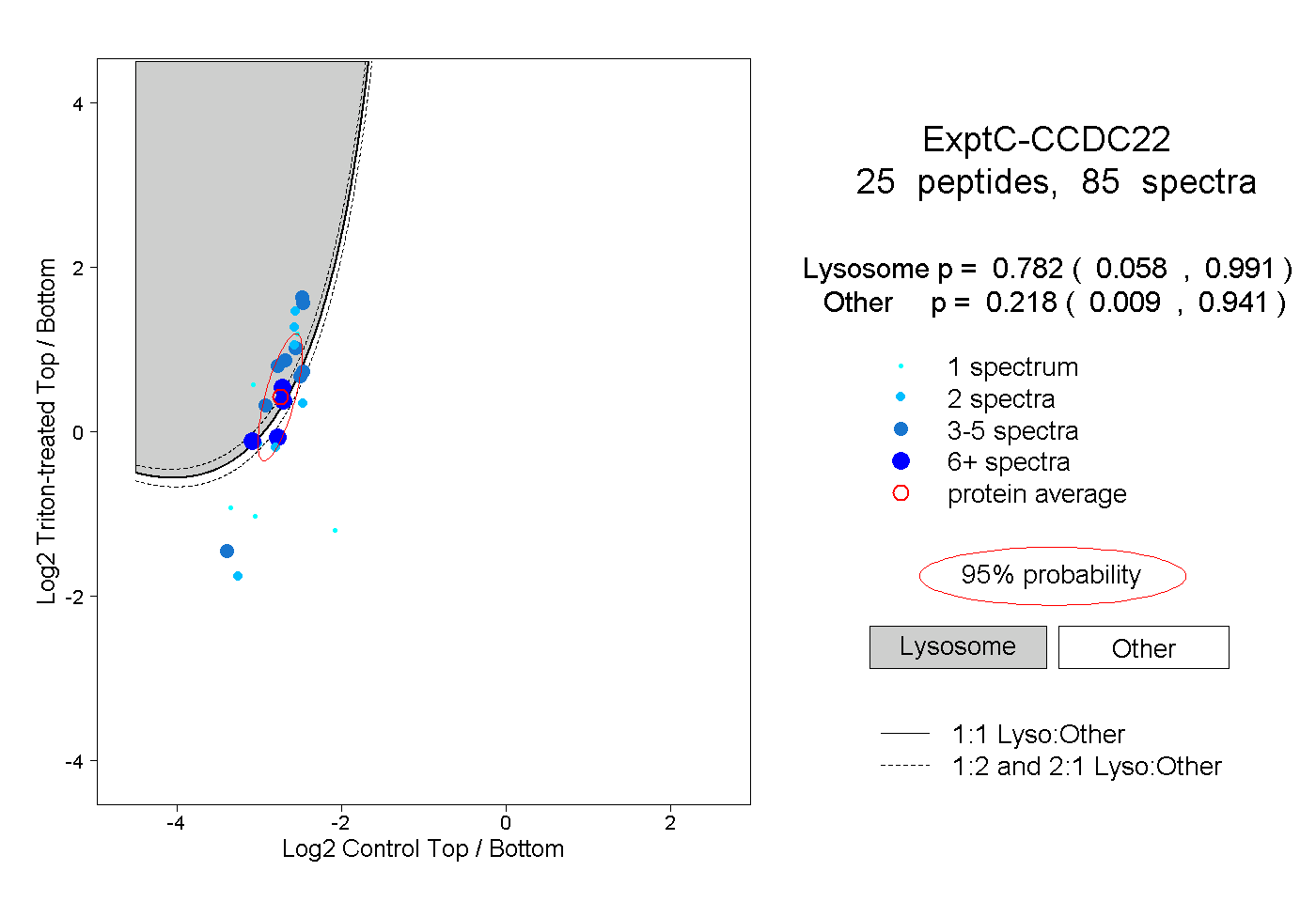 |
0.782 0.058 | 0.991 |
0.218 0.009 | 0.941 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
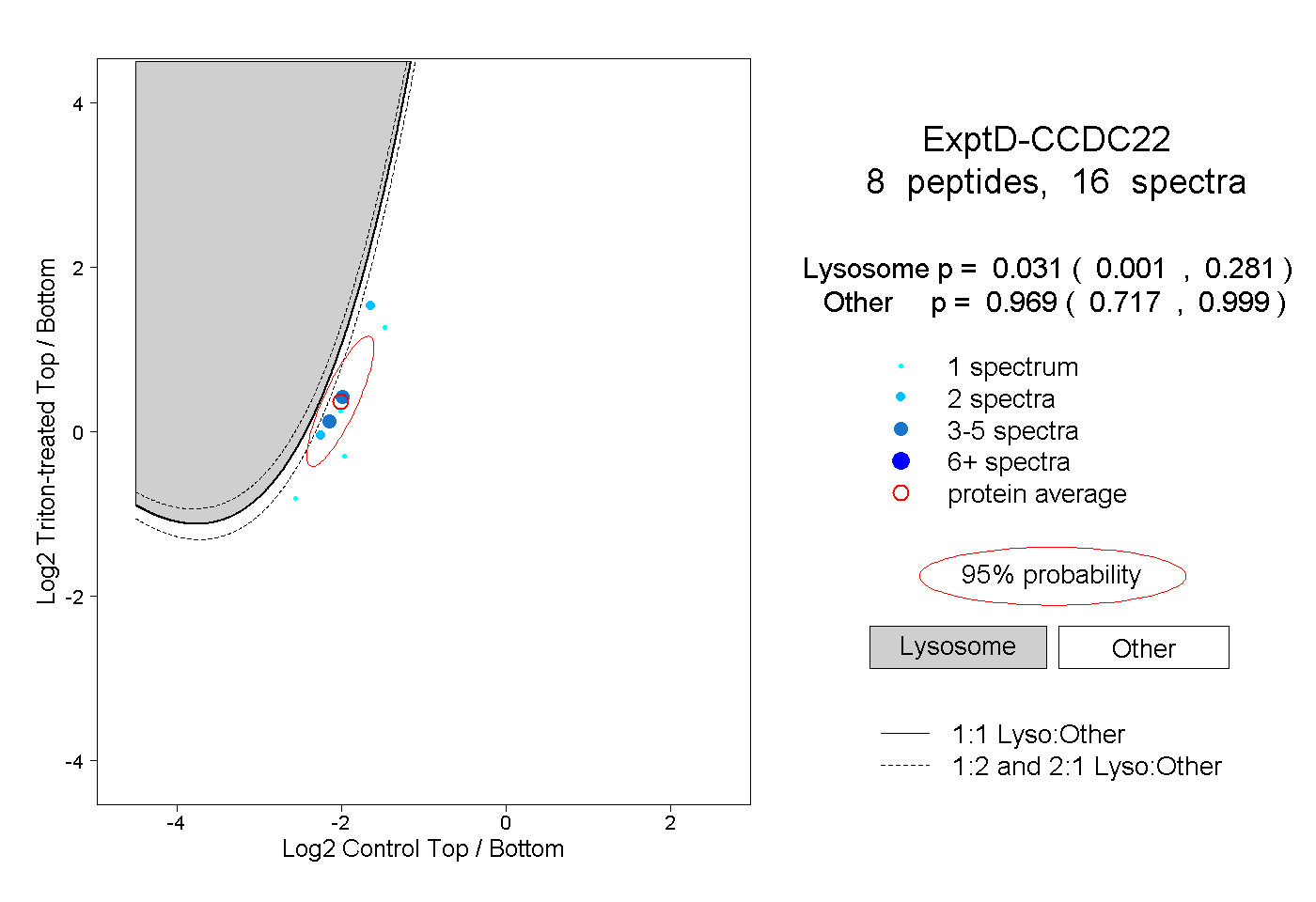 |
0.031 0.001 | 0.281 |
0.969 0.717 | 0.999 |