peptides
spectra
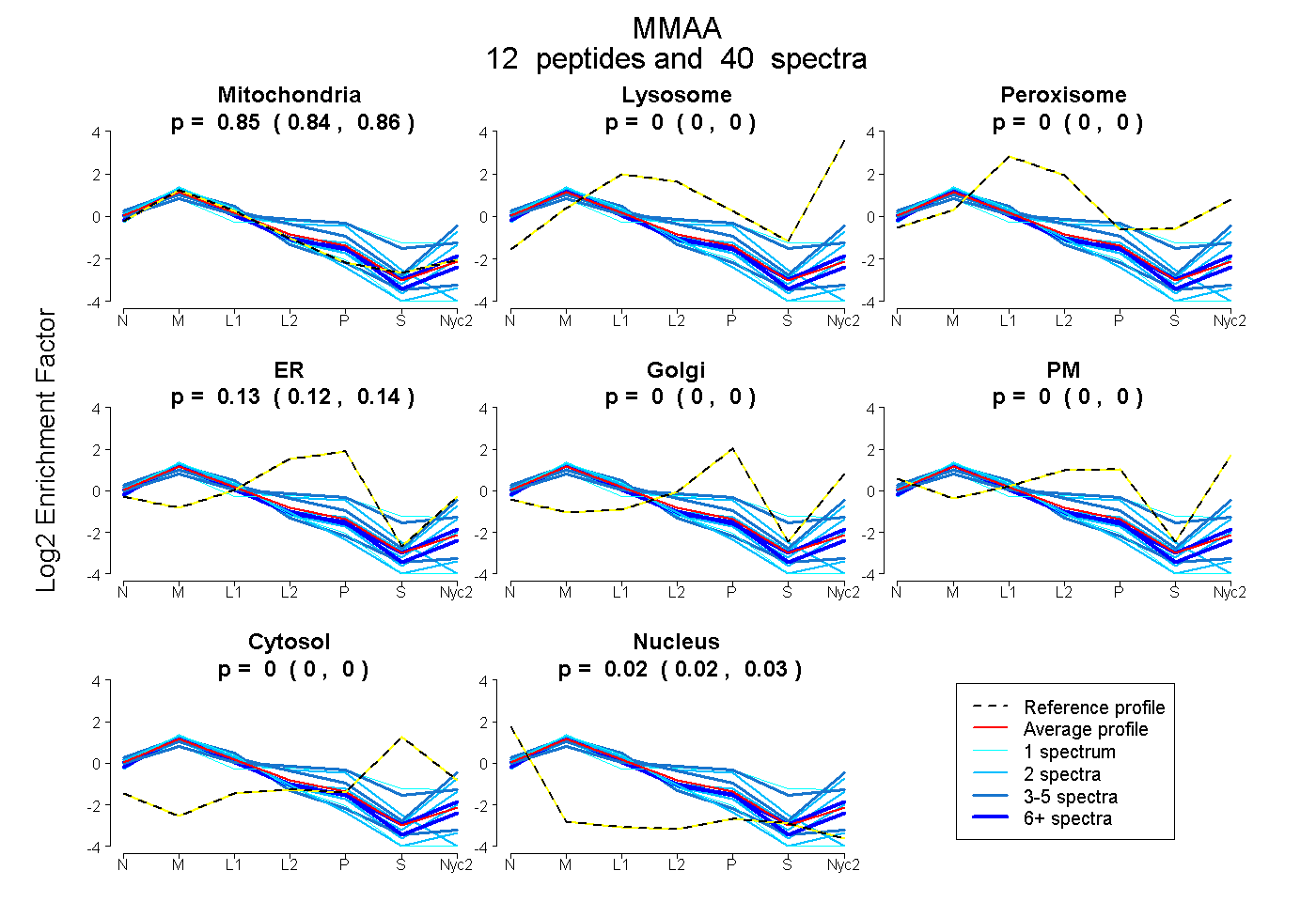
0.843 | 0.858
0.000 | 0.000
0.000 | 0.000
0.116 | 0.136
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.017 | 0.026
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
40 spectra |
 |
0.851 0.843 | 0.858 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.127 0.116 | 0.136 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.022 0.017 | 0.026 |
| 2 spectra, GIIEMADLVVITK | 0.742 | 0.004 | 0.000 | 0.000 | 0.023 | 0.232 | 0.000 | 0.000 | ||
| 10 spectra, LYMGLVQGQR | 0.896 | 0.000 | 0.000 | 0.010 | 0.090 | 0.000 | 0.000 | 0.003 | ||
| 5 spectra, SGEGITEMWDIMR | 0.623 | 0.007 | 0.000 | 0.000 | 0.000 | 0.370 | 0.000 | 0.000 | ||
| 2 spectra, EQIPLMER | 0.890 | 0.000 | 0.000 | 0.000 | 0.034 | 0.076 | 0.000 | 0.000 | ||
| 2 spectra, ACLAEAITLVESTHTR | 0.731 | 0.000 | 0.000 | 0.194 | 0.000 | 0.000 | 0.000 | 0.075 | ||
| 1 spectrum, VGLSGPPGAGK | 0.912 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.088 | ||
| 2 spectra, STFIECFGK | 0.926 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.074 | ||
| 1 spectrum, MTELSR | 0.507 | 0.000 | 0.072 | 0.171 | 0.121 | 0.000 | 0.129 | 0.000 | ||
| 2 spectra, AADLLLK | 0.885 | 0.000 | 0.000 | 0.043 | 0.000 | 0.026 | 0.000 | 0.046 | ||
| 3 spectra, VLAHQR | 0.522 | 0.000 | 0.099 | 0.219 | 0.083 | 0.000 | 0.077 | 0.000 | ||
| 4 spectra, DMNAYIRPSPTSGTLGGVTR | 0.917 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.083 | ||
| 6 spectra, EVLSGALSPGR | 0.884 | 0.000 | 0.000 | 0.068 | 0.000 | 0.000 | 0.000 | 0.048 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
11 spectra |
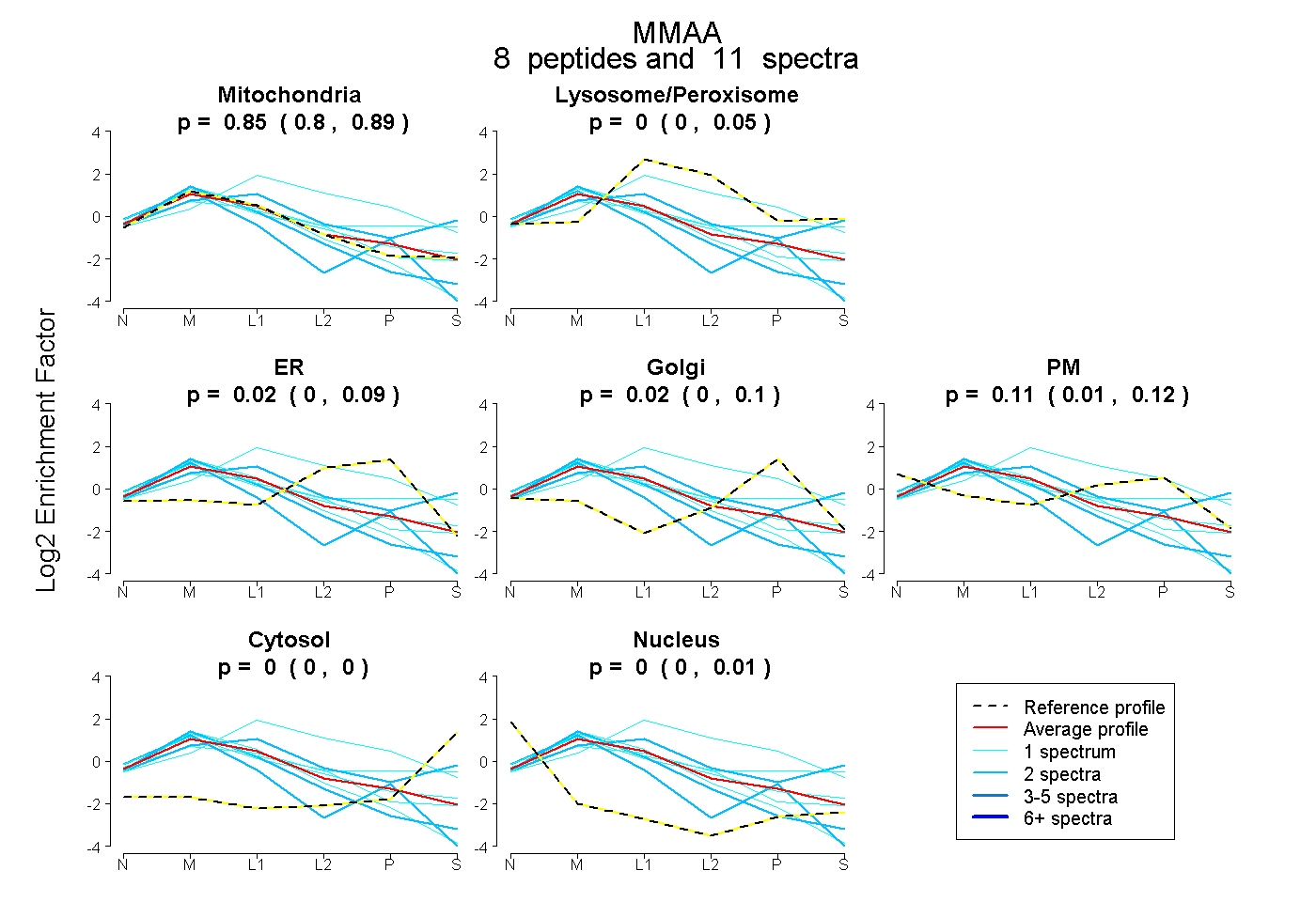 |
0.852 0.799 | 0.887 |
0.000 0.000 | 0.052 |
0.019 0.000 | 0.088 |
0.019 0.000 | 0.097 |
0.110 0.008 | 0.121 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.009 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
85 spectra |
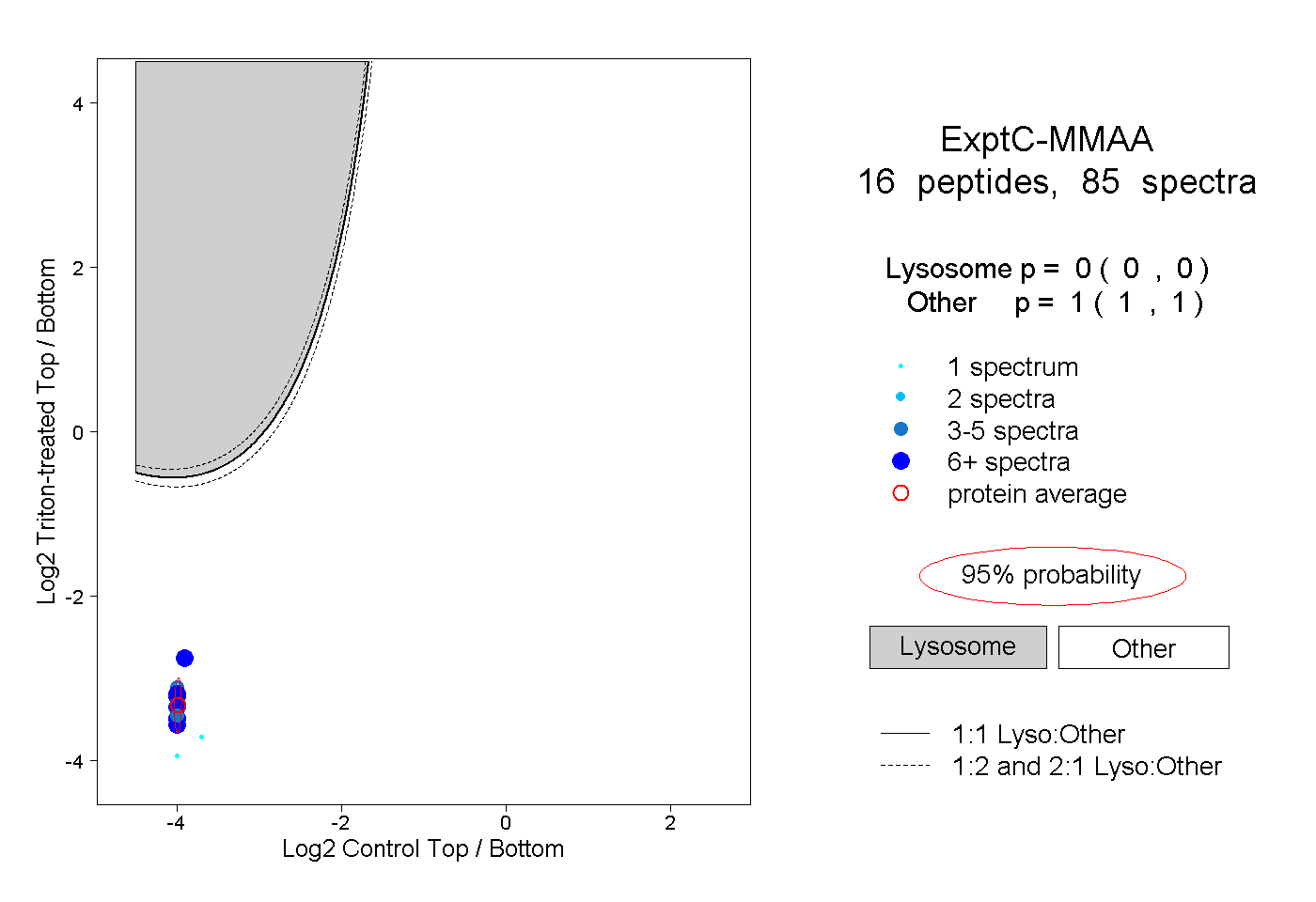 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
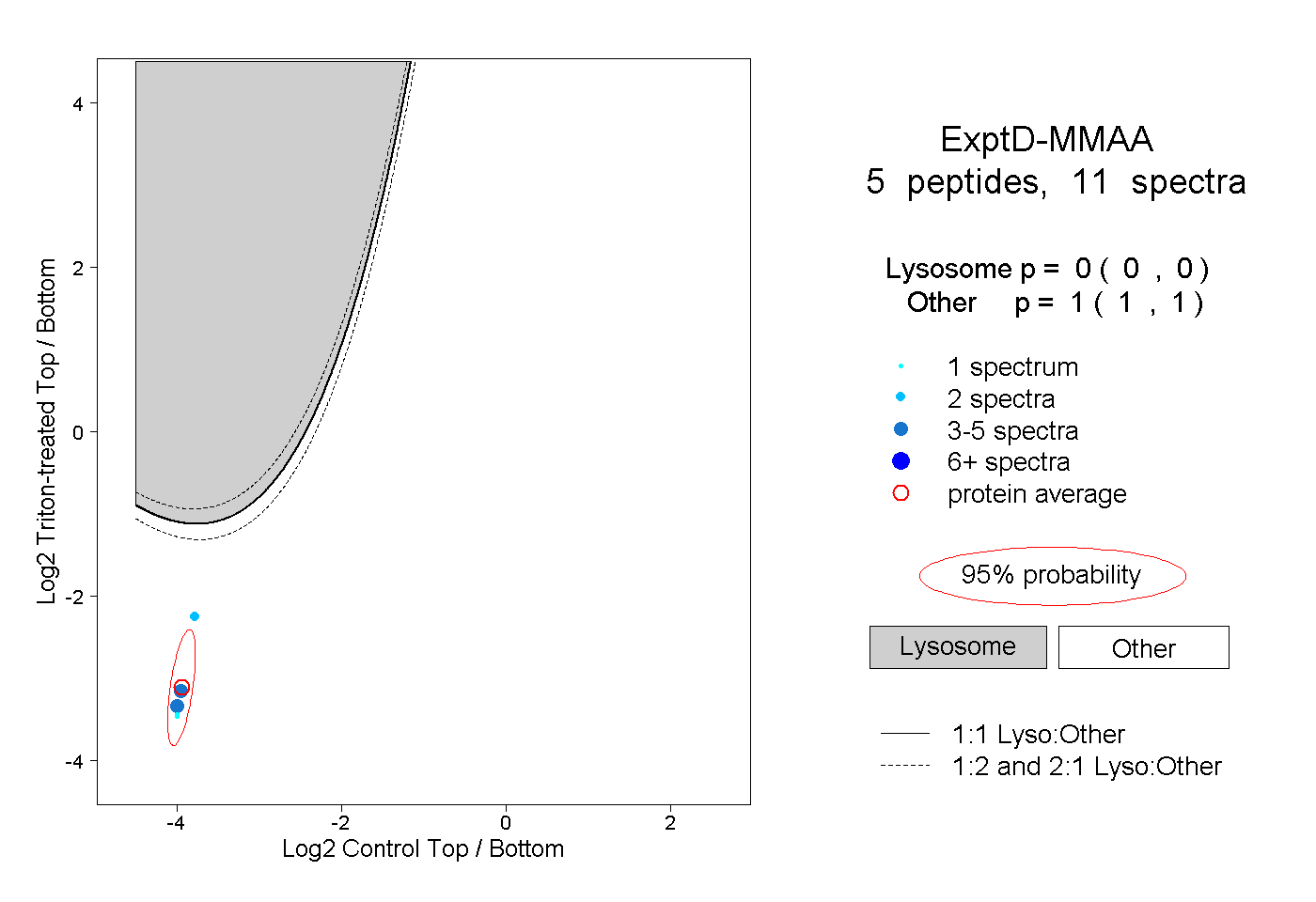 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |