peptides
spectra
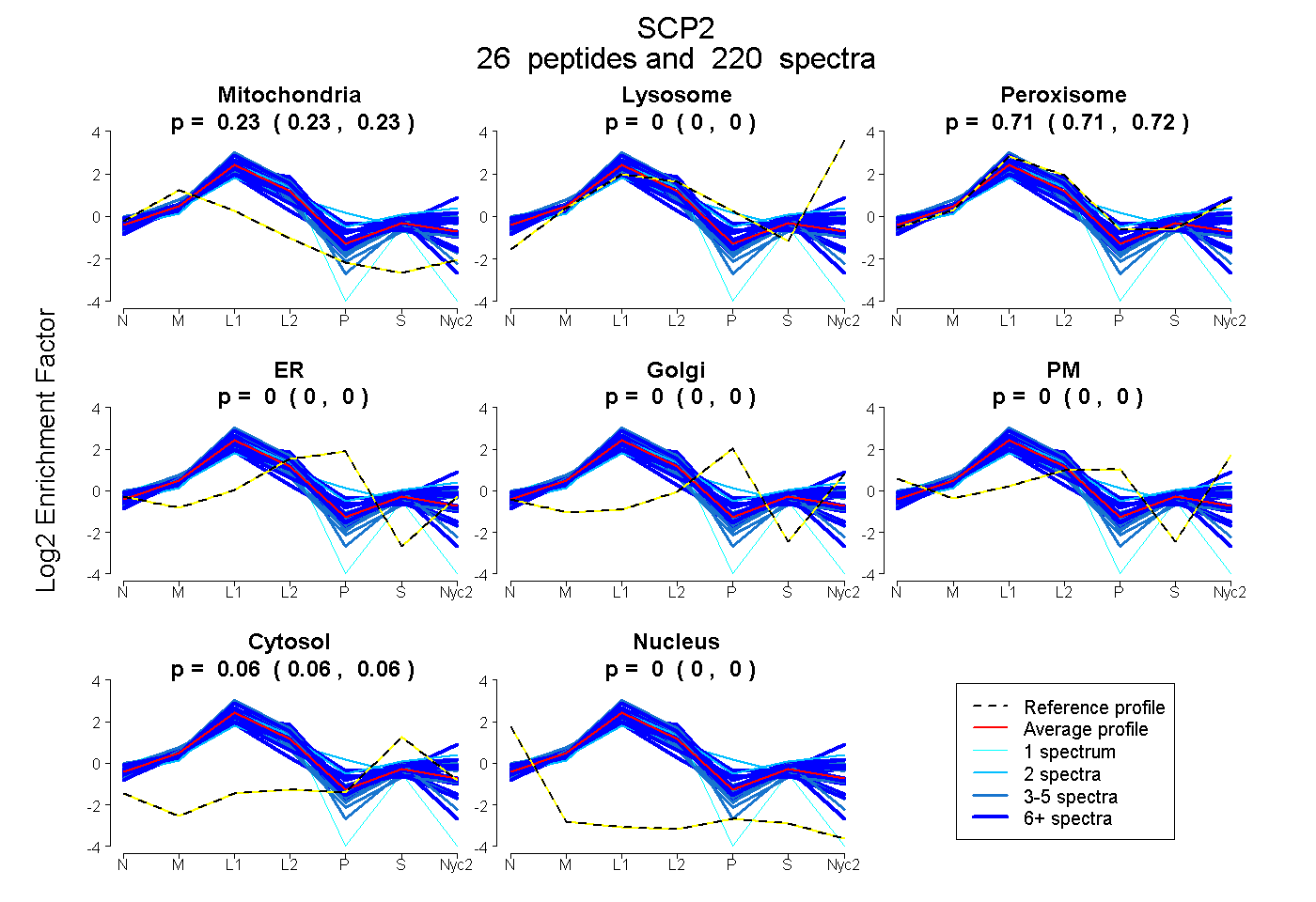
0.226 | 0.230
0.000 | 0.000
0.711 | 0.716
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.057 | 0.059
0.000 | 0.000
peptides
spectra
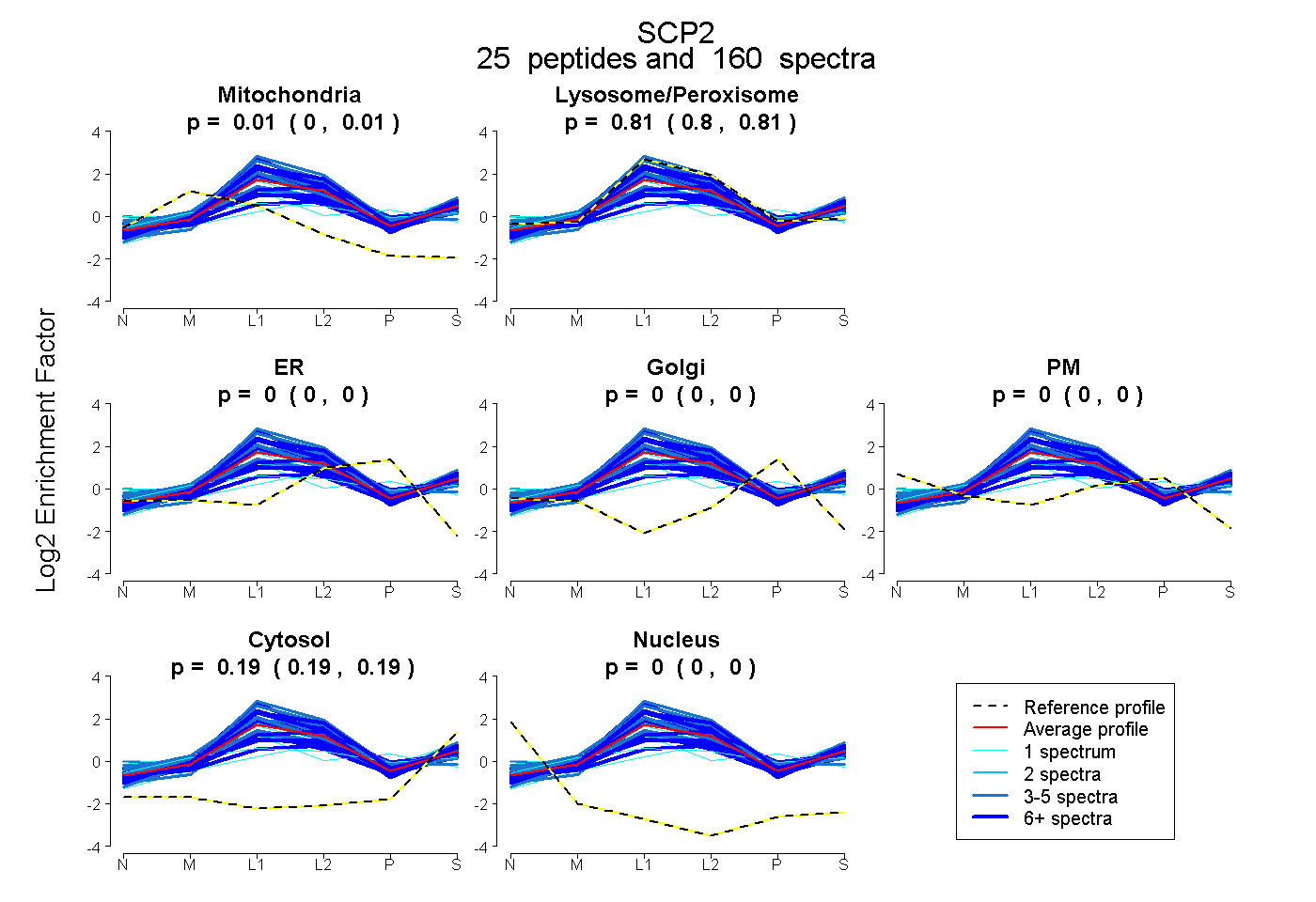
0.003 | 0.007
0.802 | 0.808
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.187 | 0.192
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
220 spectra |
 |
0.228 0.226 | 0.230 |
0.000 0.000 | 0.000 |
0.714 0.711 | 0.716 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.058 0.057 | 0.059 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
160 spectra |
 |
0.005 0.003 | 0.007 |
0.805 0.802 | 0.808 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.190 0.187 | 0.192 |
0.000 0.000 | 0.000 |
| 4 spectra, EHMETYGTK | 0.000 | 0.831 | 0.000 | 0.000 | 0.000 | 0.169 | 0.000 | |||
| 1 spectrum, ADCTITMADSDLLALMTGK | 0.000 | 0.528 | 0.101 | 0.000 | 0.000 | 0.371 | 0.000 | |||
| 9 spectra, MGFPEAASSFR | 0.023 | 0.678 | 0.028 | 0.000 | 0.000 | 0.272 | 0.000 | |||
| 24 spectra, IGGIFAFK | 0.015 | 0.806 | 0.000 | 0.000 | 0.000 | 0.180 | 0.000 | |||
| 1 spectrum, GHPLGATGLAQCAELCWQLR | 0.076 | 0.591 | 0.000 | 0.257 | 0.000 | 0.042 | 0.034 | |||
| 2 spectra, HSVNNPYSQFQDEYSLDEIMK | 0.056 | 0.686 | 0.000 | 0.000 | 0.000 | 0.258 | 0.000 | |||
| 8 spectra, HIDVLINK | 0.000 | 0.876 | 0.000 | 0.000 | 0.000 | 0.124 | 0.000 | |||
| 3 spectra, GSVLPDSDK | 0.000 | 0.706 | 0.000 | 0.000 | 0.122 | 0.172 | 0.000 | |||
| 3 spectra, HGLQSK | 0.128 | 0.828 | 0.000 | 0.042 | 0.000 | 0.002 | 0.000 | |||
| 3 spectra, LQSLQLQPDK | 0.051 | 0.712 | 0.000 | 0.000 | 0.000 | 0.237 | 0.000 | |||
| 9 spectra, WVINPSGGLISK | 0.000 | 0.916 | 0.000 | 0.000 | 0.000 | 0.084 | 0.000 | |||
| 9 spectra, EATWVVDVK | 0.161 | 0.624 | 0.000 | 0.000 | 0.028 | 0.188 | 0.000 | |||
| 1 spectrum, DGPGGK | 0.000 | 0.741 | 0.000 | 0.000 | 0.096 | 0.163 | 0.000 | |||
| 7 spectra, YGMSACPFAPQLFGSAGK | 0.000 | 0.756 | 0.000 | 0.000 | 0.000 | 0.244 | 0.000 | |||
| 1 spectrum, THQISAAPTSSAGDGFK | 0.066 | 0.560 | 0.000 | 0.187 | 0.000 | 0.187 | 0.000 | |||
| 4 spectra, VEHFAK | 0.000 | 0.970 | 0.000 | 0.000 | 0.000 | 0.030 | 0.000 | |||
| 24 spectra, FMKPGGENSR | 0.000 | 0.852 | 0.000 | 0.025 | 0.000 | 0.123 | 0.000 | |||
| 6 spectra, IAGNMGLAMK | 0.000 | 0.613 | 0.027 | 0.000 | 0.000 | 0.361 | 0.000 | |||
| 7 spectra, MNPQSAFFQGK | 0.000 | 0.683 | 0.013 | 0.007 | 0.000 | 0.297 | 0.000 | |||
| 3 spectra, ANLIFK | 0.038 | 0.795 | 0.000 | 0.000 | 0.000 | 0.121 | 0.045 | |||
| 3 spectra, SNPLEK | 0.097 | 0.794 | 0.000 | 0.032 | 0.000 | 0.077 | 0.000 | |||
| 12 spectra, VALQHNLGLGGAAVVTLYR | 0.000 | 0.867 | 0.000 | 0.000 | 0.000 | 0.133 | 0.000 | |||
| 8 spectra, DYPDLAK | 0.004 | 0.933 | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | |||
| 5 spectra, GDNTYGGK | 0.000 | 0.938 | 0.000 | 0.000 | 0.000 | 0.062 | 0.000 | |||
| 3 spectra, GSLGTK | 0.054 | 0.814 | 0.000 | 0.000 | 0.000 | 0.132 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
2050 spectra |
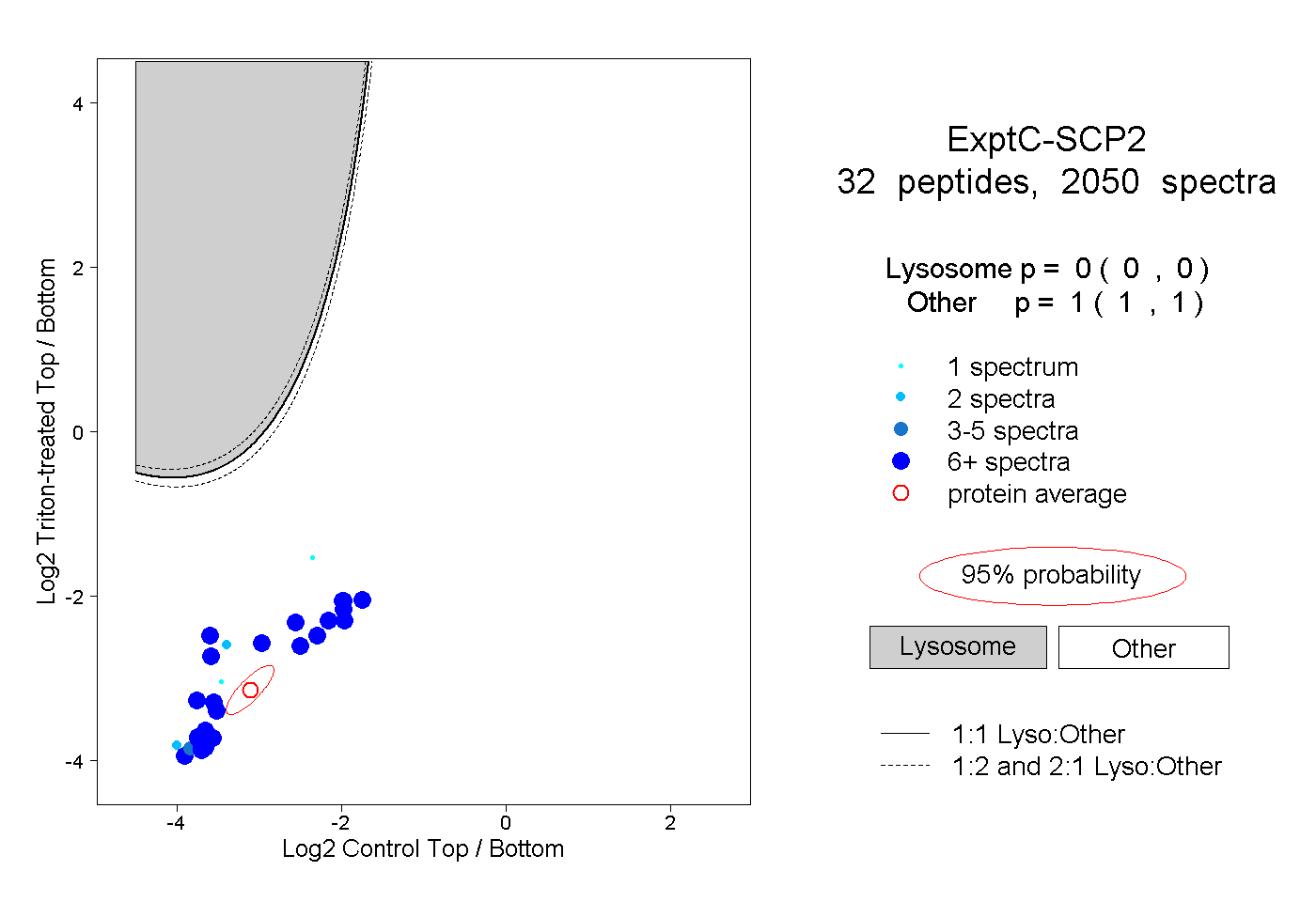 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
124 spectra |
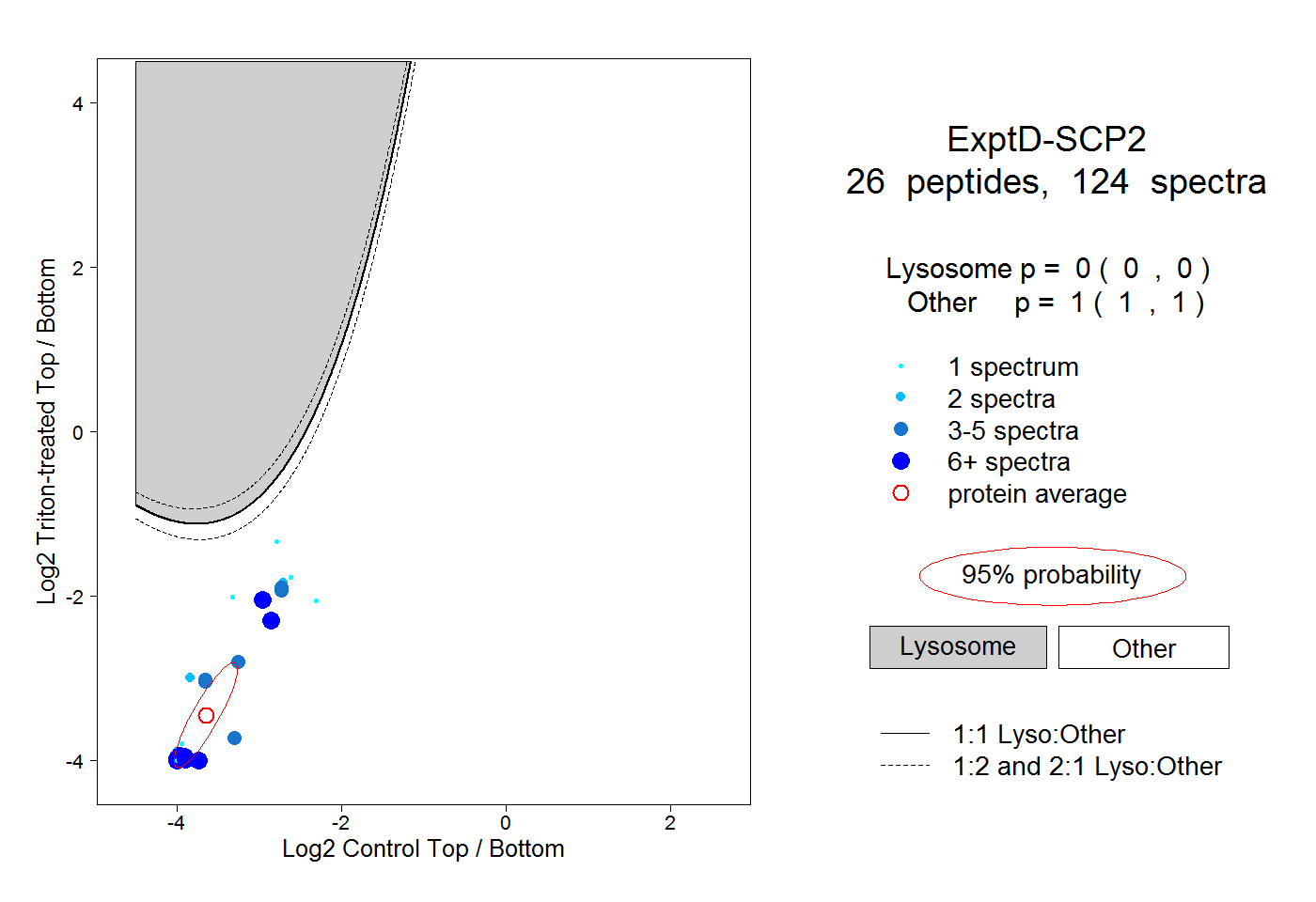 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |