peptides
spectra
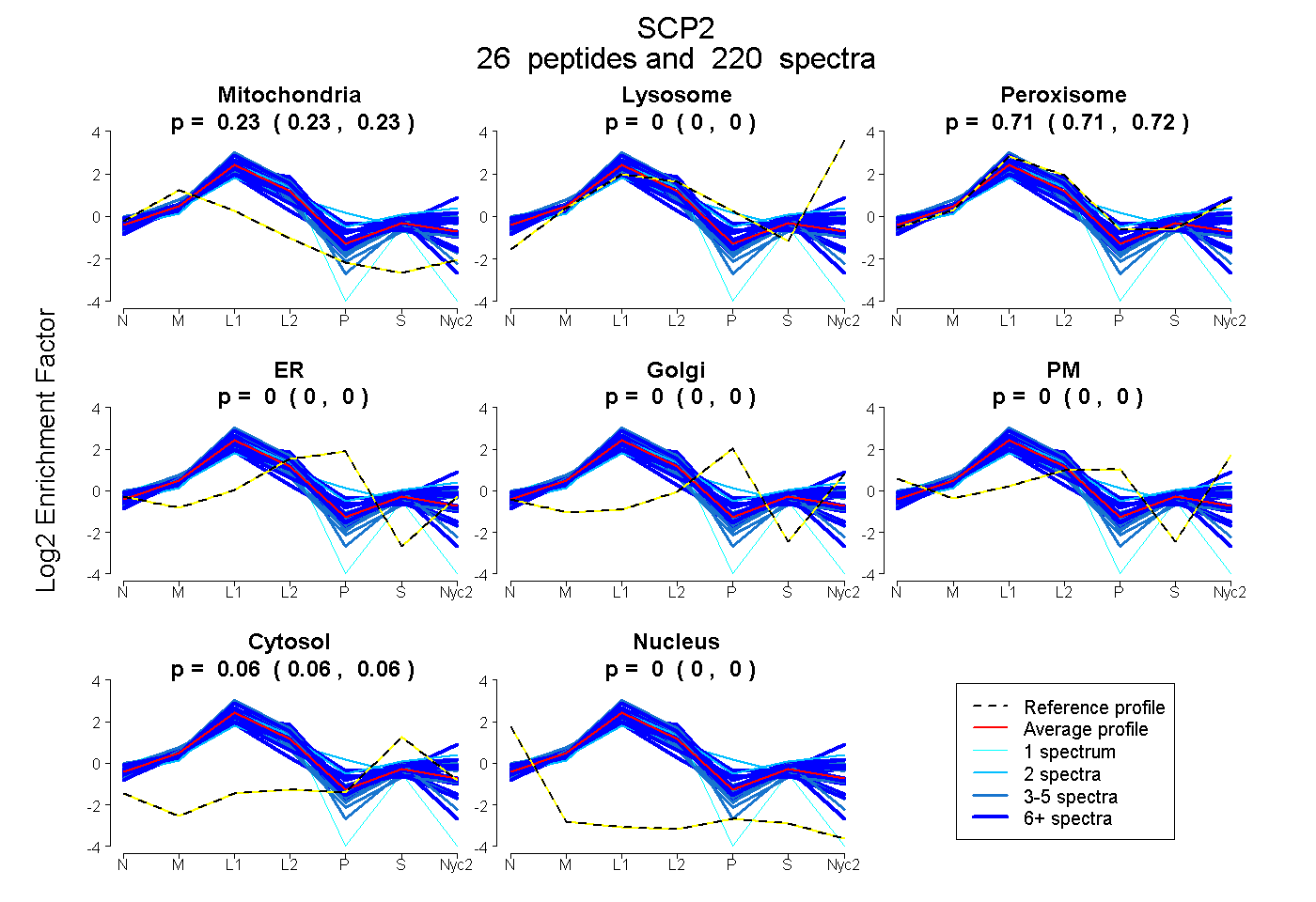
0.226 | 0.230
0.000 | 0.000
0.711 | 0.716
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.057 | 0.059
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
220 spectra |
 |
0.228 0.226 | 0.230 |
0.000 0.000 | 0.000 |
0.714 0.711 | 0.716 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.058 0.057 | 0.059 |
0.000 0.000 | 0.000 |
| 6 spectra, EHMETYGTK | 0.150 | 0.000 | 0.821 | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 | ||
| 10 spectra, ADCTITMADSDLLALMTGK | 0.457 | 0.000 | 0.457 | 0.000 | 0.000 | 0.000 | 0.083 | 0.002 | ||
| 2 spectra, QVPGAK | 0.000 | 0.000 | 0.878 | 0.000 | 0.000 | 0.000 | 0.122 | 0.000 | ||
| 33 spectra, MGFPEAASSFR | 0.103 | 0.000 | 0.830 | 0.000 | 0.000 | 0.000 | 0.067 | 0.000 | ||
| 3 spectra, LEEEGEEFVK | 0.293 | 0.000 | 0.654 | 0.000 | 0.000 | 0.000 | 0.013 | 0.039 | ||
| 19 spectra, IGGIFAFK | 0.291 | 0.000 | 0.693 | 0.000 | 0.000 | 0.000 | 0.016 | 0.000 | ||
| 1 spectrum, HSVNNPYSQFQDEYSLDEIMK | 0.680 | 0.000 | 0.320 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, HIDVLINK | 0.214 | 0.000 | 0.710 | 0.000 | 0.000 | 0.000 | 0.076 | 0.000 | ||
| 3 spectra, GSVLPDSDK | 0.402 | 0.000 | 0.578 | 0.000 | 0.000 | 0.000 | 0.019 | 0.000 | ||
| 2 spectra, HGLQSK | 0.185 | 0.000 | 0.544 | 0.190 | 0.000 | 0.000 | 0.082 | 0.000 | ||
| 5 spectra, LQSLQLQPDK | 0.428 | 0.000 | 0.548 | 0.000 | 0.000 | 0.000 | 0.024 | 0.000 | ||
| 6 spectra, WVINPSGGLISK | 0.145 | 0.000 | 0.747 | 0.000 | 0.000 | 0.000 | 0.109 | 0.000 | ||
| 12 spectra, MVGYDMSK | 0.026 | 0.126 | 0.769 | 0.000 | 0.000 | 0.000 | 0.079 | 0.000 | ||
| 9 spectra, EATWVVDVK | 0.243 | 0.000 | 0.676 | 0.000 | 0.000 | 0.000 | 0.081 | 0.000 | ||
| 5 spectra, AVEIVAQEMVTDMPSTFEEK | 0.194 | 0.000 | 0.806 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, YGMSACPFAPQLFGSAGK | 0.276 | 0.000 | 0.628 | 0.000 | 0.000 | 0.000 | 0.096 | 0.000 | ||
| 6 spectra, THQISAAPTSSAGDGFK | 0.352 | 0.000 | 0.618 | 0.000 | 0.000 | 0.000 | 0.030 | 0.000 | ||
| 11 spectra, VEHFAK | 0.107 | 0.000 | 0.857 | 0.000 | 0.000 | 0.000 | 0.036 | 0.000 | ||
| 23 spectra, FMKPGGENSR | 0.129 | 0.000 | 0.836 | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | ||
| 10 spectra, IAGNMGLAMK | 0.273 | 0.000 | 0.663 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | ||
| 6 spectra, MNPQSAFFQGK | 0.217 | 0.000 | 0.681 | 0.000 | 0.022 | 0.000 | 0.052 | 0.028 | ||
| 6 spectra, ANLIFK | 0.393 | 0.000 | 0.484 | 0.000 | 0.000 | 0.000 | 0.123 | 0.000 | ||
| 5 spectra, SNPLEK | 0.135 | 0.000 | 0.852 | 0.000 | 0.000 | 0.000 | 0.013 | 0.000 | ||
| 4 spectra, VALQHNLGLGGAAVVTLYR | 0.332 | 0.000 | 0.634 | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | ||
| 4 spectra, GDNTYGGK | 0.134 | 0.000 | 0.836 | 0.000 | 0.000 | 0.000 | 0.030 | 0.000 | ||
| 8 spectra, GSLGTK | 0.054 | 0.000 | 0.824 | 0.000 | 0.000 | 0.000 | 0.122 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
160 spectra |
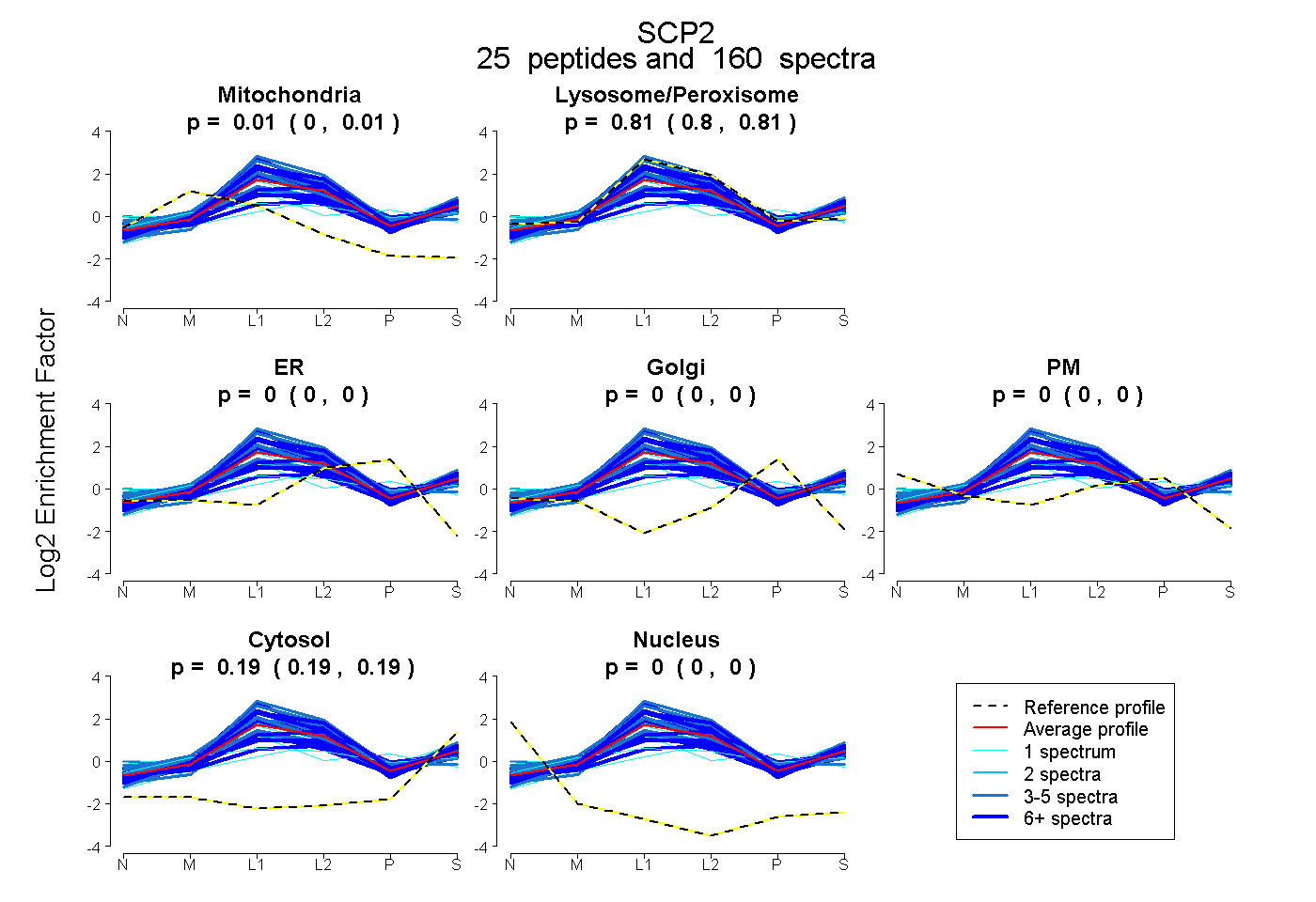 |
0.005 0.003 | 0.007 |
0.805 0.802 | 0.808 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.190 0.187 | 0.192 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
2050 spectra |
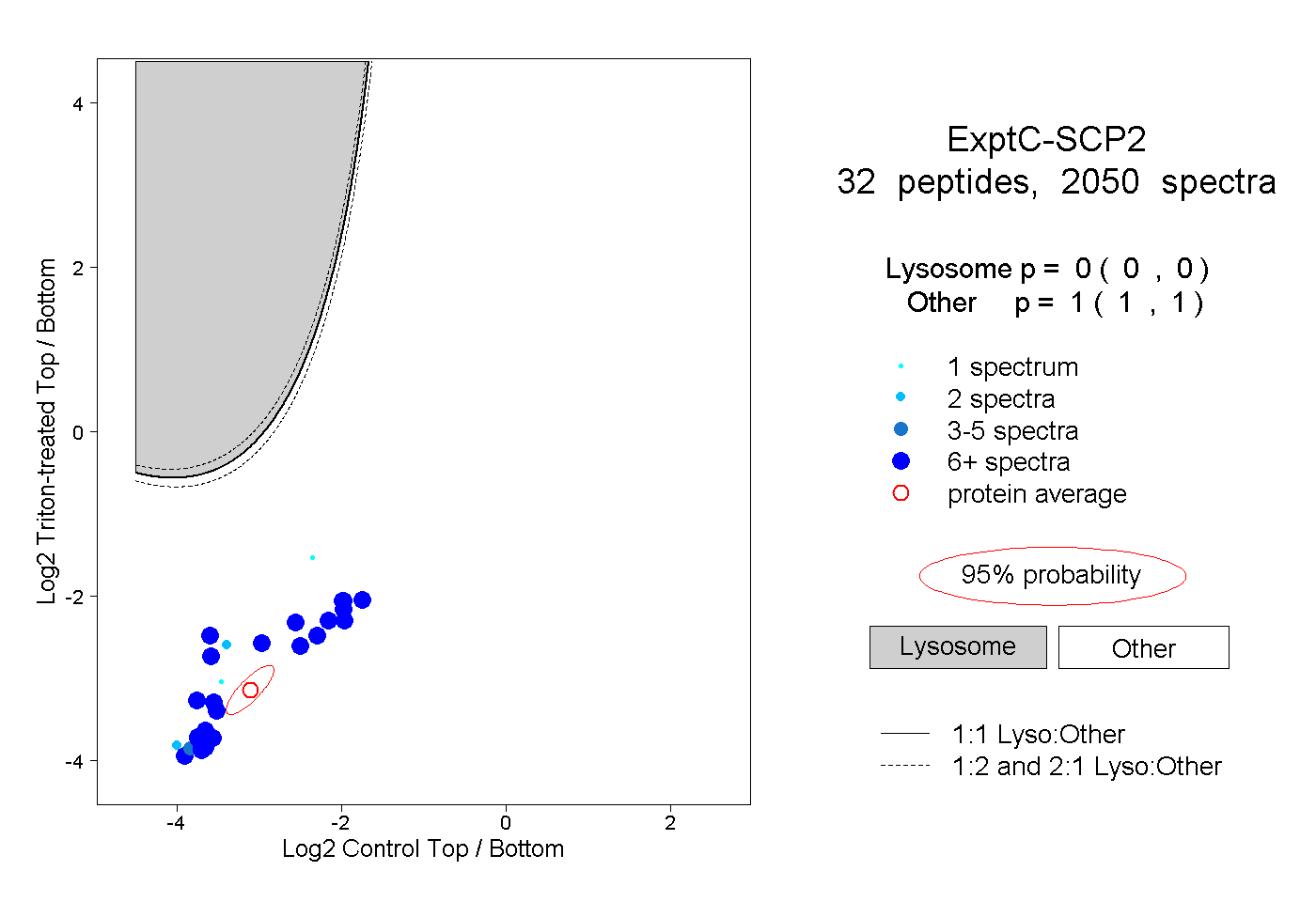 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
124 spectra |
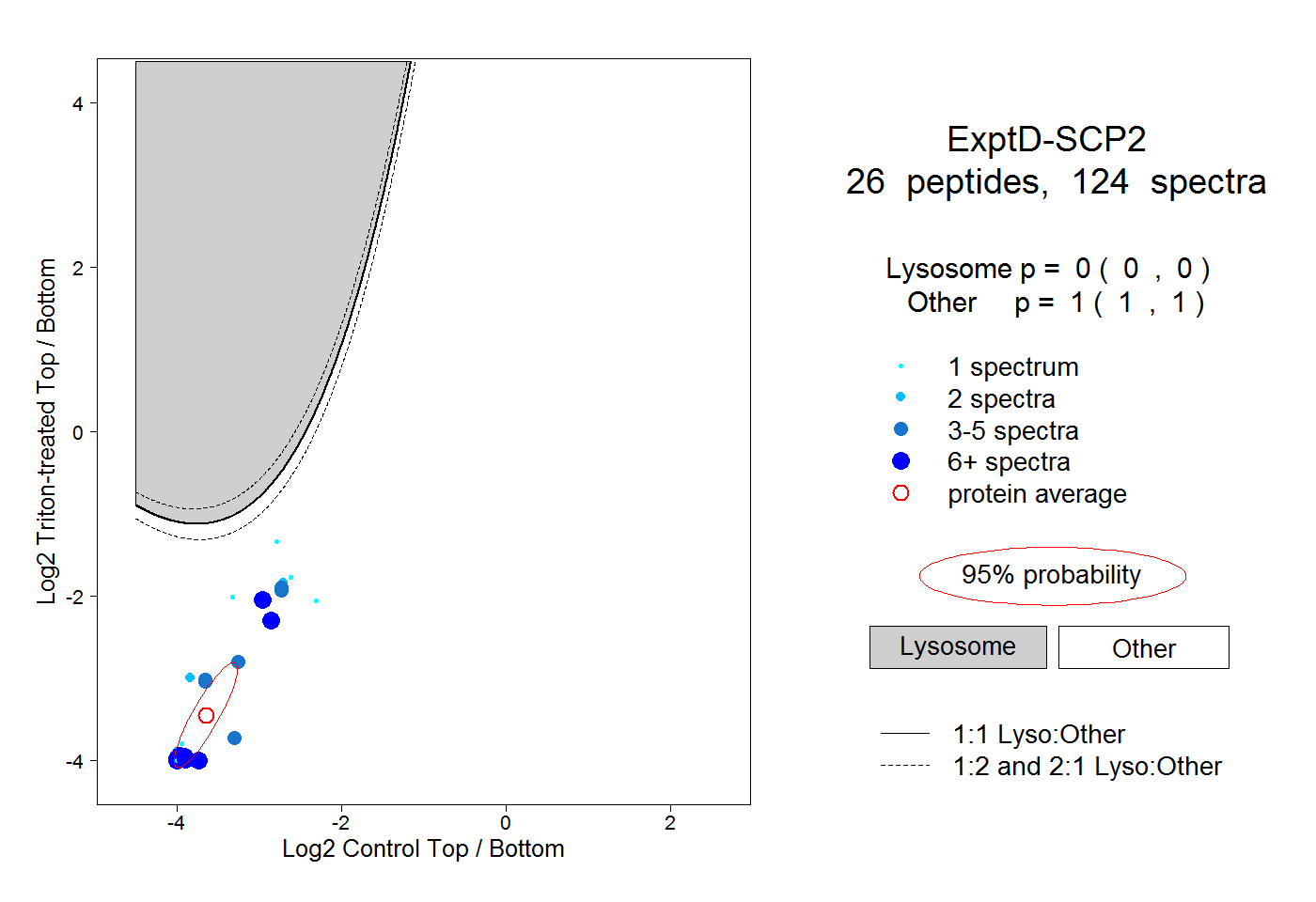 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |