peptides
spectra
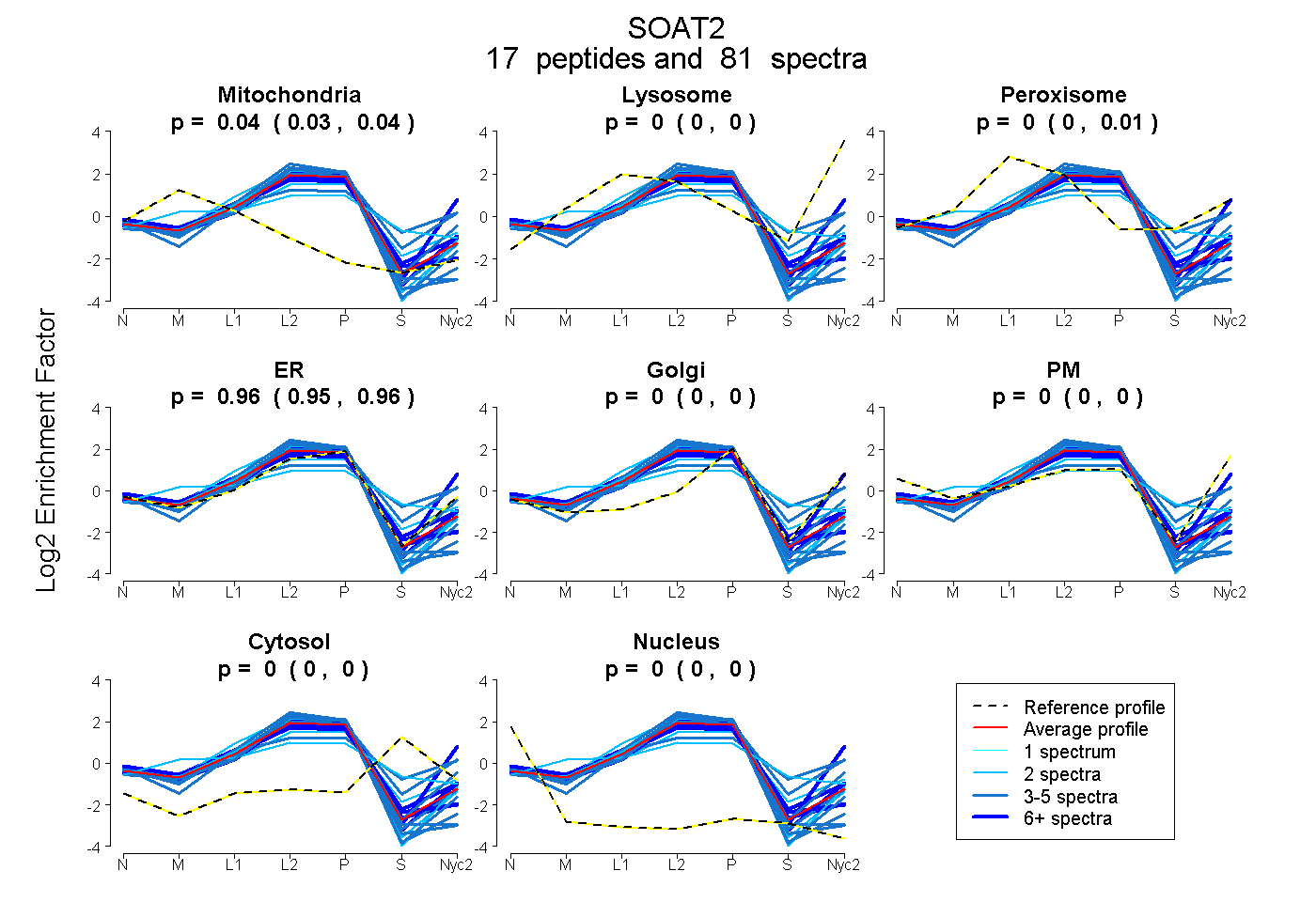
0.035 | 0.045
0.000 | 0.000
0.000 | 0.008
0.953 | 0.961
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
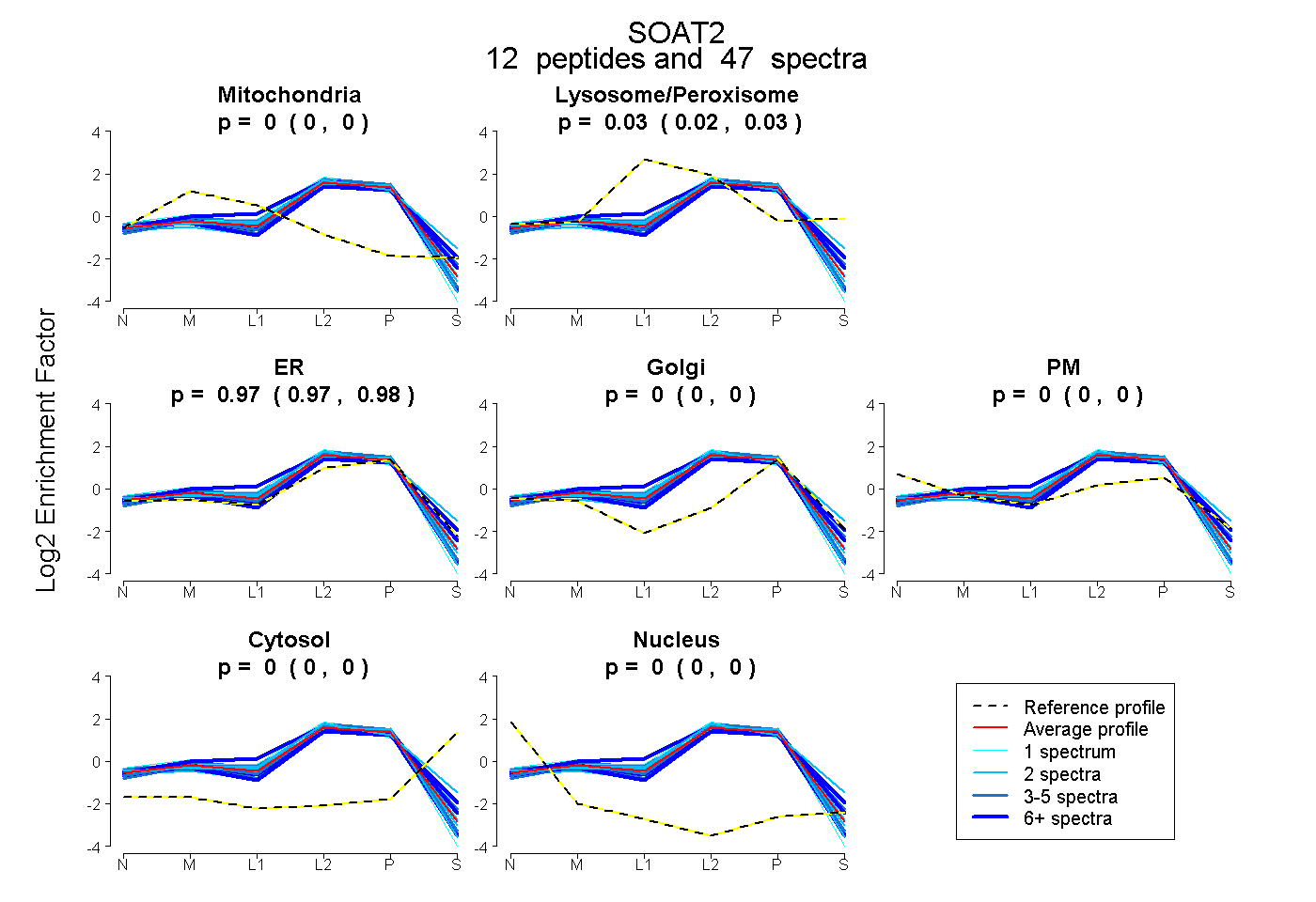
0.000 | 0.000
0.018 | 0.032
0.967 | 0.981
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
81 spectra |
 |
0.041 0.035 | 0.045 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.008 |
0.959 0.953 | 0.961 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
47 spectra |
 |
0.000 0.000 | 0.000 |
0.025 0.018 | 0.032 |
0.975 0.967 | 0.981 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, SYSFLR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VFITR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, SLLDELMEVQHFR | 0.000 | 0.086 | 0.914 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, ELAELMDR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, QDRPLPSTASDSTR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, LWARPR | 0.001 | 0.062 | 0.936 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, CVLVFEQVR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, APDLVQWTR | 0.000 | 0.136 | 0.864 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EPFSTR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, HCPLPQPTFWELVTPR | 0.000 | 0.183 | 0.817 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TQCLEQAQR | 0.000 | 0.210 | 0.790 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AIWEAVQAYPK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
195 spectra |
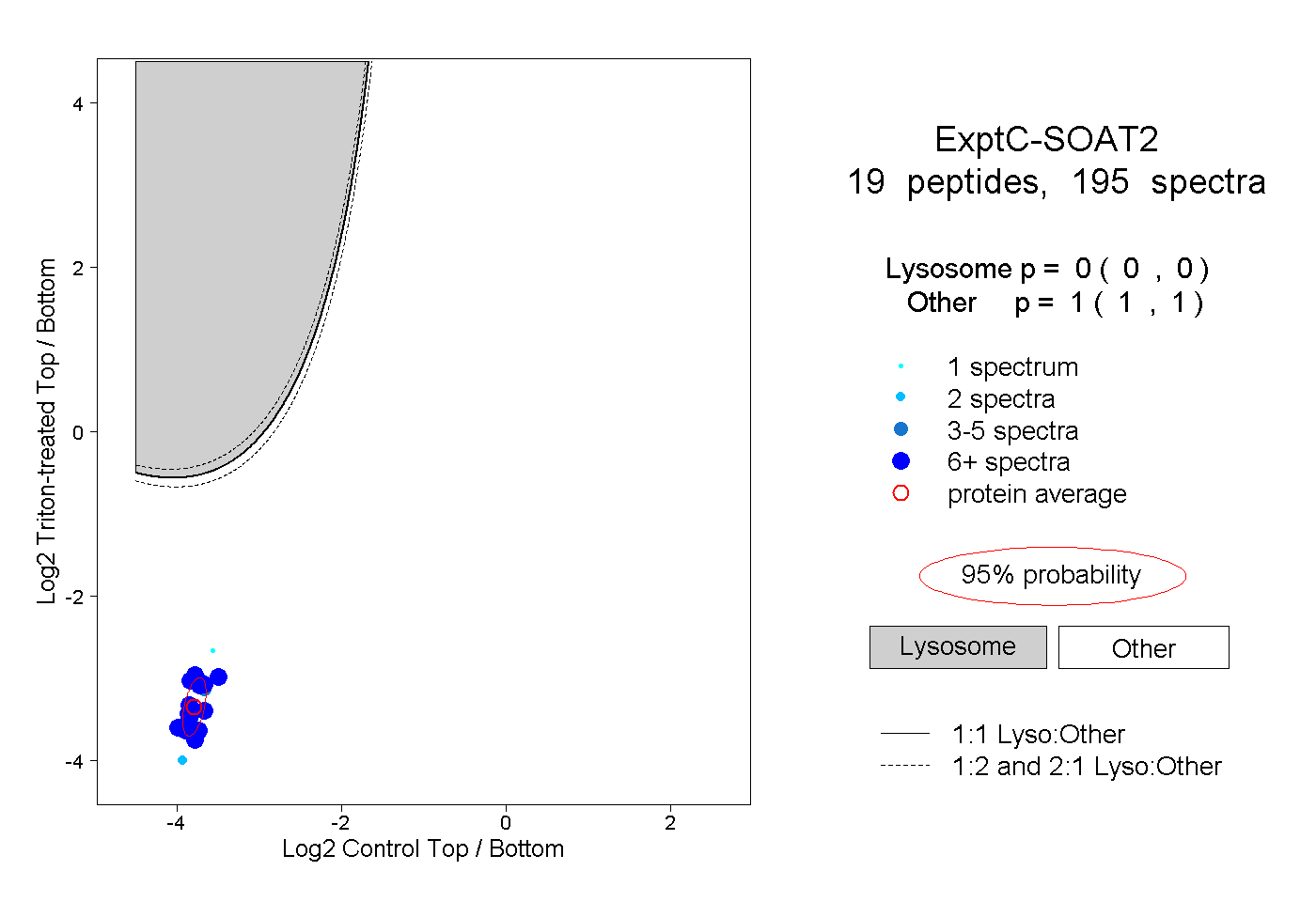 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
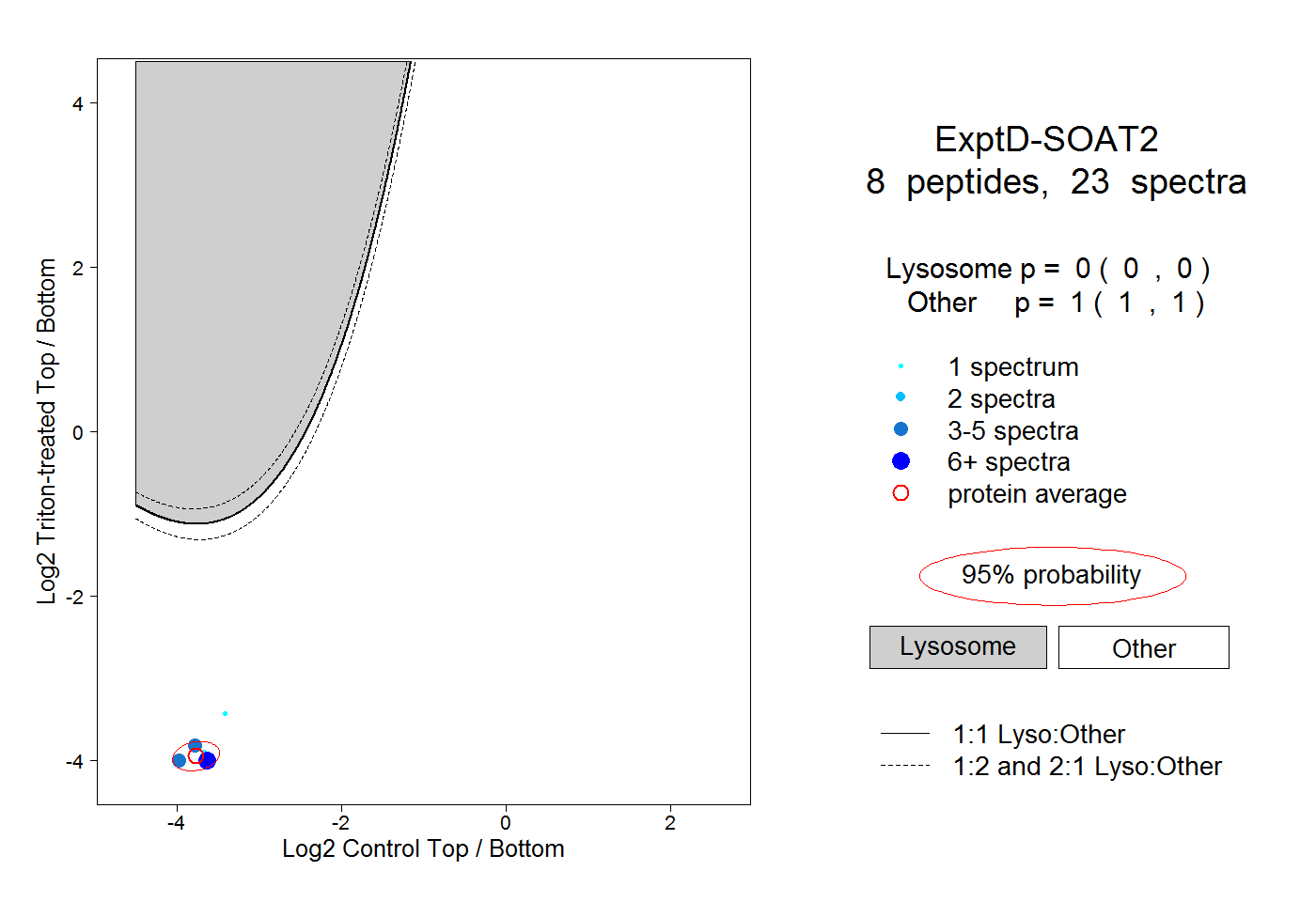 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |