peptides
spectra
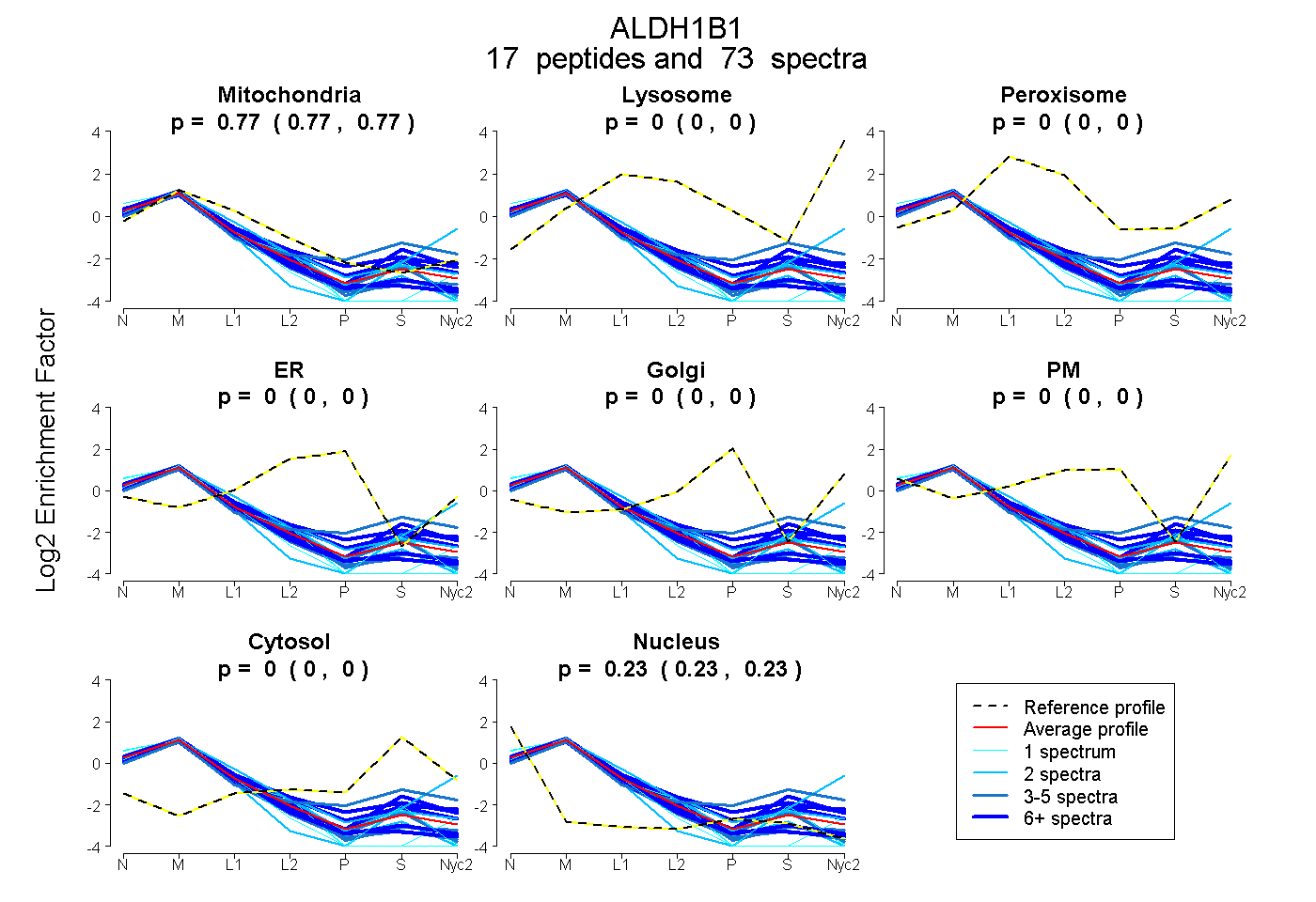
0.770 | 0.774
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.225 | 0.230
peptides
spectra
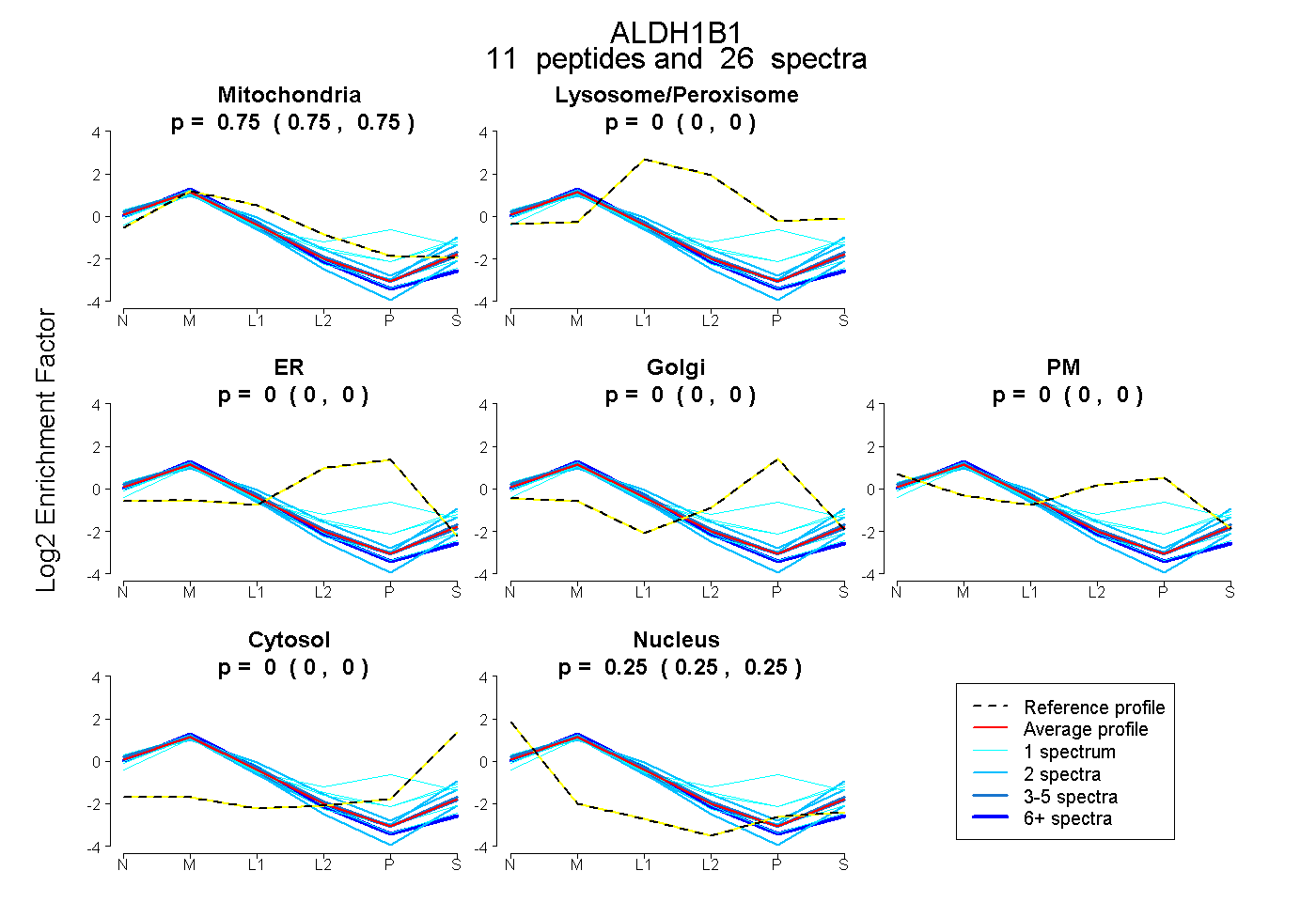
0.747 | 0.754
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.246 | 0.253
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
73 spectra |
 |
0.772 0.770 | 0.774 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.228 0.225 | 0.230 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
 |
0.751 0.747 | 0.754 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.249 0.246 | 0.253 |
| 1 spectrum, YNQLFINNEWHDAVSK | 0.733 | 0.000 | 0.000 | 0.000 | 0.000 | 0.145 | 0.122 | |||
| 1 spectrum, LAPALATGNTVVMK | 0.633 | 0.000 | 0.000 | 0.311 | 0.000 | 0.057 | 0.000 | |||
| 1 spectrum, LEEVLER | 0.720 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.280 | |||
| 8 spectra, ILGYIR | 0.747 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.253 | |||
| 3 spectra, IEEVIQR | 0.728 | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | 0.266 | |||
| 1 spectrum, TFPTVNPTTGEVIGHVAEGDR | 0.749 | 0.000 | 0.000 | 0.000 | 0.000 | 0.126 | 0.125 | |||
| 1 spectrum, LLQDCR | 0.737 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.263 | |||
| 4 spectra, TFVEESIYHEFLER | 0.751 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.249 | |||
| 2 spectra, LADLVER | 0.673 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.327 | |||
| 2 spectra, ADVDLAVR | 0.653 | 0.000 | 0.000 | 0.000 | 0.000 | 0.148 | 0.199 | |||
| 2 spectra, EEIFGPVQPLFK | 0.784 | 0.000 | 0.000 | 0.000 | 0.000 | 0.042 | 0.174 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
162 spectra |
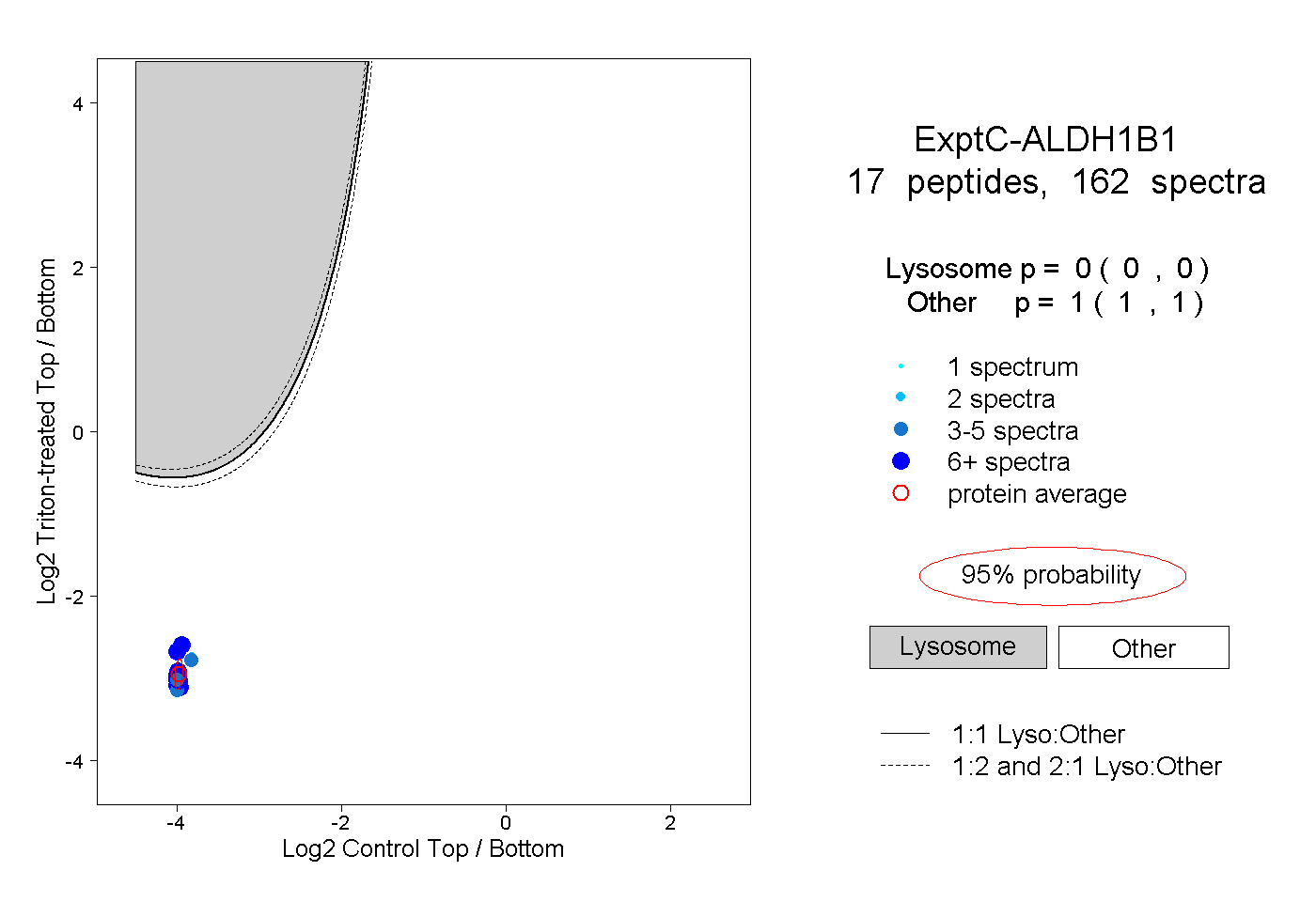 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
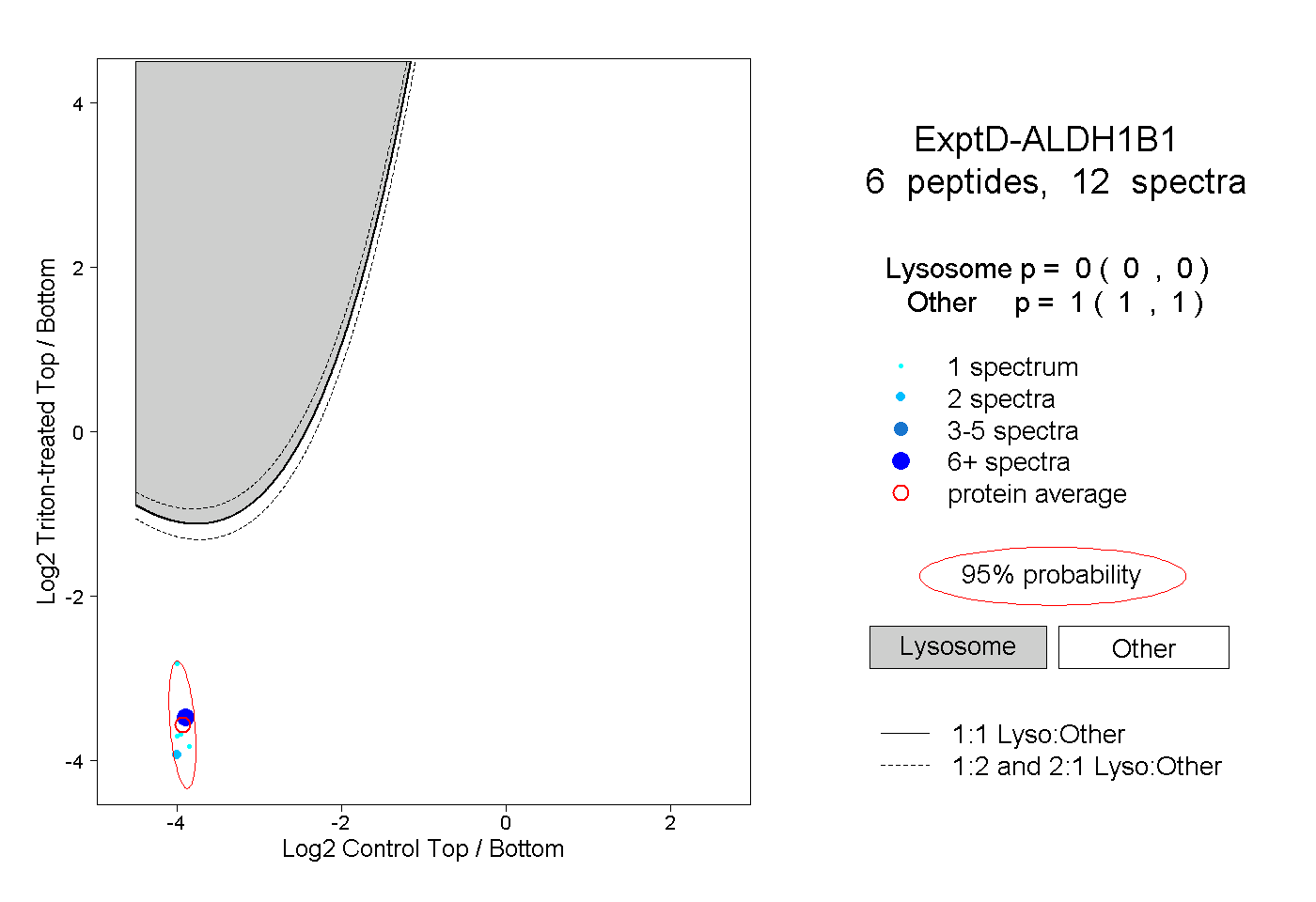 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |