peptides
spectra
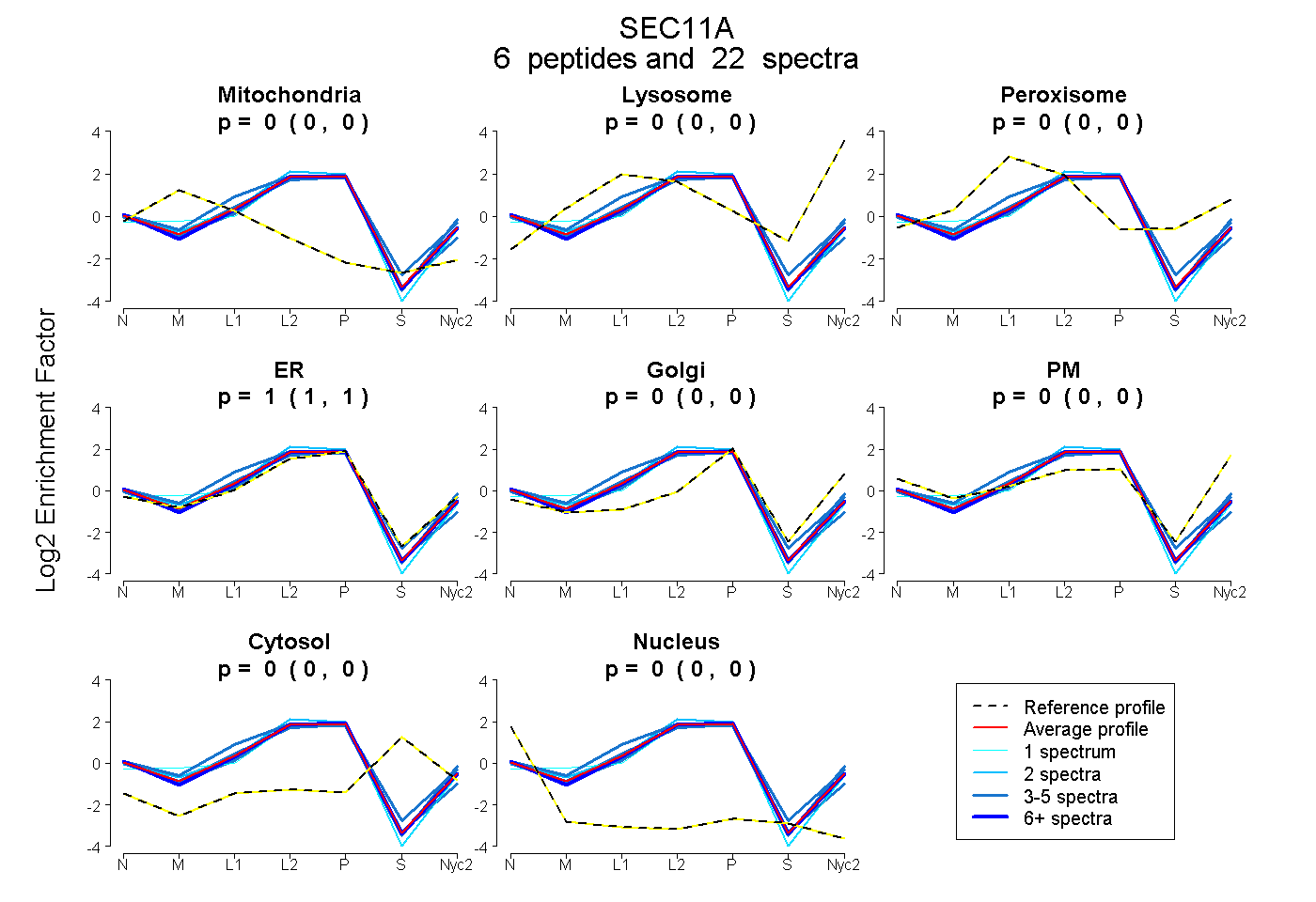
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 8 spectra, VGEIVVFR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, QGQHWLEK | 0.031 | 0.000 | 0.000 | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, MLSLDFLDDVR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, VEDPIR | 0.000 | 0.000 | 0.051 | 0.911 | 0.000 | 0.038 | 0.000 | 0.000 | ||
| 3 spectra, QDGHIK | 0.000 | 0.000 | 0.000 | 0.978 | 0.000 | 0.000 | 0.000 | 0.022 | ||
| 5 spectra, EIPIVHR | 0.000 | 0.000 | 0.040 | 0.960 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
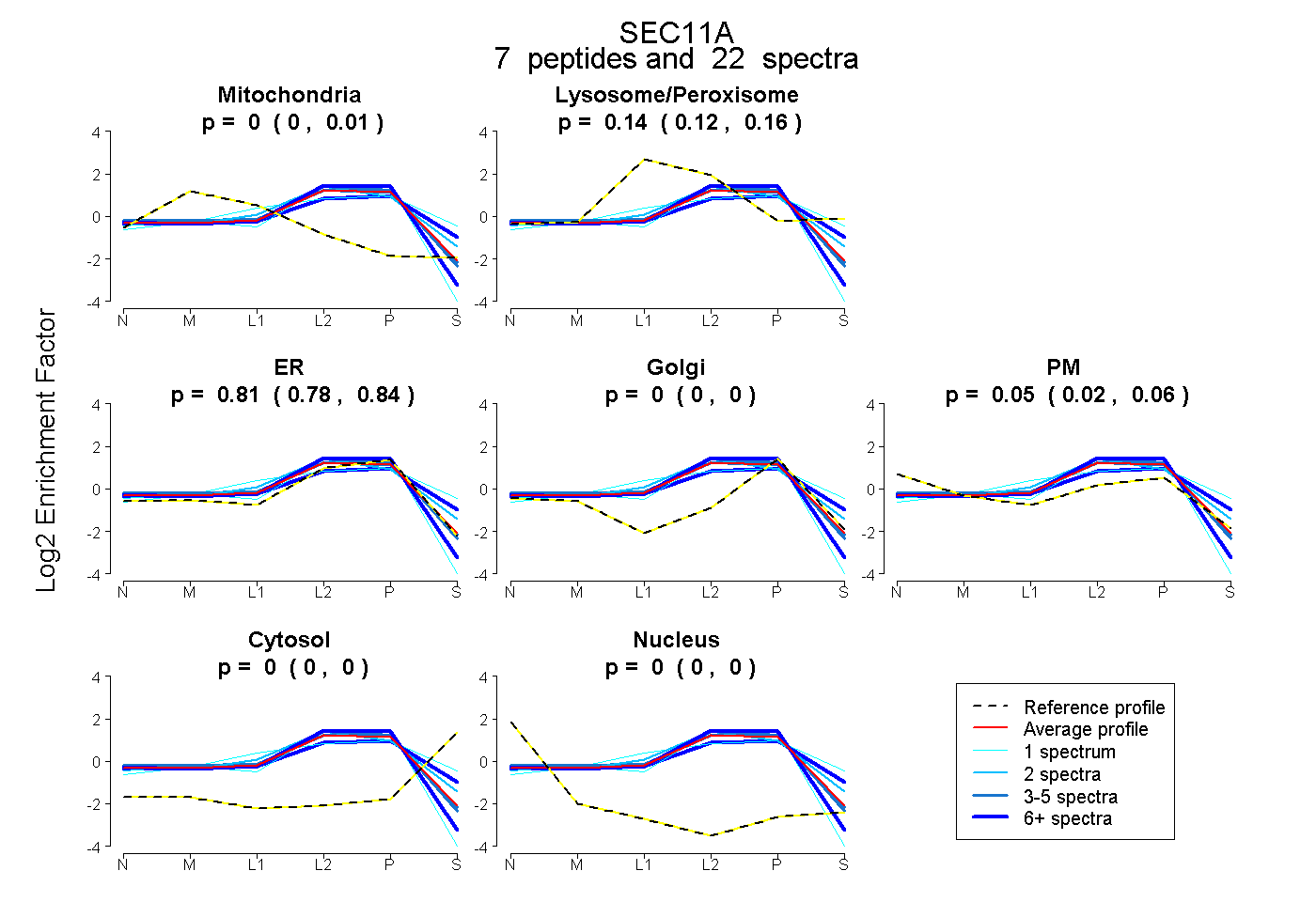 |
0.000 0.000 | 0.005 |
0.144 0.124 | 0.160 |
0.809 0.776 | 0.836 |
0.000 0.000 | 0.000 |
0.047 0.023 | 0.062 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
63 spectra |
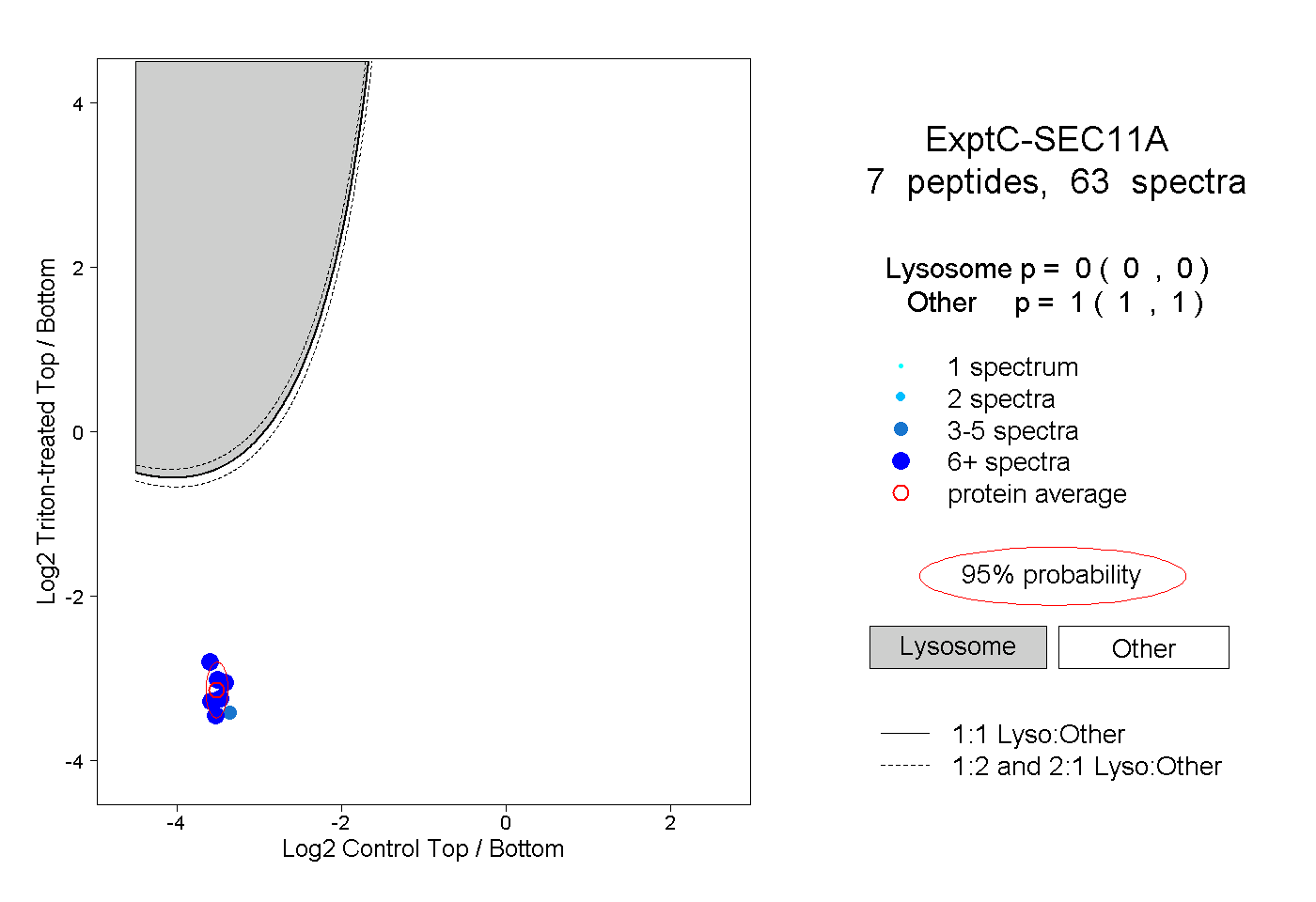 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
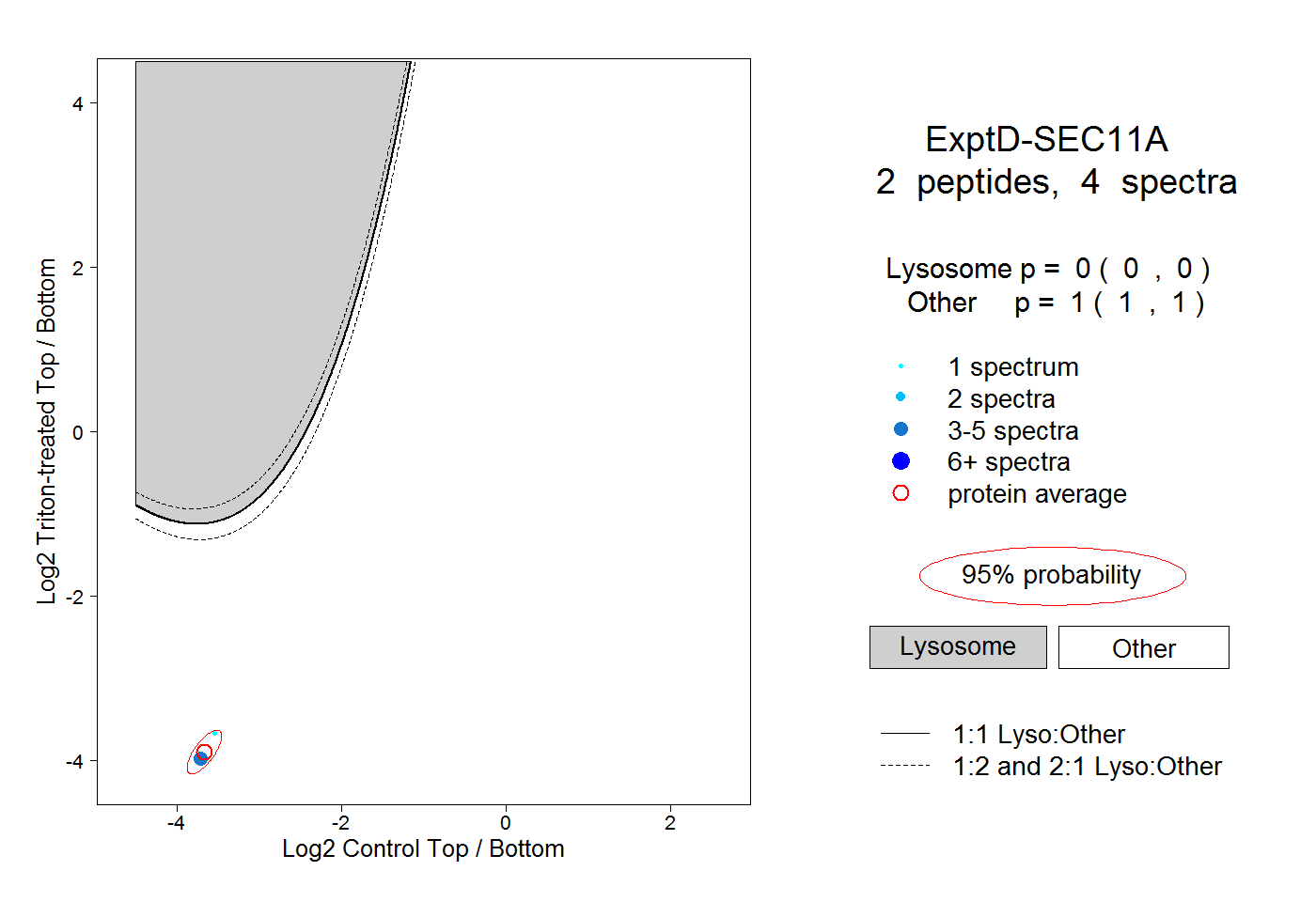 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |