peptides
spectra
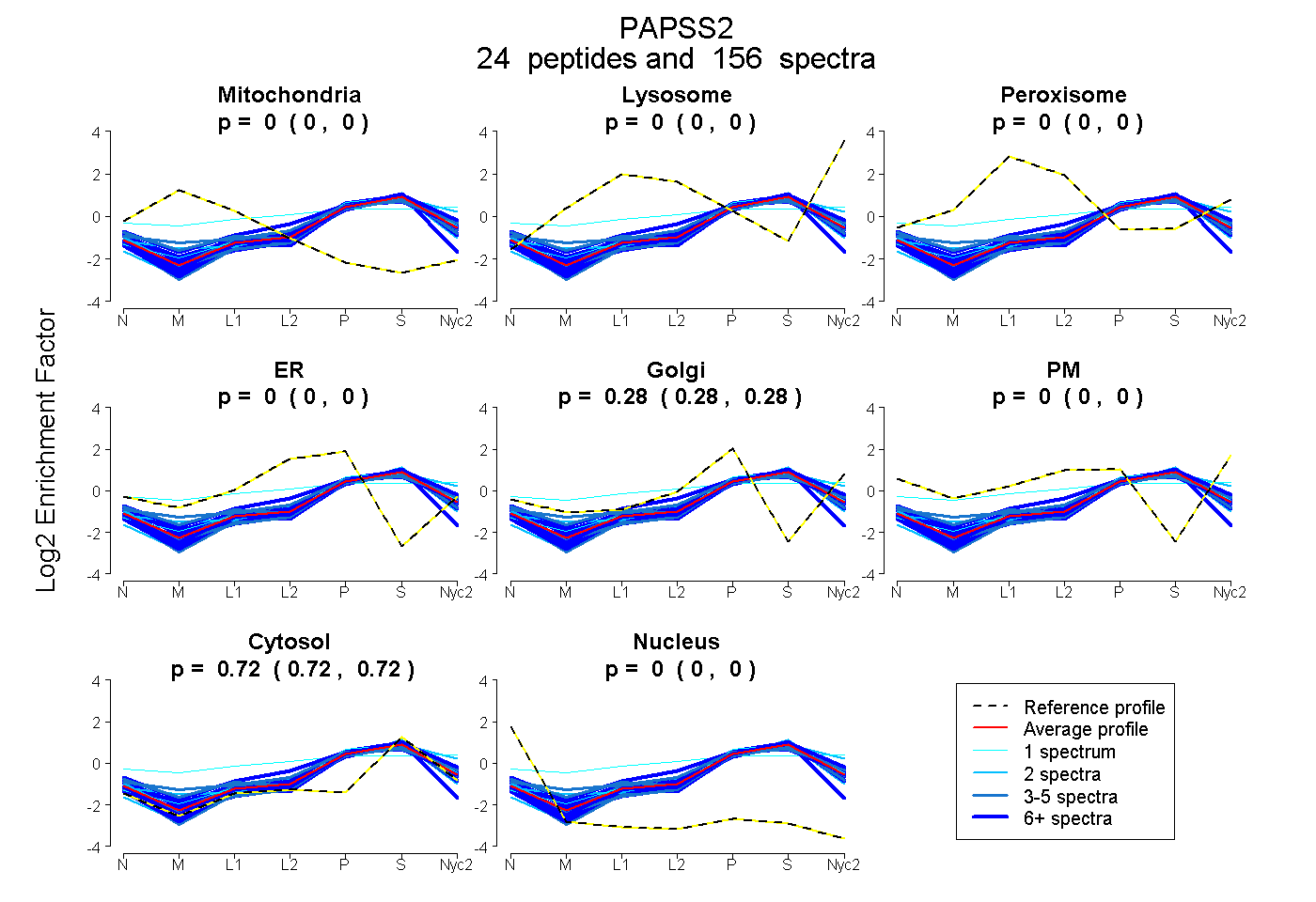
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.277 | 0.279
0.000 | 0.000
0.721 | 0.723
0.000 | 0.000
peptides
spectra
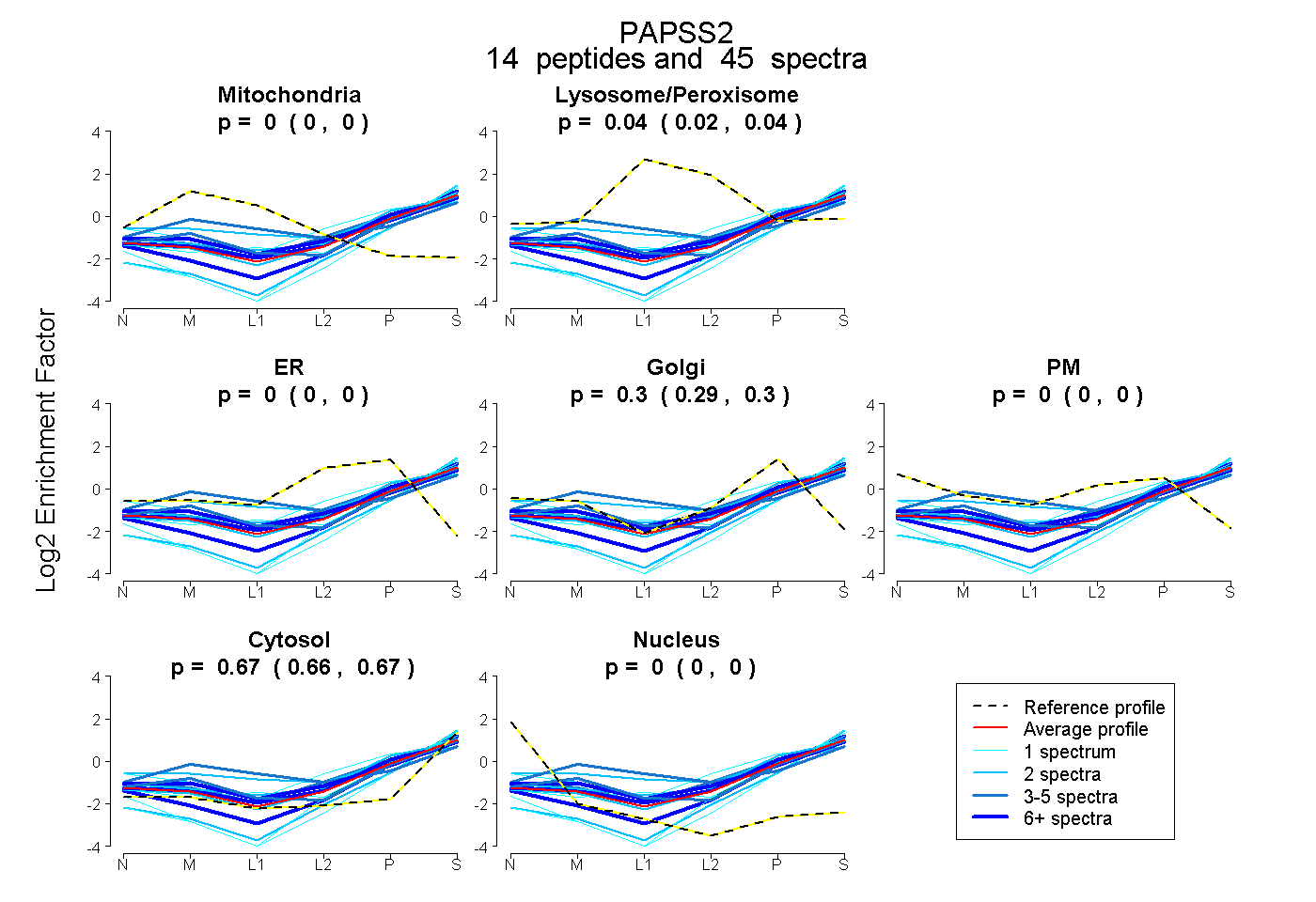
0.000 | 0.000
0.024 | 0.045
0.000 | 0.000
0.289 | 0.305
0.000 | 0.000
0.661 | 0.672
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
156 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.278 0.277 | 0.279 |
0.000 0.000 | 0.000 |
0.722 0.721 | 0.723 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
45 spectra |
 |
0.000 0.000 | 0.000 |
0.035 0.024 | 0.045 |
0.000 0.000 | 0.000 |
0.298 0.289 | 0.305 |
0.000 0.000 | 0.000 |
0.667 0.661 | 0.672 |
0.000 0.000 | 0.000 |
| 5 spectra, VLTDYYR | 0.000 | 0.066 | 0.000 | 0.291 | 0.000 | 0.643 | 0.000 | |||
| 1 spectrum, MIAGANFYIVGR | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | 0.957 | 0.000 | |||
| 3 spectra, AELETLPSLPITK | 0.000 | 0.099 | 0.000 | 0.323 | 0.000 | 0.578 | 0.000 | |||
| 8 spectra, VALLQDPEFYEHR | 0.000 | 0.115 | 0.000 | 0.283 | 0.000 | 0.602 | 0.000 | |||
| 2 spectra, FALMYEGR | 0.000 | 0.000 | 0.000 | 0.073 | 0.000 | 0.927 | 0.000 | |||
| 2 spectra, LTPLELK | 0.000 | 0.112 | 0.000 | 0.323 | 0.000 | 0.565 | 0.000 | |||
| 1 spectrum, GQVVGTR | 0.000 | 0.098 | 0.000 | 0.205 | 0.000 | 0.697 | 0.000 | |||
| 8 spectra, DDDVPLDWR | 0.000 | 0.000 | 0.000 | 0.237 | 0.000 | 0.763 | 0.000 | |||
| 2 spectra, EGEDPPDGFMAPK | 0.000 | 0.003 | 0.030 | 0.294 | 0.000 | 0.673 | 0.000 | |||
| 3 spectra, NPVHNGHALLMQDTR | 0.107 | 0.260 | 0.000 | 0.157 | 0.000 | 0.476 | 0.000 | |||
| 6 spectra, HDEFDFISGTR | 0.000 | 0.058 | 0.000 | 0.324 | 0.000 | 0.618 | 0.000 | |||
| 2 spectra, DLYEPTHGGK | 0.000 | 0.263 | 0.000 | 0.271 | 0.000 | 0.466 | 0.000 | |||
| 1 spectrum, GCTVWLTGLSGAGK | 0.000 | 0.155 | 0.000 | 0.400 | 0.000 | 0.445 | 0.000 | |||
| 1 spectrum, GIHELFVPENK | 0.000 | 0.000 | 0.000 | 0.166 | 0.000 | 0.834 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
134 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
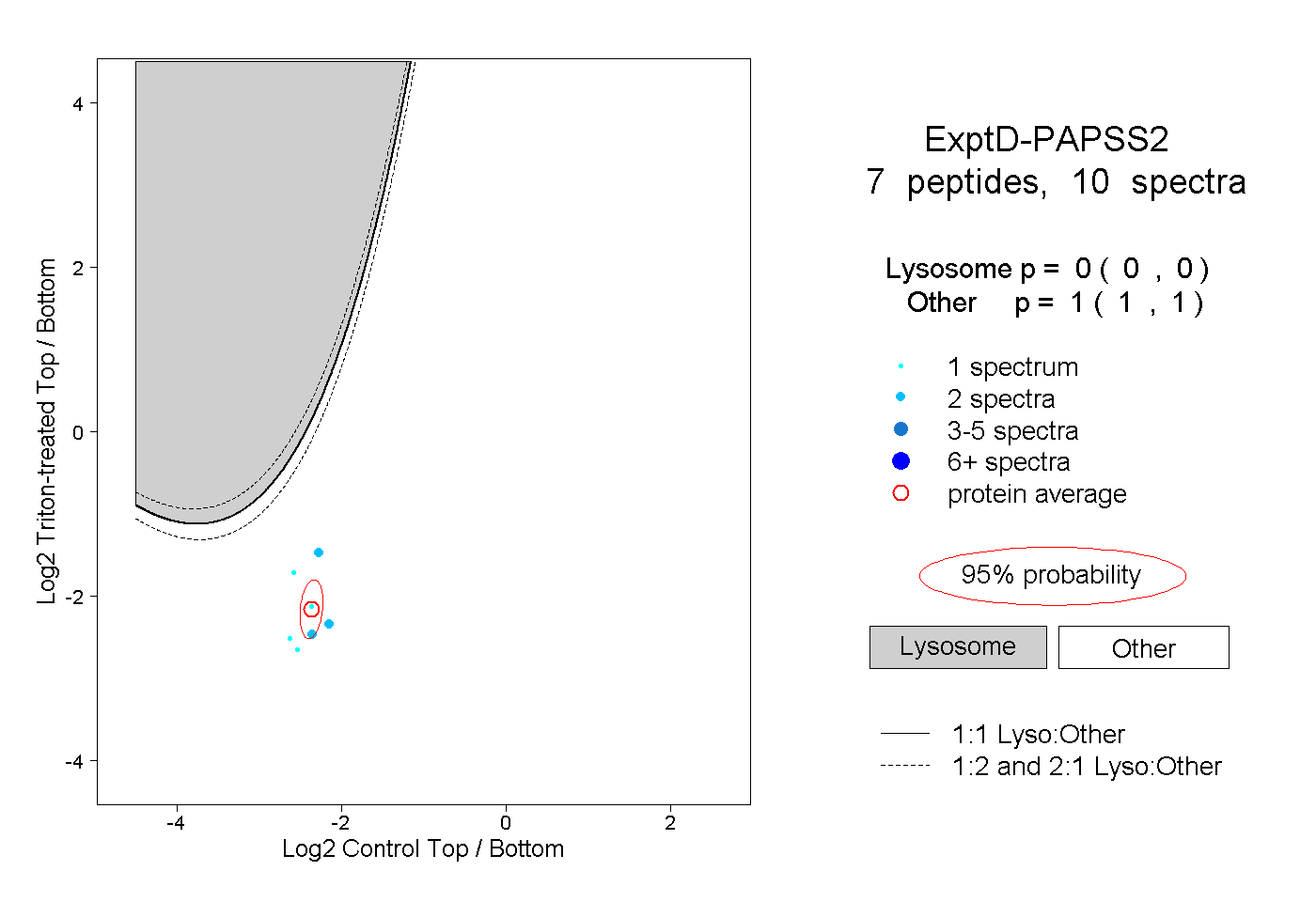 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |