peptides
spectra
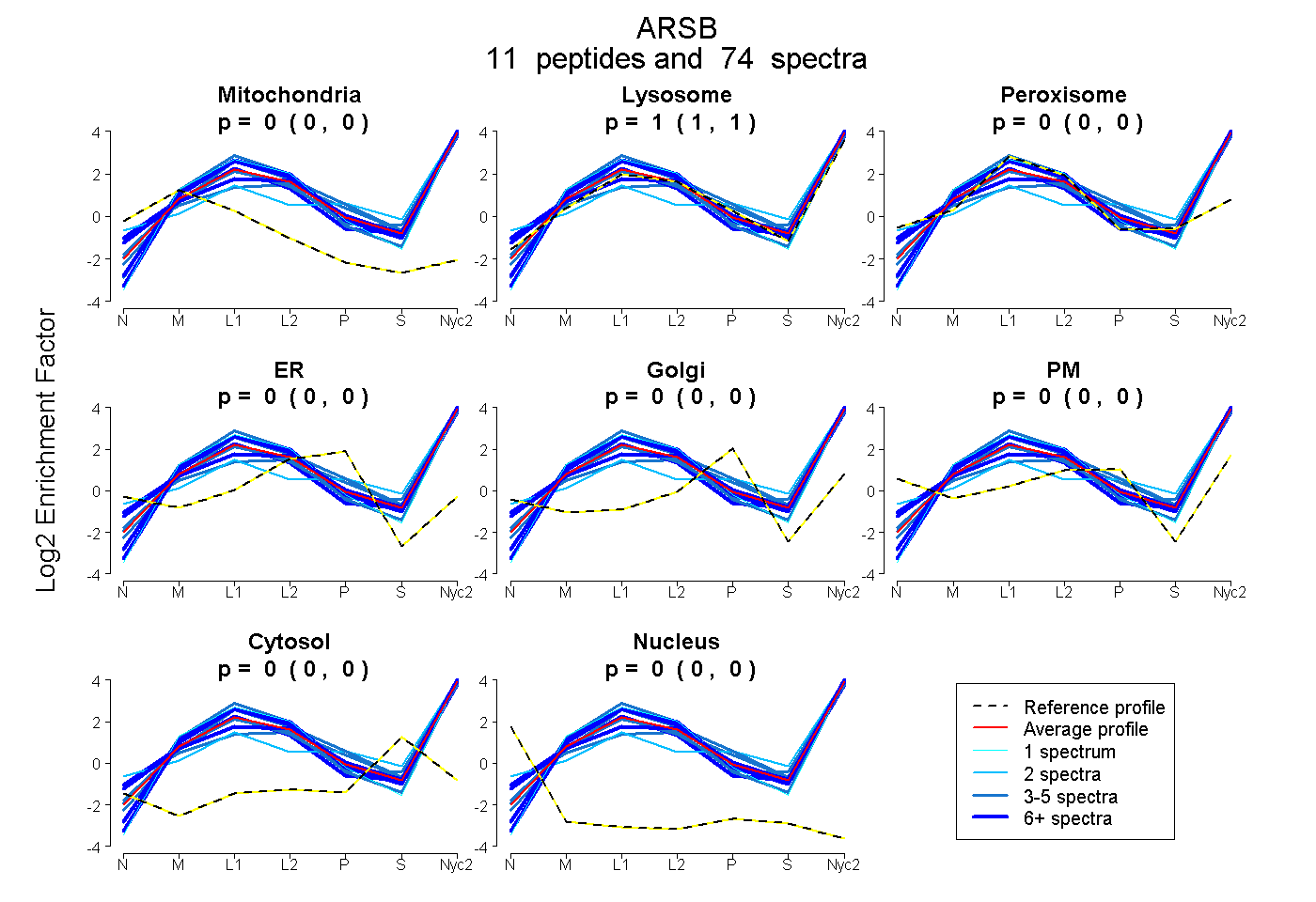
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
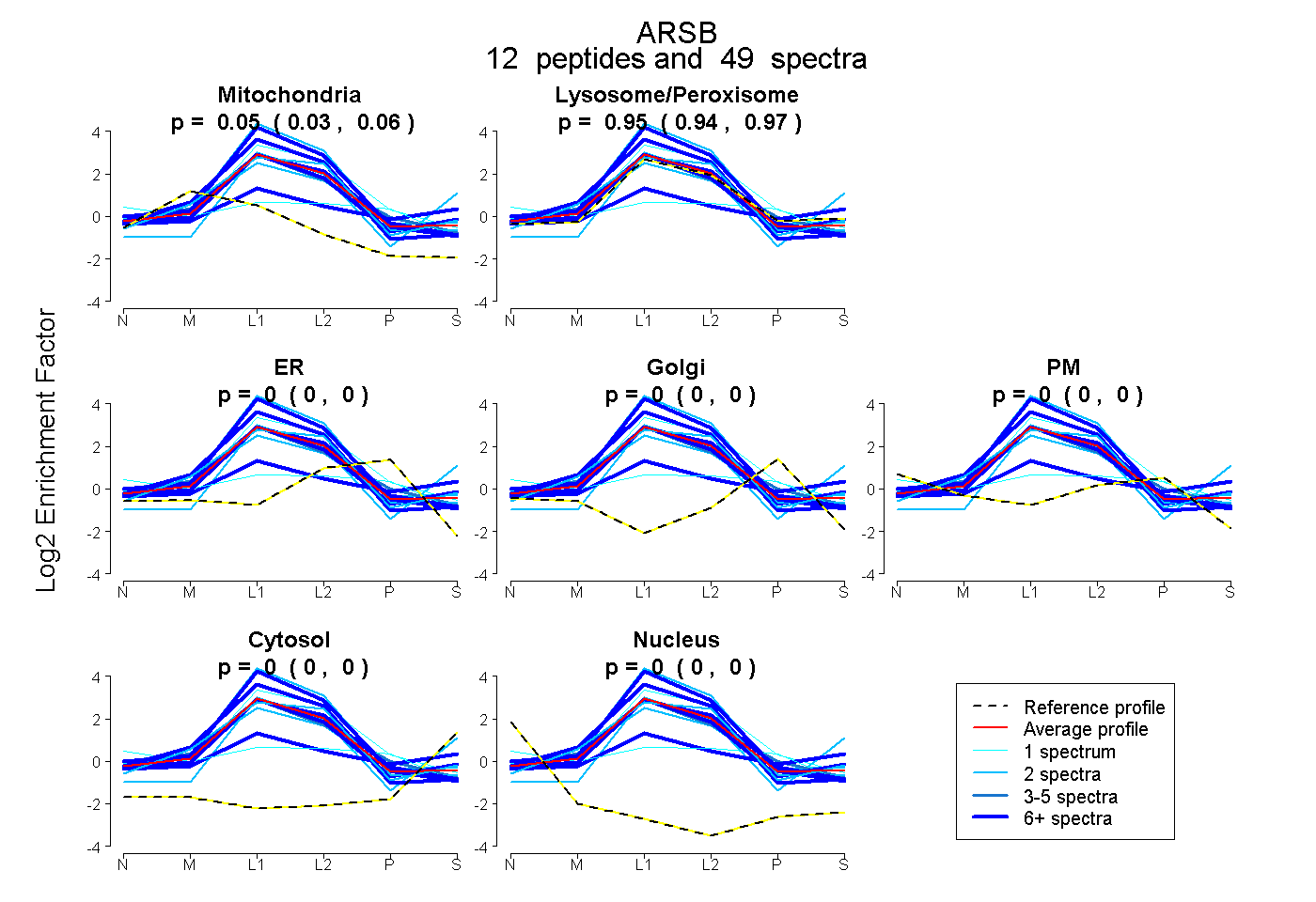
0.031 | 0.057
0.940 | 0.966
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
74 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
49 spectra |
 |
0.045 0.031 | 0.057 |
0.955 0.940 | 0.966 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 8 spectra, LLPQLLK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, EHPHIVQNLLSR | 0.025 | 0.677 | 0.000 | 0.095 | 0.000 | 0.203 | 0.000 | |||
| 2 spectra, WHLGMYR | 0.043 | 0.957 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, SGGNNWPLR | 0.018 | 0.982 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ECLPTR | 0.093 | 0.905 | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | |||
| 9 spectra, SQLLTGR | 0.067 | 0.933 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DGEEPAK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GTLWEGGIR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, CALDLR | 0.000 | 0.920 | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | |||
| 2 spectra, DAGYATHMVGK | 0.136 | 0.864 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EYTDIYSTNIFTK | 0.028 | 0.380 | 0.000 | 0.000 | 0.592 | 0.000 | 0.000 | |||
| 6 spectra, GAGFVASPLLK | 0.052 | 0.948 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
279 spectra |
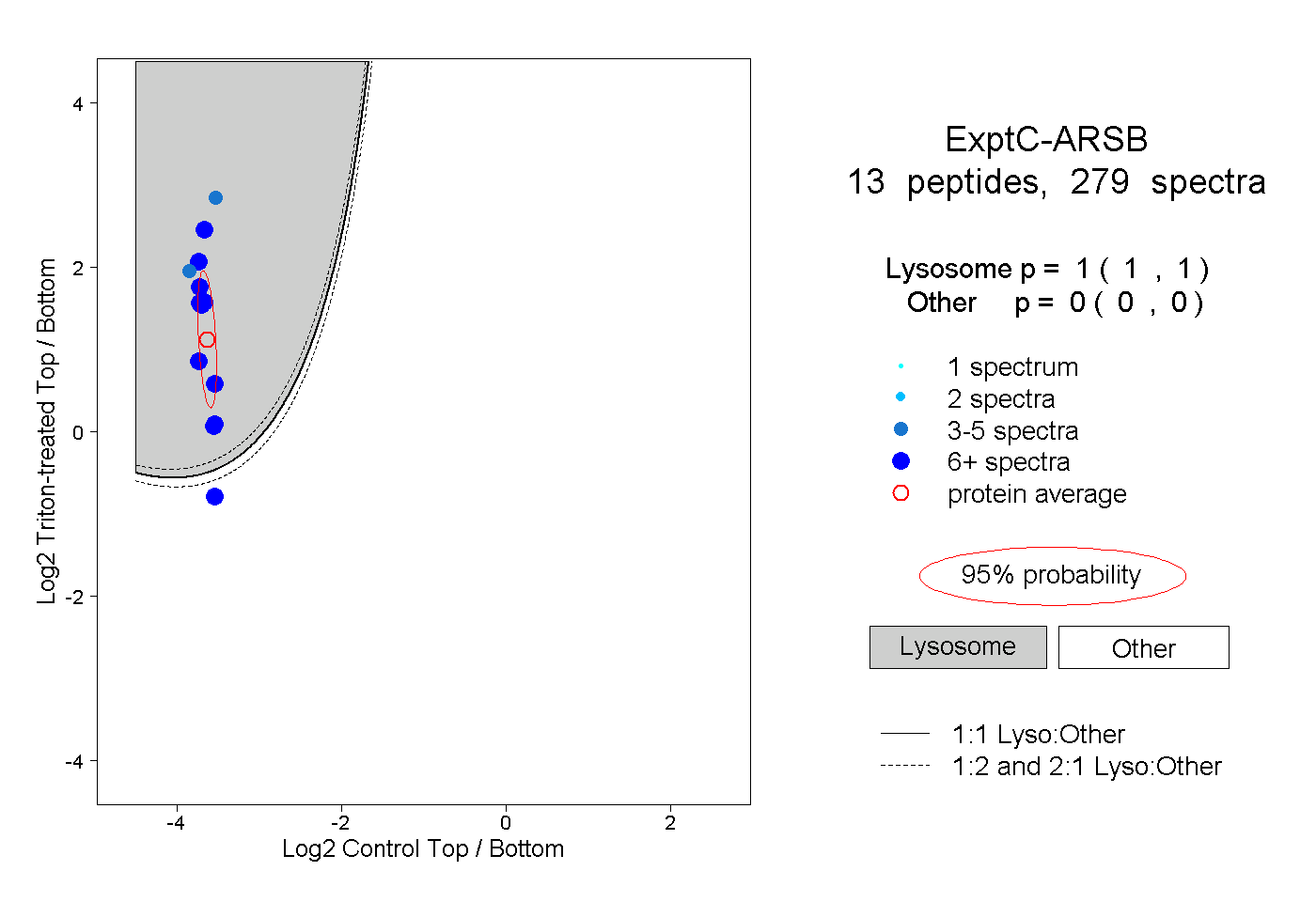 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
22 spectra |
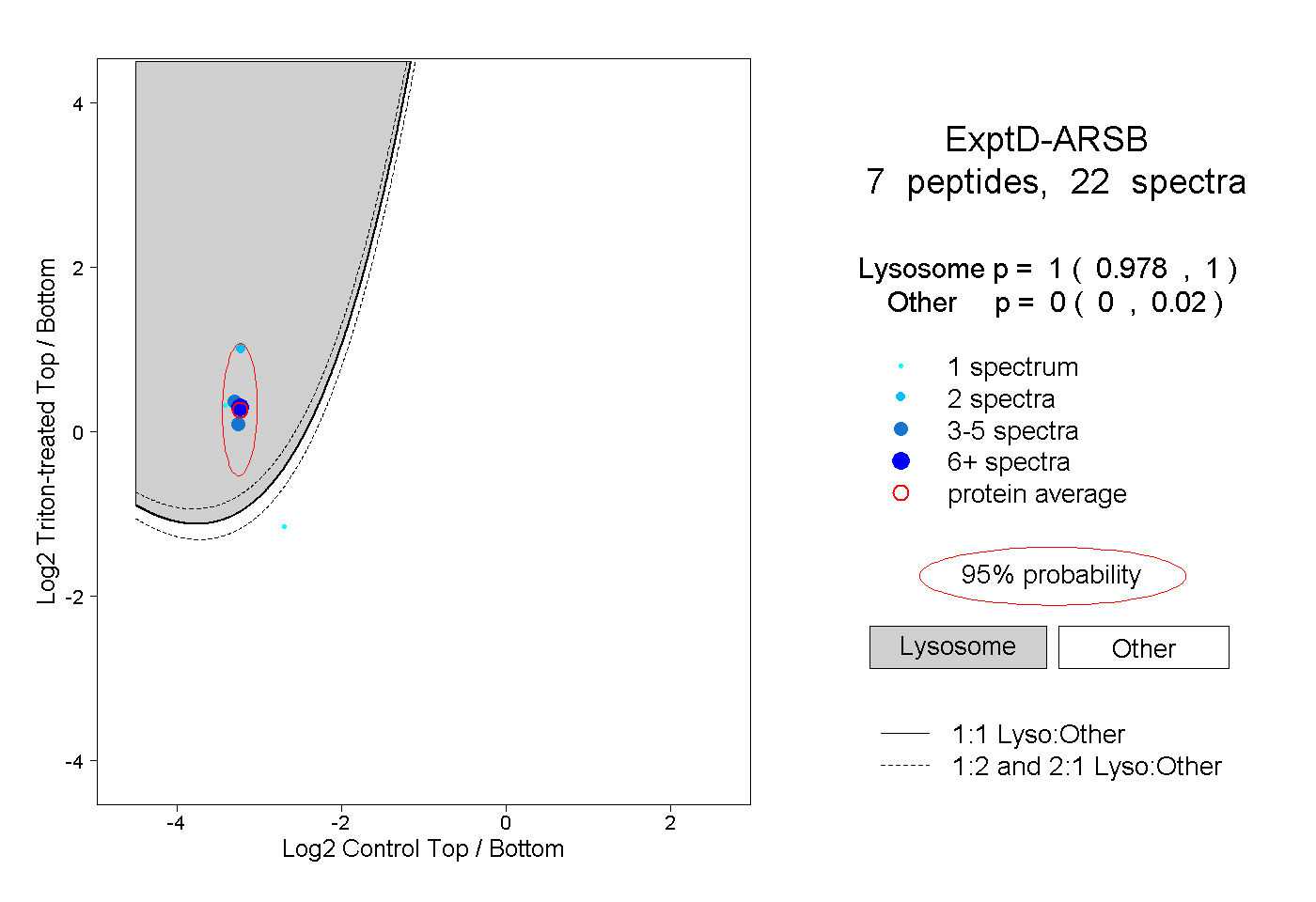 |
1.000 0.978 | 1.000 |
0.000 0.000 | 0.020 |