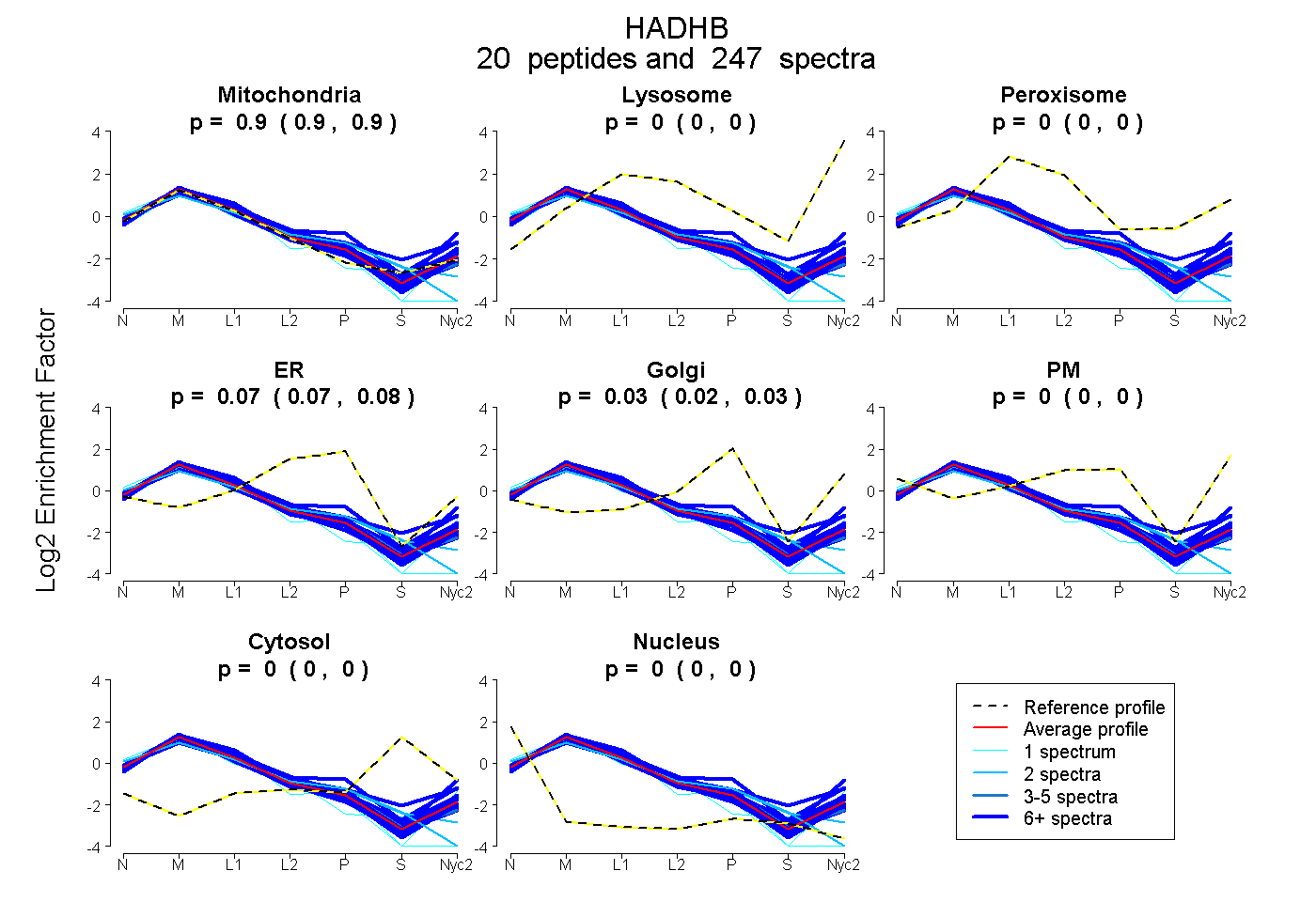
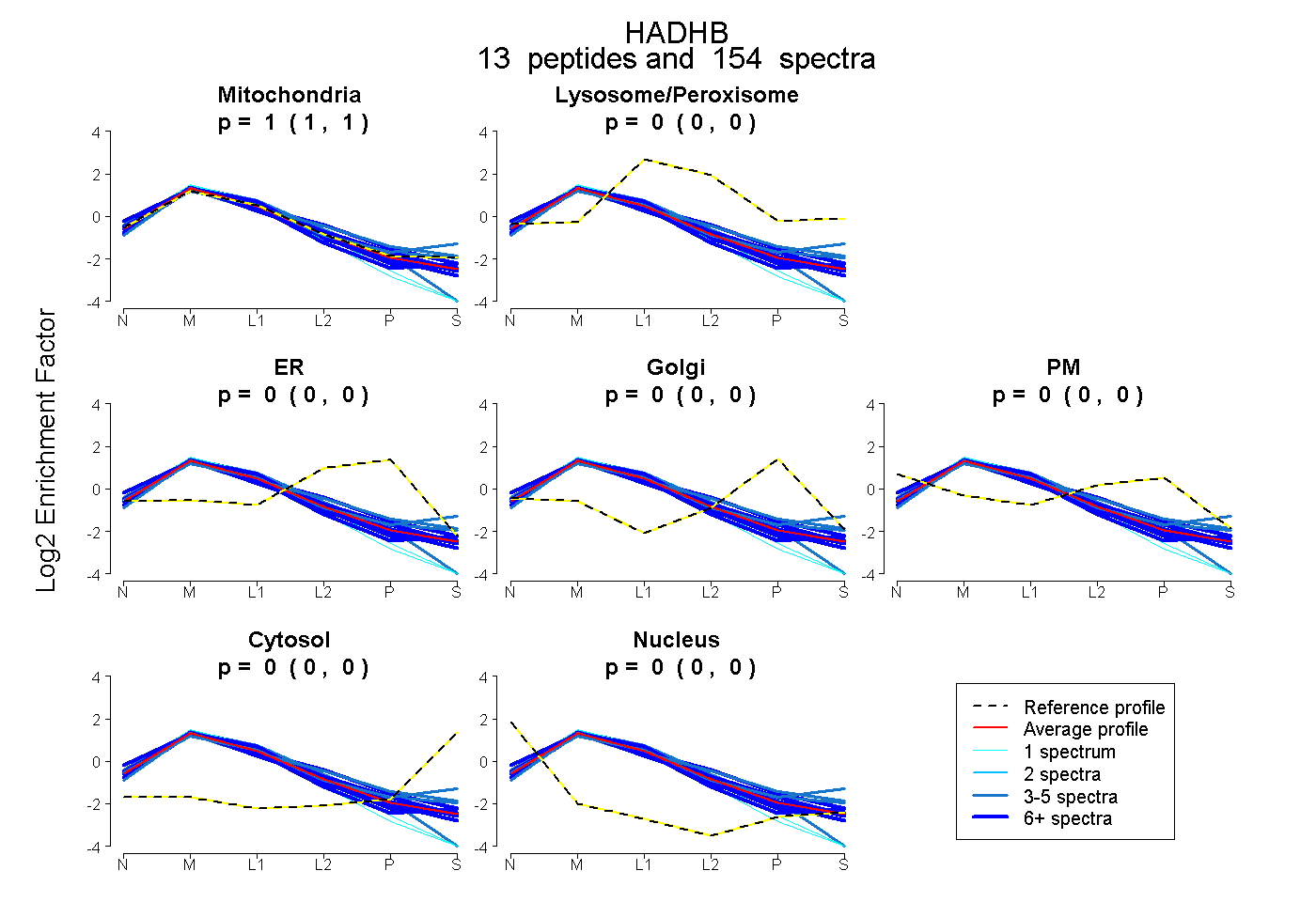
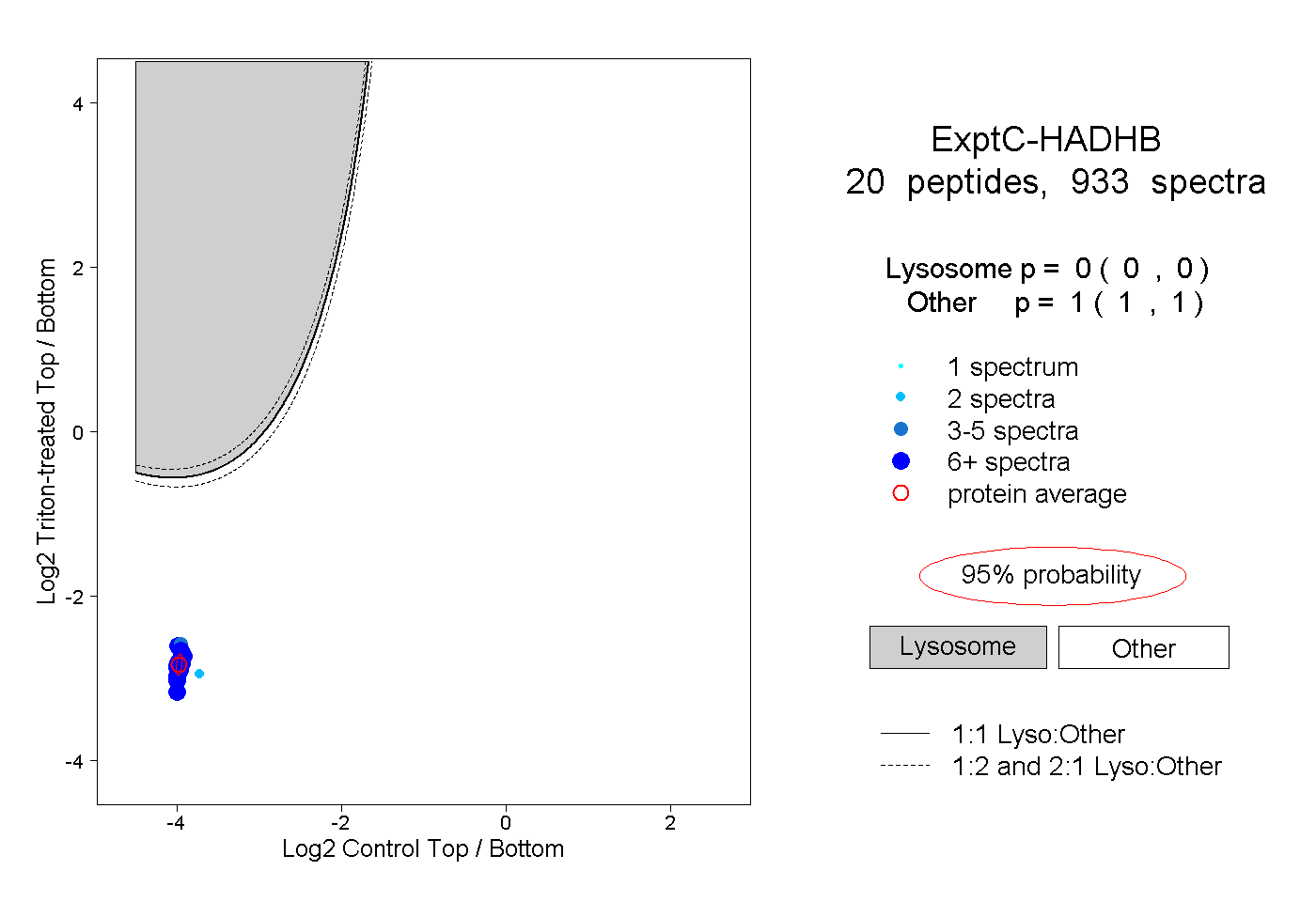
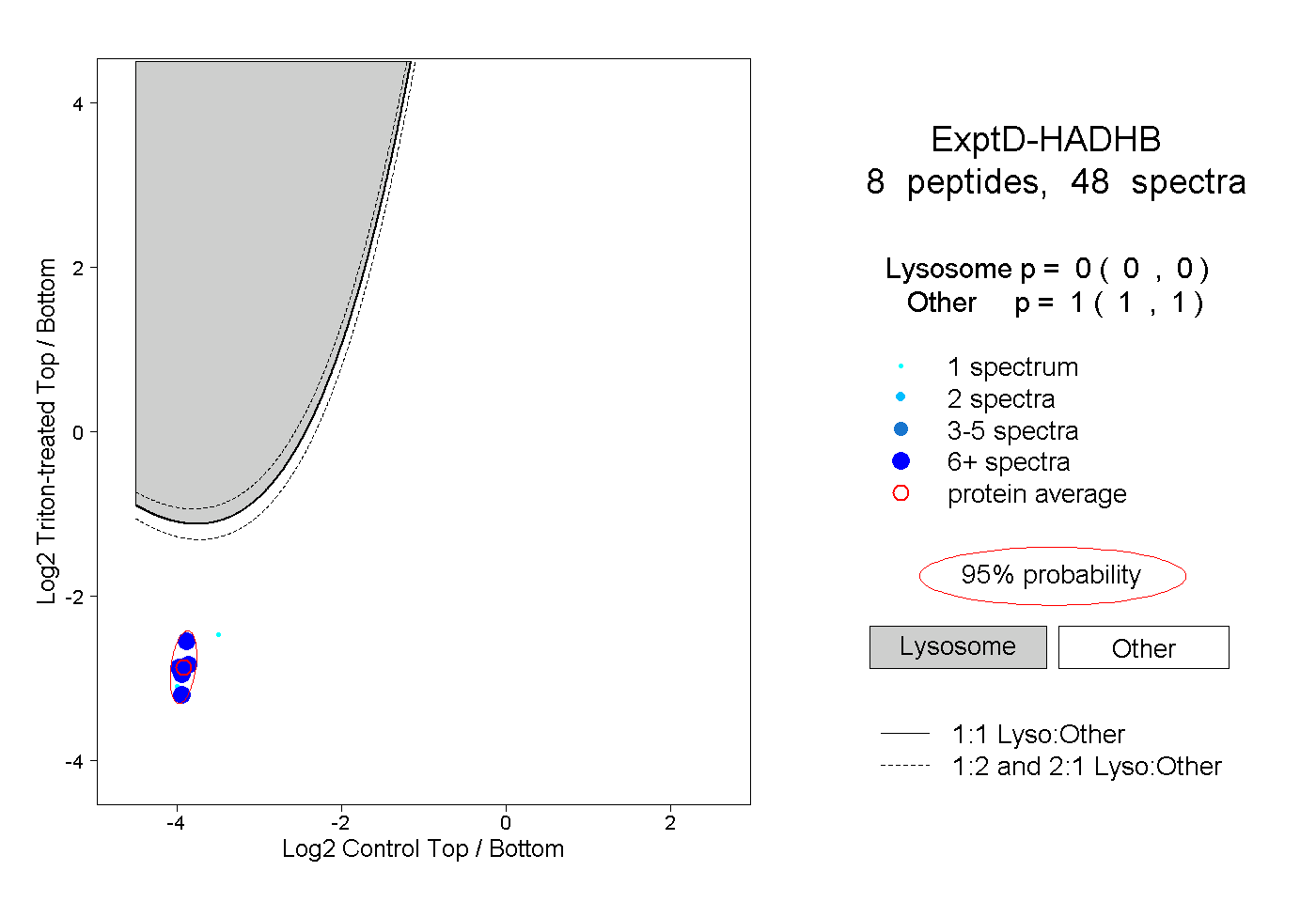
| 72 spectra, LAAAFAVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DFIYVSQDPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 36 spectra, MMLDLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 50 spectra, NIVVVEGVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, IPFLLSGTSYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 74 spectra, DLMPHDLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 108 spectra, LSLLTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 80 spectra, VGAPPLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, DQLLLGPTYATPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, AMDSDWFAQNYMGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 40 spectra, DNGIRPSSLEQMAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 81 spectra, AALSGLLYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 55 spectra, SHSLAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 46 spectra, EAALGAGFSDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 100 spectra, LVMAAANR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DVVDYIIFGTVIQEVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, TSNVAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 85 spectra, TLAKPNLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 47 spectra, ALAMGYKPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LNFLSPELPAVAEFSTNETMGHSADR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |