peptides
spectra
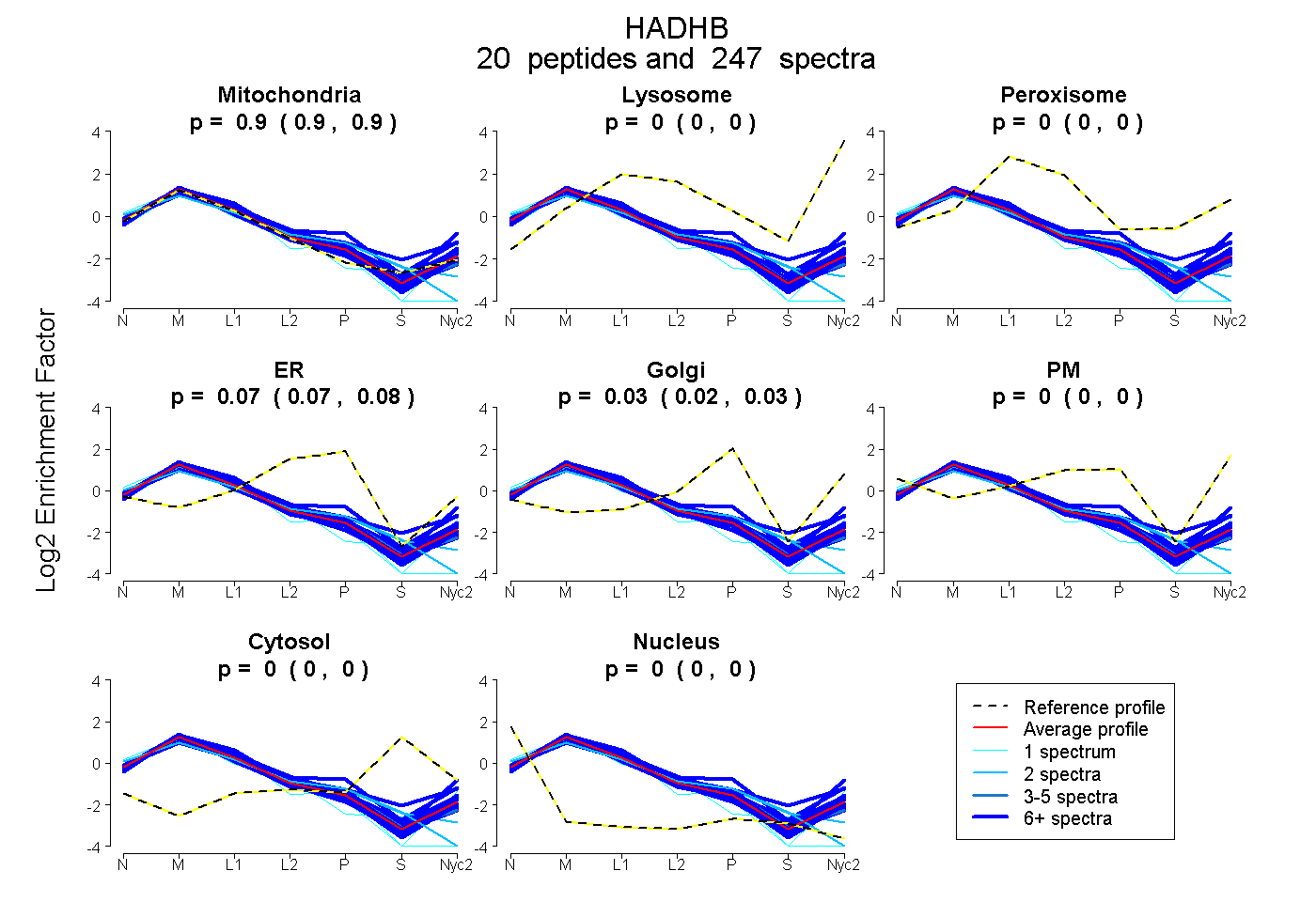
0.899 | 0.902
0.000 | 0.000
0.000 | 0.000
0.069 | 0.076
0.022 | 0.030
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
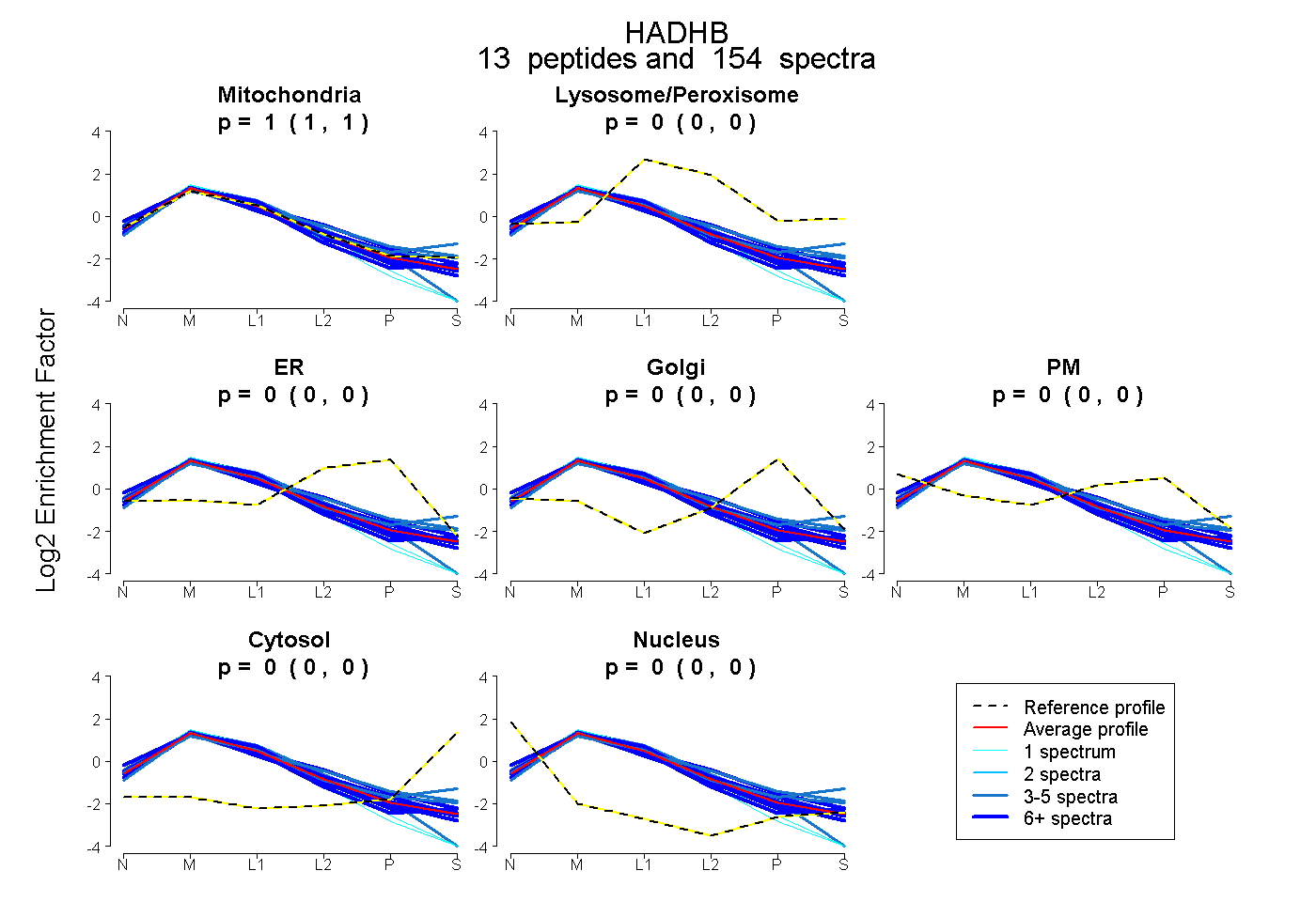
0.998 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.002
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
247 spectra |
 |
0.901 0.899 | 0.902 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.073 0.069 | 0.076 |
0.026 0.022 | 0.030 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
154 spectra |
 |
0.999 0.998 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.002 |
| 34 spectra, LAAAFAVSR | 0.955 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.045 | |||
| 3 spectra, DNGIRPSSLEQMAK | 0.942 | 0.000 | 0.000 | 0.058 | 0.000 | 0.000 | 0.000 | |||
| 30 spectra, AALSGLLYR | 0.982 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.018 | |||
| 3 spectra, SHSLAK | 0.874 | 0.022 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EAALGAGFSDK | 0.996 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.004 | |||
| 31 spectra, LVMAAANR | 0.988 | 0.000 | 0.000 | 0.012 | 0.000 | 0.000 | 0.000 | |||
| 18 spectra, NIVVVEGVR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, IPFLLSGTSYK | 0.948 | 0.000 | 0.052 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DVVDYIIFGTVIQEVK | 0.972 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.028 | |||
| 9 spectra, DLMPHDLAR | 0.893 | 0.000 | 0.107 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, TSNVAR | 0.947 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.053 | |||
| 3 spectra, VGAPPLEK | 0.859 | 0.061 | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | |||
| 3 spectra, DQLLLGPTYATPK | 0.985 | 0.000 | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
933 spectra |
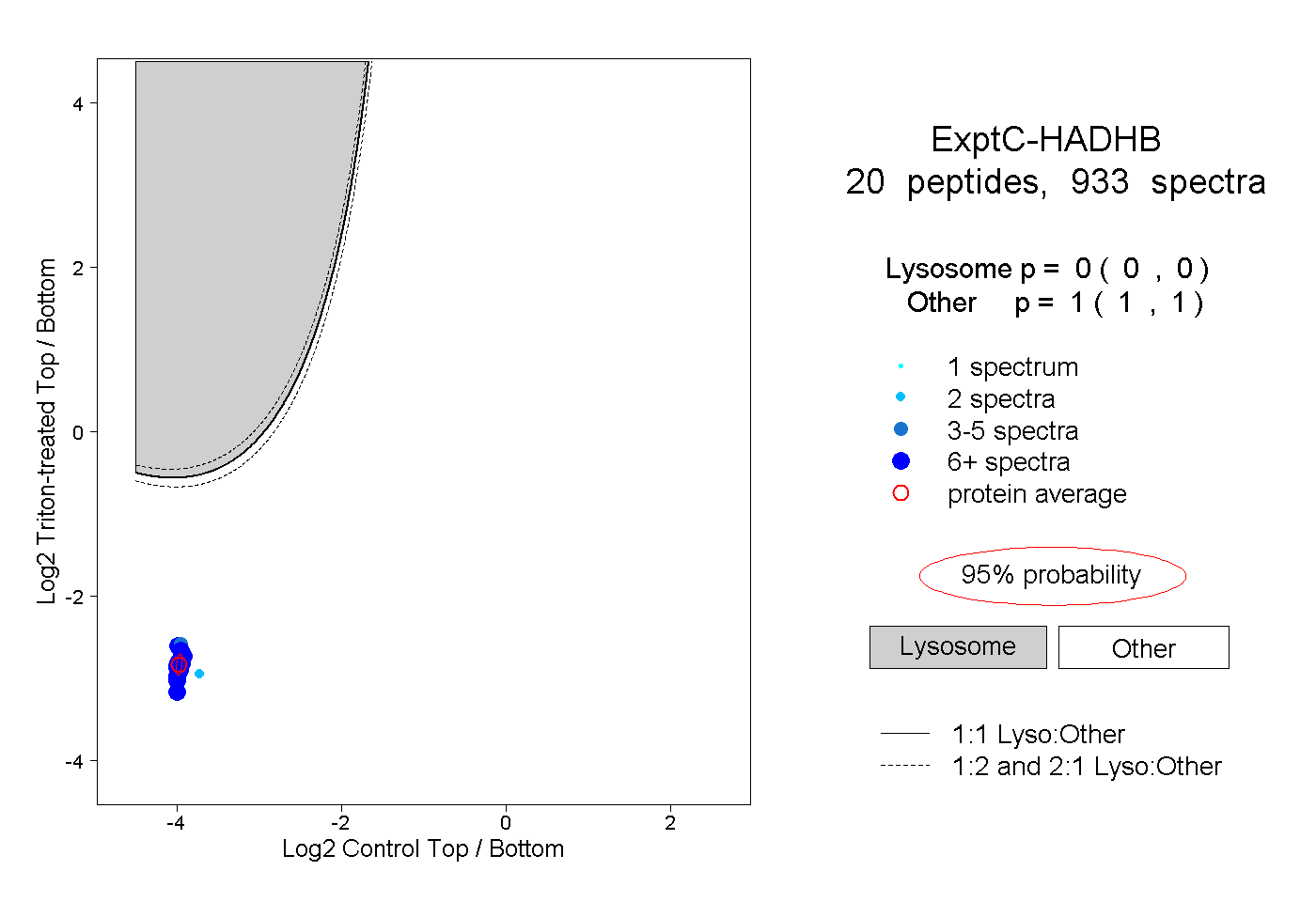 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
48 spectra |
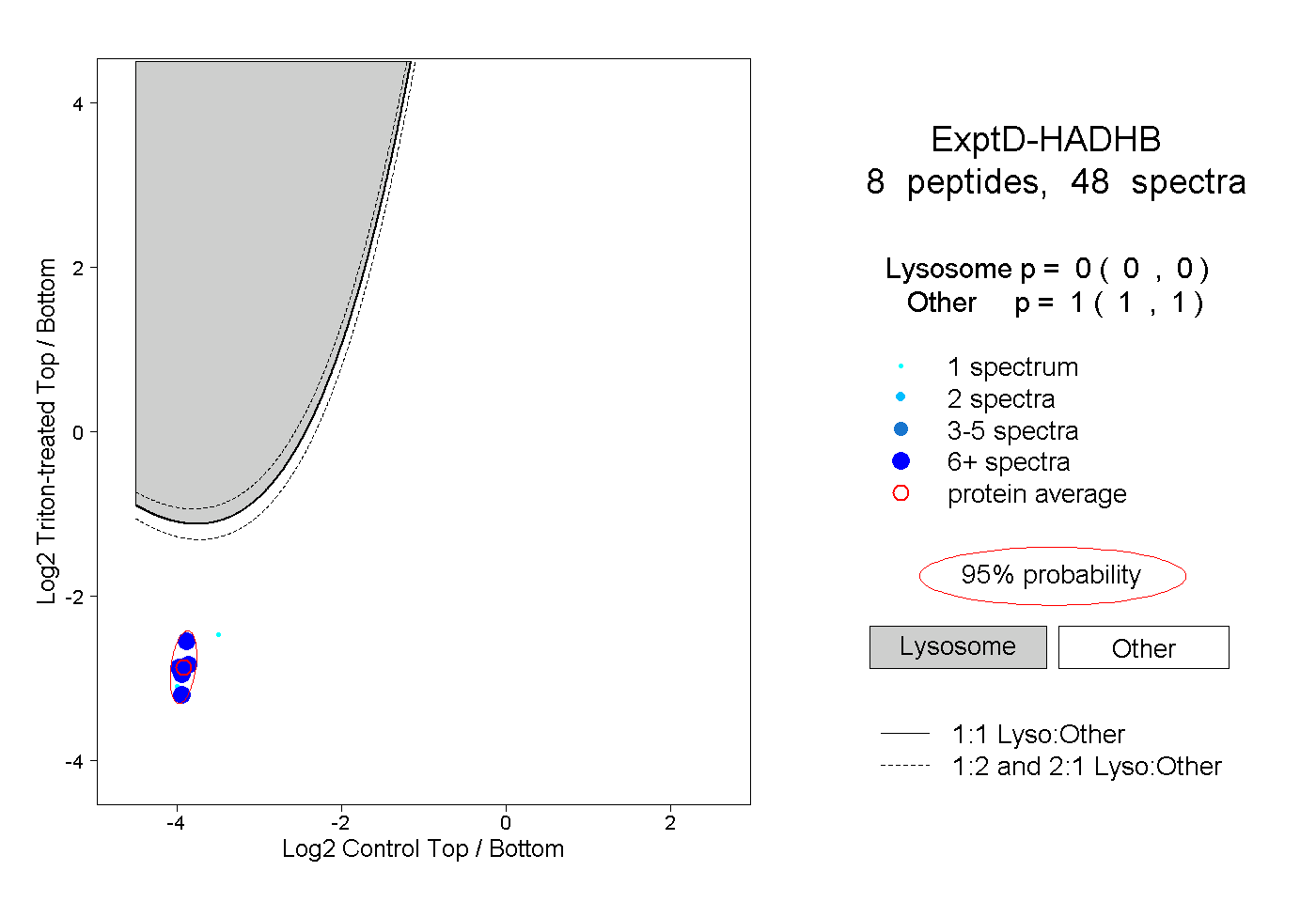 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |