peptides
spectra
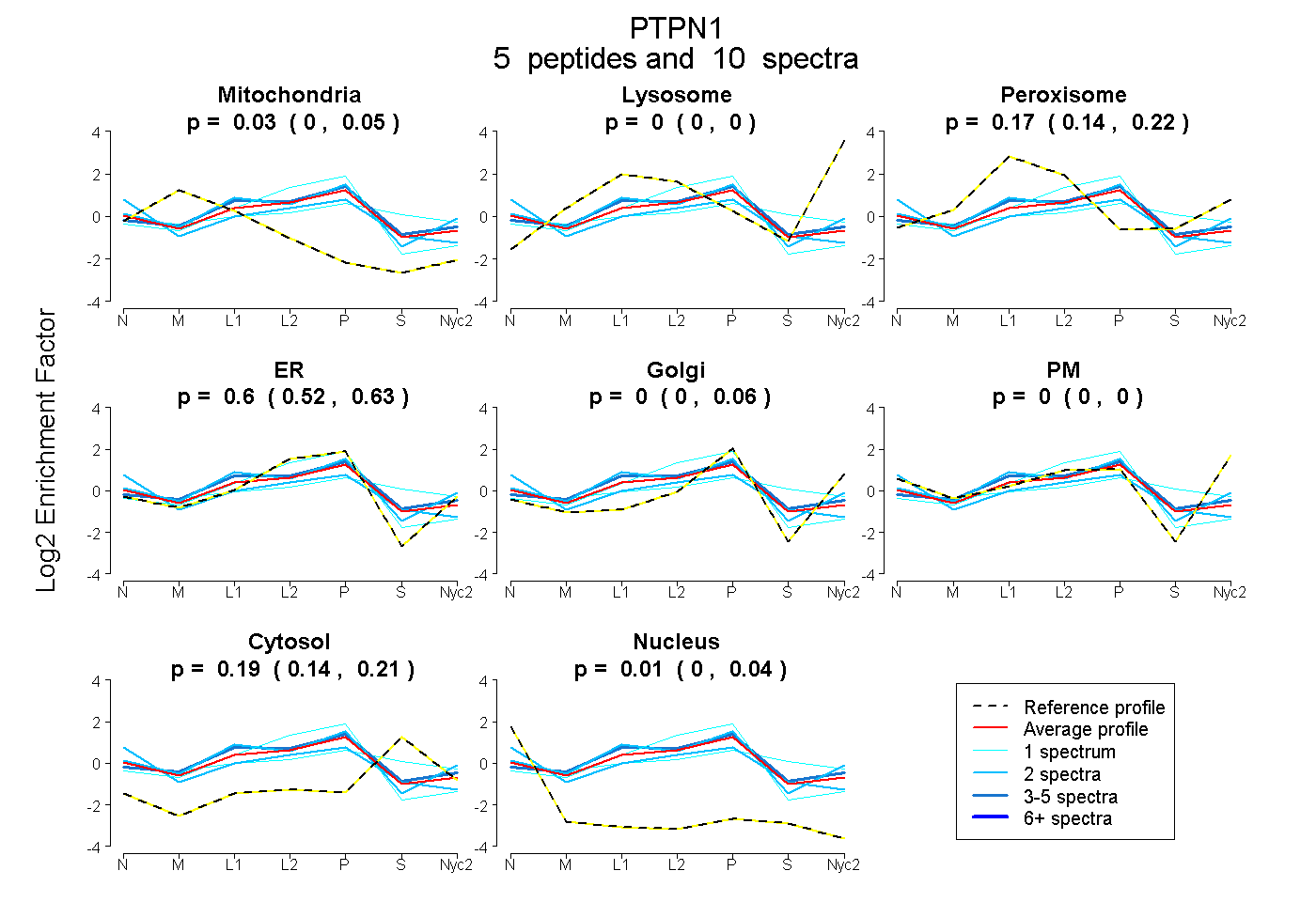
0.000 | 0.049
0.000 | 0.000
0.136 | 0.220
0.518 | 0.627
0.000 | 0.062
0.000 | 0.000
0.144 | 0.212
0.000 | 0.041
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
10 spectra |
 |
0.025 0.000 | 0.049 |
0.000 0.000 | 0.000 |
0.175 0.136 | 0.220 |
0.599 0.518 | 0.627 |
0.000 0.000 | 0.062 |
0.000 0.000 | 0.000 |
0.189 0.144 | 0.212 |
0.012 0.000 | 0.041 |
| 1 spectrum, MGLIQTADQLR | 0.037 | 0.000 | 0.029 | 0.861 | 0.000 | 0.000 | 0.073 | 0.000 | ||
| 4 spectra, GVVMLNR | 0.000 | 0.000 | 0.258 | 0.527 | 0.052 | 0.000 | 0.163 | 0.000 | ||
| 1 spectrum, EMVFDDTNLK | 0.020 | 0.000 | 0.285 | 0.128 | 0.230 | 0.000 | 0.337 | 0.000 | ||
| 2 spectra, LTLISEDVK | 0.000 | 0.000 | 0.320 | 0.333 | 0.300 | 0.000 | 0.010 | 0.037 | ||
| 2 spectra, HEASDFPCR | 0.000 | 0.000 | 0.205 | 0.491 | 0.000 | 0.000 | 0.132 | 0.172 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
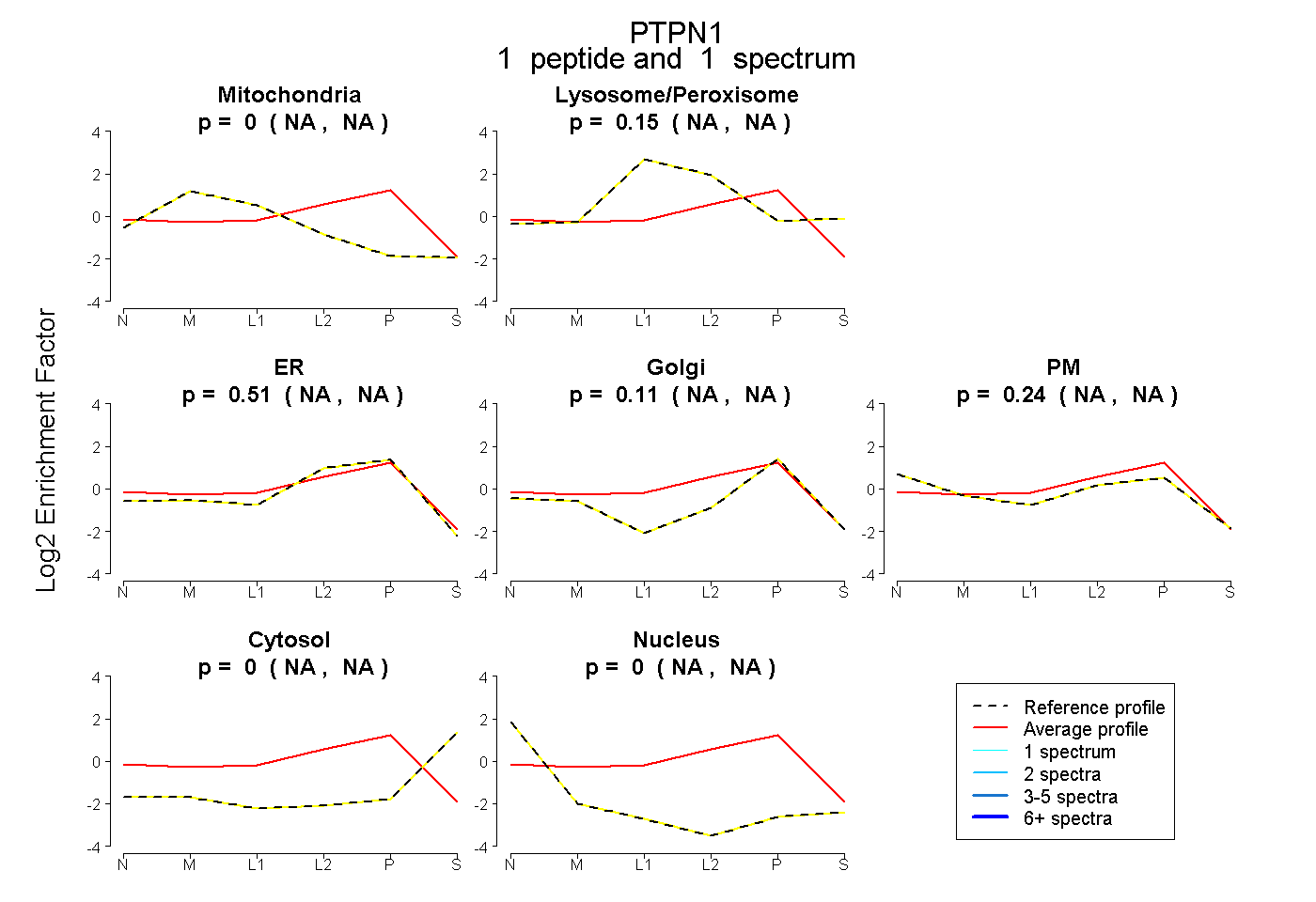 |
0.000 NA | NA |
0.146 NA | NA |
0.511 NA | NA |
0.106 NA | NA |
0.237 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
38 spectra |
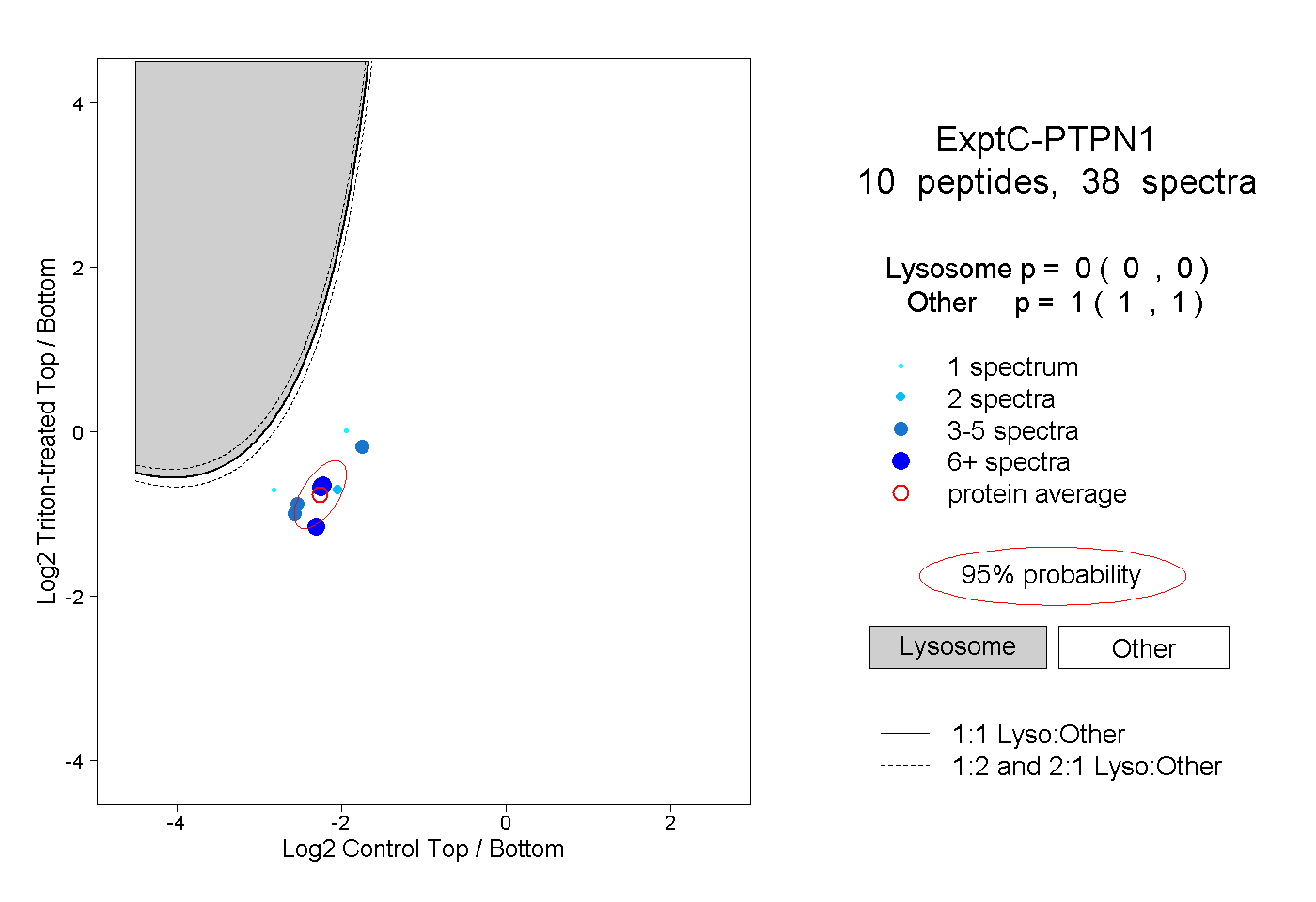 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
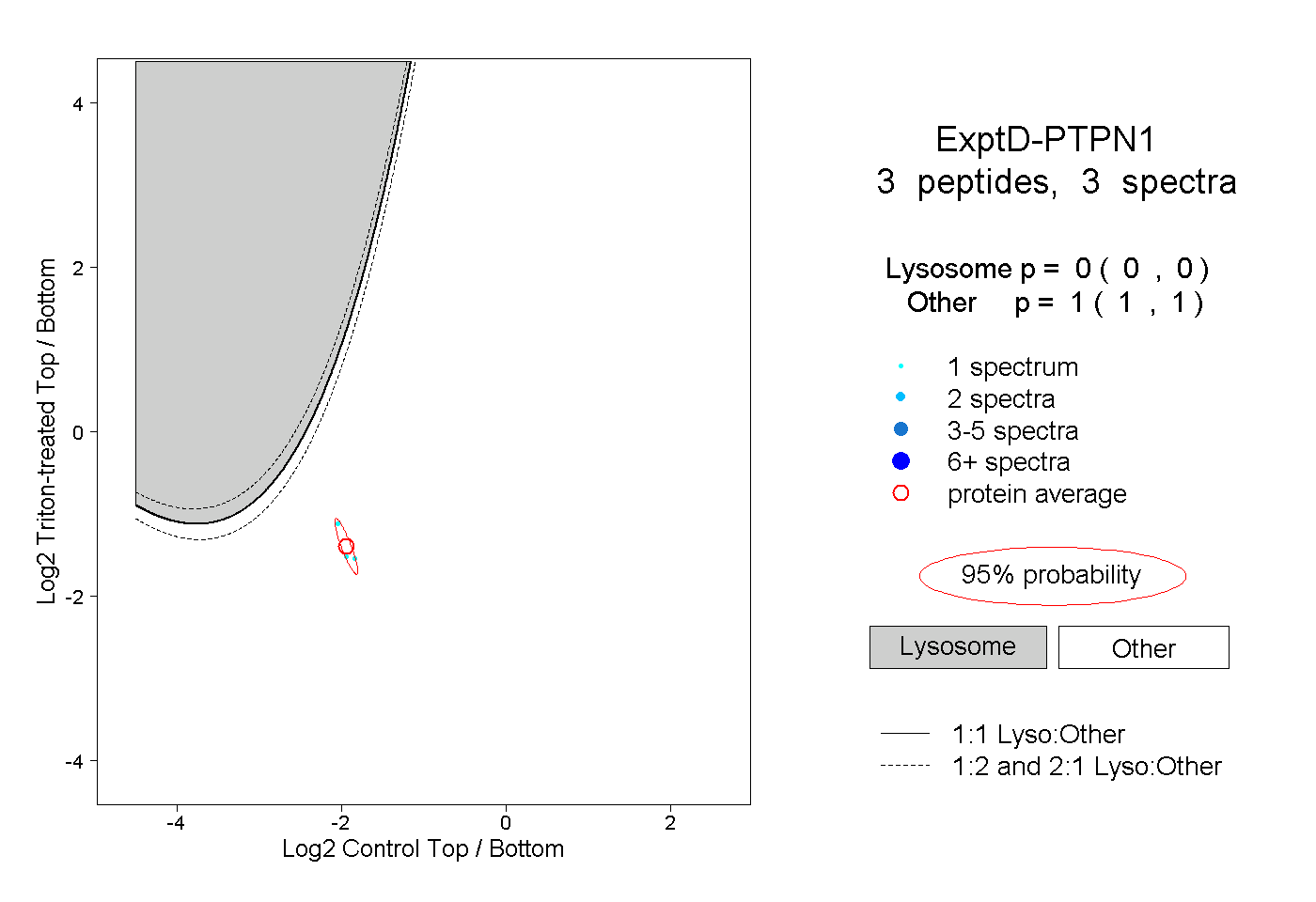 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |