peptides
spectra
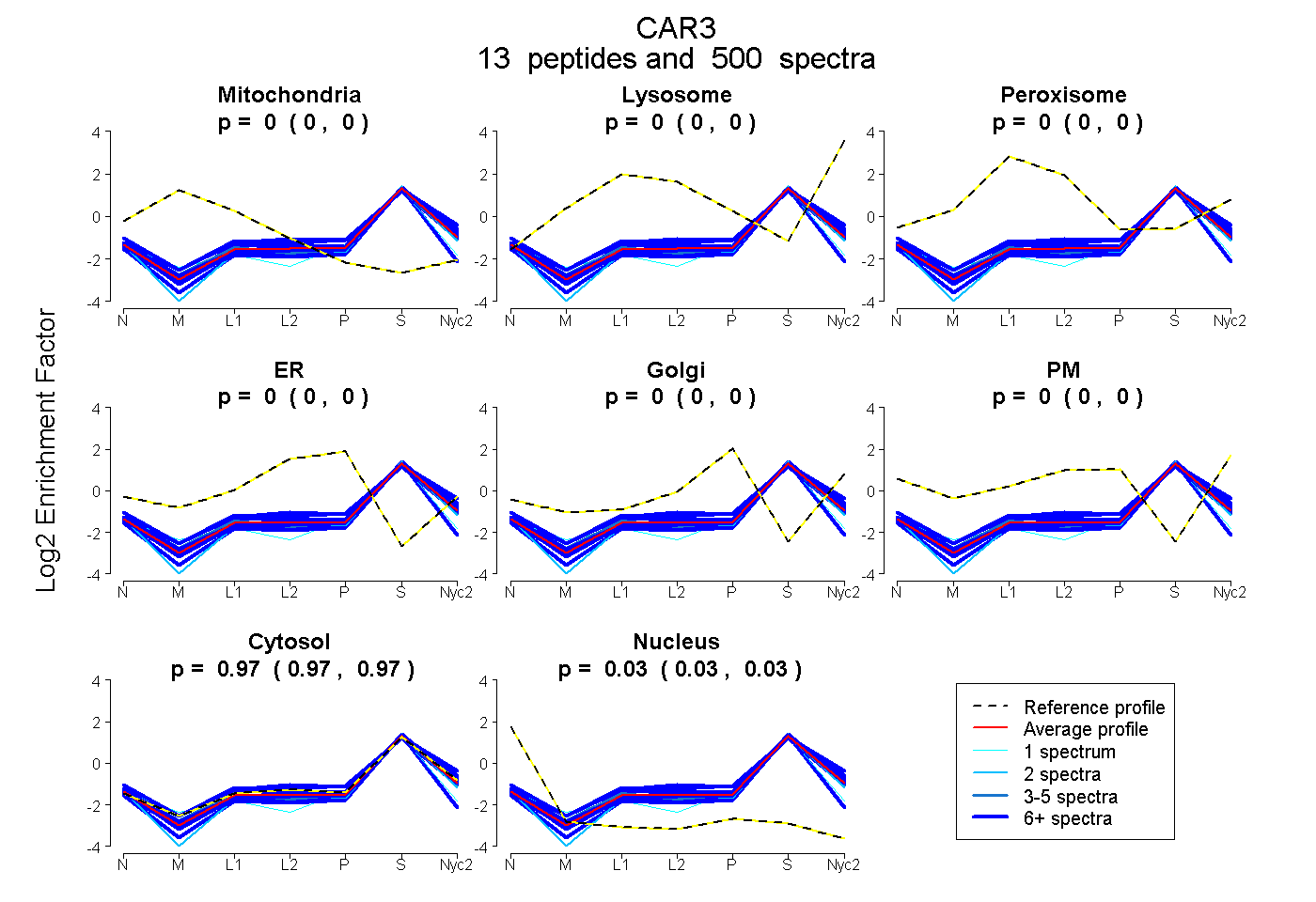
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.968 | 0.969
0.030 | 0.032
peptides
spectra
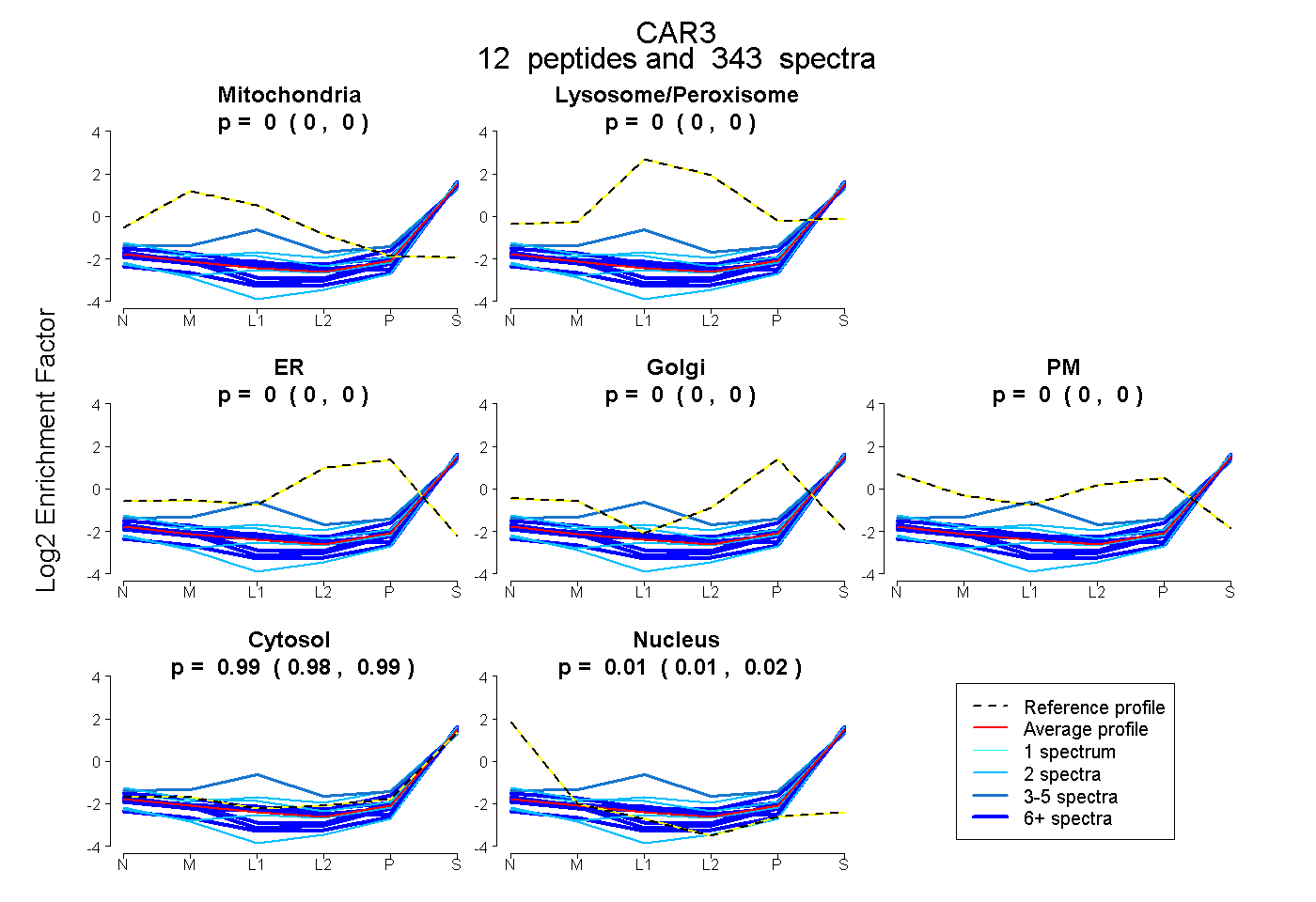
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.984 | 0.987
0.013 | 0.016
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
500 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.969 0.968 | 0.969 |
0.031 0.030 | 0.032 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
343 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.986 0.984 | 0.987 |
0.014 0.013 | 0.016 |
| 2 spectra, EPMTVSSDQMAK | 0.000 | 0.078 | 0.000 | 0.000 | 0.000 | 0.922 | 0.000 | |||
| 16 spectra, GEFQILLDALDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 24 spectra, GDNQSPIELHTK | 0.000 | 0.000 | 0.000 | 0.001 | 0.000 | 0.972 | 0.028 | |||
| 74 spectra, GGPLSGPYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.966 | 0.034 | |||
| 2 spectra, YNTFGEALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 135 spectra, VVFDDTFDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.944 | 0.056 | |||
| 19 spectra, QPDGIAVVGIFLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 21 spectra, EAPFNHFDPSCLFPACR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.998 | 0.002 | |||
| 41 spectra, YAAELHLVHWNPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.979 | 0.021 | |||
| 5 spectra, HDPSLQPWSVSYDPGSAK | 0.000 | 0.225 | 0.000 | 0.000 | 0.000 | 0.775 | 0.000 | |||
| 2 spectra, TILNNGK | 0.000 | 0.017 | 0.000 | 0.000 | 0.000 | 0.926 | 0.057 | |||
| 2 spectra, SLFASAENEPPVPLVGNWRPPQPIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.963 | 0.037 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
508 spectra |
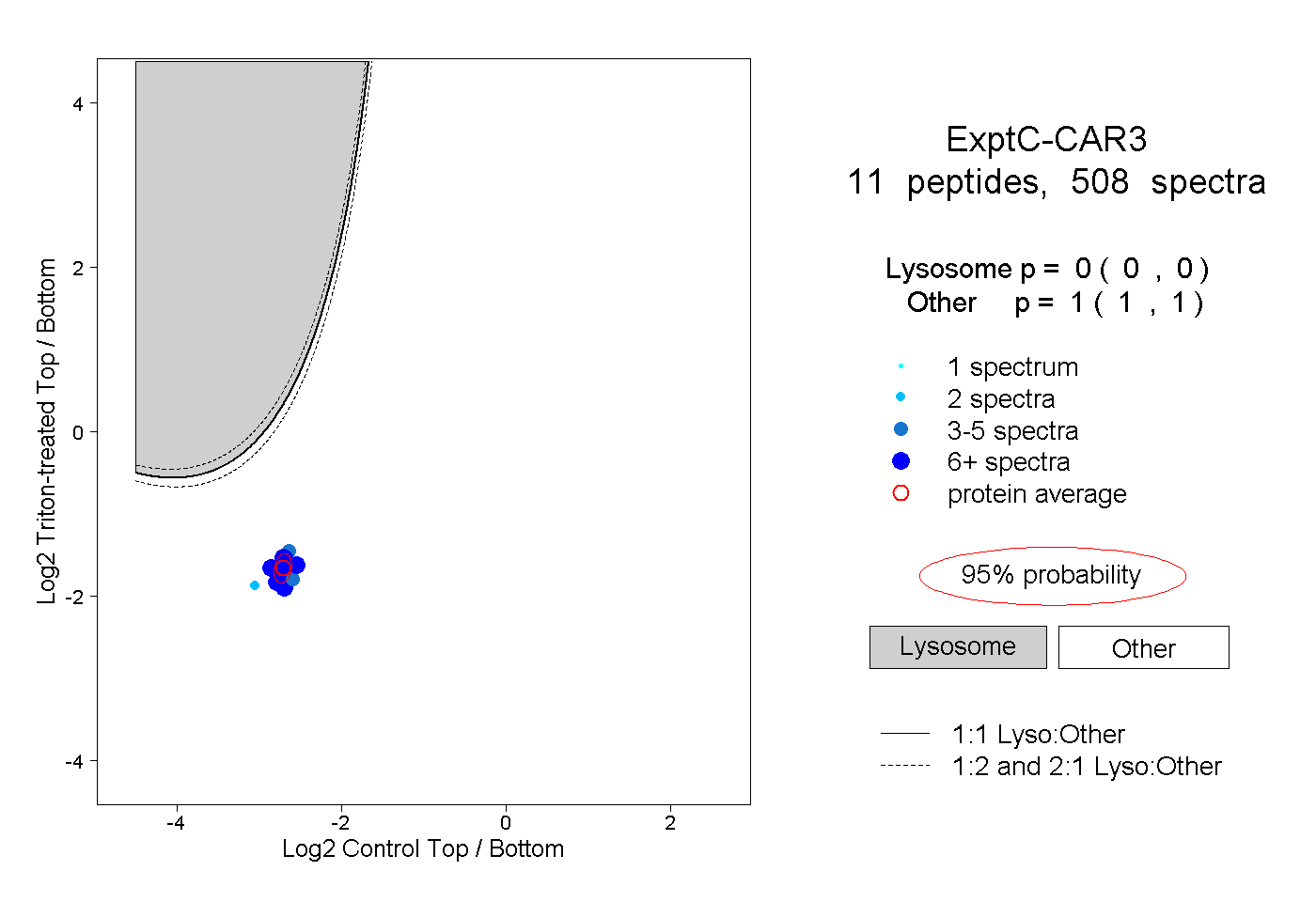 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
54 spectra |
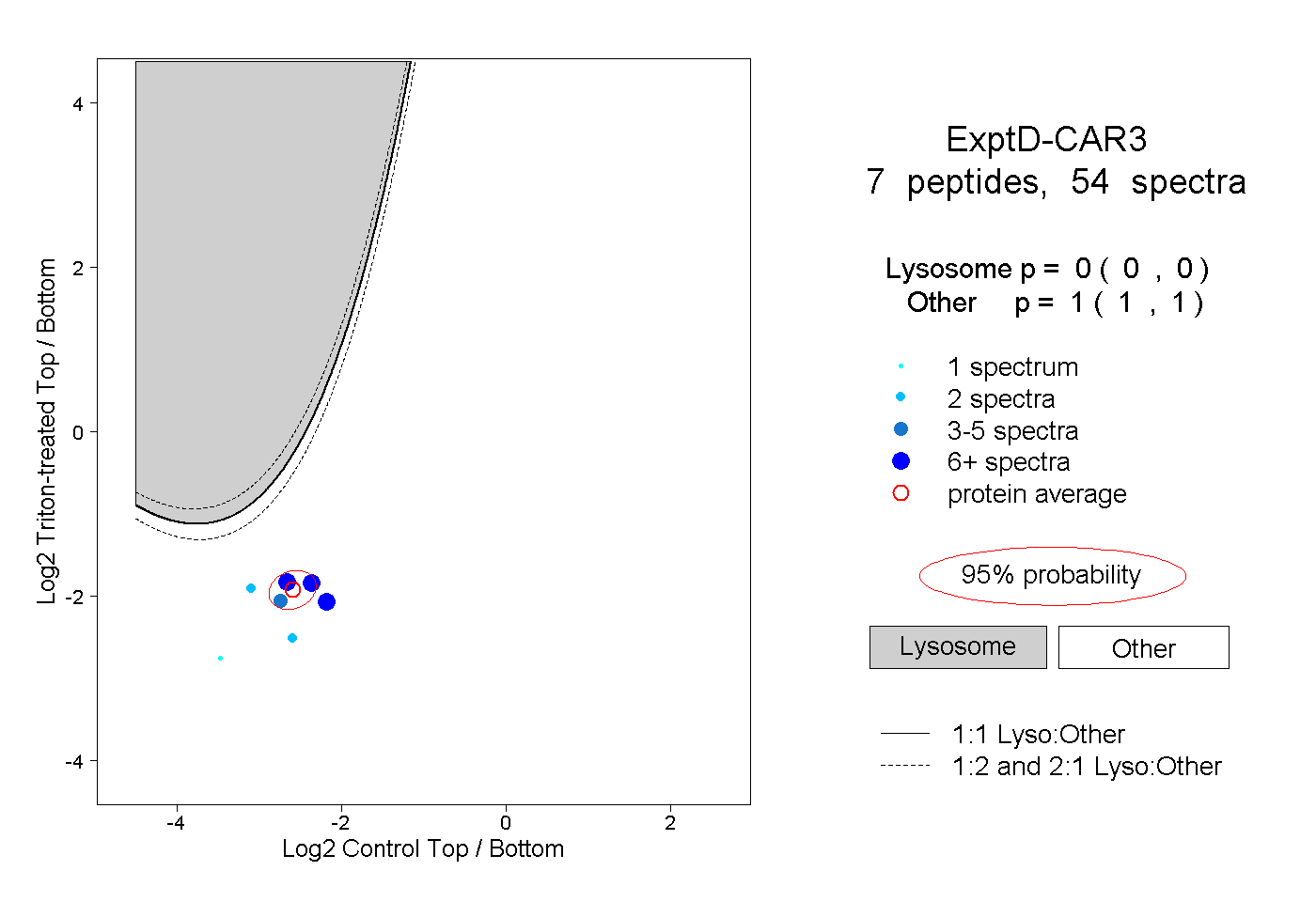 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |