peptides
spectra
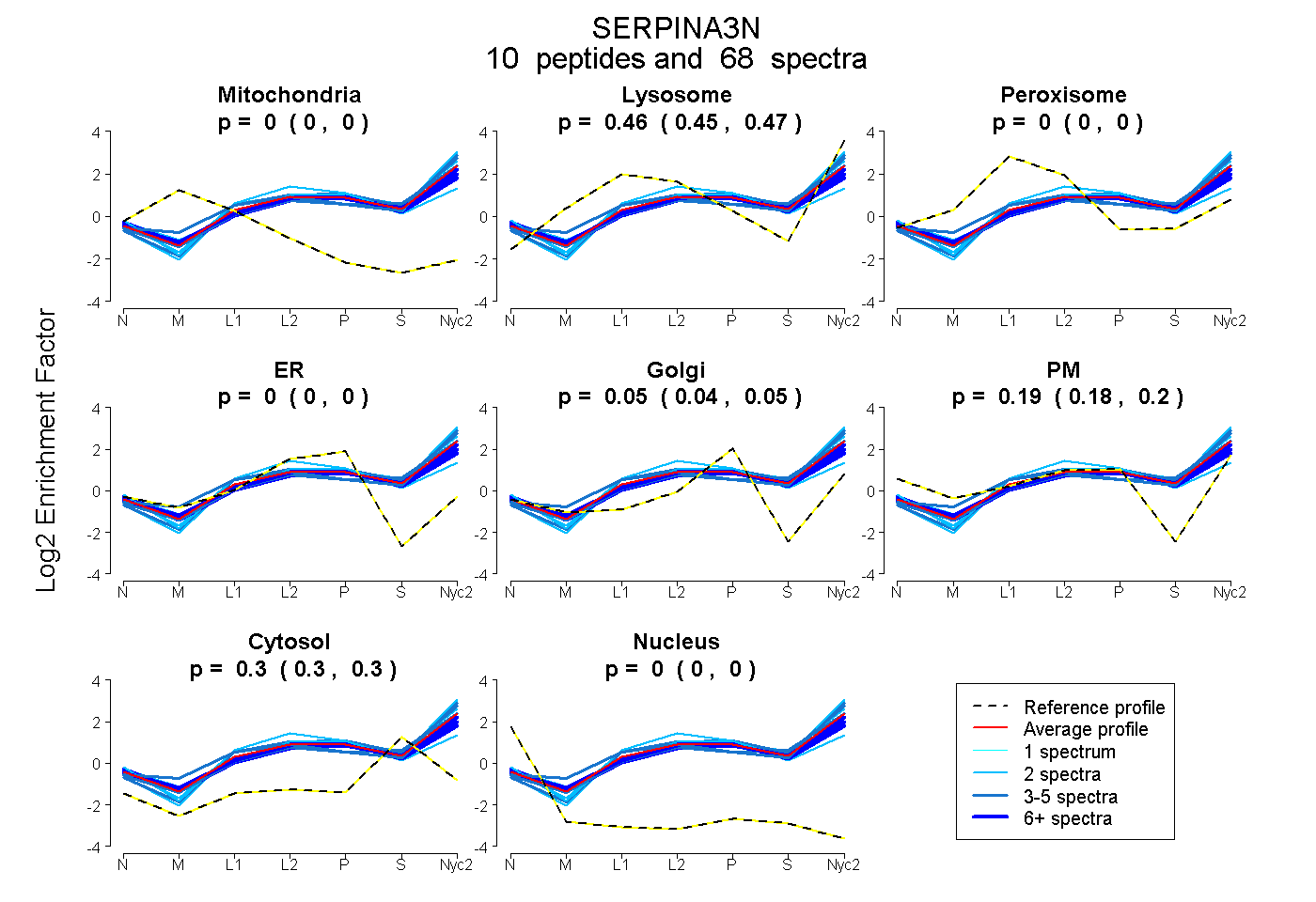
0.000 | 0.000
0.454 | 0.465
0.000 | 0.000
0.000 | 0.000
0.039 | 0.052
0.184 | 0.200
0.297 | 0.304
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
68 spectra |
 |
0.000 0.000 | 0.000 |
0.460 0.454 | 0.465 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.046 0.039 | 0.052 |
0.193 0.184 | 0.200 |
0.301 0.297 | 0.304 |
0.000 0.000 | 0.000 |
| 2 spectra, ALYQAEAFTADFQQSR | 0.000 | 0.553 | 0.000 | 0.000 | 0.129 | 0.000 | 0.318 | 0.000 | ||
| 2 spectra, DSLRPSMIDELYLPK | 0.000 | 0.550 | 0.000 | 0.000 | 0.017 | 0.171 | 0.262 | 0.000 | ||
| 2 spectra, FVPMSAK | 0.000 | 0.284 | 0.000 | 0.168 | 0.000 | 0.238 | 0.310 | 0.000 | ||
| 4 spectra, DTFQSEFYSGK | 0.000 | 0.573 | 0.000 | 0.000 | 0.142 | 0.000 | 0.285 | 0.000 | ||
| 10 spectra, LQVLAEFQEK | 0.000 | 0.435 | 0.000 | 0.000 | 0.062 | 0.189 | 0.314 | 0.000 | ||
| 12 spectra, GNSMEEILEGLK | 0.000 | 0.363 | 0.000 | 0.000 | 0.063 | 0.233 | 0.342 | 0.000 | ||
| 3 spectra, TSMVLVNYIYFK | 0.000 | 0.606 | 0.000 | 0.000 | 0.000 | 0.138 | 0.256 | 0.000 | ||
| 2 spectra, IQGLITNLAK | 0.000 | 0.510 | 0.000 | 0.000 | 0.000 | 0.266 | 0.224 | 0.000 | ||
| 3 spectra, LINDYVSK | 0.000 | 0.472 | 0.000 | 0.000 | 0.000 | 0.148 | 0.380 | 0.000 | ||
| 28 spectra, GFGHLLQR | 0.000 | 0.330 | 0.000 | 0.000 | 0.030 | 0.320 | 0.320 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
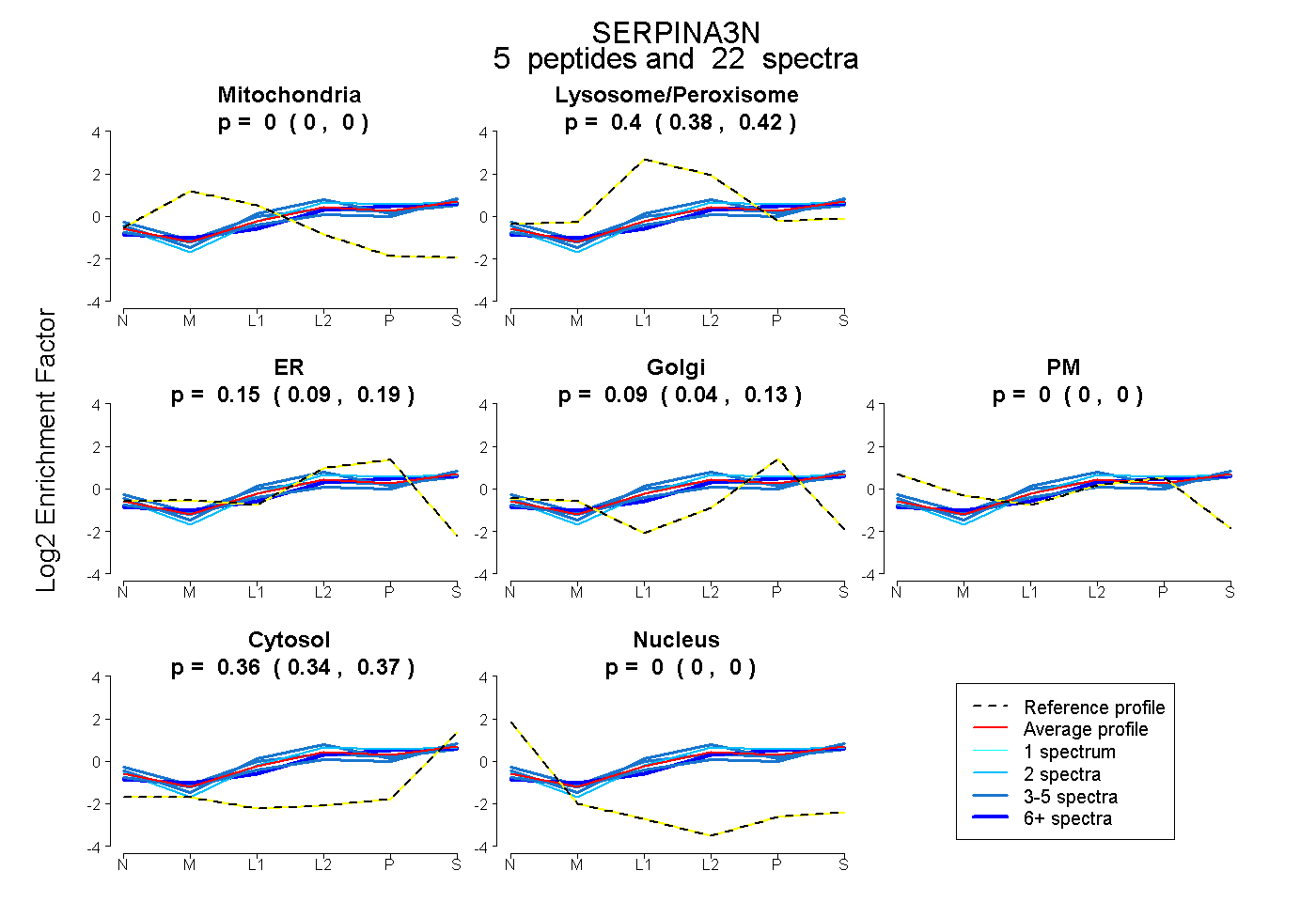 |
0.000 0.000 | 0.000 |
0.403 0.382 | 0.420 |
0.150 0.094 | 0.194 |
0.089 0.043 | 0.130 |
0.000 0.000 | 0.000 |
0.358 0.343 | 0.370 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
193 spectra |
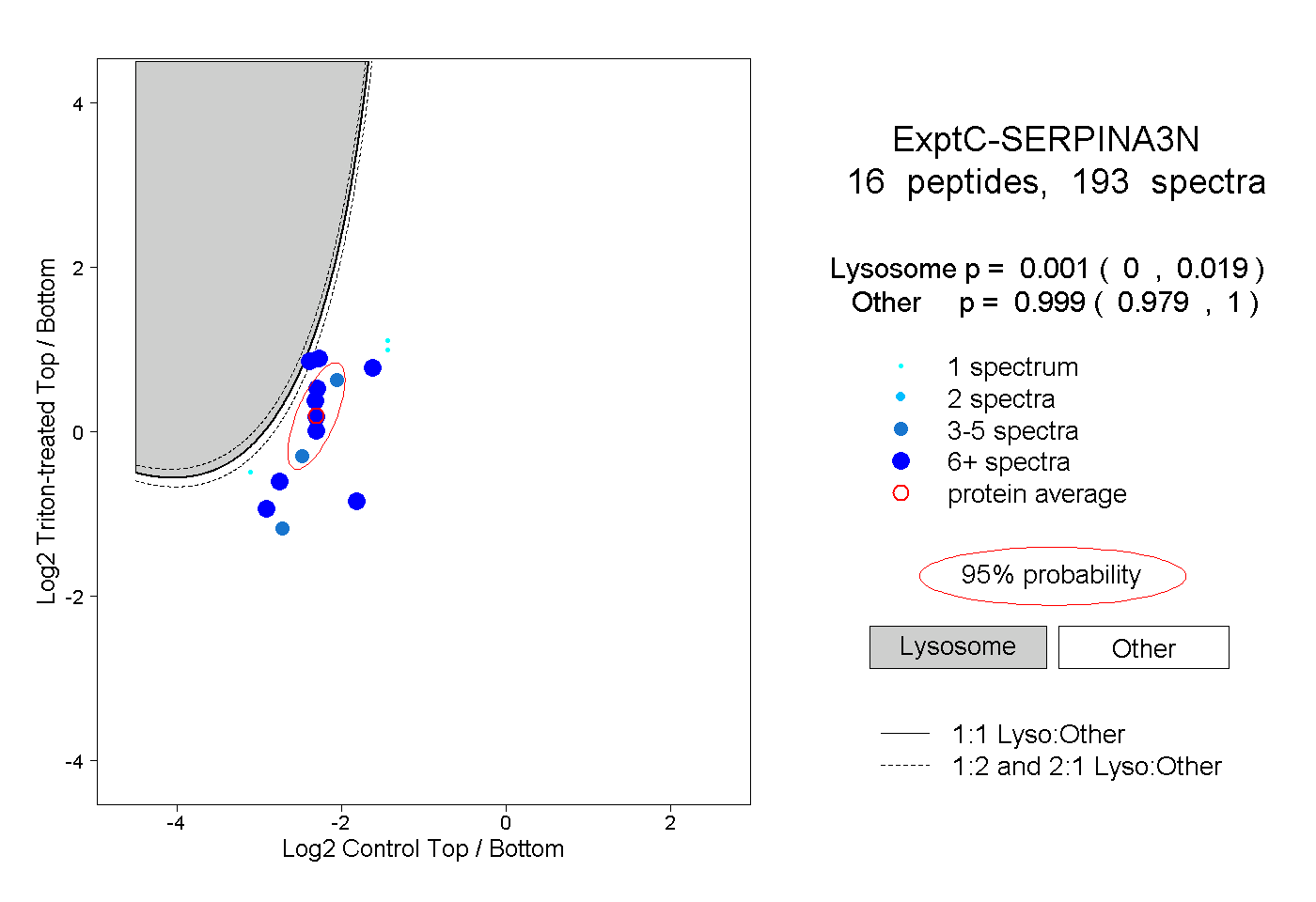 |
0.001 0.000 | 0.019 |
0.999 0.979 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
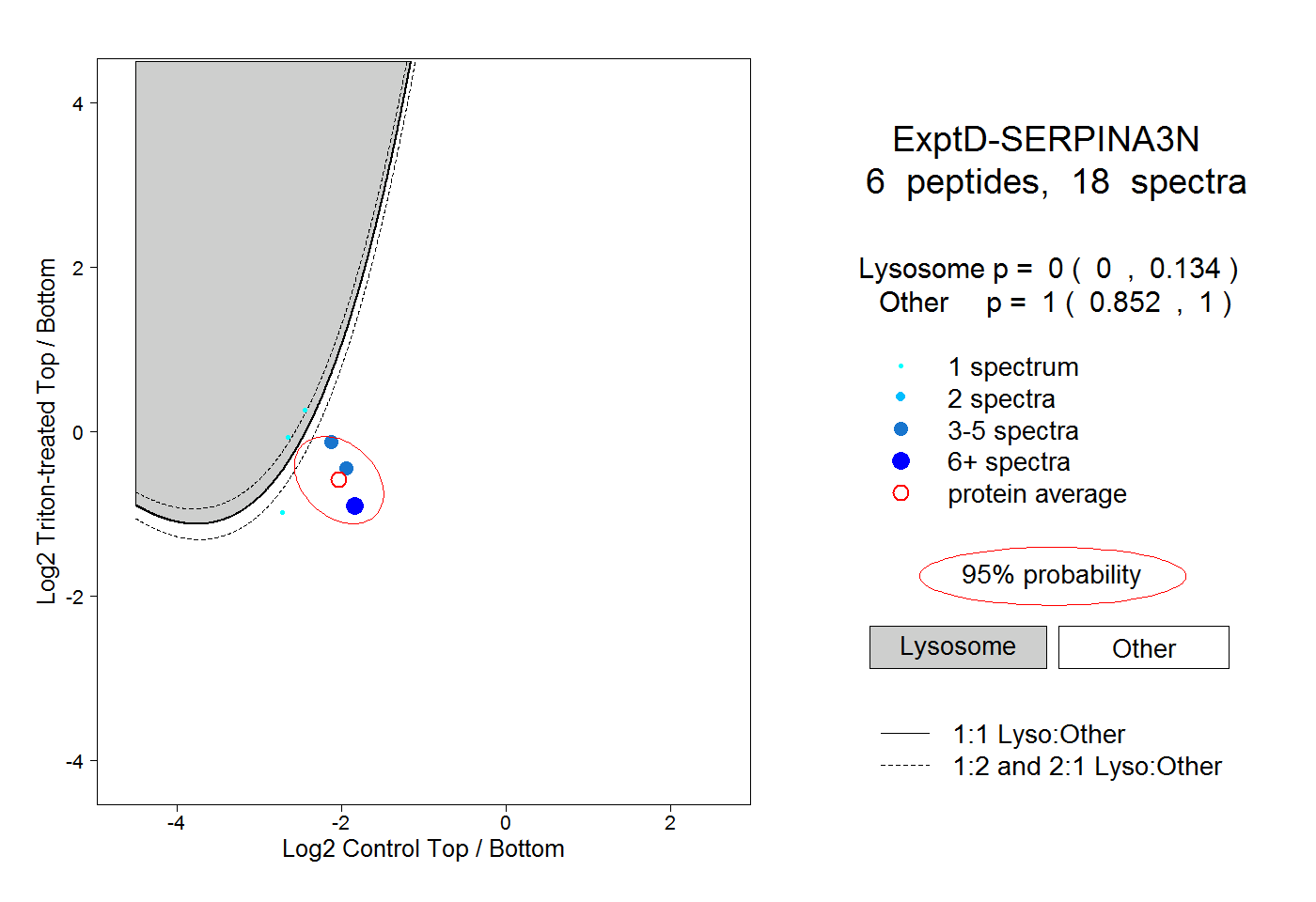 |
0.000 0.000 | 0.134 |
1.000 0.852 | 1.000 |