peptides
spectra
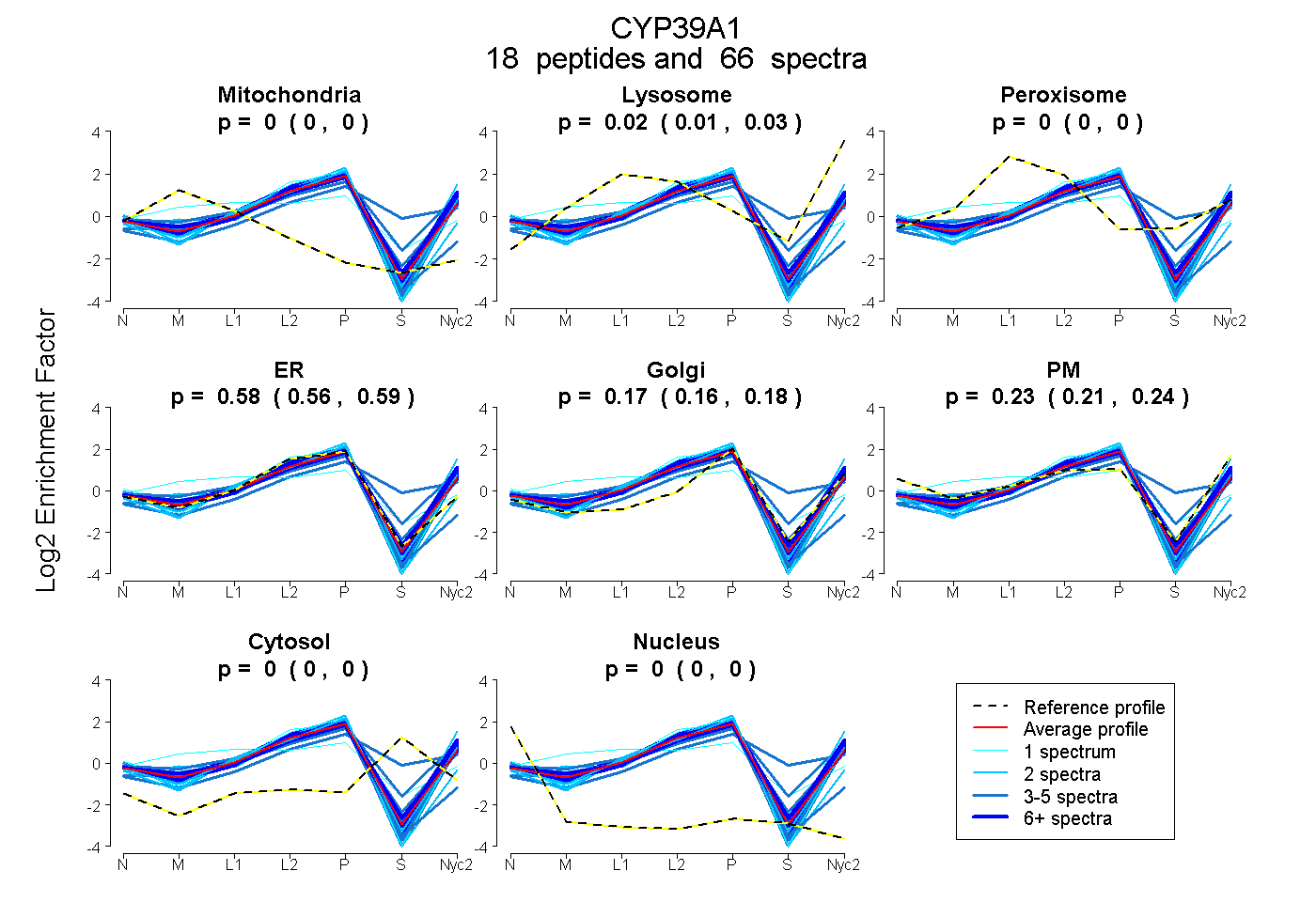
0.000 | 0.000
0.014 | 0.029
0.000 | 0.000
0.565 | 0.588
0.164 | 0.181
0.213 | 0.239
0.000 | 0.000
0.000 | 0.000
peptides
spectra
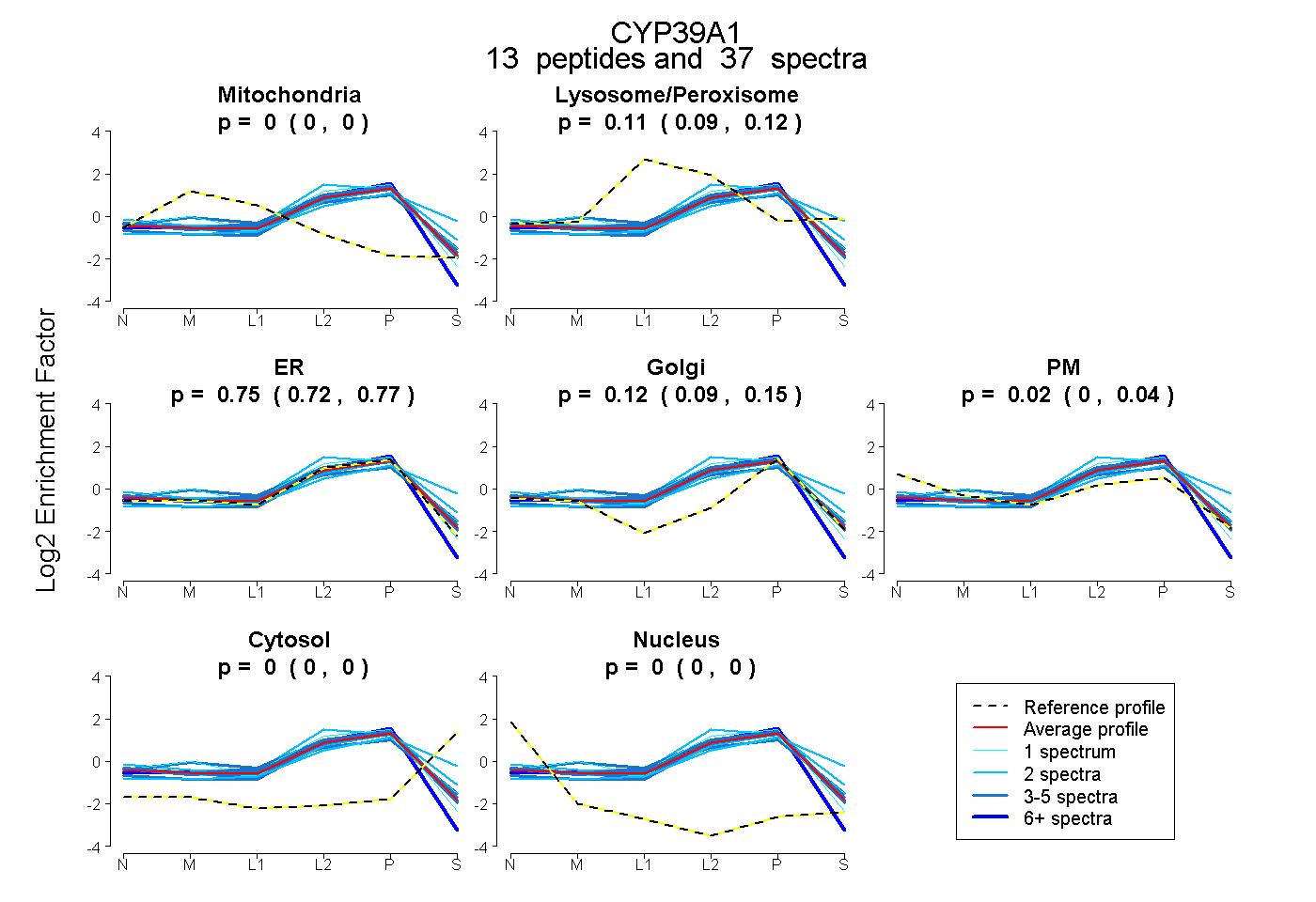
0.000 | 0.000
0.089 | 0.121
0.718 | 0.774
0.093 | 0.149
0.001 | 0.036
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
66 spectra |
 |
0.000 0.000 | 0.000 |
0.022 0.014 | 0.029 |
0.000 0.000 | 0.000 |
0.577 0.565 | 0.588 |
0.174 0.164 | 0.181 |
0.227 0.213 | 0.239 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
37 spectra |
 |
0.000 0.000 | 0.000 |
0.107 0.089 | 0.121 |
0.749 0.718 | 0.774 |
0.124 0.093 | 0.149 |
0.020 0.001 | 0.036 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, YFPEPESFKPER | 0.000 | 0.107 | 0.749 | 0.101 | 0.043 | 0.000 | 0.000 | |||
| 1 spectrum, LYVLMK | 0.000 | 0.099 | 0.696 | 0.160 | 0.045 | 0.000 | 0.000 | |||
| 2 spectra, TIVESISSVFGTAGK | 0.000 | 0.176 | 0.504 | 0.267 | 0.000 | 0.054 | 0.000 | |||
| 6 spectra, APLEFIEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EFYQHFK | 0.000 | 0.114 | 0.840 | 0.000 | 0.046 | 0.000 | 0.000 | |||
| 1 spectrum, IQVSENDLK | 0.042 | 0.179 | 0.391 | 0.357 | 0.031 | 0.000 | 0.000 | |||
| 2 spectra, YLLYPATLNTLFMK | 0.000 | 0.217 | 0.410 | 0.167 | 0.000 | 0.206 | 0.000 | |||
| 4 spectra, NIFFALHEK | 0.000 | 0.115 | 0.837 | 0.012 | 0.037 | 0.000 | 0.000 | |||
| 3 spectra, GLFLTDK | 0.042 | 0.227 | 0.435 | 0.269 | 0.028 | 0.000 | 0.000 | |||
| 3 spectra, YGPVFTVFAVGK | 0.000 | 0.119 | 0.660 | 0.135 | 0.086 | 0.000 | 0.000 | |||
| 1 spectrum, WLLALFEK | 0.000 | 0.039 | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, APGVITR | 0.000 | 0.000 | 0.926 | 0.027 | 0.000 | 0.047 | 0.000 | |||
| 4 spectra, WCILESIR | 0.000 | 0.018 | 0.856 | 0.001 | 0.118 | 0.007 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
91 spectra |
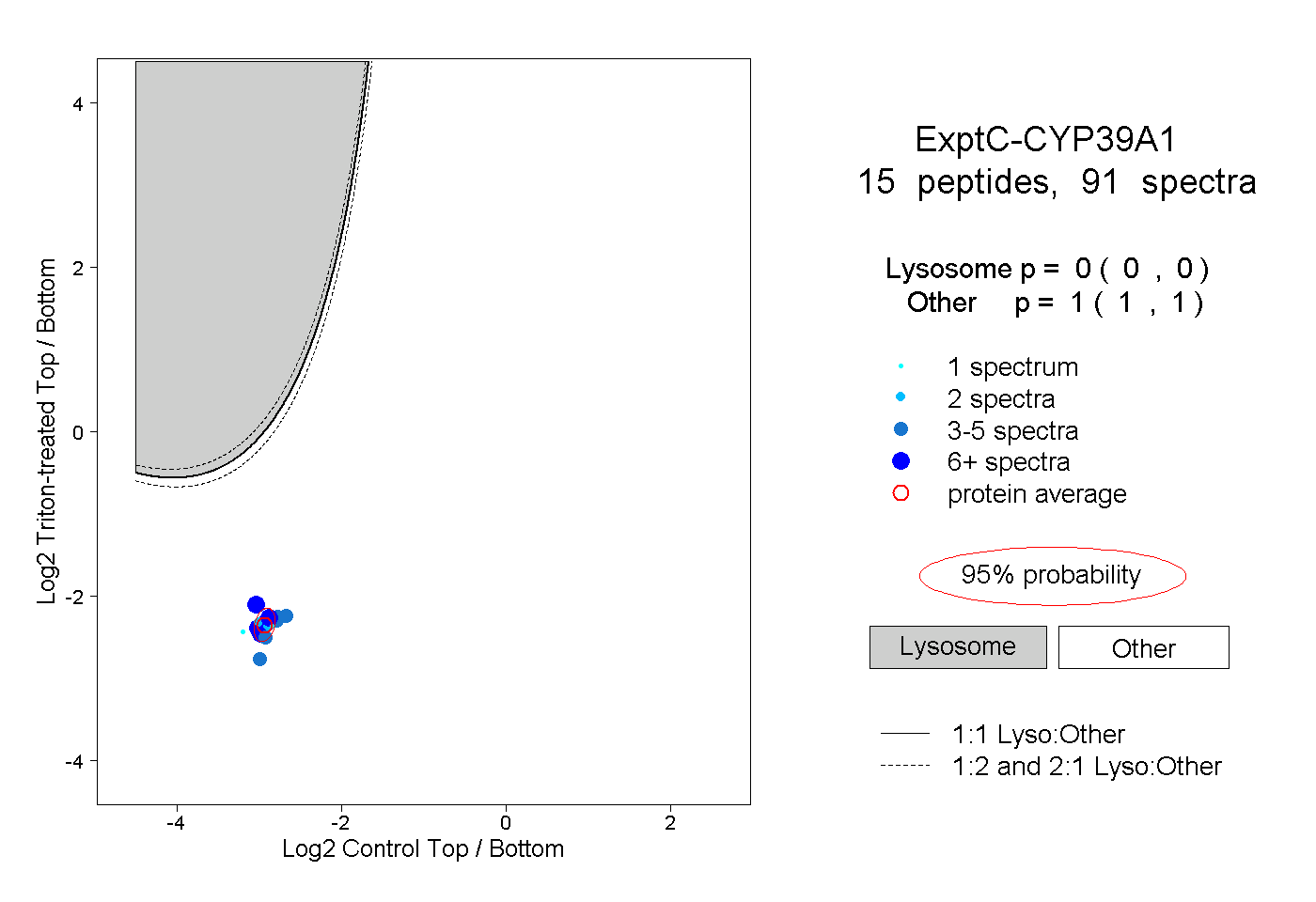 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
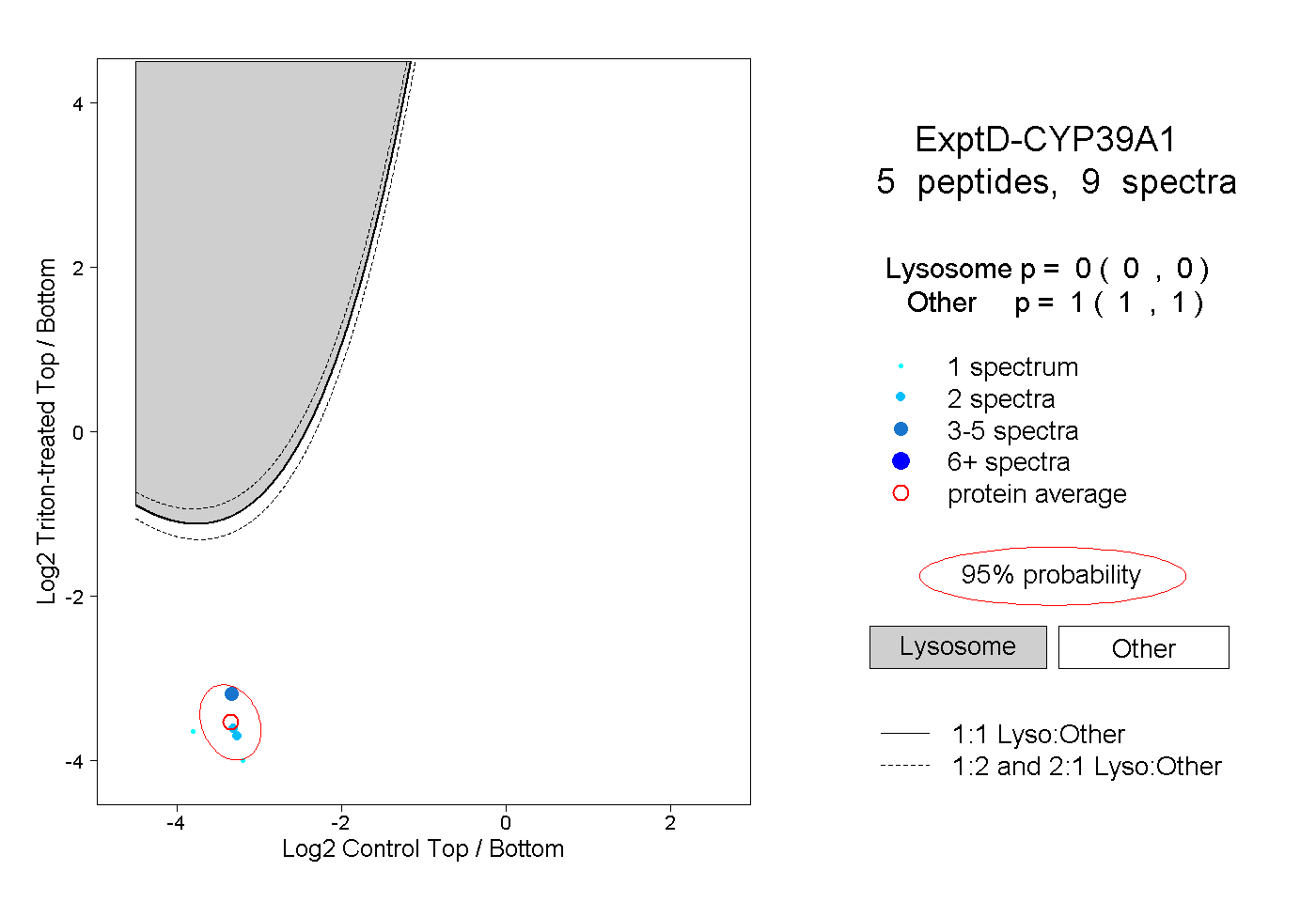 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |