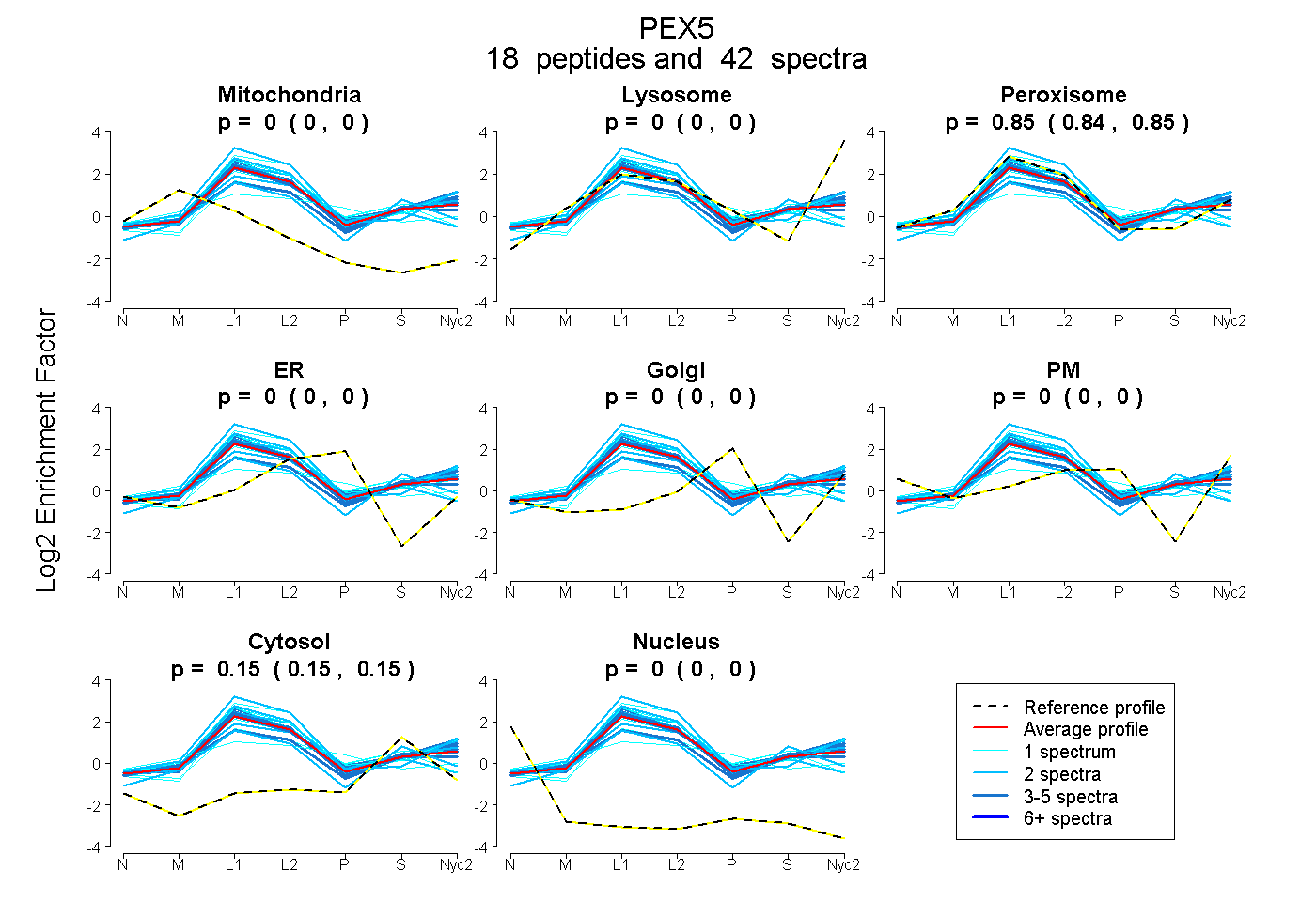
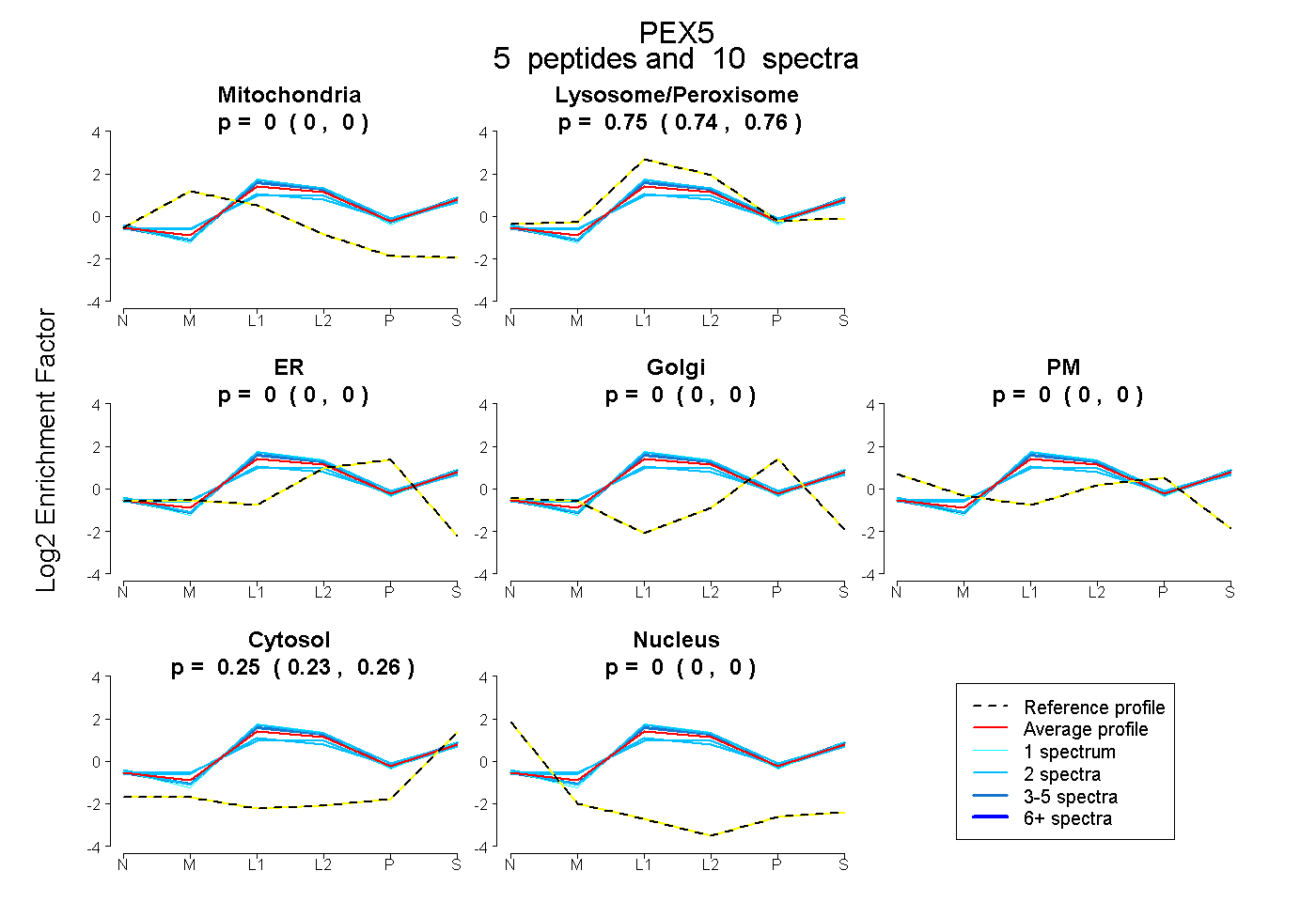
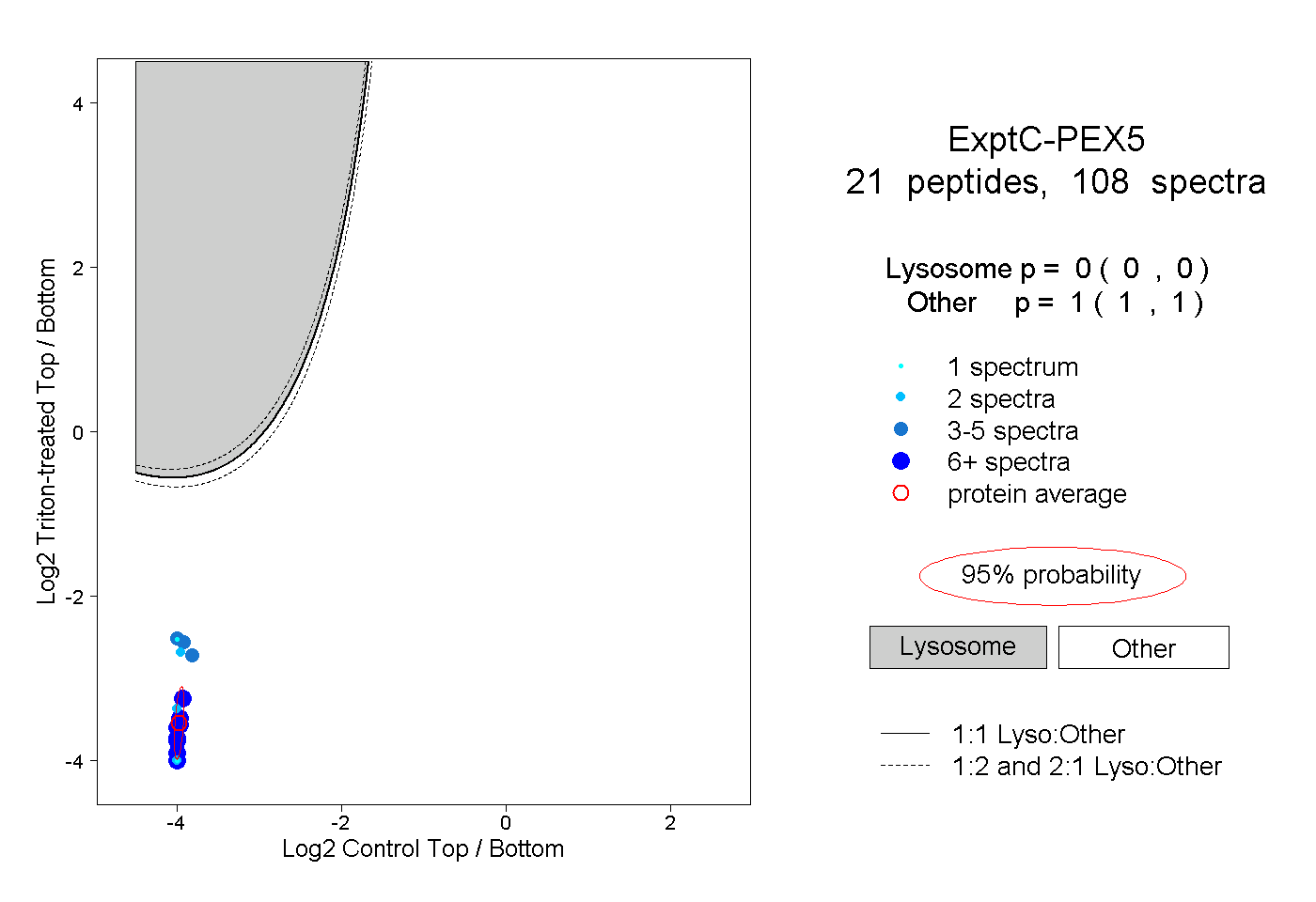
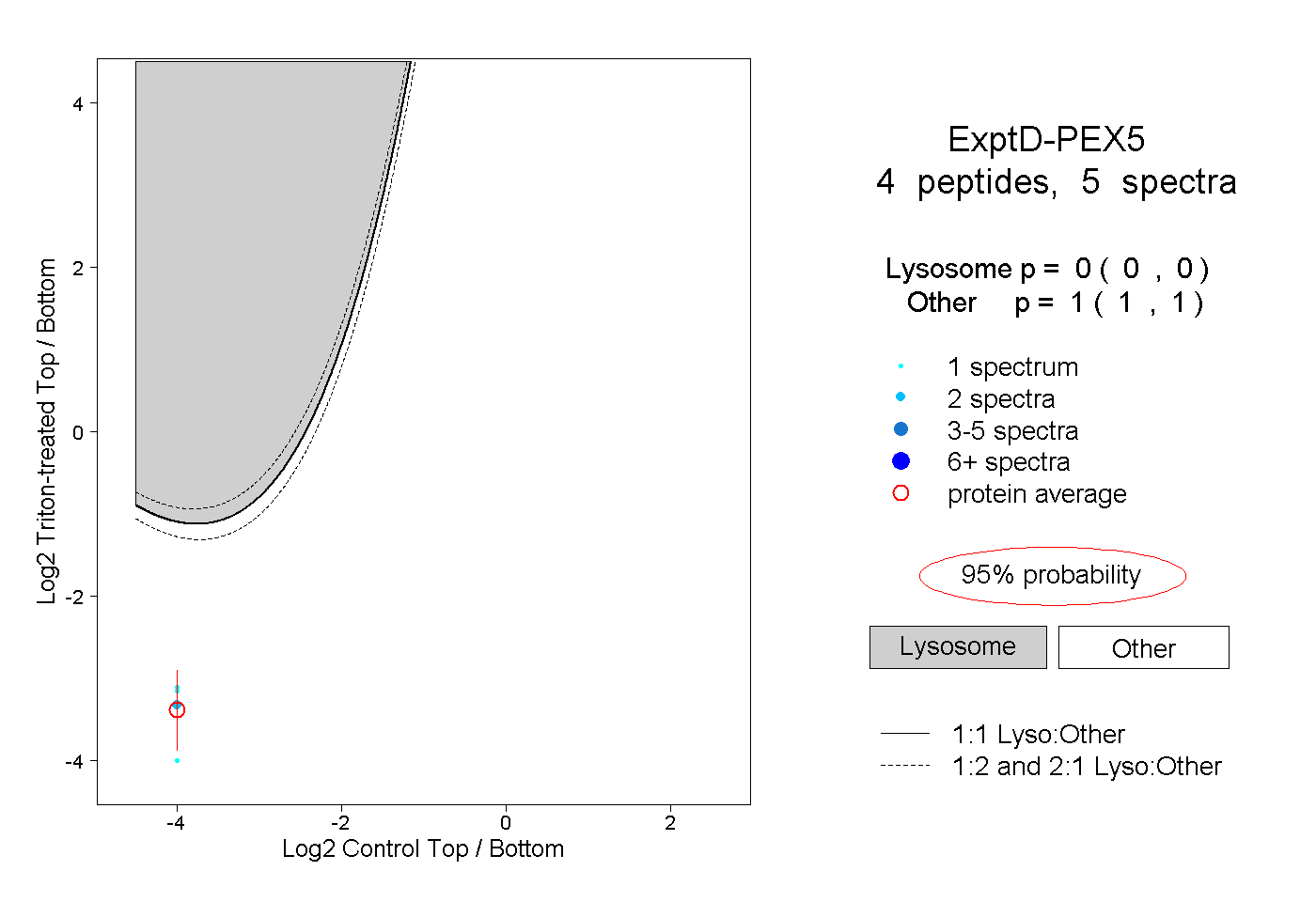
| 1 spectrum, LANSEGTSEAWVDQFTRPGNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LATHFTQDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LANSEFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LALSMLGQSDAYGAADAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LQAELEEMAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TALMALAVSFTNESLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, CLELKPDNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ELFLAAVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QIGEGQVSLESAAGSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QACETLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GEGGAMSENIWSTLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LWLGDPEGTSTTDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, DHPQPFEEGLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, YNLGISCINLGAHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ALELQPGYIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, APQTFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, EAVEHFLEALNMQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DAEAHPWLSDYDDLTSASYDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ELVESECGGANPLMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GYQFEEENPLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LAALQVEFER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |