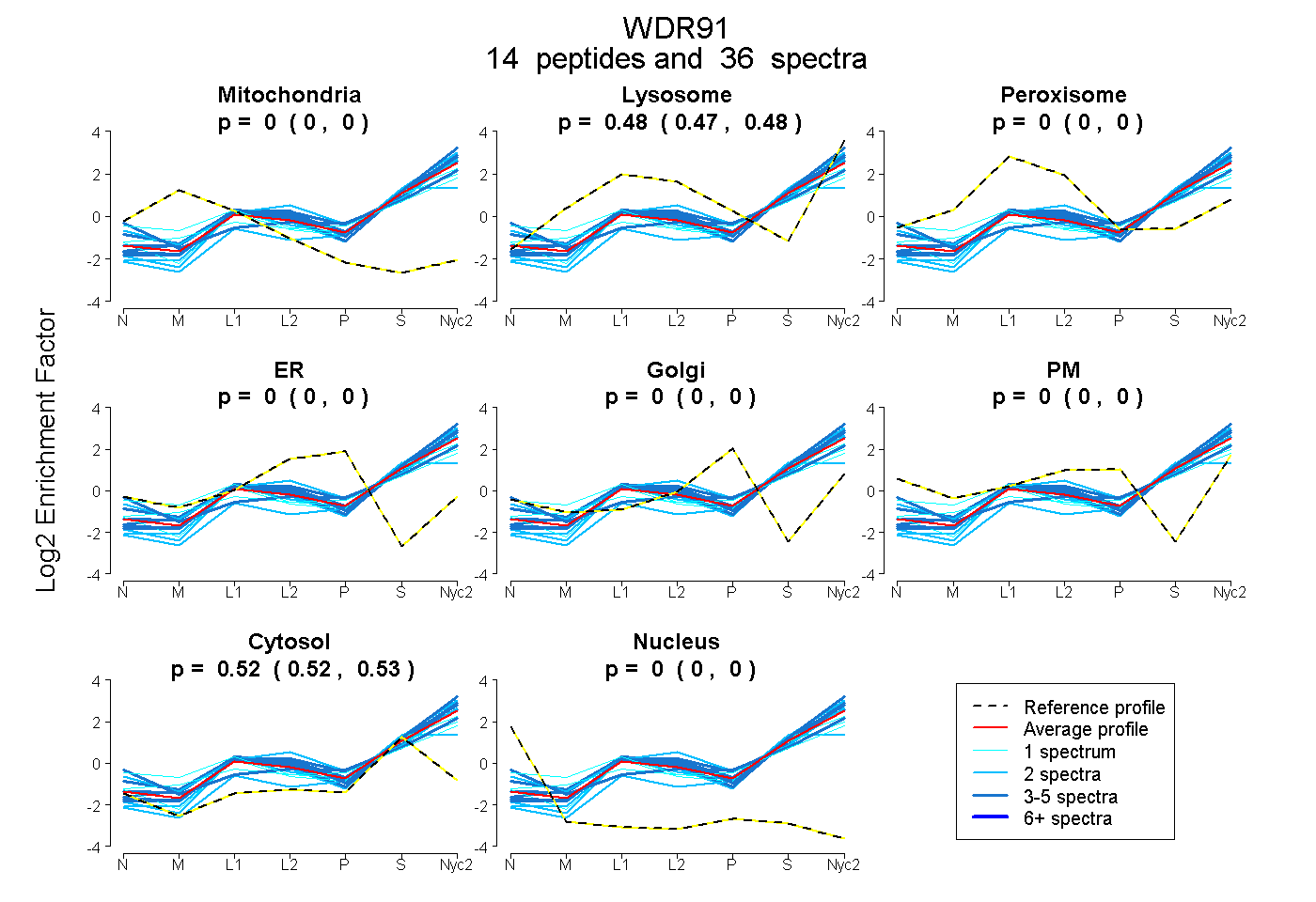
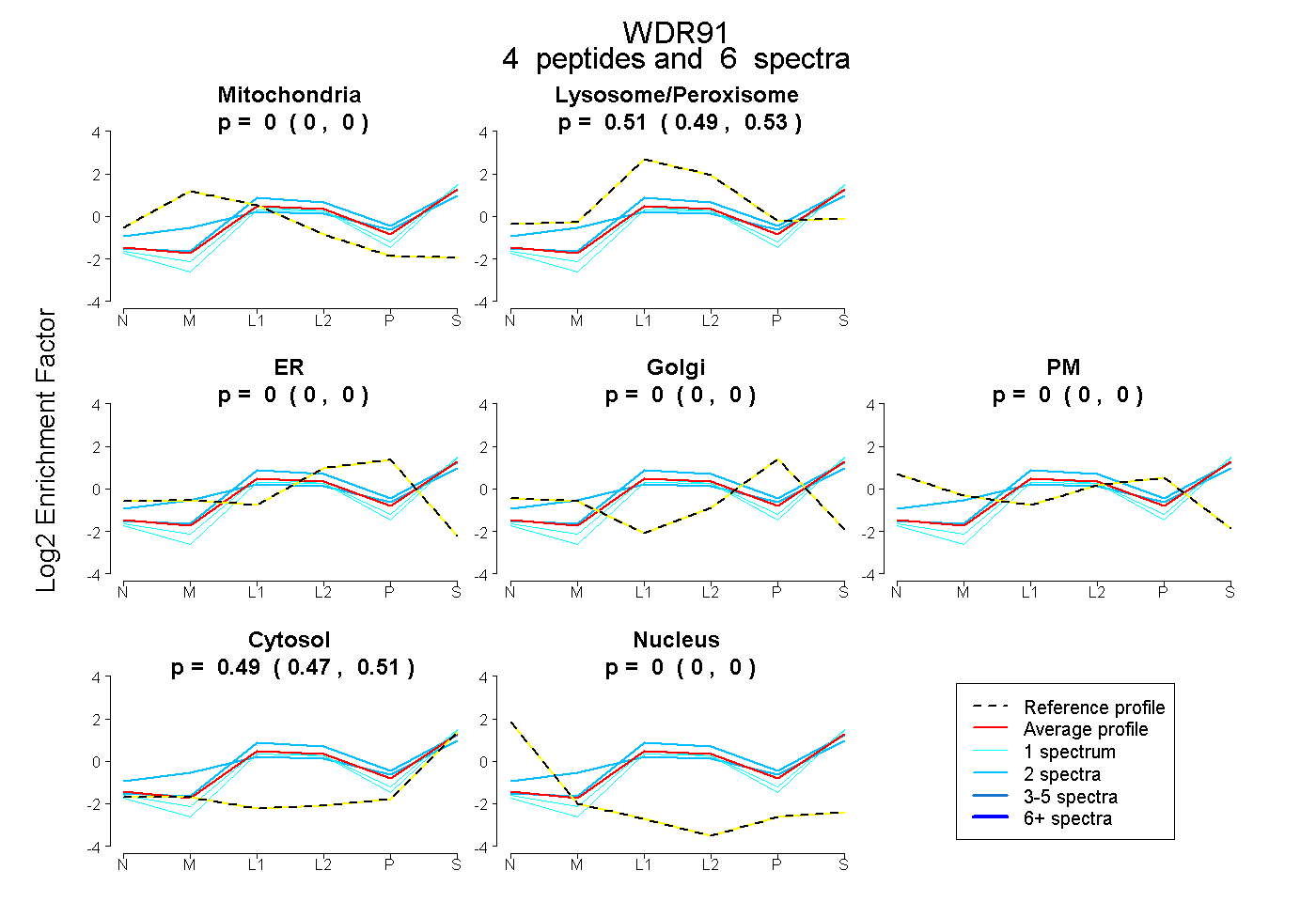
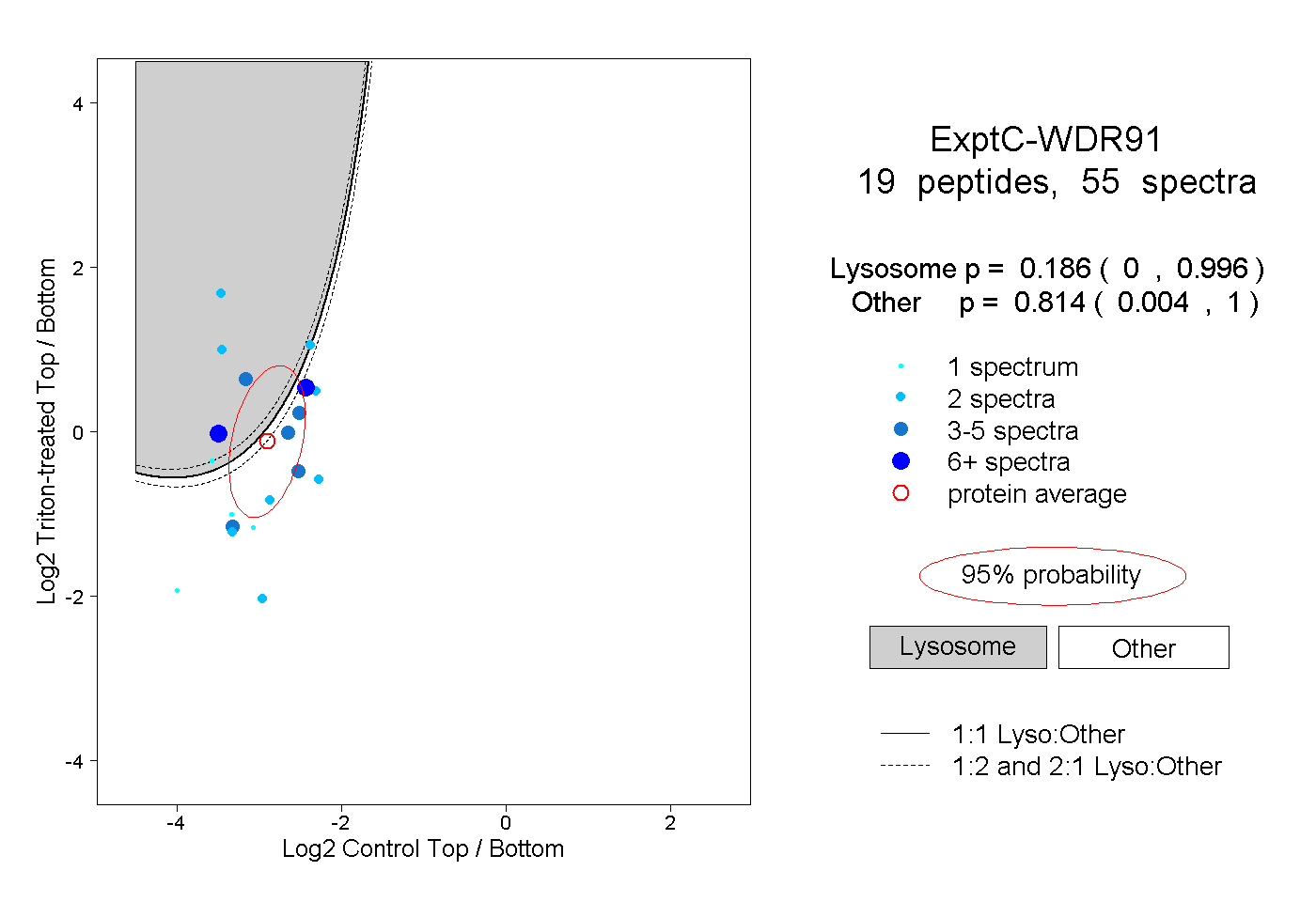
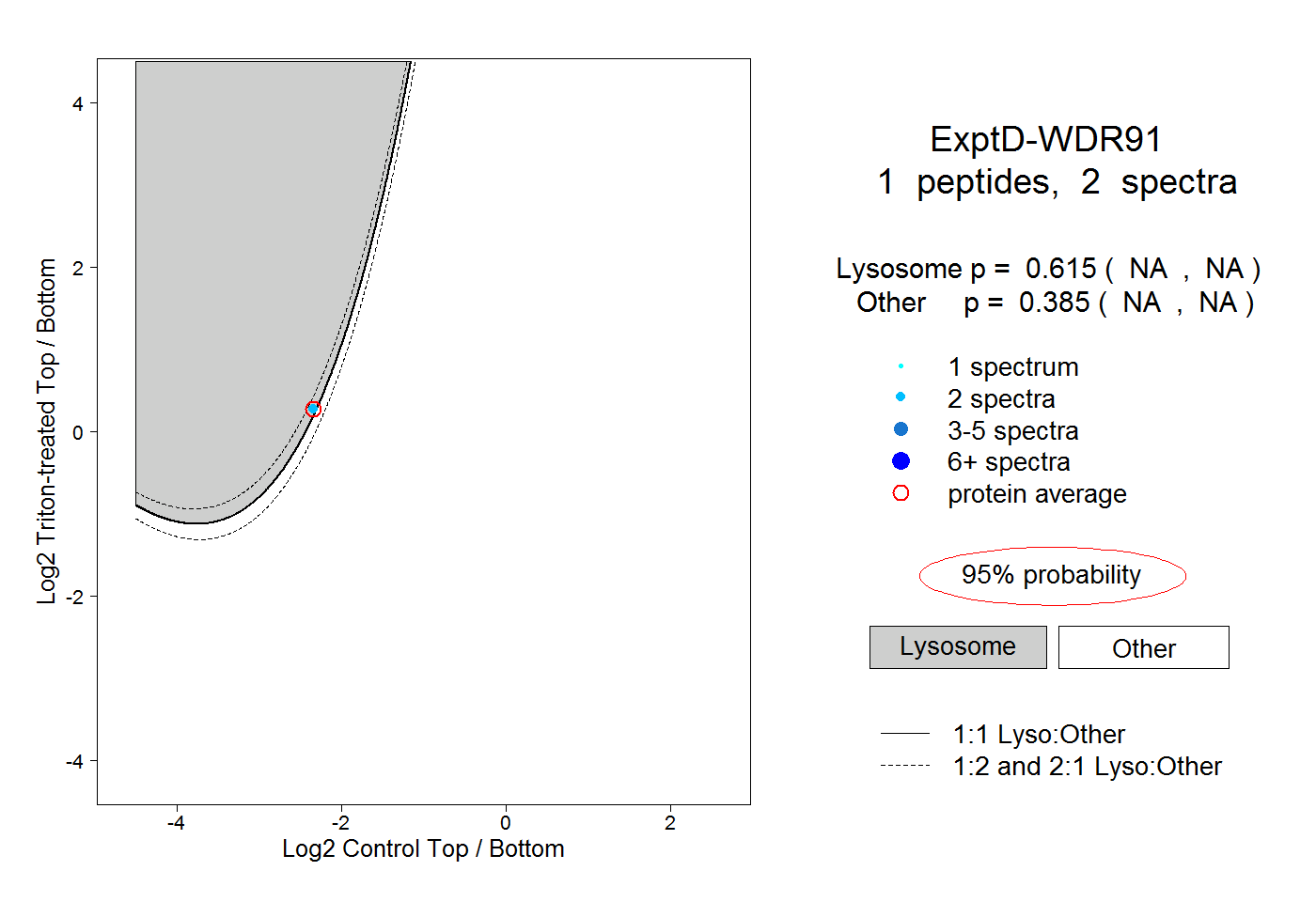
| 1 spectrum, LEDIYRPTINK |
|
0.793 |
|
|
|
|
|
|
|
0.207 |
| 2 spectra, LTTLLAHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ASSISK |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 4 spectra, LLLLGSGVGTVR |
|
0.026 |
|
|
|
|
|
|
|
0.974 |
| 1 spectrum, LPPYVSSMDR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 5 spectra, LGSEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VLENCLSLGGHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EEQQQEEAAALVQHK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, SPLLSLEWATK |
|
0.548 |
|
|
|
|
|
|
|
0.452 |
| 1 spectrum, QVQVPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LLLWDTK |
|
0.064 |
|
|
|
|
|
|
|
0.936 |
| 2 spectra, EYLLFR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, FIQWNIHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ELLSTSSSQTQCAEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LSPAQGPPQAQSSAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AQEFFAK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 5 spectra, LFALQAEVHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GFTHTLR |
|
0.991 |
|
|
|
|
|
|
|
0.009 |
| 4 spectra, GMNQVPGK |
|
0.023 |
|
|
|
|
|
|
|
0.977 |