peptides
spectra
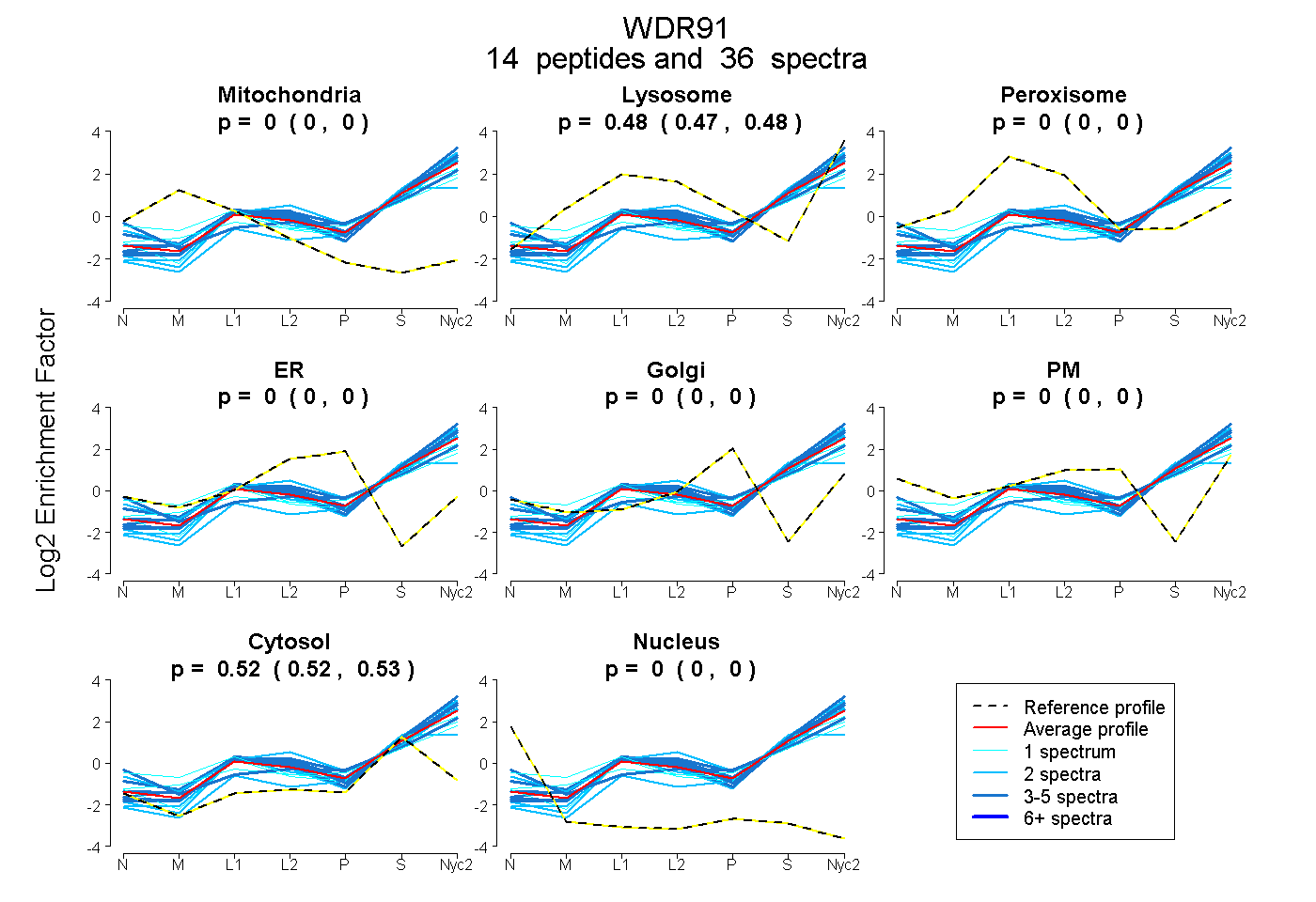
0.000 | 0.000
0.473 | 0.482
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.517 | 0.526
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
36 spectra |
 |
0.000 0.000 | 0.000 |
0.478 0.473 | 0.482 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.522 0.517 | 0.526 |
0.000 0.000 | 0.000 |
| 2 spectra, QATELQNQAEWK | 0.000 | 0.570 | 0.000 | 0.000 | 0.000 | 0.000 | 0.430 | 0.000 | ||
| 3 spectra, LLLLGSGVGTVR | 0.000 | 0.498 | 0.000 | 0.000 | 0.000 | 0.000 | 0.502 | 0.000 | ||
| 1 spectrum, LPPYVSSMDR | 0.000 | 0.403 | 0.000 | 0.000 | 0.000 | 0.000 | 0.597 | 0.000 | ||
| 1 spectrum, VASLDVDGVIK | 0.000 | 0.454 | 0.000 | 0.000 | 0.000 | 0.052 | 0.493 | 0.000 | ||
| 4 spectra, TDELVR | 0.000 | 0.335 | 0.000 | 0.000 | 0.000 | 0.140 | 0.524 | 0.000 | ||
| 2 spectra, EEQQQEEAAALVQHK | 0.000 | 0.483 | 0.000 | 0.000 | 0.000 | 0.000 | 0.517 | 0.000 | ||
| 2 spectra, LLLWDTK | 0.000 | 0.234 | 0.000 | 0.000 | 0.000 | 0.000 | 0.766 | 0.000 | ||
| 2 spectra, EYLLFR | 0.000 | 0.464 | 0.000 | 0.000 | 0.000 | 0.000 | 0.536 | 0.000 | ||
| 4 spectra, FIQWNIHK | 0.000 | 0.529 | 0.000 | 0.000 | 0.000 | 0.000 | 0.471 | 0.000 | ||
| 4 spectra, LFALQAEVHR | 0.000 | 0.574 | 0.000 | 0.000 | 0.000 | 0.000 | 0.426 | 0.000 | ||
| 5 spectra, TNQVQEENEVLR | 0.000 | 0.545 | 0.000 | 0.000 | 0.000 | 0.000 | 0.455 | 0.000 | ||
| 3 spectra, GFTHTLR | 0.000 | 0.524 | 0.000 | 0.000 | 0.000 | 0.000 | 0.476 | 0.000 | ||
| 1 spectrum, QLDAEIK | 0.000 | 0.434 | 0.000 | 0.000 | 0.000 | 0.000 | 0.566 | 0.000 | ||
| 2 spectra, DYWSYLER | 0.000 | 0.466 | 0.000 | 0.000 | 0.000 | 0.000 | 0.534 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
6 spectra |
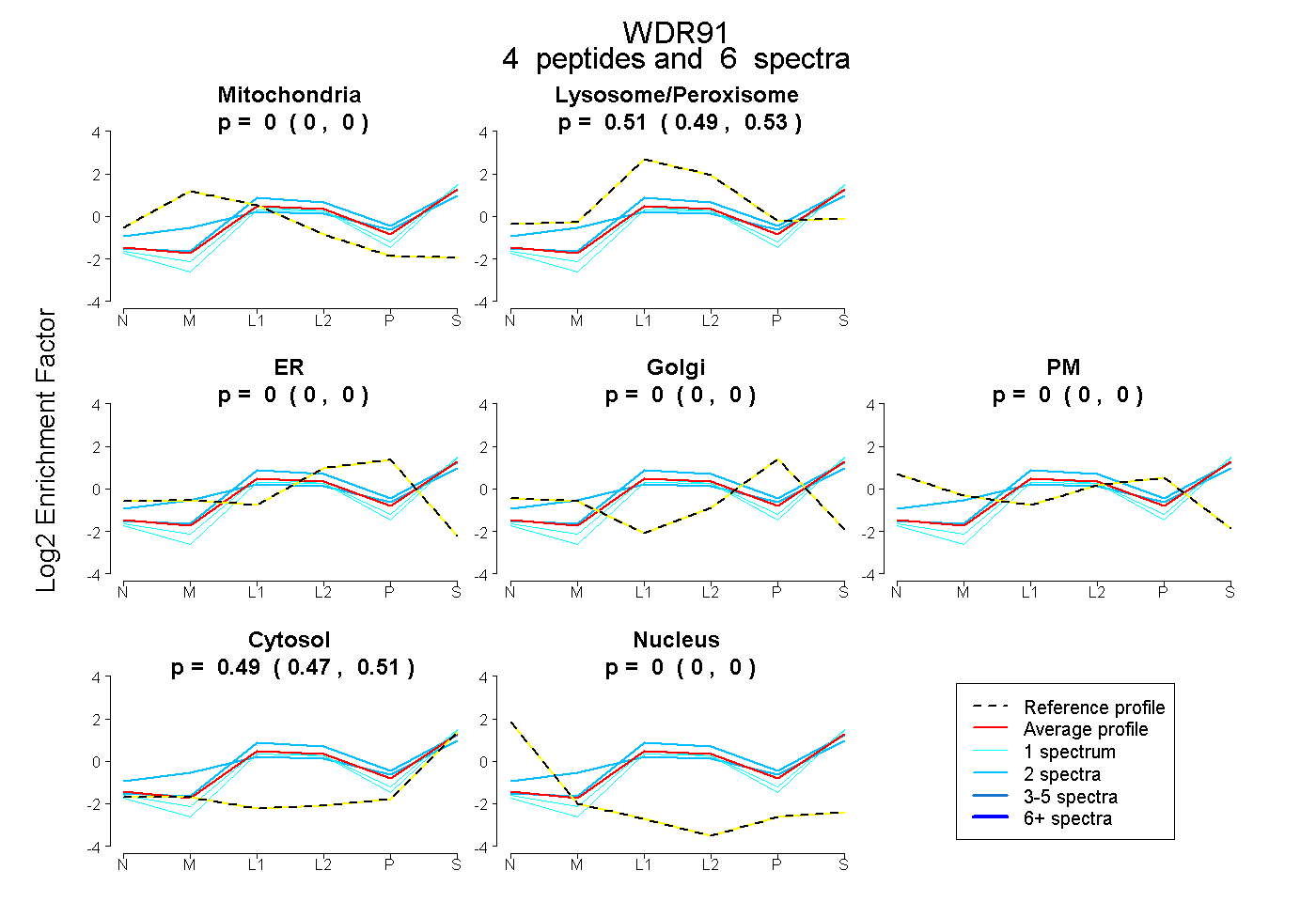 |
0.000 0.000 | 0.000 |
0.510 0.491 | 0.526 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.490 0.471 | 0.506 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
55 spectra |
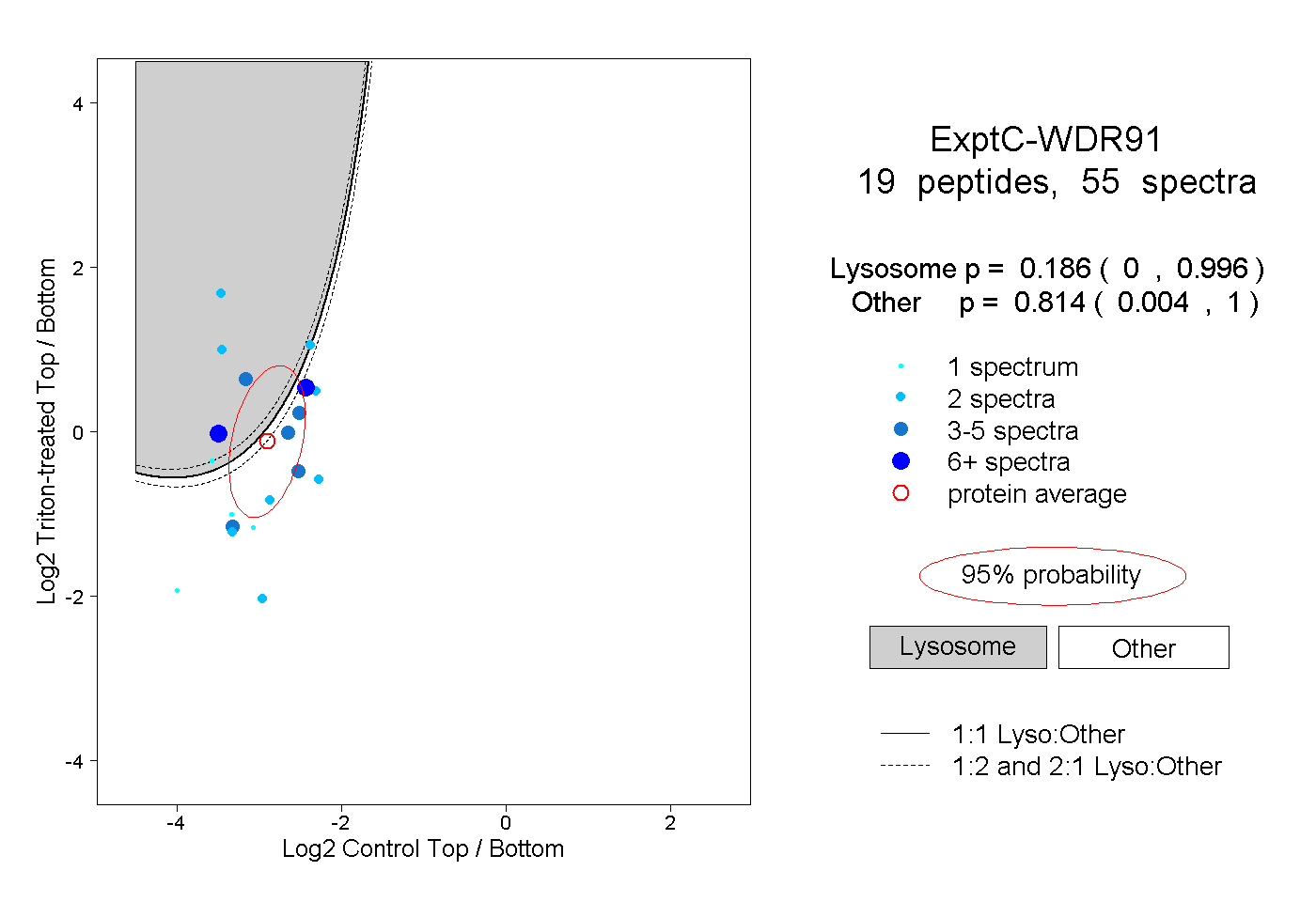 |
0.186 0.000 | 0.996 |
0.814 0.004 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
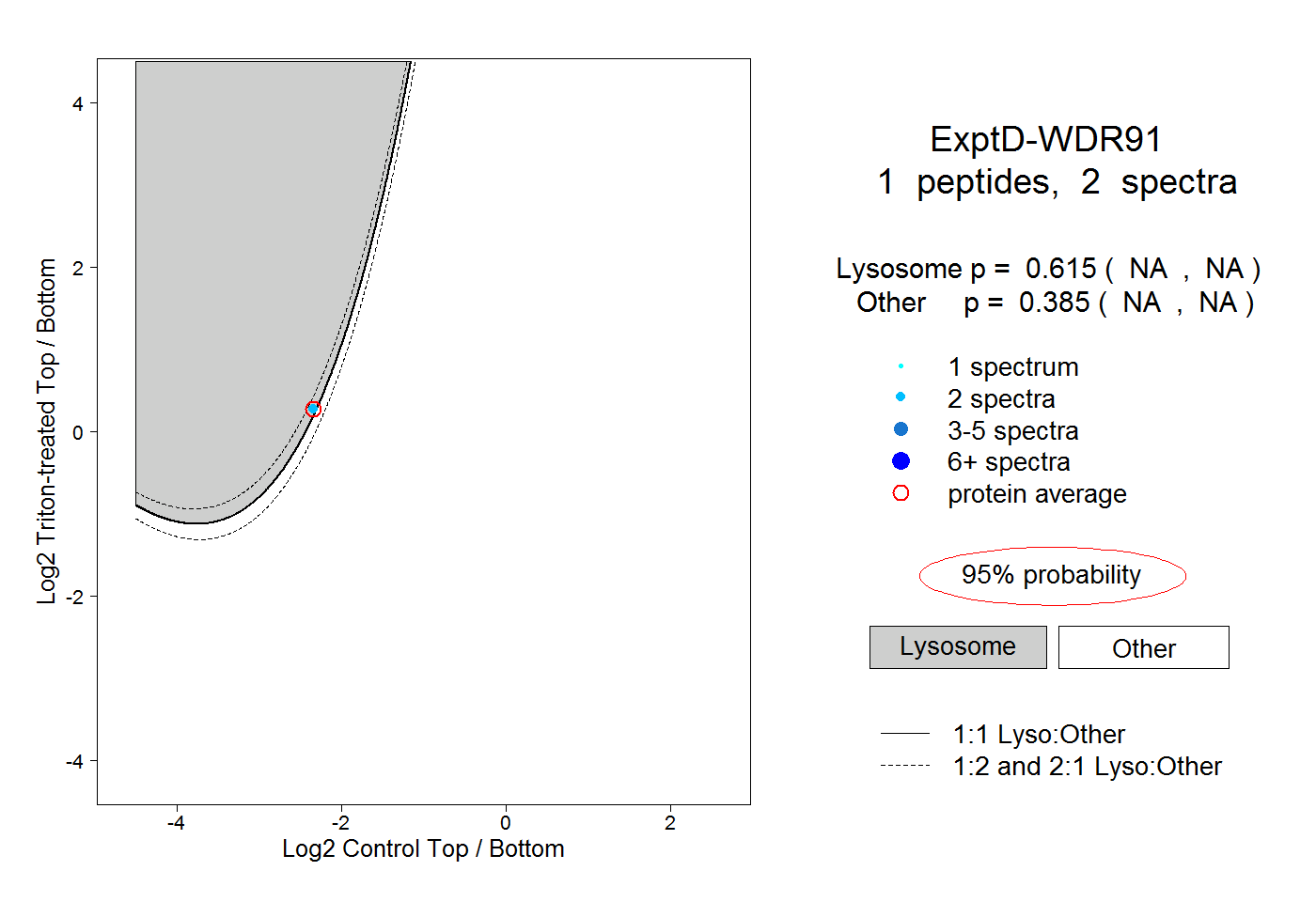 |
0.615 NA | NA |
0.385 NA | NA |