peptides
spectra
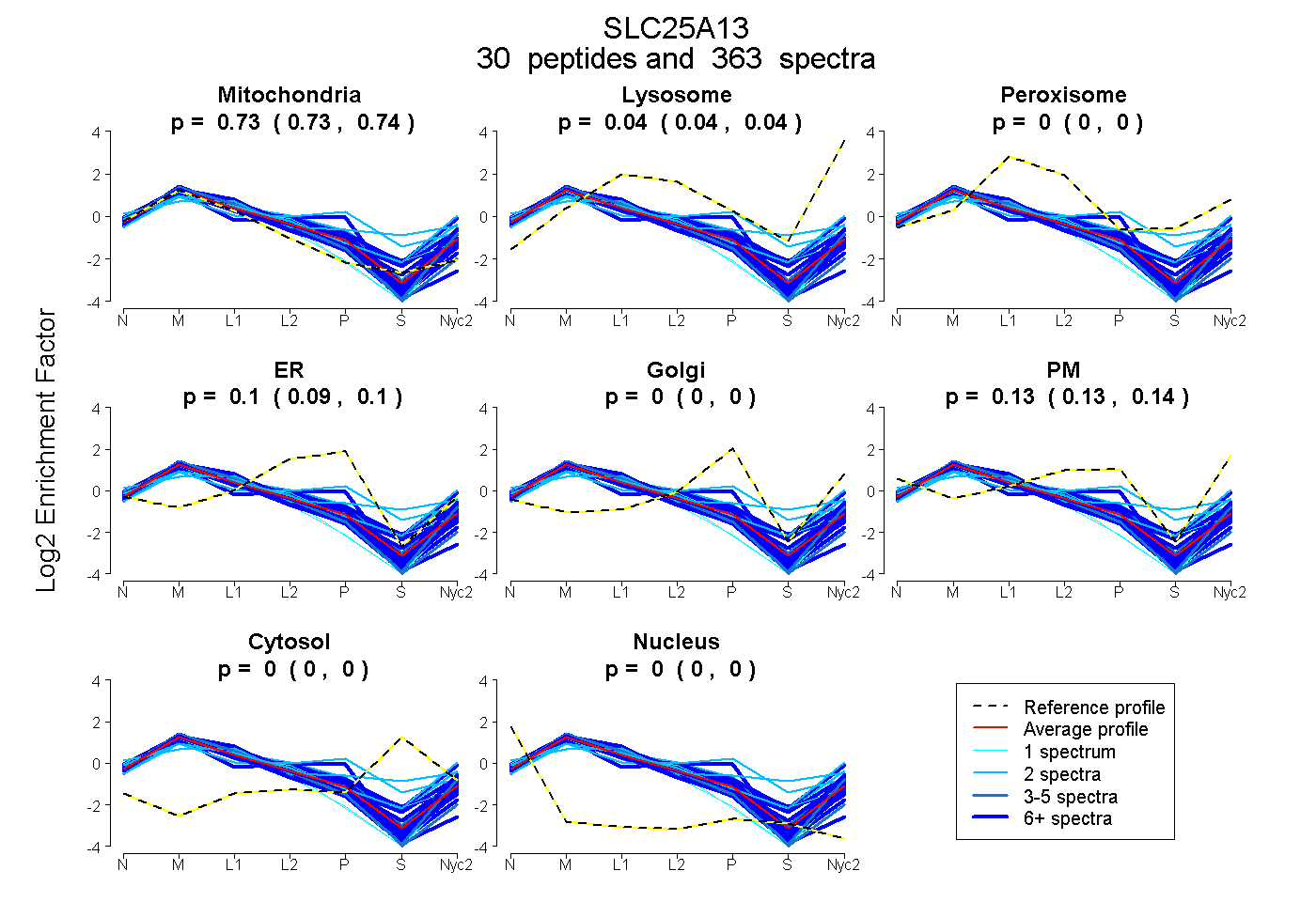
0.733 | 0.736
0.035 | 0.038
0.000 | 0.000
0.092 | 0.098
0.000 | 0.000
0.129 | 0.136
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
363 spectra |
 |
0.735 0.733 | 0.736 |
0.037 0.035 | 0.038 |
0.000 0.000 | 0.000 |
0.095 0.092 | 0.098 |
0.000 0.000 | 0.000 |
0.133 0.129 | 0.136 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 6 spectra, GLIPQLIGVAPEK | 0.803 | 0.000 | 0.000 | 0.059 | 0.000 | 0.138 | 0.000 | 0.000 | ||
| 18 spectra, LQVAGEITTGPR | 0.741 | 0.100 | 0.000 | 0.009 | 0.000 | 0.151 | 0.000 | 0.000 | ||
| 26 spectra, QAFVQR | 0.587 | 0.000 | 0.000 | 0.413 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, ADPAELK | 0.576 | 0.200 | 0.000 | 0.130 | 0.009 | 0.084 | 0.000 | 0.000 | ||
| 2 spectra, VTAVGS | 0.410 | 0.000 | 0.253 | 0.000 | 0.021 | 0.164 | 0.152 | 0.000 | ||
| 1 spectrum, TVELLSGVVDQTK | 0.703 | 0.000 | 0.098 | 0.063 | 0.000 | 0.132 | 0.004 | 0.000 | ||
| 1 spectrum, FGLGSIAGAVGATAVYPIDLVK | 0.834 | 0.000 | 0.000 | 0.054 | 0.000 | 0.112 | 0.000 | 0.000 | ||
| 15 spectra, LTVNDFVR | 0.744 | 0.050 | 0.000 | 0.000 | 0.000 | 0.207 | 0.000 | 0.000 | ||
| 9 spectra, STGSFVGELMYK | 0.760 | 0.033 | 0.000 | 0.000 | 0.000 | 0.207 | 0.000 | 0.000 | ||
| 17 spectra, AGQTTYSGVTDCFR | 0.929 | 0.000 | 0.000 | 0.071 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, YLNIFGESQPNPK | 0.601 | 0.218 | 0.000 | 0.000 | 0.000 | 0.173 | 0.000 | 0.008 | ||
| 14 spectra, ITLPAPNPDHVGGYK | 0.814 | 0.000 | 0.000 | 0.114 | 0.000 | 0.072 | 0.000 | 0.000 | ||
| 20 spectra, YEGFFGLYR | 0.702 | 0.063 | 0.000 | 0.000 | 0.000 | 0.236 | 0.000 | 0.000 | ||
| 5 spectra, NSFDCFK | 0.810 | 0.000 | 0.000 | 0.190 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 15 spectra, IYSTLAGSR | 0.676 | 0.000 | 0.000 | 0.214 | 0.000 | 0.110 | 0.000 | 0.000 | ||
| 27 spectra, VSALSVVR | 0.760 | 0.006 | 0.000 | 0.075 | 0.000 | 0.159 | 0.000 | 0.000 | ||
| 1 spectrum, FGQVTPMEVDILFQLADLYEPR | 0.880 | 0.000 | 0.000 | 0.000 | 0.000 | 0.120 | 0.000 | 0.000 | ||
| 5 spectra, LAVATFAGIENK | 0.654 | 0.074 | 0.000 | 0.183 | 0.000 | 0.088 | 0.000 | 0.000 | ||
| 15 spectra, ASGDAARPFLLQLAESAYR | 0.844 | 0.000 | 0.000 | 0.147 | 0.000 | 0.009 | 0.000 | 0.000 | ||
| 17 spectra, VTAIDFR | 0.843 | 0.000 | 0.000 | 0.023 | 0.000 | 0.134 | 0.000 | 0.000 | ||
| 33 spectra, LQVAAR | 0.693 | 0.149 | 0.041 | 0.000 | 0.000 | 0.116 | 0.000 | 0.000 | ||
| 44 spectra, GEVTFEDVR | 0.721 | 0.000 | 0.120 | 0.011 | 0.147 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, NGEFFMSPHDFVTR | 0.576 | 0.188 | 0.000 | 0.000 | 0.021 | 0.214 | 0.000 | 0.000 | ||
| 2 spectra, SSPQFGVTLLTYELLQR | 0.406 | 0.000 | 0.176 | 0.098 | 0.278 | 0.000 | 0.042 | 0.000 | ||
| 7 spectra, VALTK | 0.749 | 0.000 | 0.000 | 0.198 | 0.000 | 0.053 | 0.000 | 0.000 | ||
| 1 spectrum, EEFALAAQK | 0.853 | 0.038 | 0.000 | 0.000 | 0.000 | 0.110 | 0.000 | 0.000 | ||
| 25 spectra, MTLADIER | 0.694 | 0.059 | 0.000 | 0.167 | 0.000 | 0.081 | 0.000 | 0.000 | ||
| 3 spectra, YASIEK | 0.765 | 0.038 | 0.000 | 0.000 | 0.000 | 0.196 | 0.000 | 0.000 | ||
| 5 spectra, DIPFSAIYFPCYAHVK | 0.713 | 0.051 | 0.000 | 0.109 | 0.000 | 0.127 | 0.000 | 0.000 | ||
| 13 spectra, DLGFFGIYK | 0.734 | 0.003 | 0.000 | 0.096 | 0.000 | 0.167 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
271 spectra |
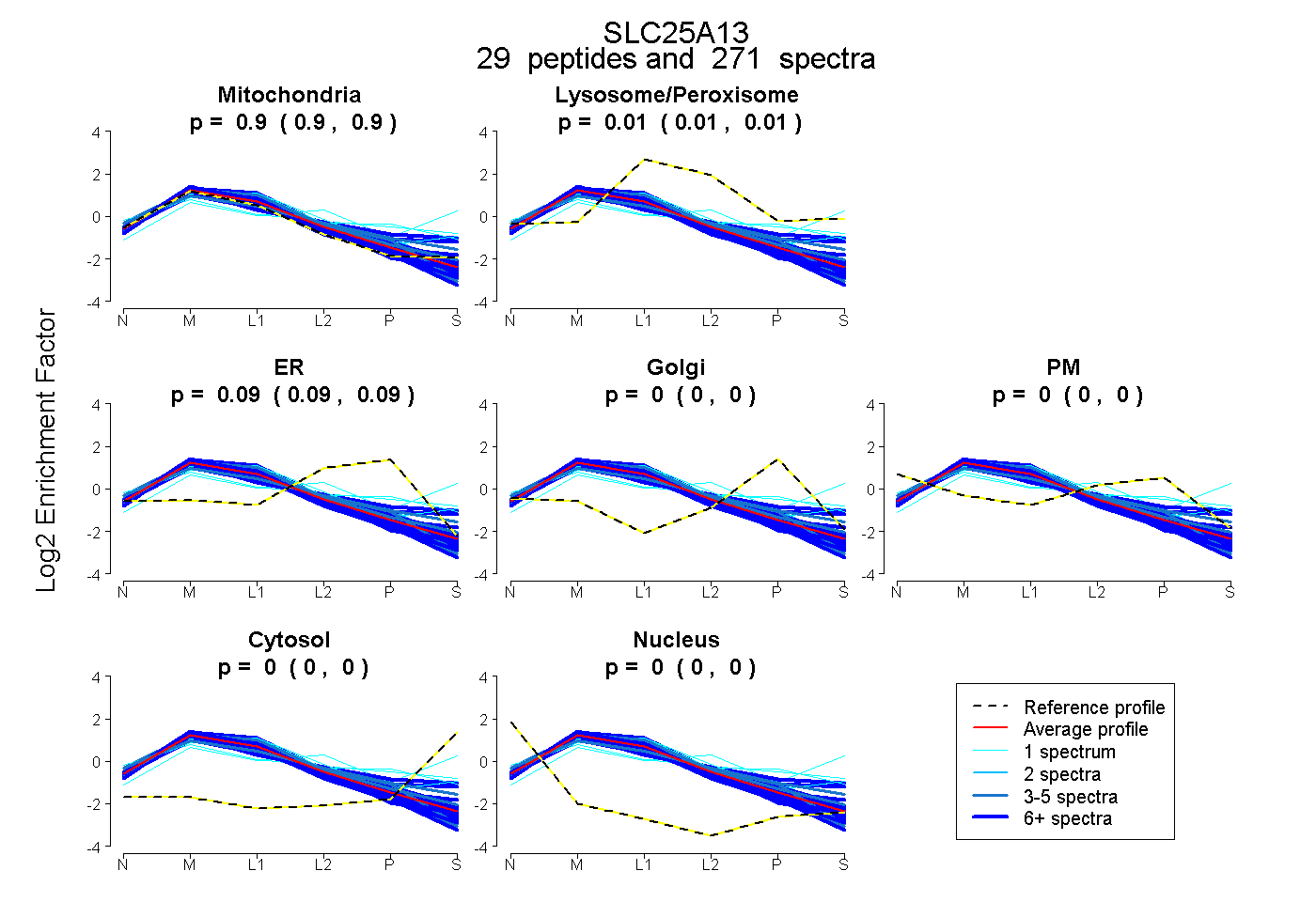 |
0.900 0.898 | 0.901 |
0.012 0.010 | 0.013 |
0.088 0.086 | 0.090 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1257 spectra |
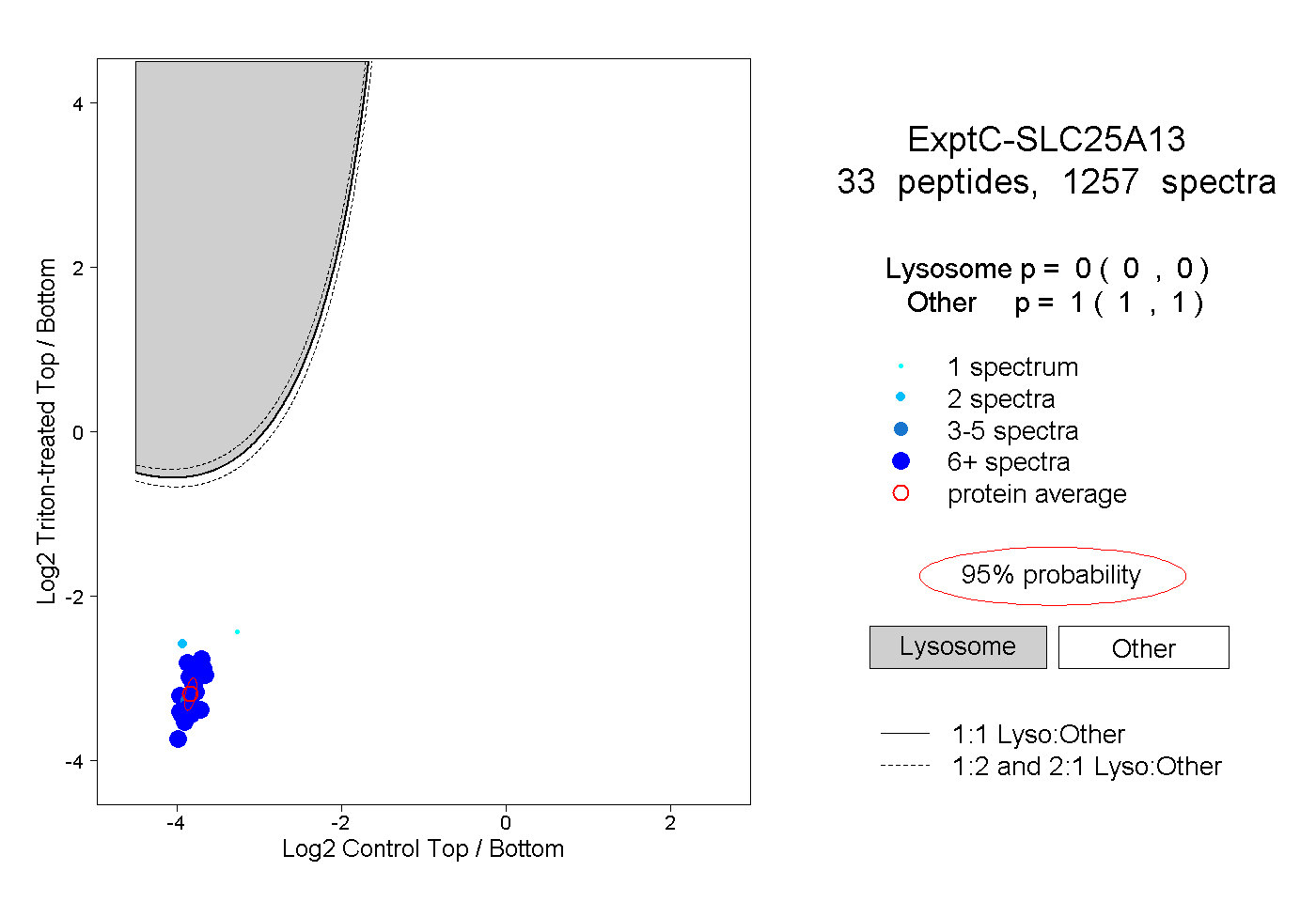 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
98 spectra |
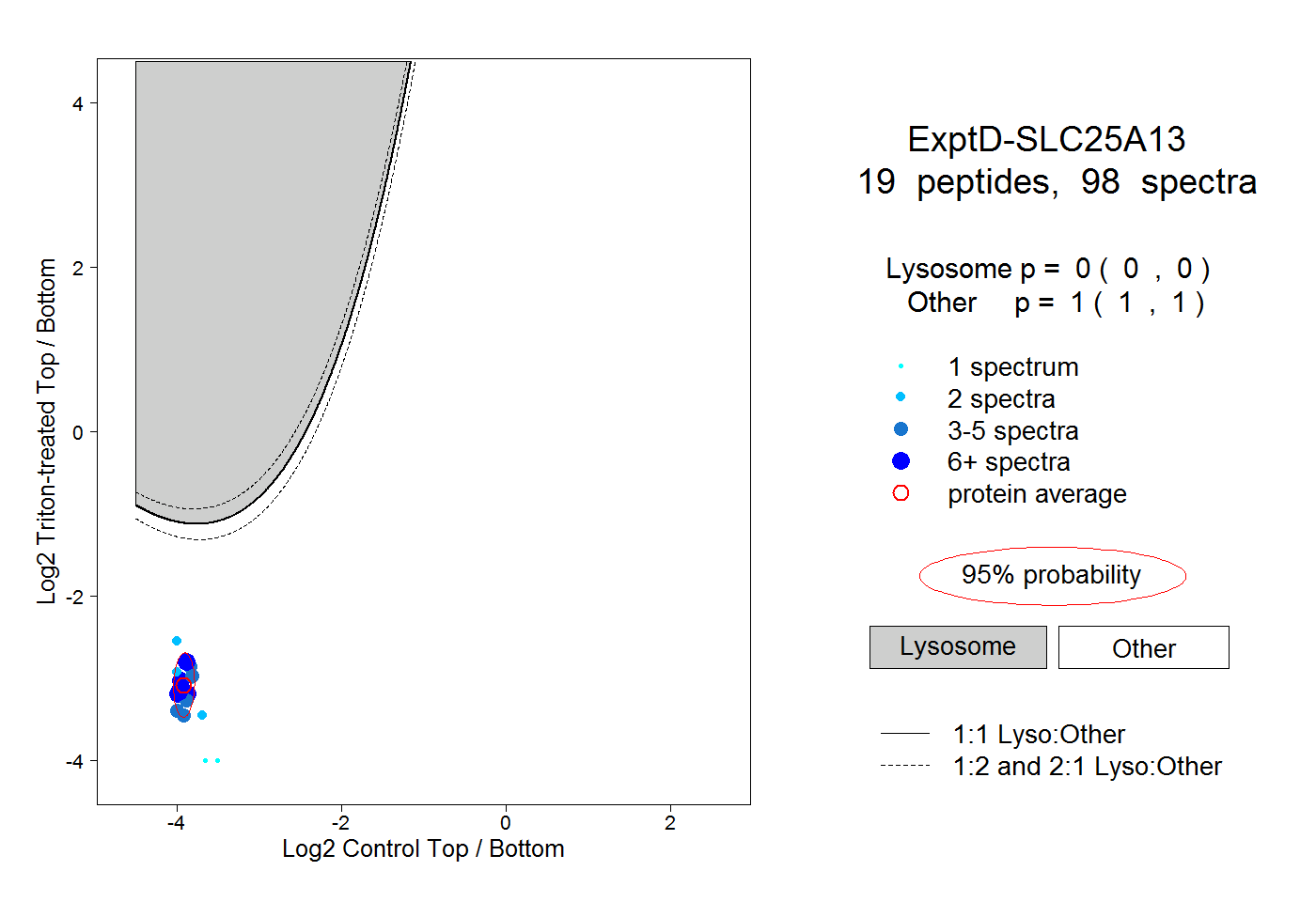 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |