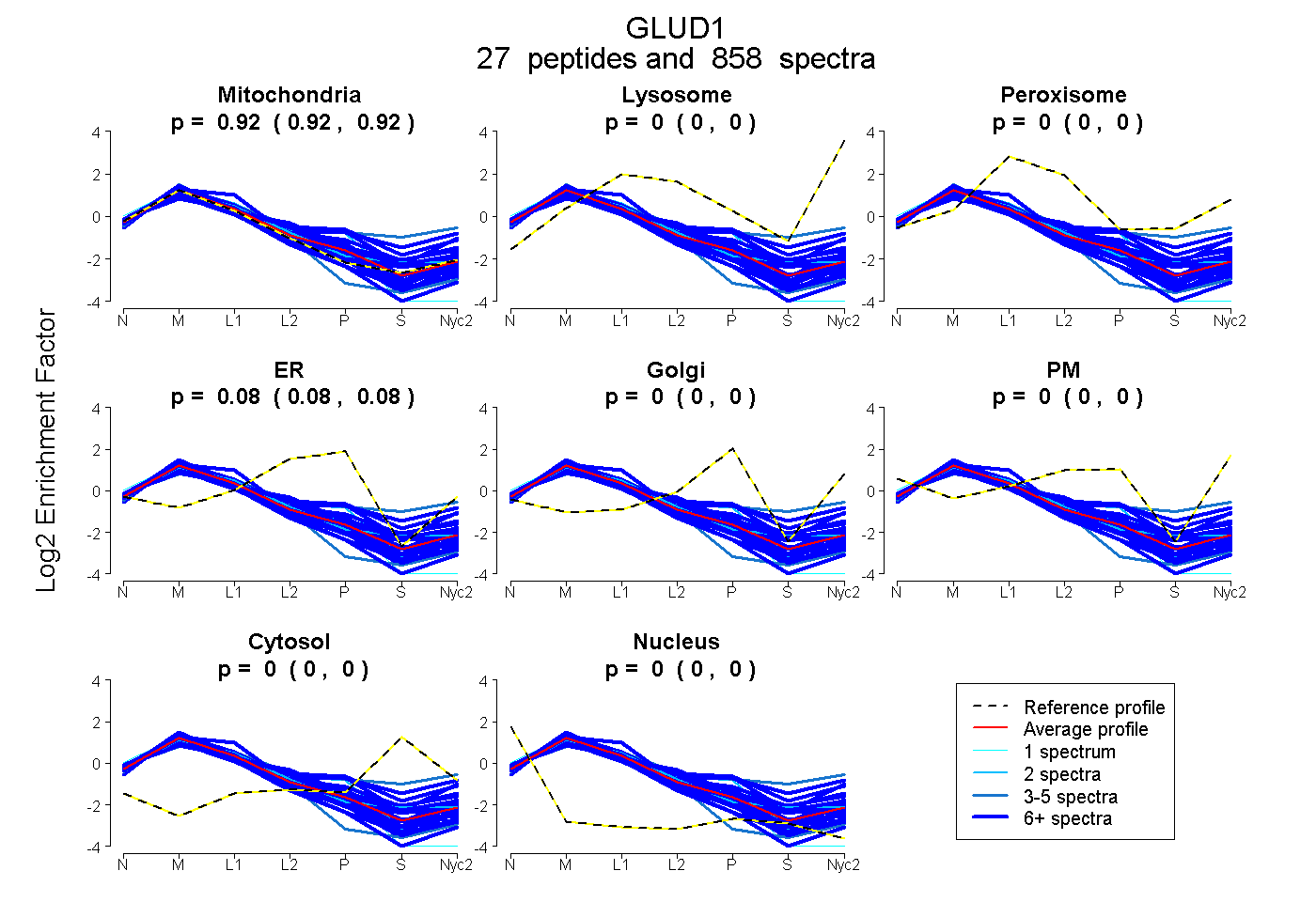
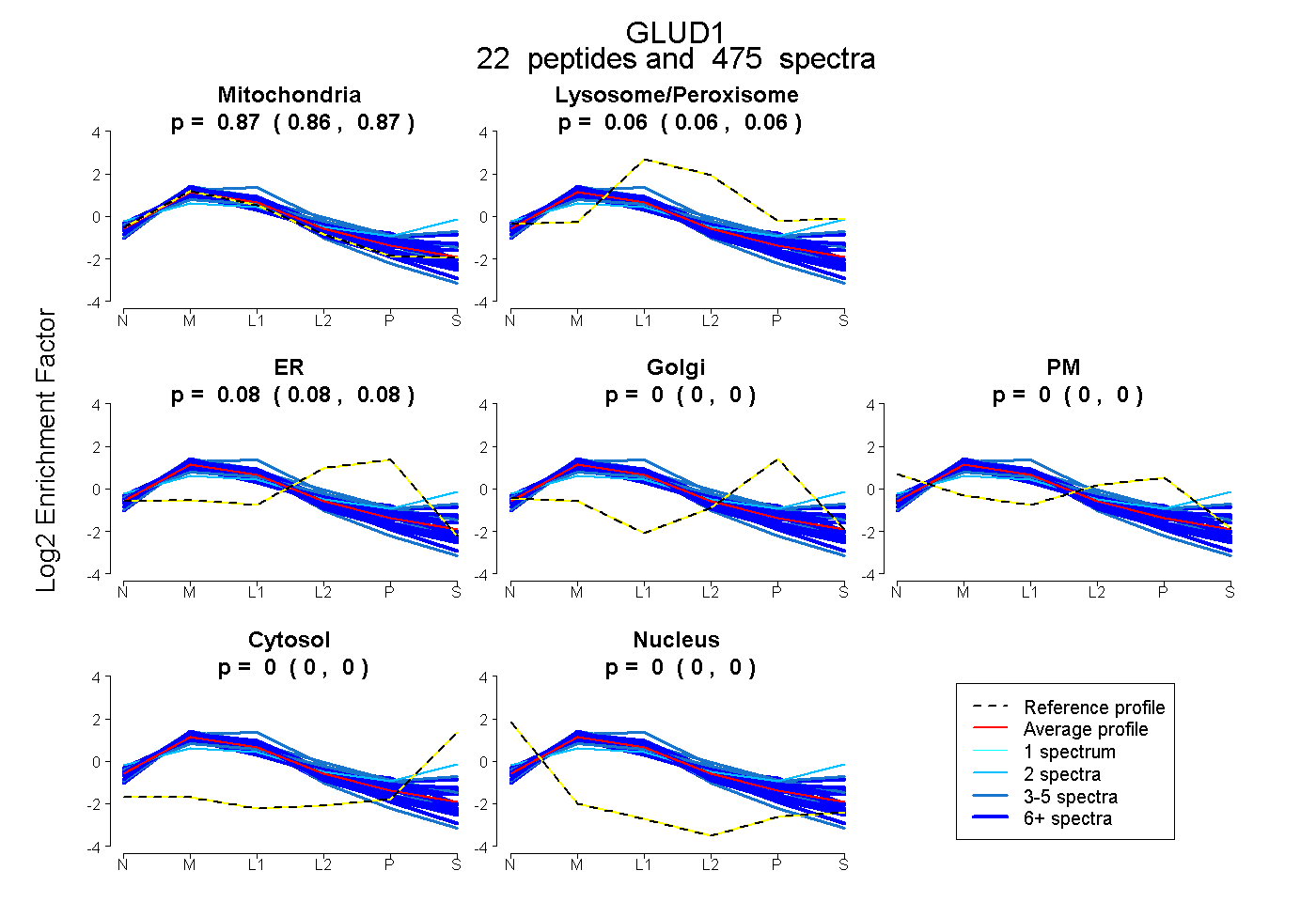
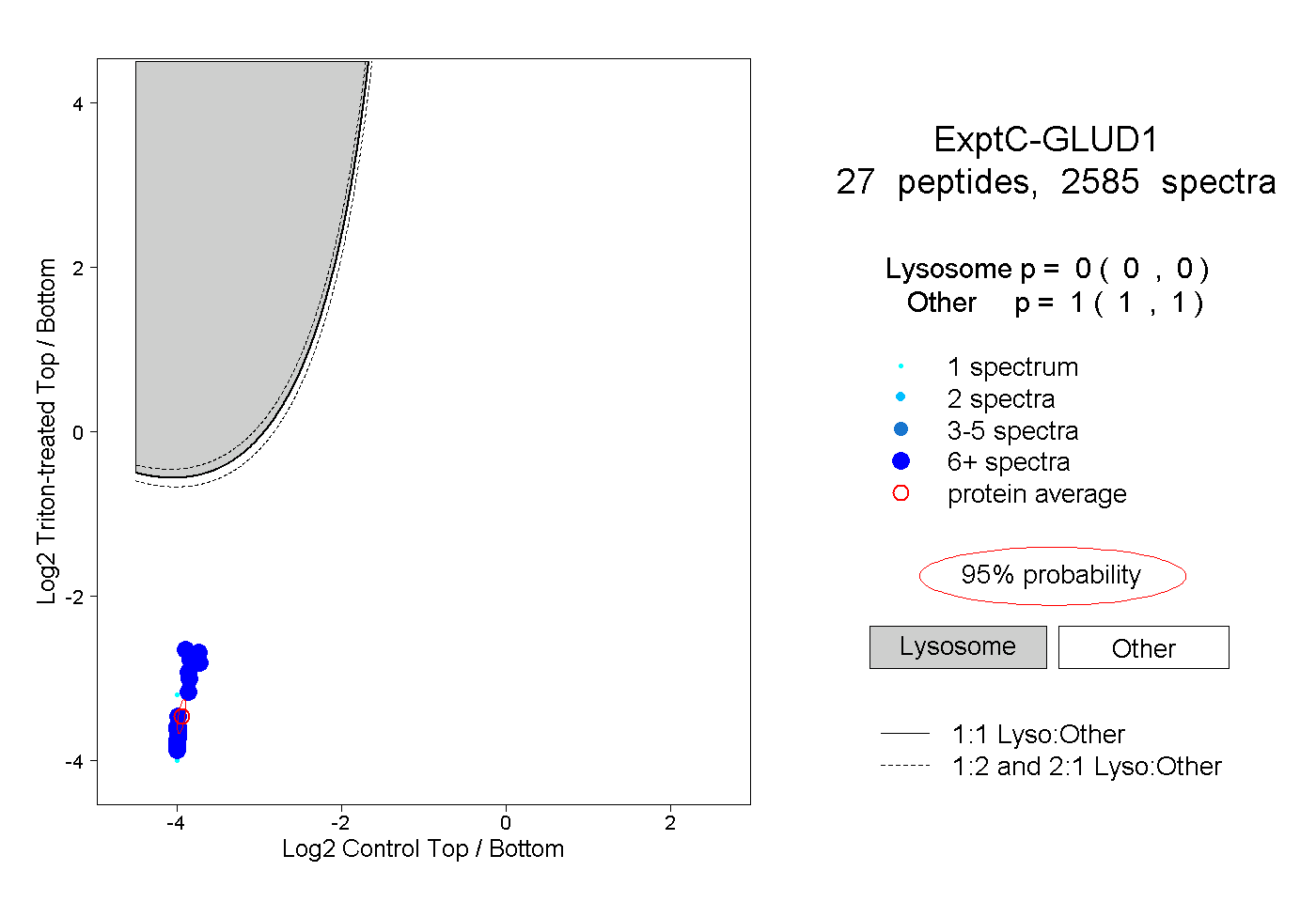
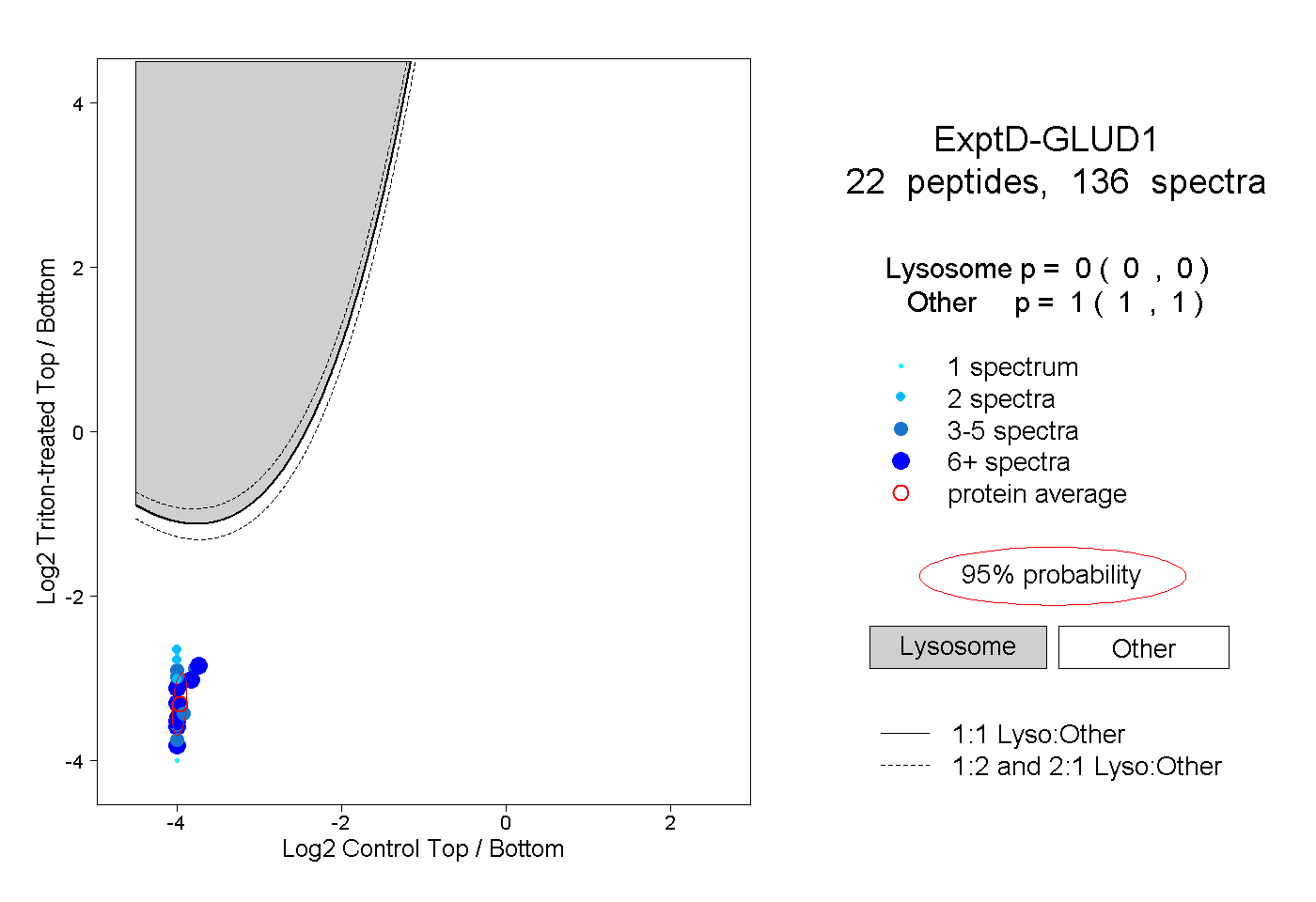
| 3 spectra, ALASLMTYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, YSTDVSVDEVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, CAVVDVPFGGAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VYNEAGVTFT |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ENEEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, NYTDNELEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DSNYHLLMSVQESLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EDDPNFFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ISATGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, GASIVEDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, YNLGLDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TAAYVNAIEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, FTMELAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NLNHVSYGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LVEDLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, DDGSWEVIEGYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LQHGSILGFPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, DIVHSGLAYTMER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, MVEGFFDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, HGGTIPVVPTAEFQDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, ISGASEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IIAEGANGPTTPEADK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |