peptides
spectra
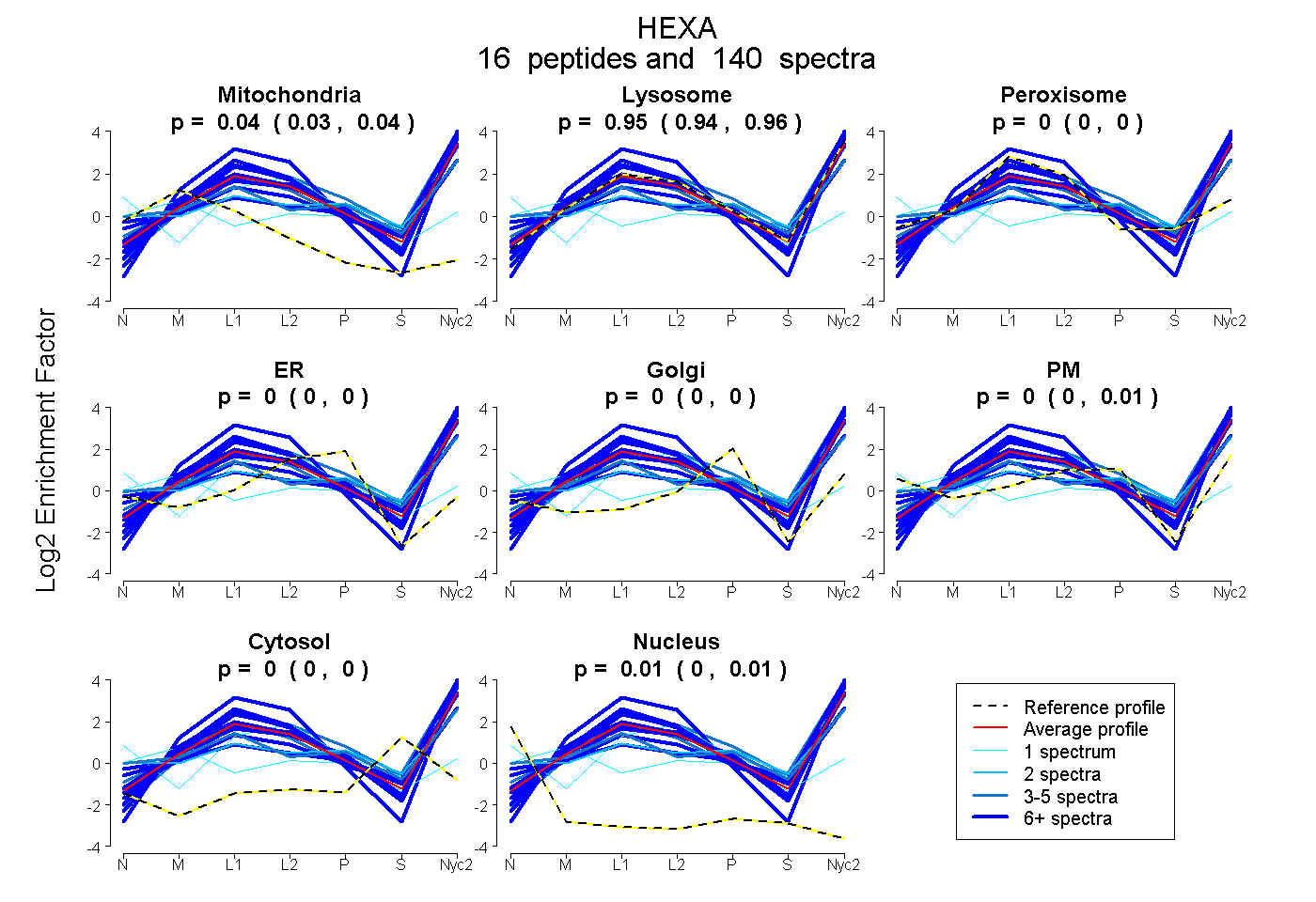
0.029 | 0.041
0.942 | 0.958
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.011
0.000 | 0.000
0.004 | 0.013
peptides
spectra
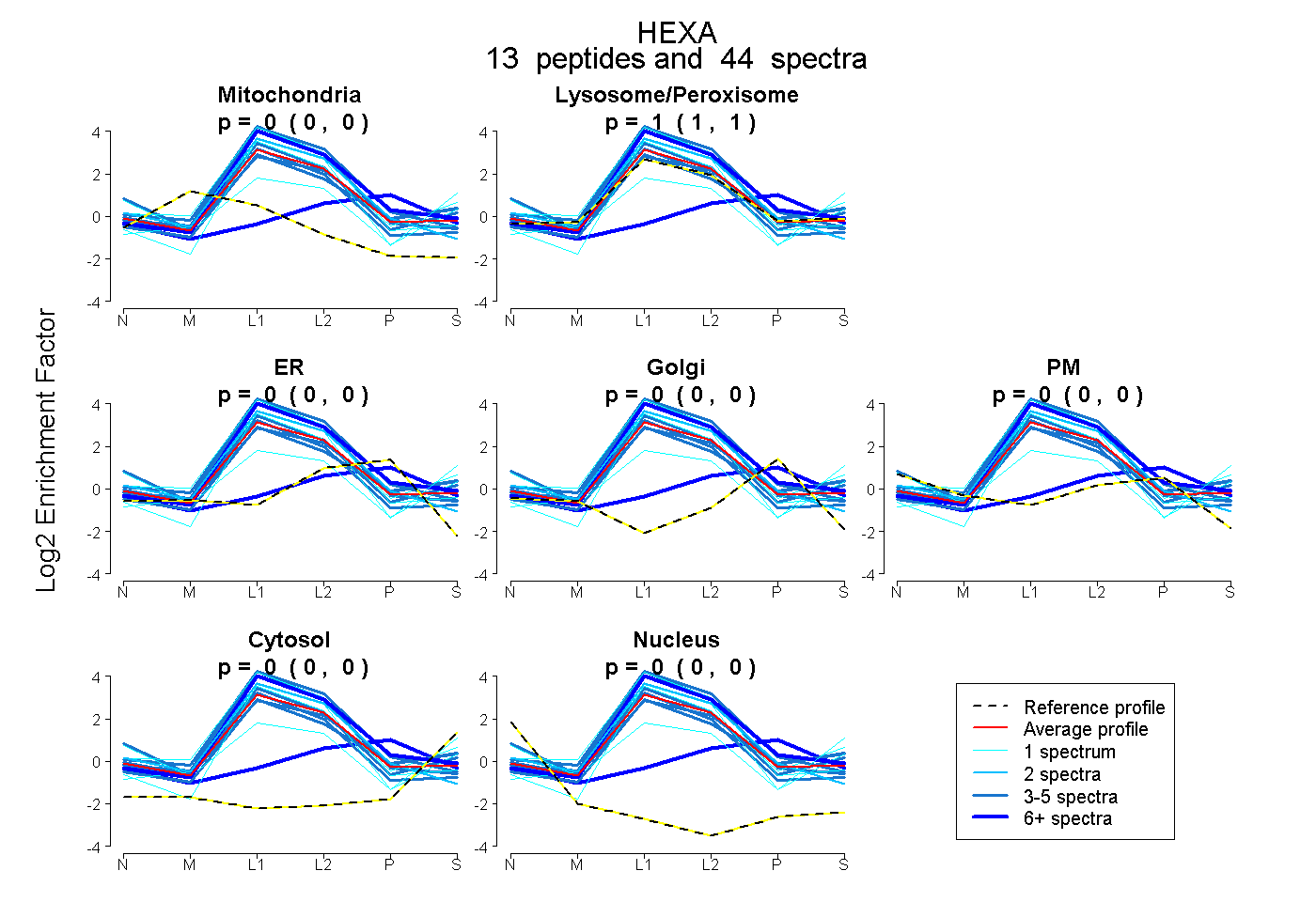
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
140 spectra |
 |
0.035 0.029 | 0.041 |
0.953 0.942 | 0.958 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.011 |
0.000 0.000 | 0.000 |
0.010 0.004 | 0.013 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
44 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 7 spectra, VRPDTIIQVWR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GLETFSQLVWK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, EIEAITQAGFR | 0.000 | 0.958 | 0.000 | 0.000 | 0.000 | 0.000 | 0.042 | |||
| 1 spectrum, VEPLAFR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, YTLYPNNFQFR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, AGAIAER | 0.000 | 0.332 | 0.257 | 0.269 | 0.000 | 0.142 | 0.000 | |||
| 3 spectra, GYVVWQEVFDNK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, YGPDWK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, GILLDTSR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SNPNIQAFMK | 0.000 | 0.823 | 0.000 | 0.000 | 0.000 | 0.019 | 0.159 | |||
| 5 spectra, ITDFPR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ALLSAPWYLNR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, GFTDYK | 0.000 | 0.972 | 0.000 | 0.000 | 0.000 | 0.028 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
573 spectra |
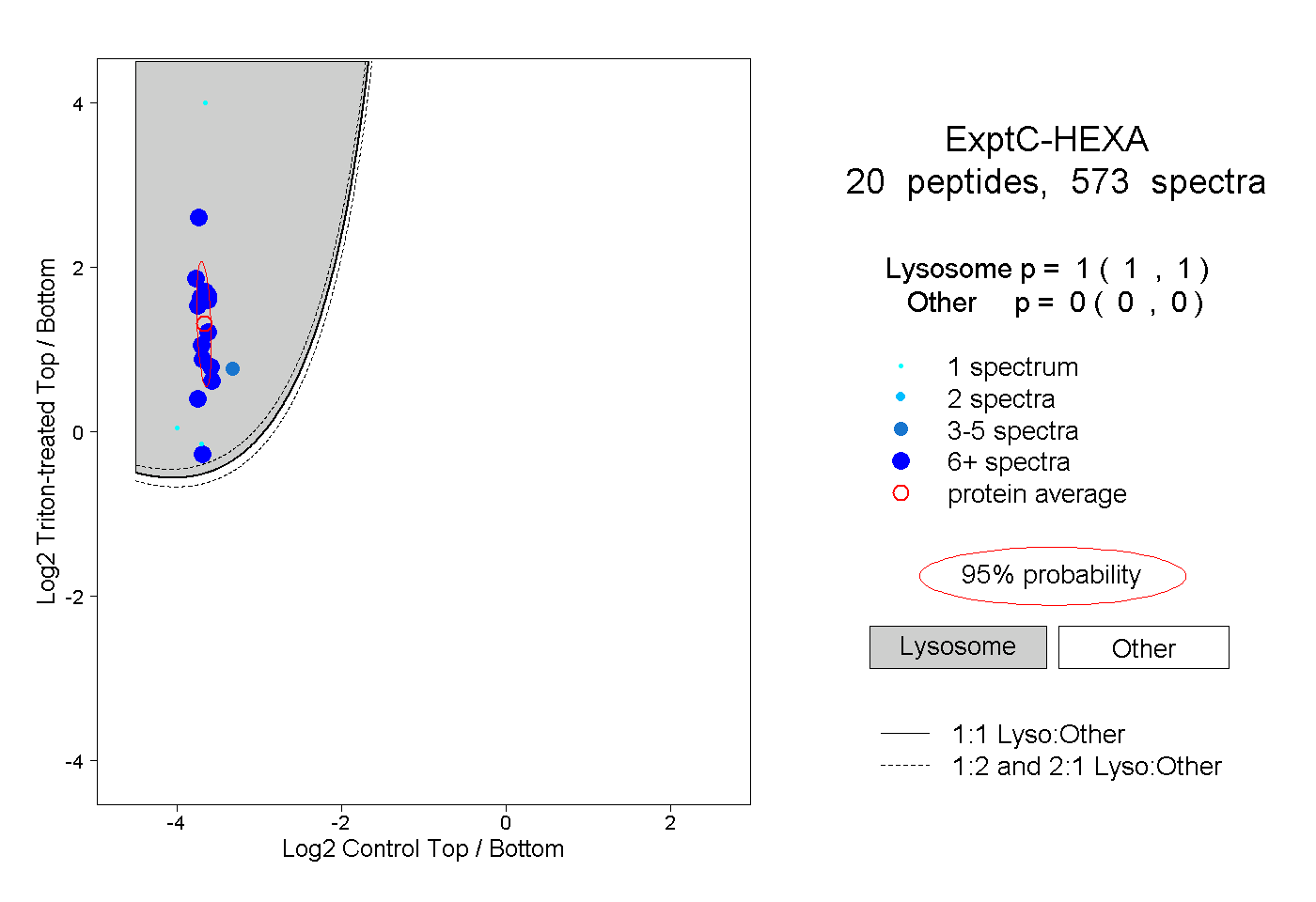 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
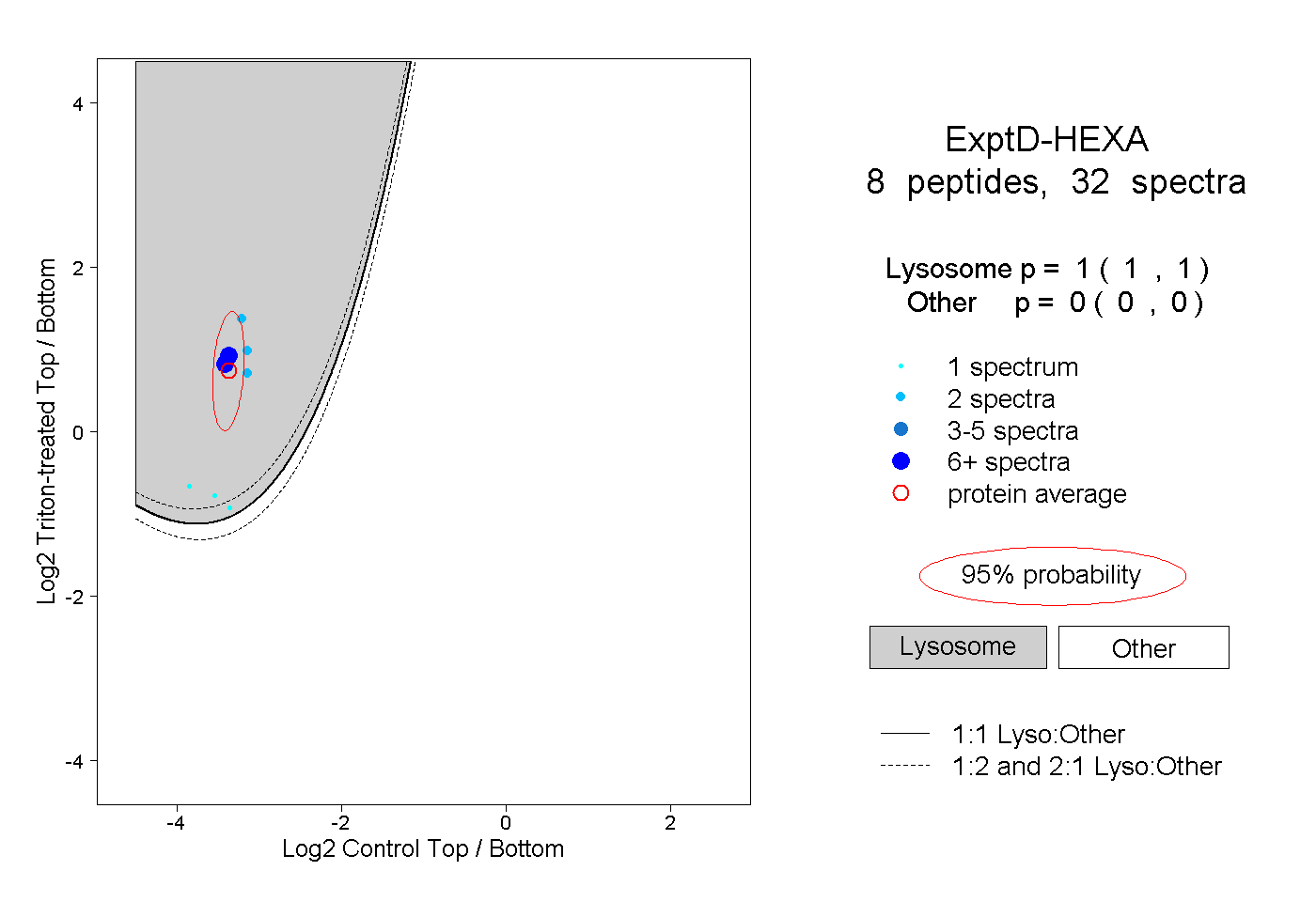 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |