peptides
spectra
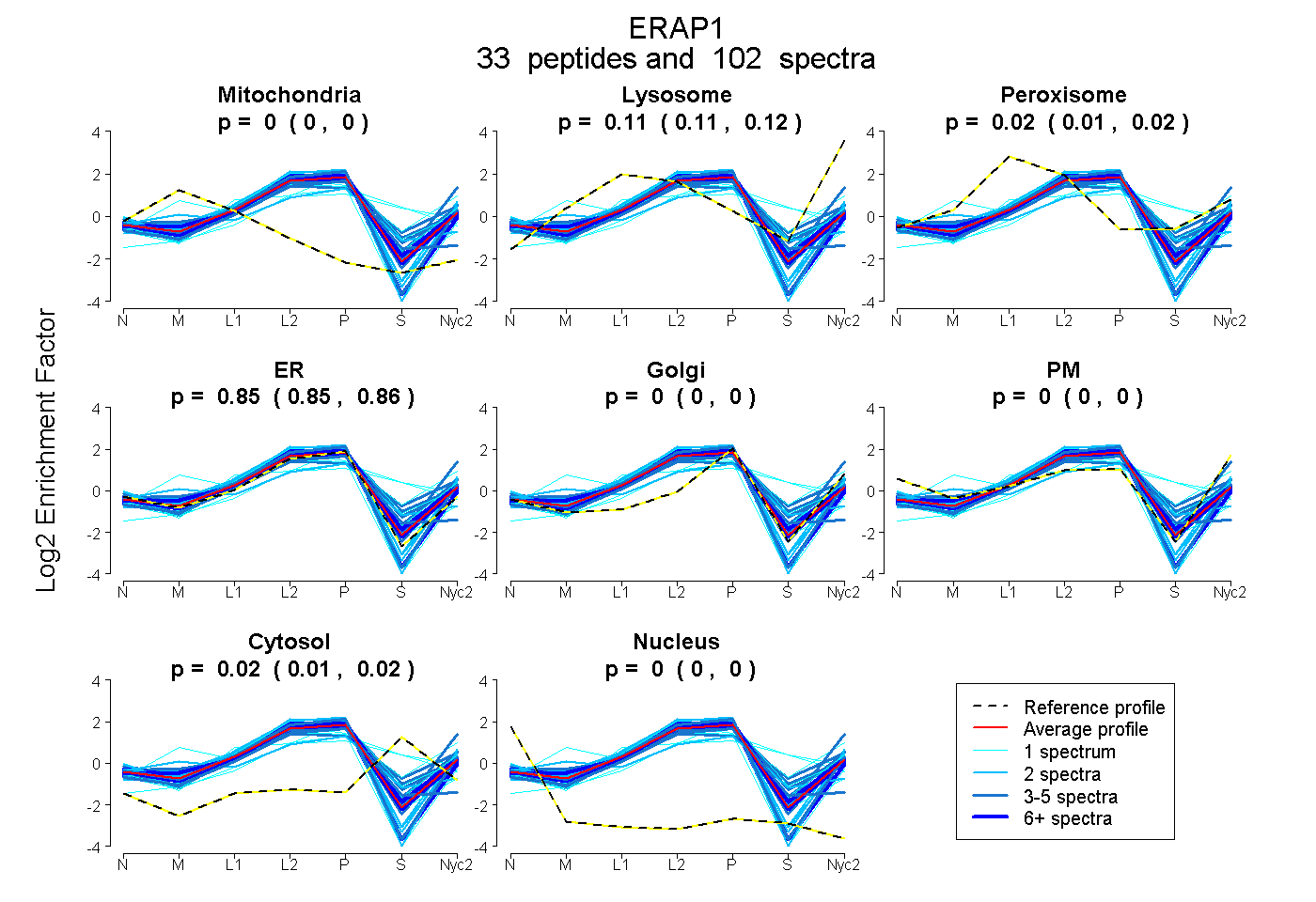
0.000 | 0.000
0.109 | 0.119
0.013 | 0.022
0.846 | 0.856
0.000 | 0.000
0.000 | 0.000
0.013 | 0.019
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
102 spectra |
 |
0.000 0.000 | 0.000 |
0.115 0.109 | 0.119 |
0.018 0.013 | 0.022 |
0.851 0.846 | 0.856 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.016 0.013 | 0.019 |
0.000 0.000 | 0.000 |
| 5 spectra, QEHYMK | 0.000 | 0.137 | 0.067 | 0.648 | 0.101 | 0.000 | 0.046 | 0.000 | ||
| 1 spectrum, ASLINNAFQLVSIGK | 0.000 | 0.000 | 0.149 | 0.612 | 0.188 | 0.000 | 0.051 | 0.000 | ||
| 7 spectra, TQEFPHILTLIGR | 0.000 | 0.105 | 0.028 | 0.865 | 0.000 | 0.000 | 0.002 | 0.000 | ||
| 10 spectra, QEVIDIK | 0.000 | 0.000 | 0.000 | 0.988 | 0.000 | 0.012 | 0.000 | 0.000 | ||
| 2 spectra, GAEEMLPEEPLK | 0.000 | 0.042 | 0.000 | 0.871 | 0.000 | 0.087 | 0.000 | 0.000 | ||
| 1 spectrum, ASFSIK | 0.000 | 0.069 | 0.120 | 0.409 | 0.000 | 0.000 | 0.402 | 0.000 | ||
| 3 spectra, HLAISNMPLVK | 0.000 | 0.144 | 0.138 | 0.497 | 0.035 | 0.039 | 0.146 | 0.000 | ||
| 4 spectra, YQLCVQR | 0.000 | 0.000 | 0.005 | 0.827 | 0.000 | 0.000 | 0.168 | 0.000 | ||
| 4 spectra, SDSVQR | 0.000 | 0.074 | 0.096 | 0.702 | 0.000 | 0.000 | 0.129 | 0.000 | ||
| 4 spectra, NPVGYPLAWK | 0.000 | 0.198 | 0.000 | 0.443 | 0.030 | 0.330 | 0.000 | 0.000 | ||
| 1 spectrum, ASNGASFLWNNMR | 0.000 | 0.142 | 0.005 | 0.854 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, ESALLYDK | 0.000 | 0.119 | 0.043 | 0.736 | 0.000 | 0.000 | 0.102 | 0.000 | ||
| 5 spectra, EMFDEVSYEK | 0.000 | 0.038 | 0.101 | 0.738 | 0.000 | 0.000 | 0.123 | 0.000 | ||
| 6 spectra, GFPLITITVR | 0.000 | 0.134 | 0.033 | 0.808 | 0.000 | 0.000 | 0.025 | 0.000 | ||
| 1 spectrum, LQWLLDQSFK | 0.104 | 0.120 | 0.000 | 0.619 | 0.000 | 0.157 | 0.000 | 0.000 | ||
| 1 spectrum, MAFPCFDEPALK | 0.000 | 0.000 | 0.072 | 0.928 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, MSTYLVAFIISDFK | 0.000 | 0.182 | 0.051 | 0.438 | 0.000 | 0.189 | 0.140 | 0.000 | ||
| 2 spectra, SMMNTWTLQK | 0.000 | 0.107 | 0.000 | 0.856 | 0.000 | 0.000 | 0.038 | 0.000 | ||
| 2 spectra, DYLSADTFK | 0.000 | 0.105 | 0.126 | 0.764 | 0.000 | 0.004 | 0.000 | 0.000 | ||
| 3 spectra, YQSSLSSTEK | 0.000 | 0.012 | 0.000 | 0.908 | 0.000 | 0.080 | 0.000 | 0.000 | ||
| 1 spectrum, CVQQTIETIEENIR | 0.000 | 0.099 | 0.100 | 0.802 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, GACILNMLR | 0.000 | 0.101 | 0.038 | 0.837 | 0.000 | 0.000 | 0.025 | 0.000 | ||
| 1 spectrum, ALDLILYLK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, SSASSK | 0.000 | 0.013 | 0.000 | 0.786 | 0.000 | 0.200 | 0.000 | 0.000 | ||
| 4 spectra, ILAATQFEPTAAR | 0.000 | 0.168 | 0.000 | 0.819 | 0.000 | 0.014 | 0.000 | 0.000 | ||
| 7 spectra, VEEYFFGK | 0.000 | 0.110 | 0.023 | 0.843 | 0.000 | 0.000 | 0.024 | 0.000 | ||
| 1 spectrum, SVTVAEGLIEDHFDITVK | 0.000 | 0.071 | 0.090 | 0.728 | 0.000 | 0.000 | 0.111 | 0.000 | ||
| 1 spectrum, TDVIILPEAVEWIK | 0.000 | 0.136 | 0.059 | 0.791 | 0.000 | 0.000 | 0.014 | 0.000 | ||
| 2 spectra, FMEFVSVTVTHPELK | 0.000 | 0.091 | 0.000 | 0.909 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, GFFSSLK | 0.000 | 0.137 | 0.000 | 0.852 | 0.000 | 0.011 | 0.000 | 0.000 | ||
| 1 spectrum, DMVEVETQFK | 0.000 | 0.081 | 0.045 | 0.451 | 0.000 | 0.000 | 0.423 | 0.000 | ||
| 2 spectra, SQLLLLACVHR | 0.102 | 0.000 | 0.083 | 0.659 | 0.002 | 0.000 | 0.154 | 0.000 | ||
| 2 spectra, QTWTDEGSVSER | 0.000 | 0.000 | 0.000 | 0.783 | 0.000 | 0.217 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
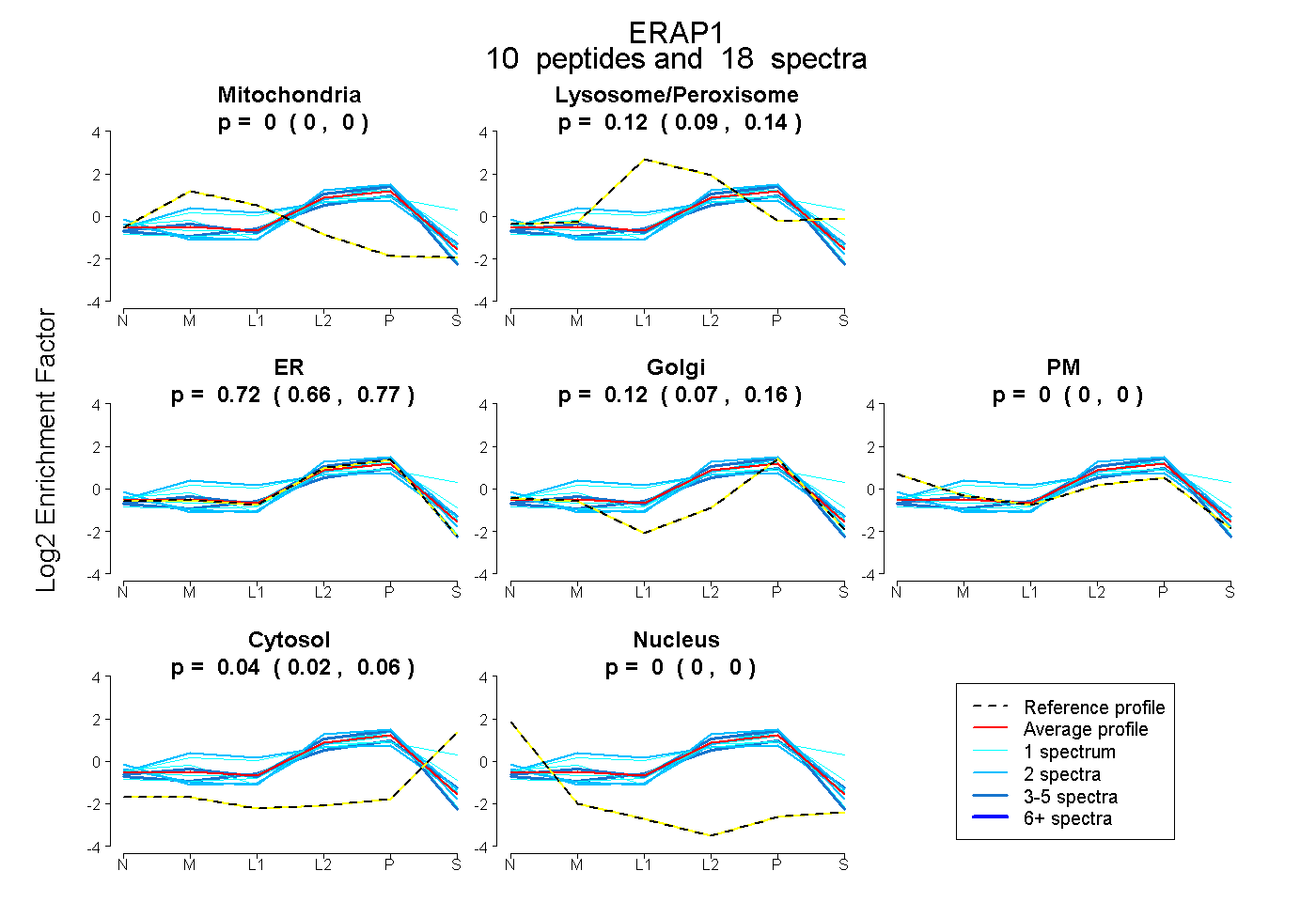 |
0.000 0.000 | 0.000 |
0.120 0.094 | 0.141 |
0.724 0.662 | 0.772 |
0.116 0.069 | 0.156 |
0.000 0.000 | 0.000 |
0.041 0.023 | 0.056 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
80 spectra |
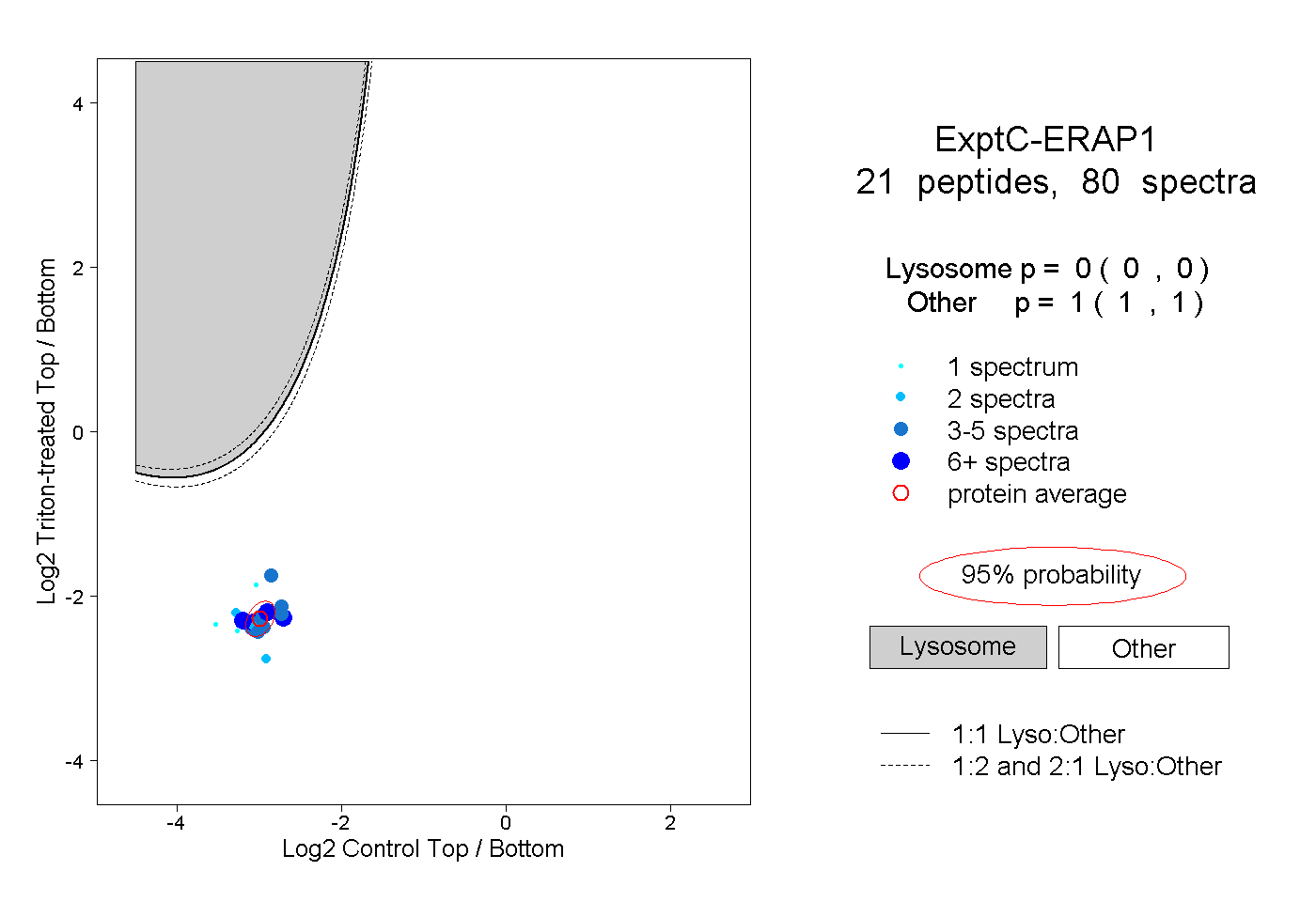 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
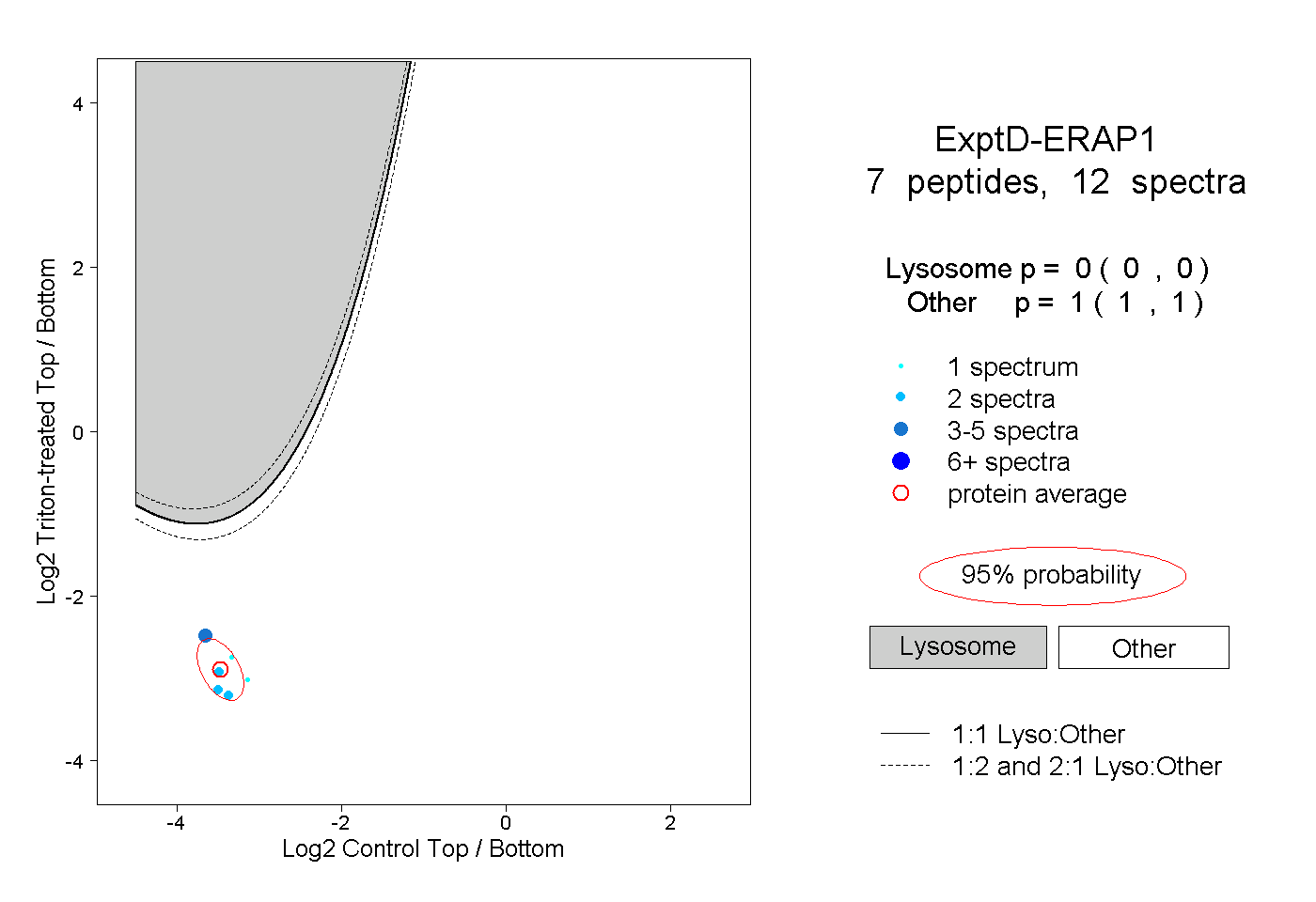 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |