peptides
spectra
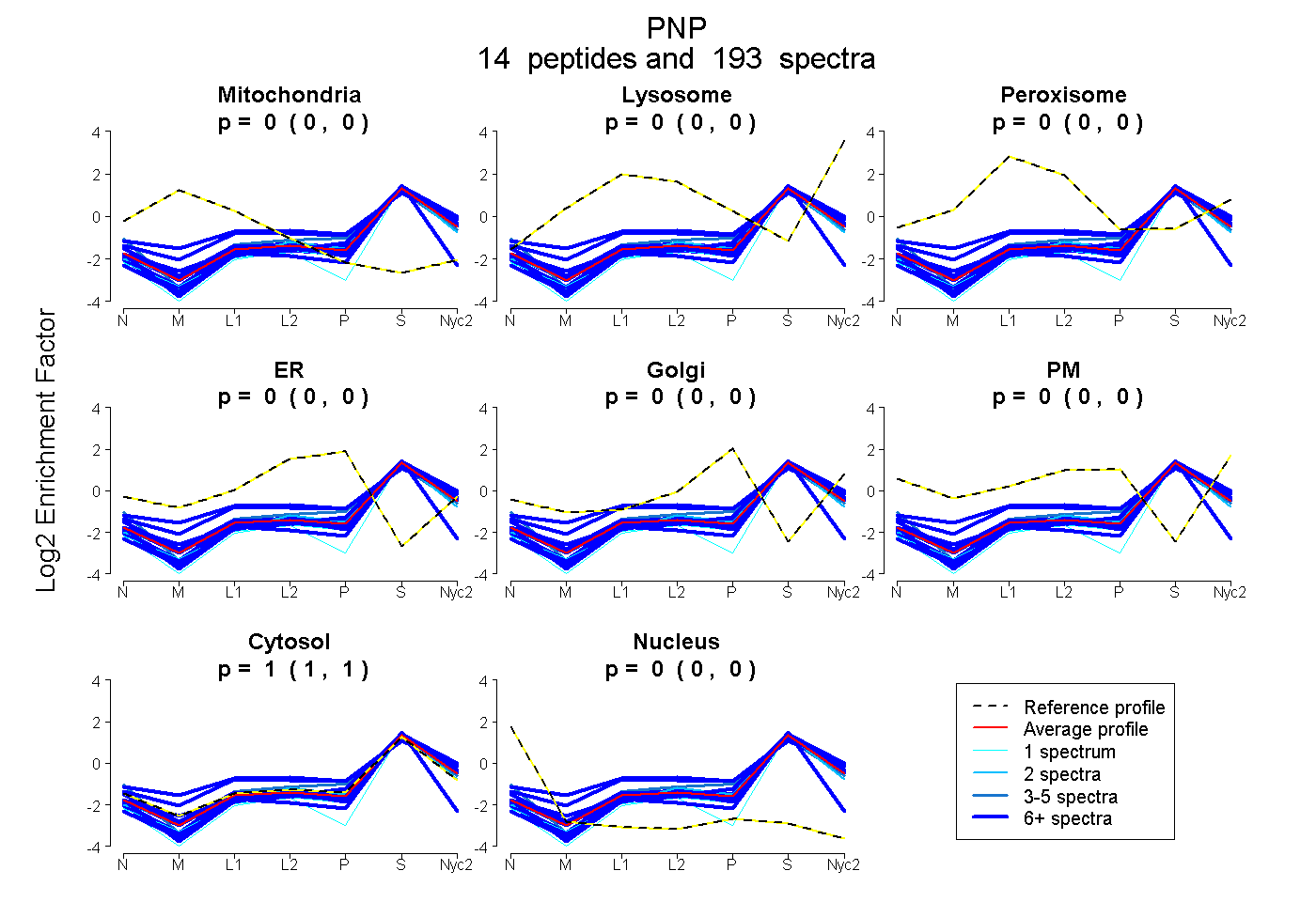
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
peptides
spectra
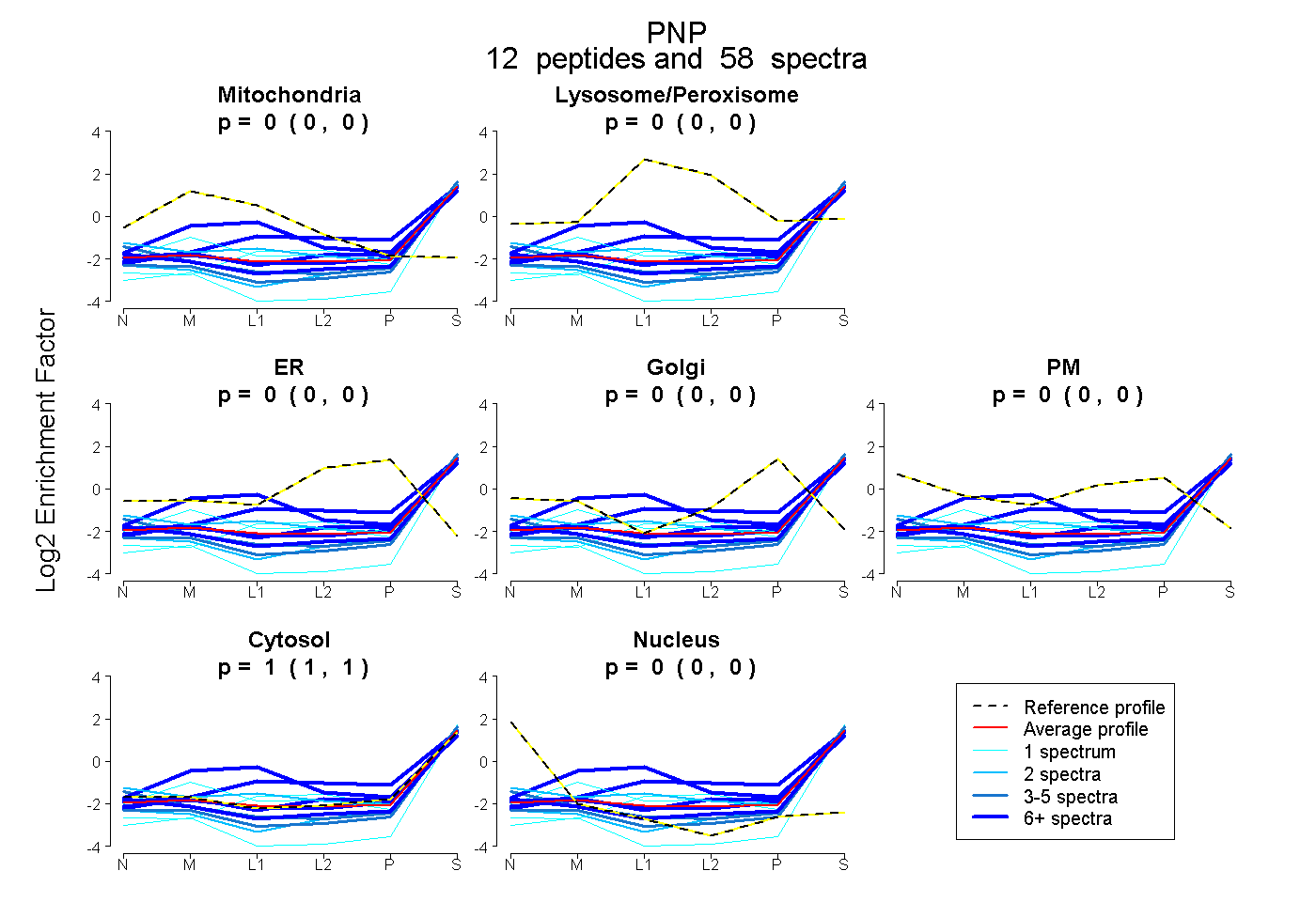
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
193 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
58 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 4 spectra, TAEWLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.922 | 0.078 | |||
| 1 spectrum, HRPQVAVICGSGLGGLTAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, VVMDYNNLEK | 0.000 | 0.092 | 0.000 | 0.000 | 0.000 | 0.878 | 0.031 | |||
| 7 spectra, VTFPVR | 0.000 | 0.004 | 0.000 | 0.000 | 0.000 | 0.996 | 0.000 | |||
| 7 spectra, DHINLPGFCGQNPLR | 0.000 | 0.218 | 0.000 | 0.000 | 0.000 | 0.782 | 0.000 | |||
| 1 spectrum, LTQPQAFDYNEIPNFPQSTVQGHAGR | 0.098 | 0.000 | 0.000 | 0.000 | 0.000 | 0.902 | 0.000 | |||
| 12 spectra, VFHLLGVDTLVVTNAAGGLNPK | 0.144 | 0.205 | 0.000 | 0.000 | 0.000 | 0.651 | 0.000 | |||
| 2 spectra, ASHQEVLEAGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, FPAMSDAYDR | 0.000 | 0.028 | 0.000 | 0.000 | 0.000 | 0.972 | 0.000 | |||
| 3 spectra, LVFGFLNGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 8 spectra, VFGFSLITNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.967 | 0.033 | |||
| 10 spectra, FEVGDIMLIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
164 spectra |
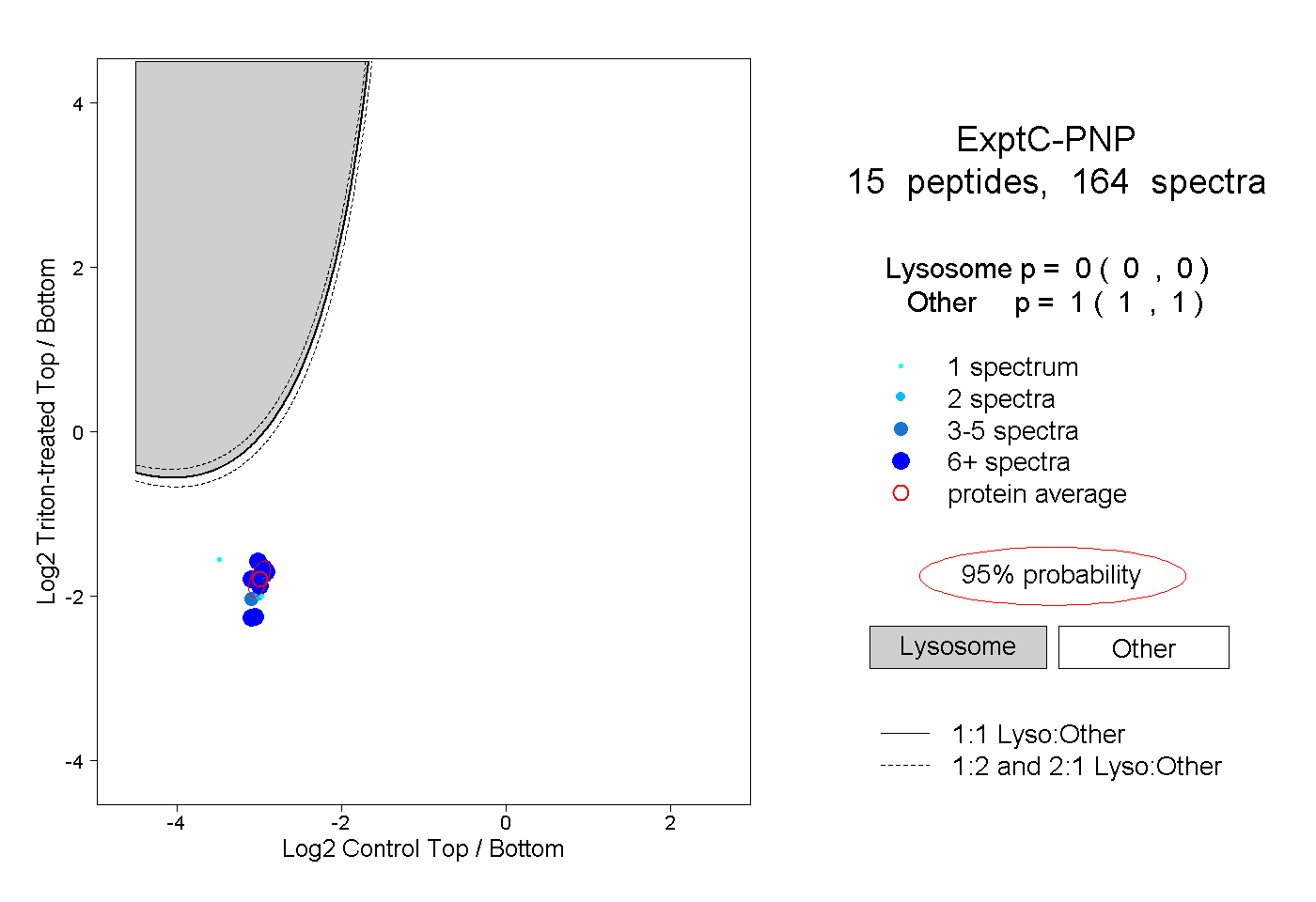 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
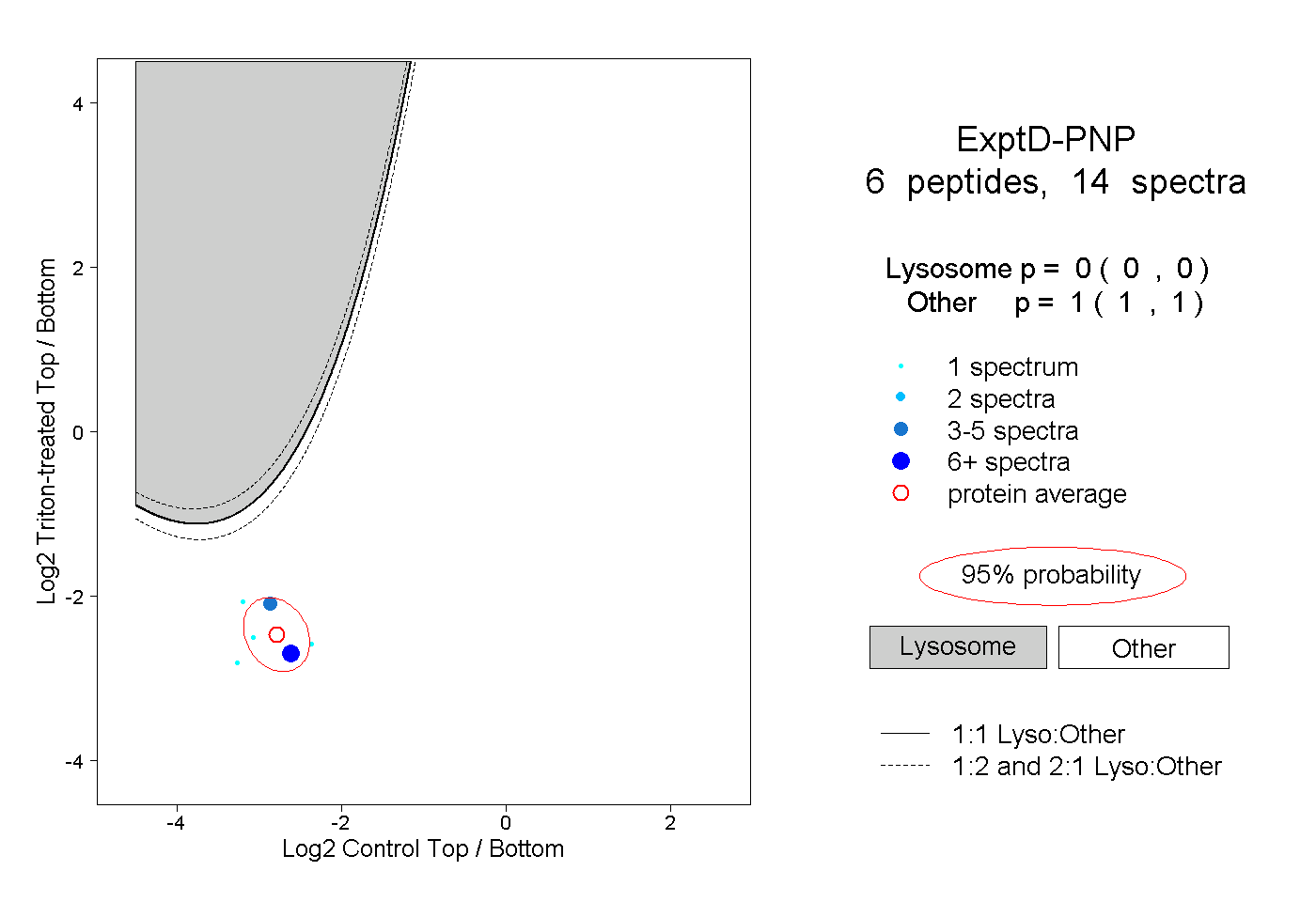 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |