peptides
spectra

0.031 | 0.053
0.000 | 0.000
0.000 | 0.007
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.945 | 0.963
0.000 | 0.000
peptides
spectra
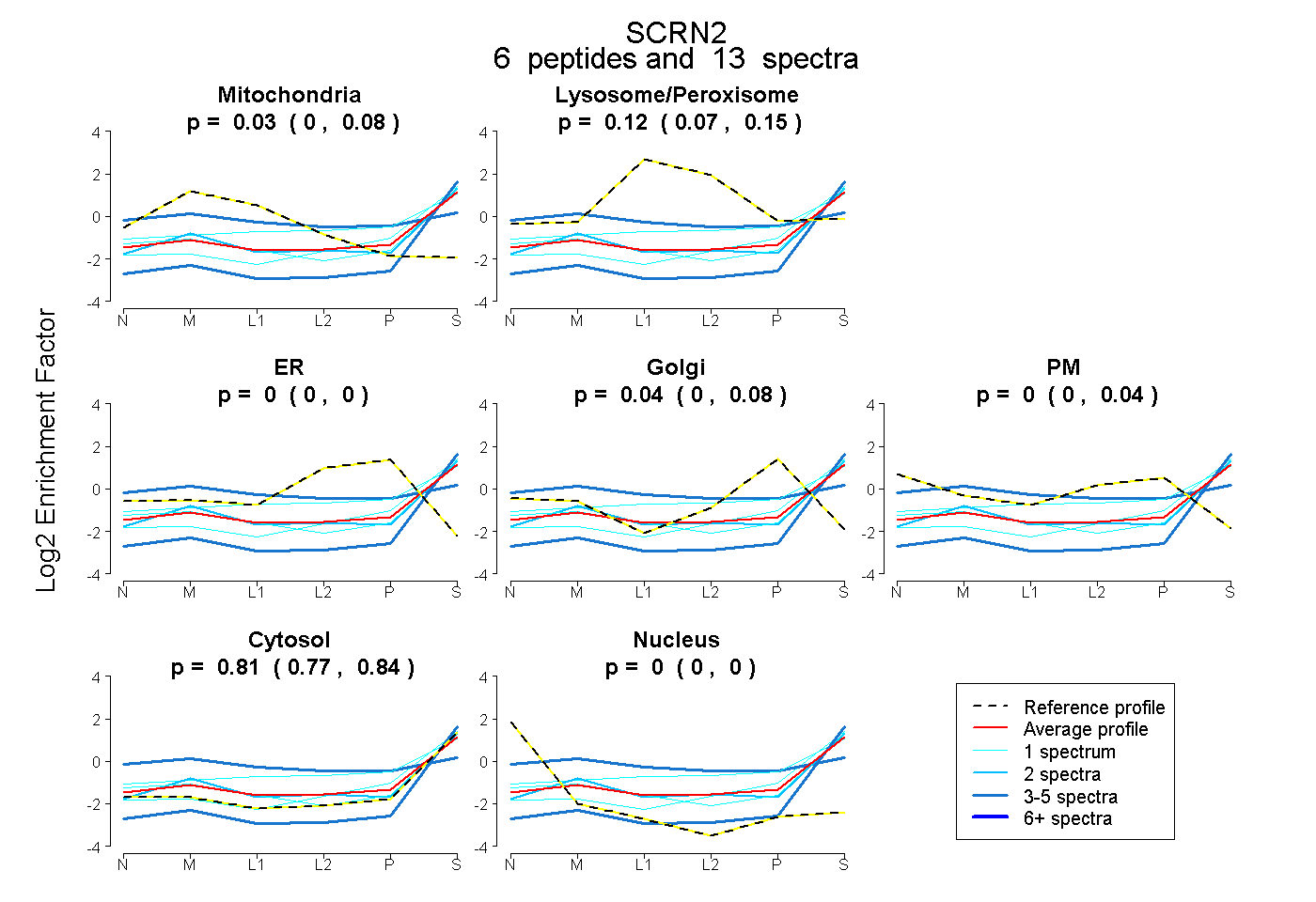
0.000 | 0.077
0.069 | 0.150
0.000 | 0.000
0.000 | 0.080
0.000 | 0.041
0.770 | 0.837
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
44 spectra |
 |
0.045 0.031 | 0.053 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.007 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.955 0.945 | 0.963 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
 |
0.031 0.000 | 0.077 |
0.116 0.069 | 0.150 |
0.000 0.000 | 0.000 |
0.044 0.000 | 0.080 |
0.000 0.000 | 0.041 |
0.808 0.770 | 0.837 |
0.000 0.000 | 0.000 |
| 1 spectrum, LWAAQR | 0.098 | 0.041 | 0.000 | 0.000 | 0.000 | 0.861 | 0.000 | |||
| 1 spectrum, GHQAALGLMDEQEQAQLR | 0.000 | 0.320 | 0.000 | 0.106 | 0.000 | 0.574 | 0.000 | |||
| 4 spectra, SSTAQAAVHVIAGLLDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, LQCTYIEVEQVWK | 0.095 | 0.067 | 0.000 | 0.000 | 0.000 | 0.838 | 0.000 | |||
| 1 spectrum, AGCEMLQR | 0.000 | 0.000 | 0.082 | 0.006 | 0.000 | 0.912 | 0.000 | |||
| 4 spectra, DEVQEVVFIPAGTHTPGSR | 0.143 | 0.237 | 0.000 | 0.000 | 0.295 | 0.325 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
23 spectra |
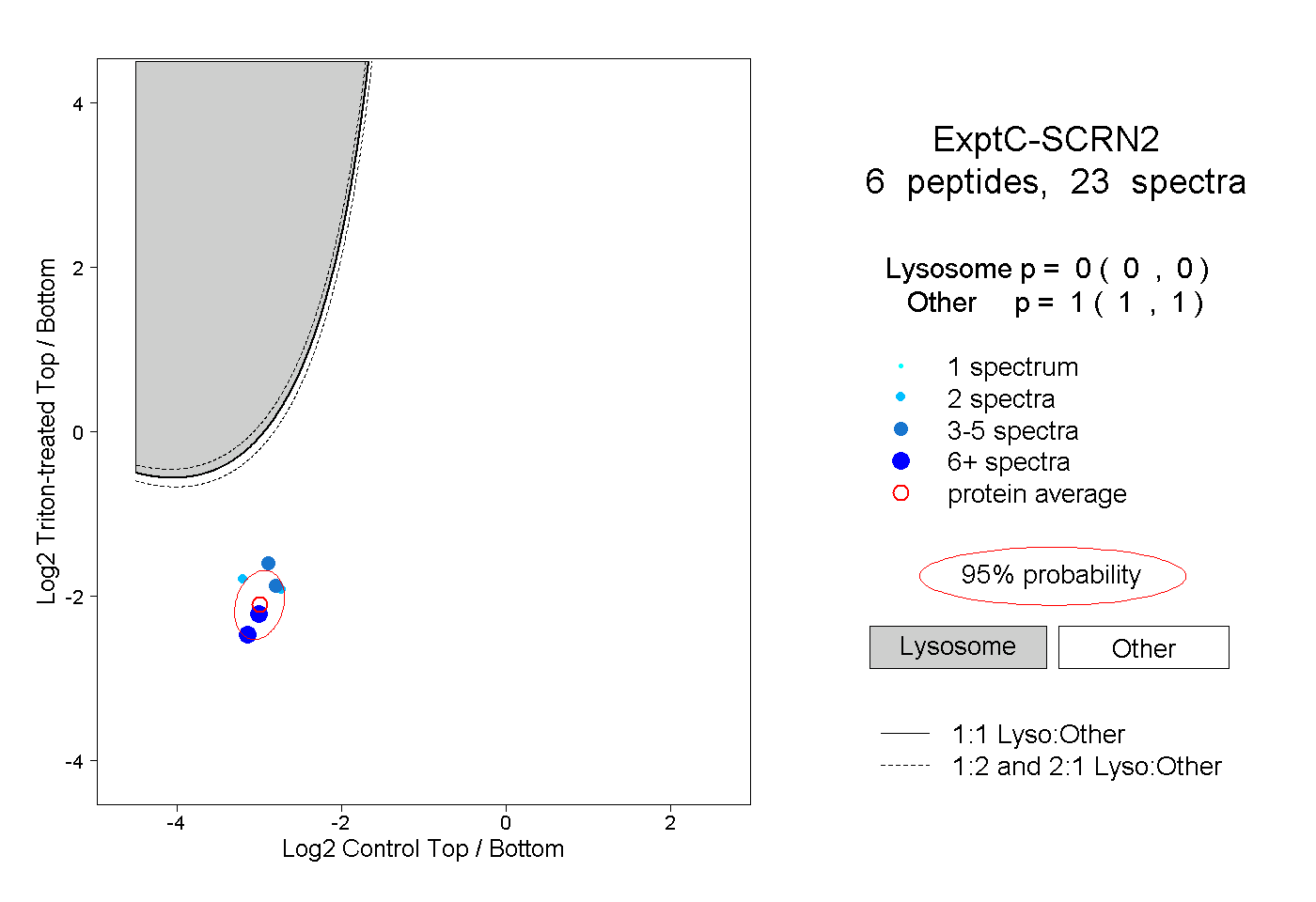 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
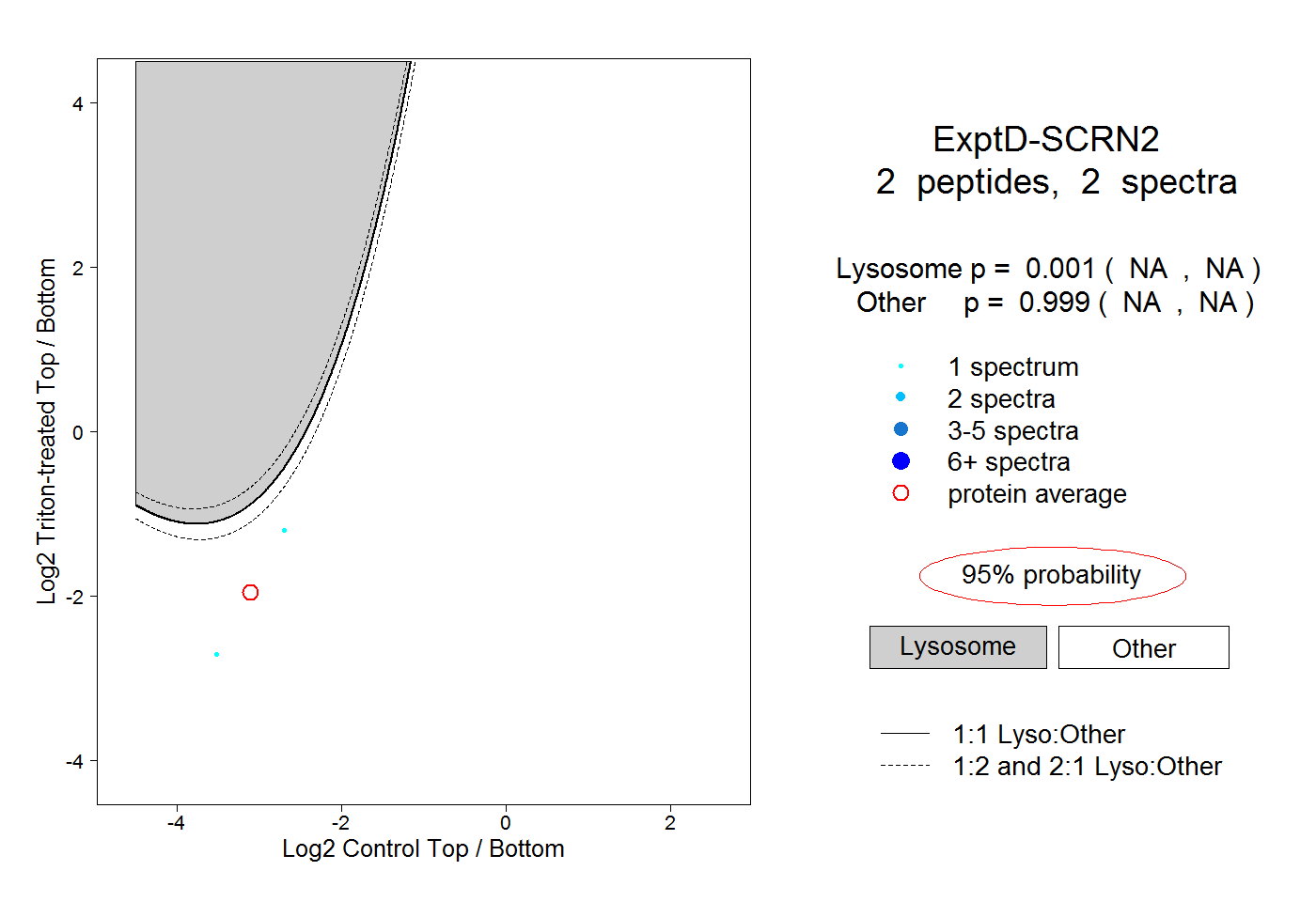 |
0.001 NA | NA |
0.999 NA | NA |