peptides
spectra
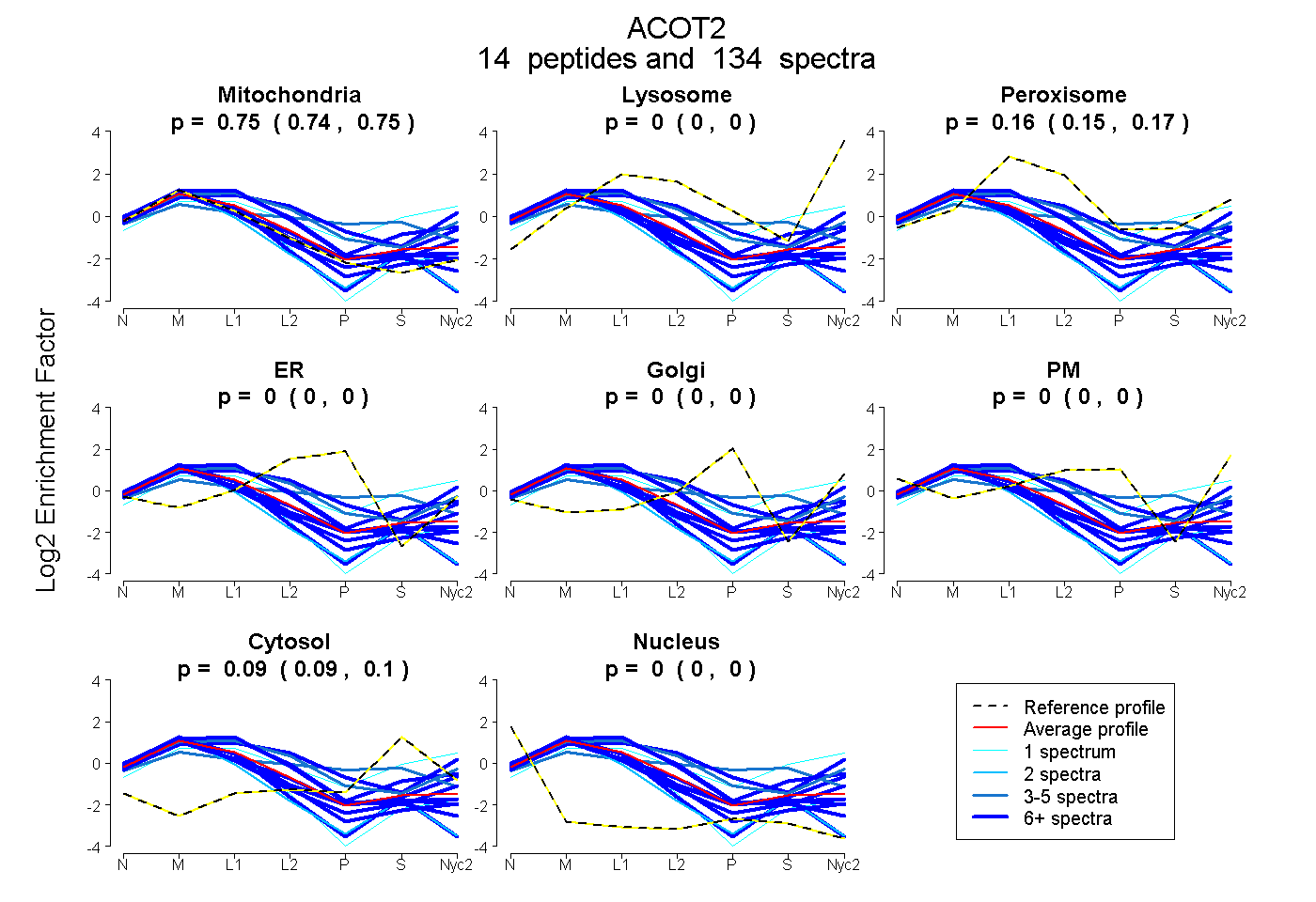
0.738 | 0.751
0.000 | 0.000
0.153 | 0.166
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.091 | 0.098
0.000 | 0.000
peptides
spectra
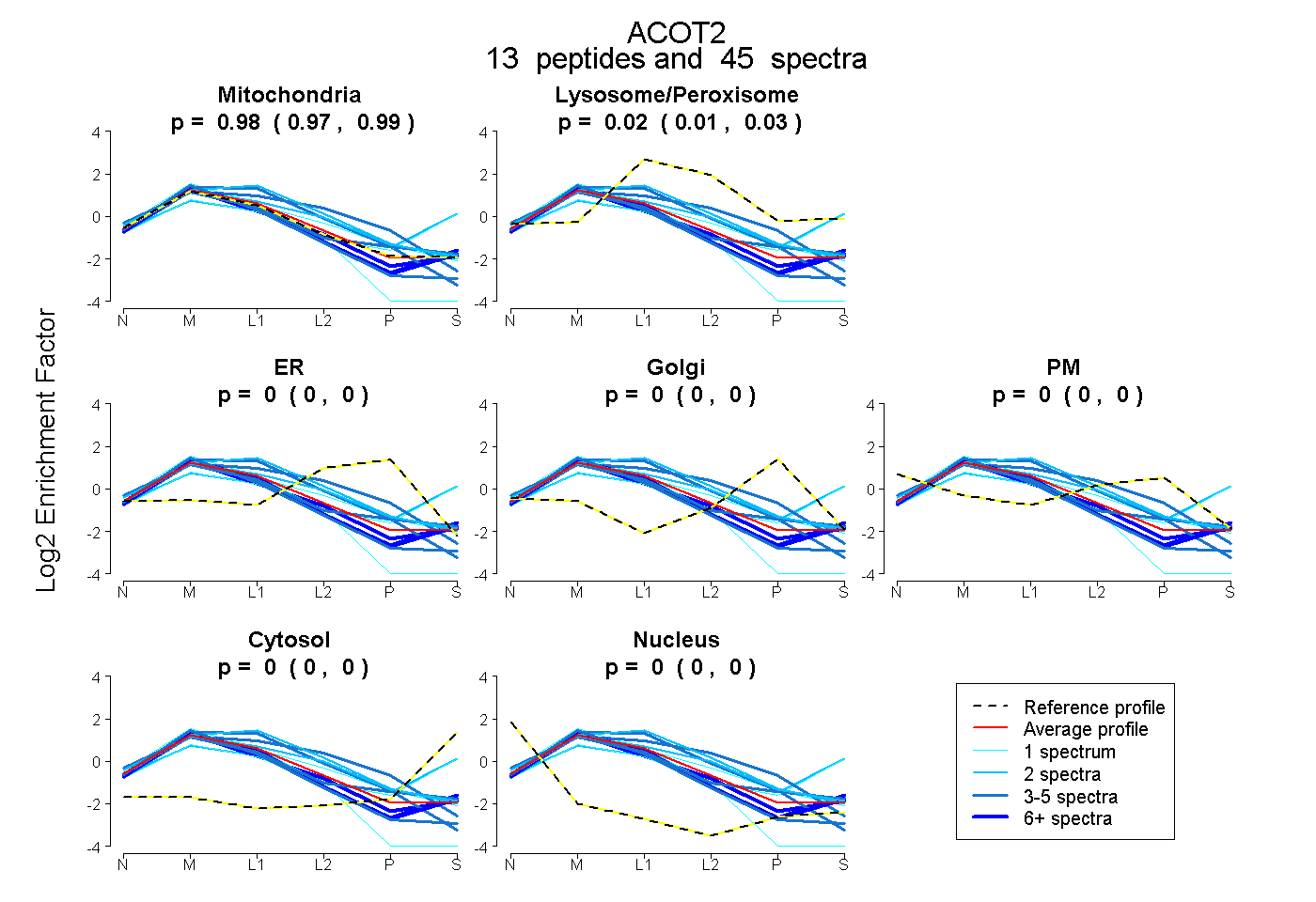
0.968 | 0.989
0.008 | 0.030
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
134 spectra |
 |
0.745 0.738 | 0.751 |
0.000 0.000 | 0.000 |
0.160 0.153 | 0.166 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.095 0.091 | 0.098 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
45 spectra |
 |
0.980 0.968 | 0.989 |
0.020 0.008 | 0.030 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 9 spectra, GGELGLAMASFLK | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | 0.009 | |||
| 1 spectrum, DETIPPVSLLR | 0.839 | 0.046 | 0.095 | 0.000 | 0.021 | 0.000 | 0.000 | |||
| 1 spectrum, GHPEVK | 0.945 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.055 | |||
| 2 spectra, LQAHGK | 0.737 | 0.263 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, SFIPVER | 0.946 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.054 | |||
| 4 spectra, LAQAVHER | 0.898 | 0.001 | 0.000 | 0.049 | 0.051 | 0.000 | 0.000 | |||
| 7 spectra, IEYFEEAVNYLR | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | 0.020 | 0.013 | |||
| 3 spectra, HFMAPGVR | 0.631 | 0.136 | 0.233 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, ADAGGELDLAR | 0.954 | 0.000 | 0.000 | 0.000 | 0.000 | 0.041 | 0.005 | |||
| 2 spectra, SCWDEPLSITVR | 0.772 | 0.139 | 0.089 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DVQKPYVVELEVLDGHEPDGGQR | 0.507 | 0.183 | 0.000 | 0.000 | 0.000 | 0.310 | 0.000 | |||
| 1 spectrum, GPGIGLLGISK | 0.527 | 0.158 | 0.000 | 0.000 | 0.000 | 0.314 | 0.000 | |||
| 3 spectra, GLAPEQPVTLR | 0.868 | 0.056 | 0.075 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
402 spectra |
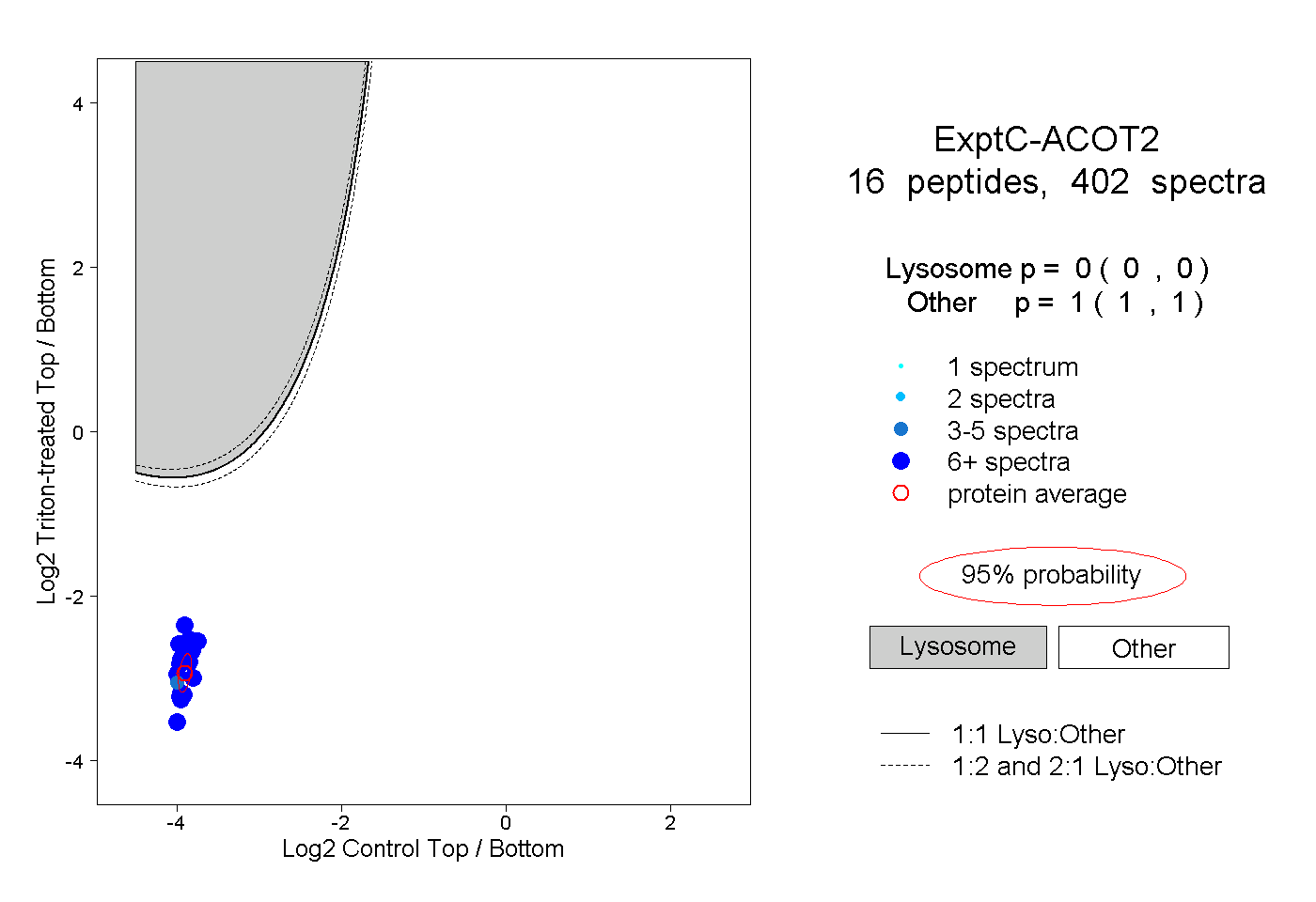 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
46 spectra |
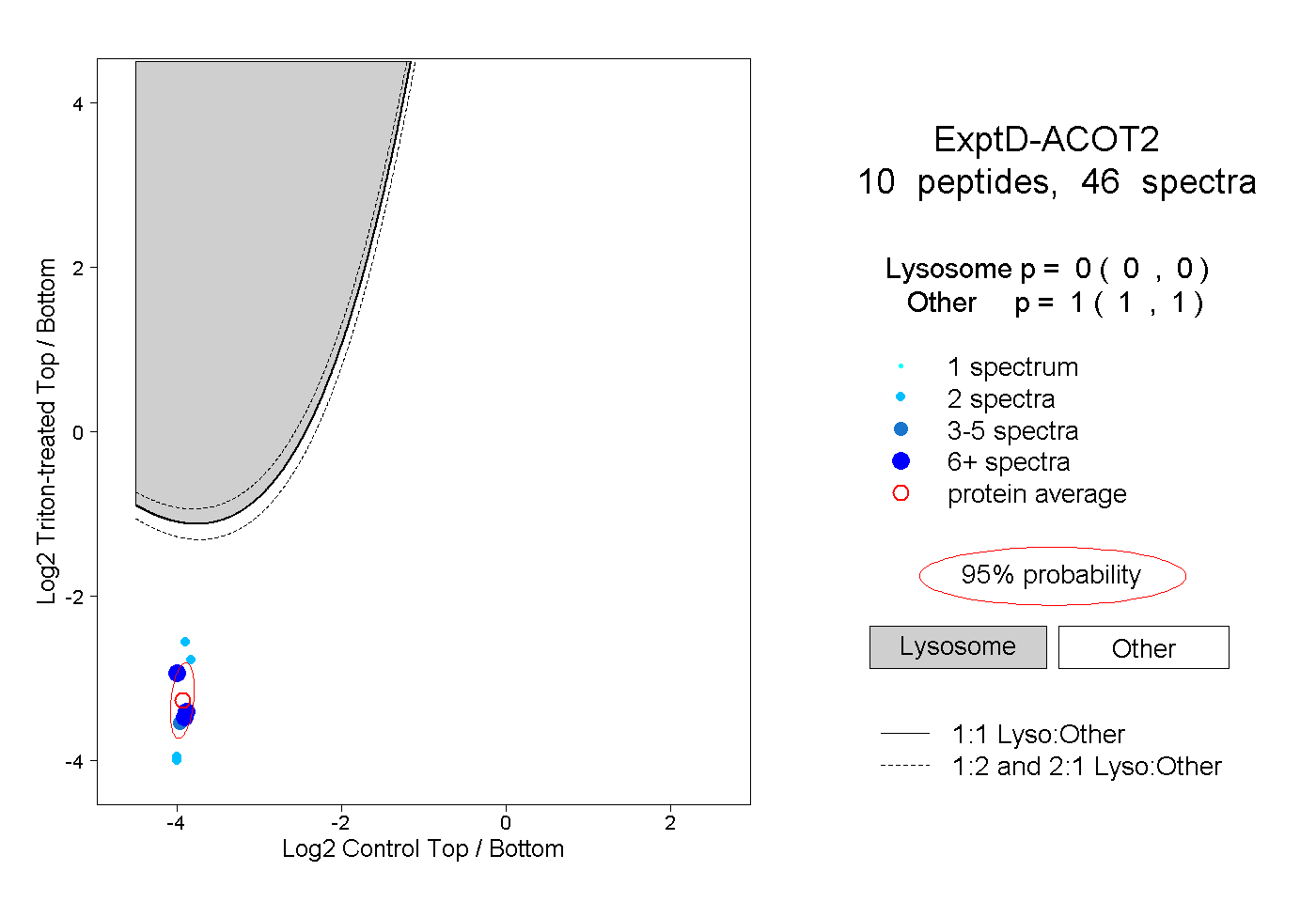 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |