peptides
spectra
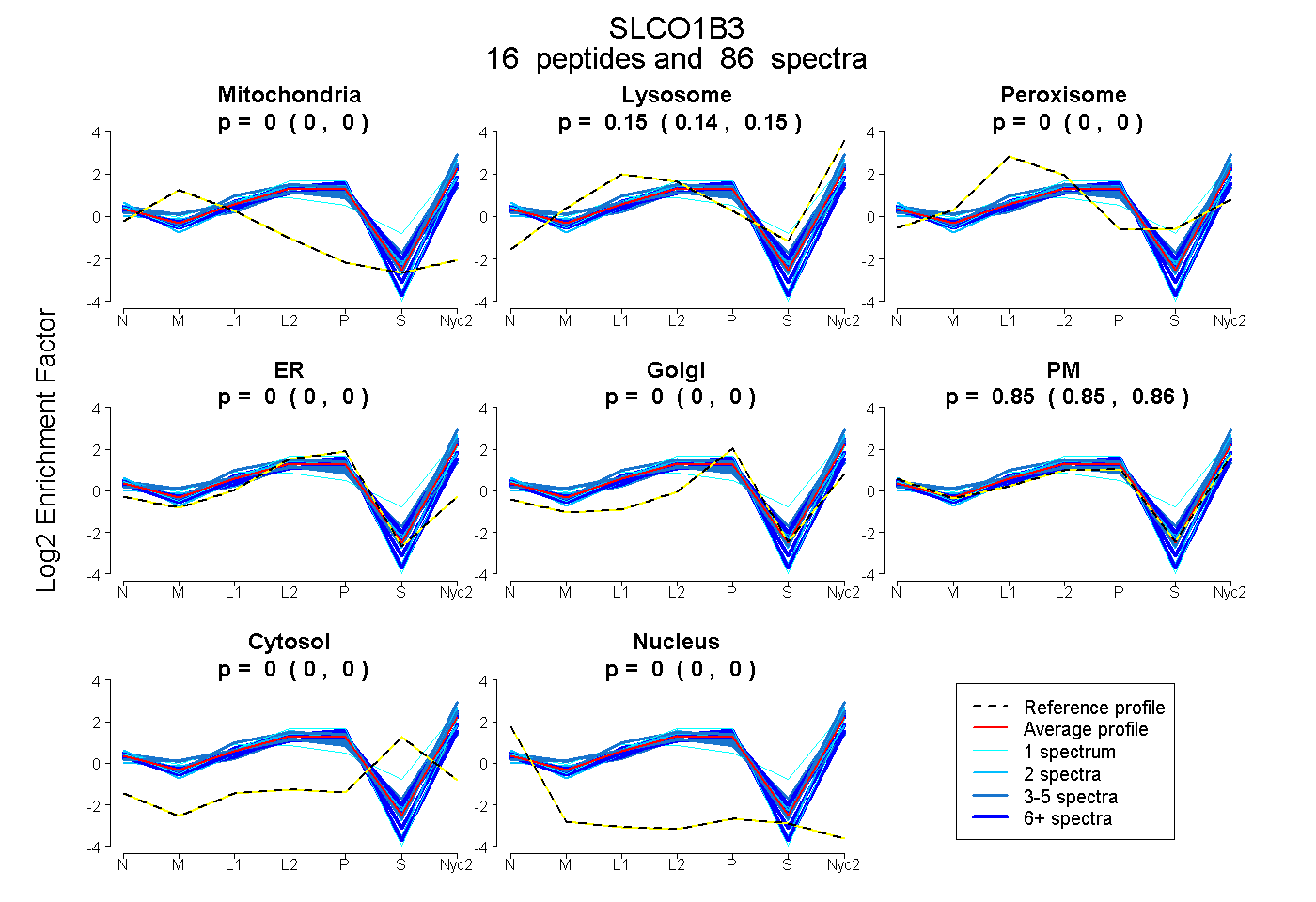
0.000 | 0.000
0.142 | 0.150
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.849 | 0.857
0.000 | 0.000
0.000 | 0.000
peptides
spectra
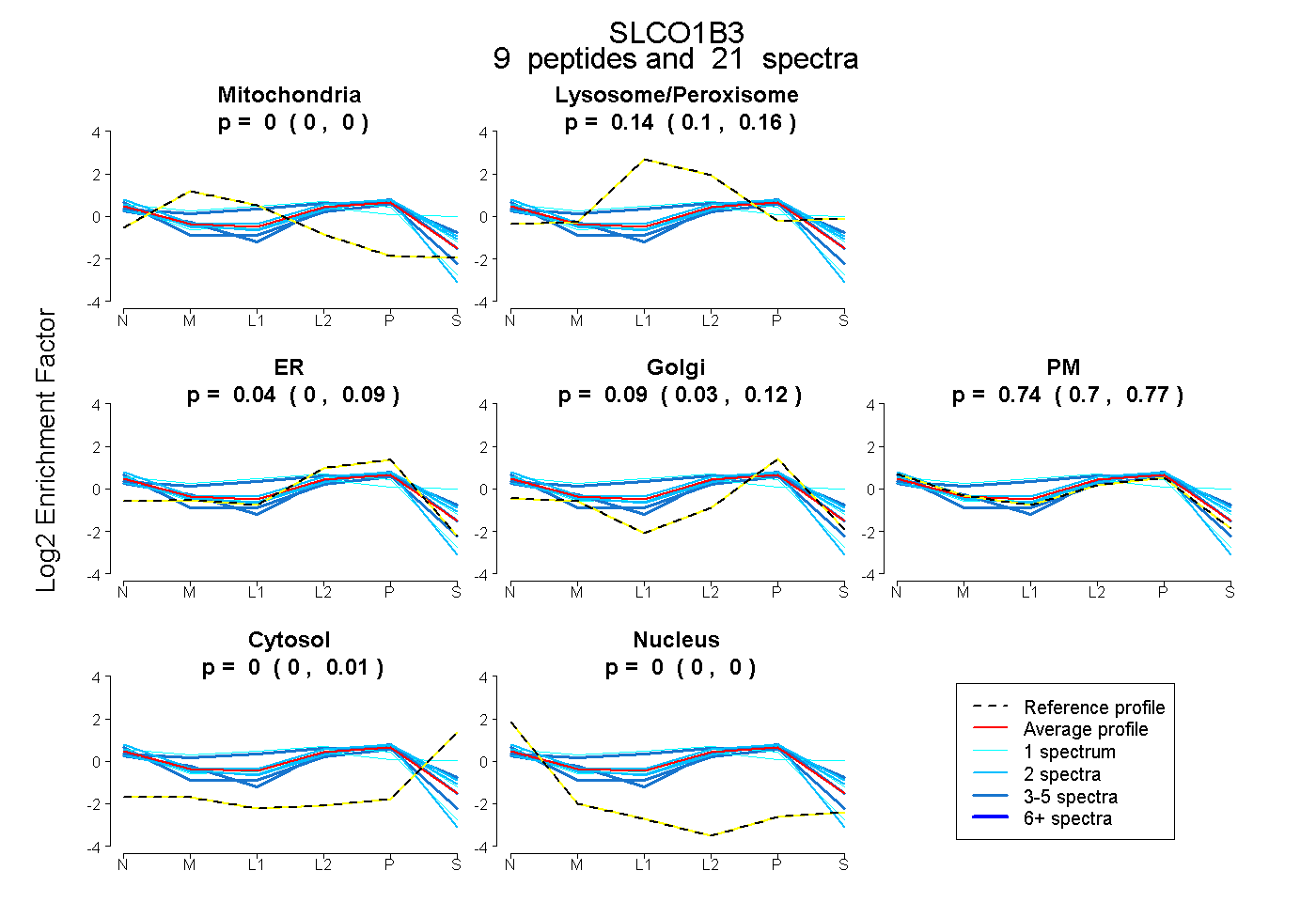
0.000 | 0.000
0.101 | 0.165
0.000 | 0.089
0.031 | 0.125
0.698 | 0.770
0.000 | 0.008
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
86 spectra |
 |
0.000 0.000 | 0.000 |
0.147 0.142 | 0.150 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.853 0.849 | 0.857 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.137 0.101 | 0.165 |
0.039 0.000 | 0.089 |
0.086 0.031 | 0.125 |
0.737 0.698 | 0.770 |
0.000 0.000 | 0.008 |
0.000 0.000 | 0.000 |
| 2 spectra, QFTDEGNPDSVNK | 0.000 | 0.205 | 0.000 | 0.274 | 0.469 | 0.051 | 0.000 | |||
| 2 spectra, ITPNDAR | 0.000 | 0.149 | 0.000 | 0.091 | 0.711 | 0.048 | 0.000 | |||
| 1 spectrum, FIEQQFGR | 0.168 | 0.132 | 0.236 | 0.000 | 0.464 | 0.000 | 0.000 | |||
| 4 spectra, SLAMGFHSLIIR | 0.119 | 0.164 | 0.270 | 0.000 | 0.447 | 0.000 | 0.000 | |||
| 1 spectrum, GIGETPIVPLGISYLDDFAK | 0.000 | 0.149 | 0.025 | 0.132 | 0.676 | 0.018 | 0.000 | |||
| 1 spectrum, LTSVGIAK | 0.000 | 0.255 | 0.000 | 0.000 | 0.519 | 0.225 | 0.000 | |||
| 2 spectra, SVQPELK | 0.000 | 0.000 | 0.259 | 0.000 | 0.741 | 0.000 | 0.000 | |||
| 5 spectra, ALGGVVMK | 0.000 | 0.077 | 0.002 | 0.004 | 0.774 | 0.143 | 0.000 | |||
| 3 spectra, QEEQDPSNMTGFLR | 0.000 | 0.000 | 0.245 | 0.085 | 0.620 | 0.050 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
128 spectra |
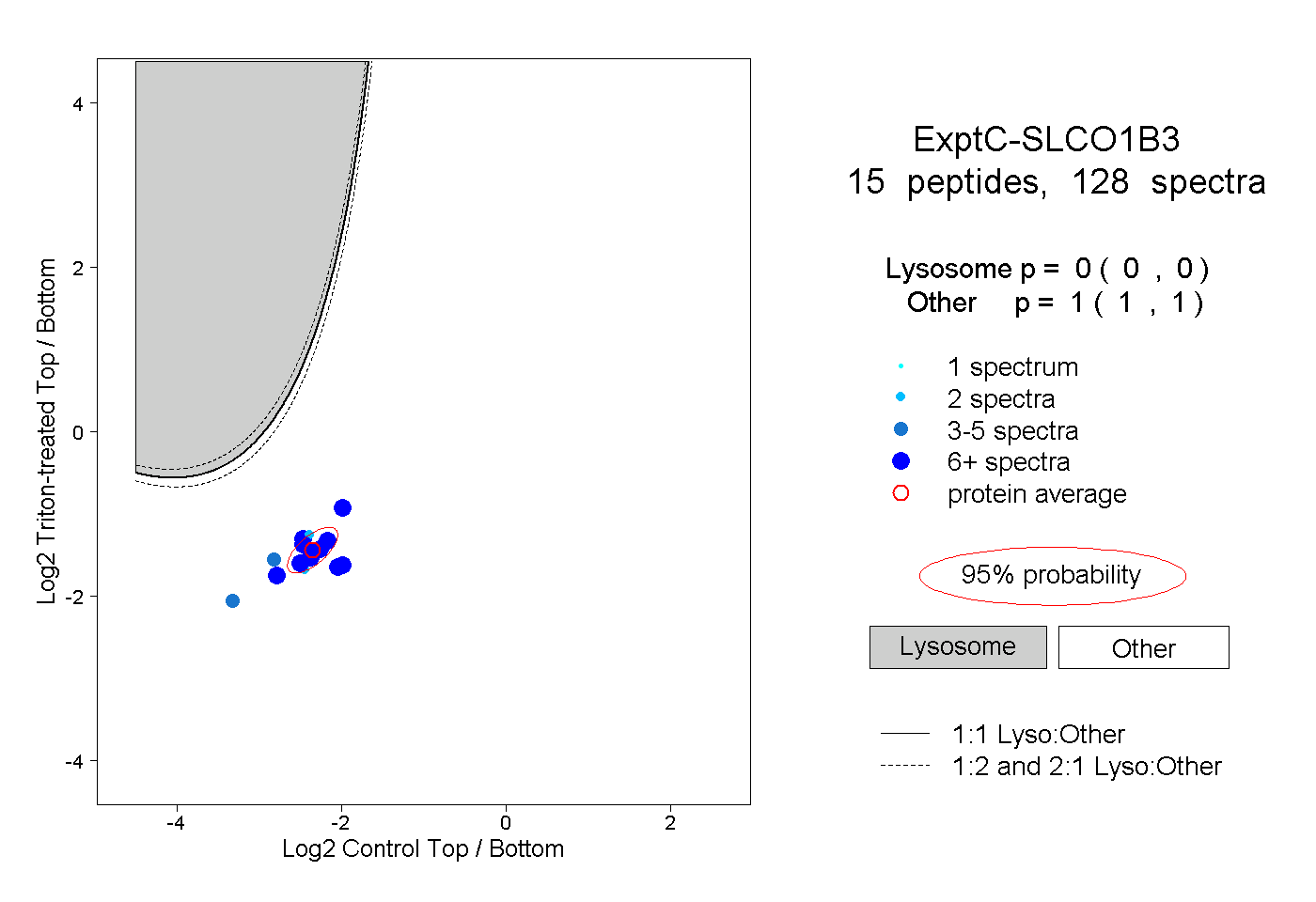 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
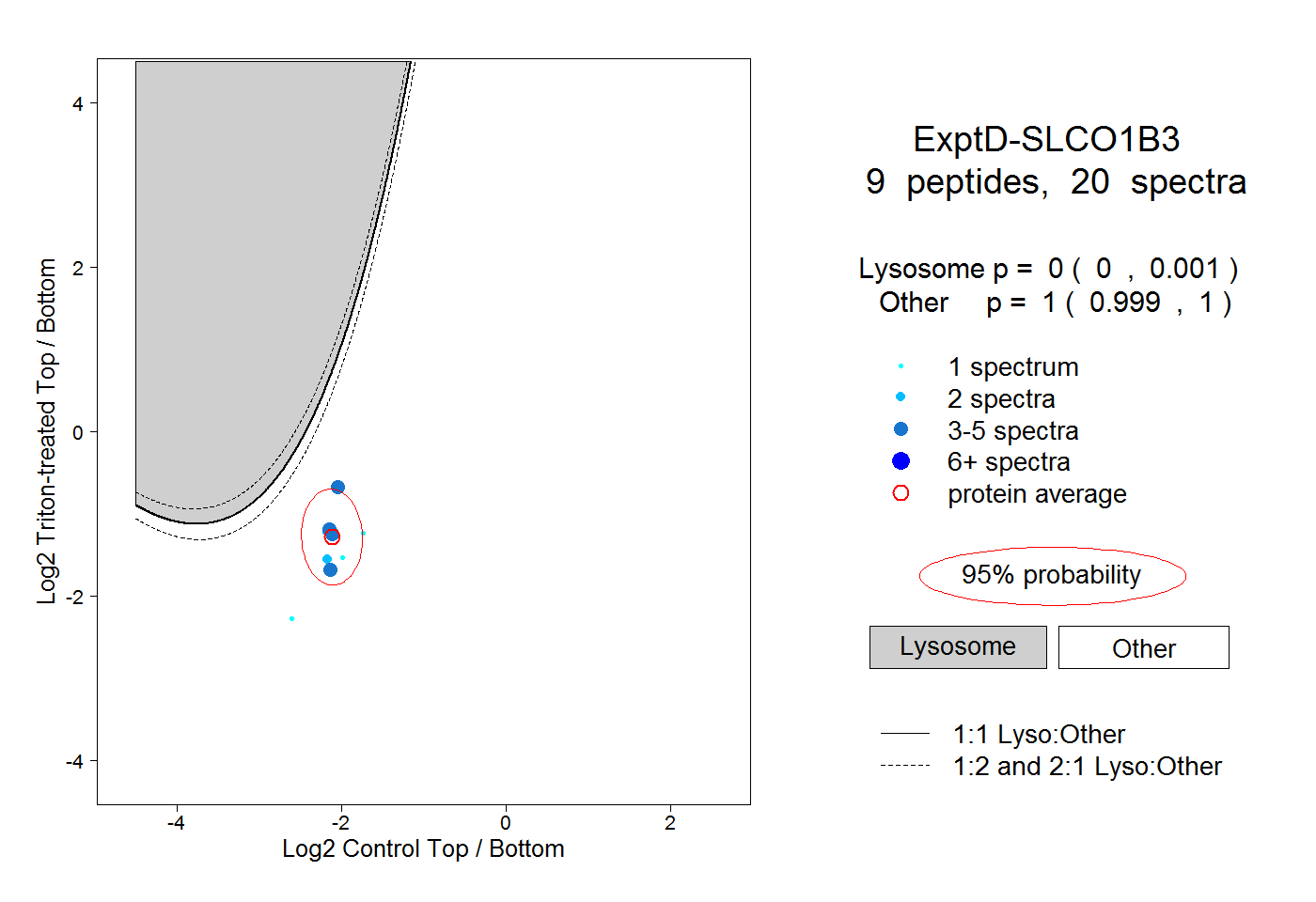 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |