peptides
spectra
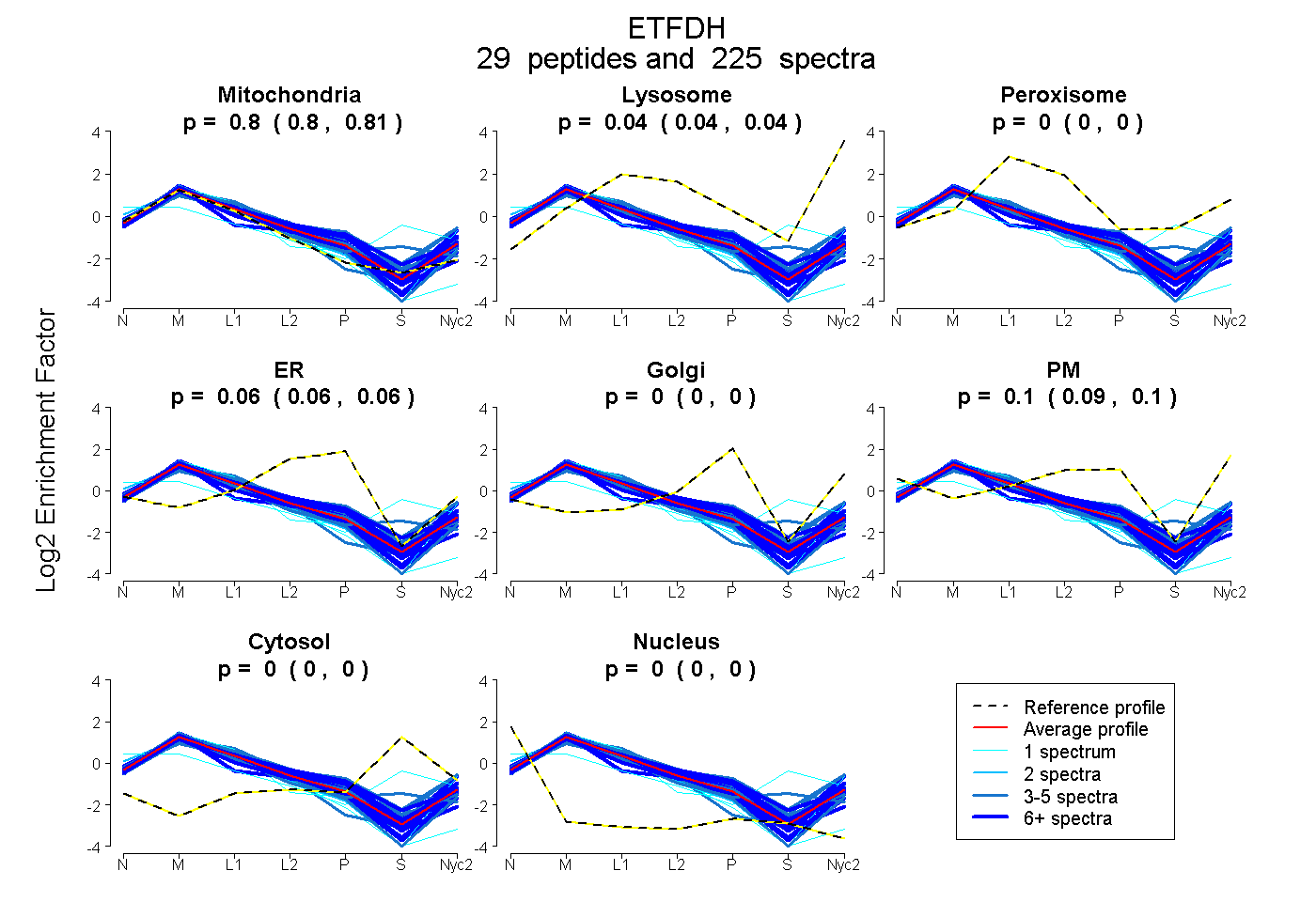
0.803 | 0.805
0.037 | 0.040
0.000 | 0.000
0.056 | 0.062
0.000 | 0.000
0.094 | 0.101
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
225 spectra |
 |
0.804 0.803 | 0.805 |
0.039 0.037 | 0.040 |
0.000 0.000 | 0.000 |
0.059 0.056 | 0.062 |
0.000 0.000 | 0.000 |
0.098 0.094 | 0.101 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 6 spectra, VTIFAEGCHGHLAK | 0.720 | 0.049 | 0.000 | 0.217 | 0.000 | 0.014 | 0.000 | 0.000 | ||
| 5 spectra, HHPSIRPTLEGGK | 0.649 | 0.137 | 0.000 | 0.000 | 0.043 | 0.171 | 0.000 | 0.000 | ||
| 2 spectra, ALNEGGLQSIPK | 0.824 | 0.000 | 0.004 | 0.099 | 0.000 | 0.072 | 0.000 | 0.000 | ||
| 7 spectra, LQINAQNCVHCK | 0.885 | 0.000 | 0.000 | 0.093 | 0.000 | 0.000 | 0.000 | 0.023 | ||
| 11 spectra, GLELHAK | 0.831 | 0.041 | 0.000 | 0.096 | 0.000 | 0.033 | 0.000 | 0.000 | ||
| 14 spectra, DDSIPVNR | 0.818 | 0.035 | 0.000 | 0.014 | 0.055 | 0.079 | 0.000 | 0.000 | ||
| 7 spectra, VDHTVGWPLDR | 0.709 | 0.074 | 0.000 | 0.103 | 0.000 | 0.114 | 0.000 | 0.000 | ||
| 12 spectra, GTHTAMK | 0.894 | 0.000 | 0.000 | 0.106 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, VCLVEK | 0.760 | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | 0.157 | 0.000 | ||
| 2 spectra, QLAAEQEK | 0.917 | 0.000 | 0.000 | 0.019 | 0.000 | 0.065 | 0.000 | 0.000 | ||
| 11 spectra, NLSIYDGPEQR | 0.818 | 0.077 | 0.000 | 0.043 | 0.049 | 0.014 | 0.000 | 0.000 | ||
| 4 spectra, AAQIGAHTLSGACLDPAAFK | 0.768 | 0.144 | 0.000 | 0.062 | 0.004 | 0.021 | 0.000 | 0.000 | ||
| 6 spectra, ASCDAQTYGIGLK | 0.753 | 0.083 | 0.000 | 0.000 | 0.000 | 0.163 | 0.000 | 0.000 | ||
| 1 spectrum, IPVPILPGLPMNNHGNYIVR | 0.830 | 0.039 | 0.000 | 0.000 | 0.000 | 0.131 | 0.000 | 0.000 | ||
| 4 spectra, QSWVWK | 0.793 | 0.087 | 0.000 | 0.002 | 0.076 | 0.042 | 0.000 | 0.000 | ||
| 5 spectra, GIATNDVGIQK | 0.615 | 0.115 | 0.022 | 0.000 | 0.135 | 0.113 | 0.000 | 0.000 | ||
| 15 spectra, ELWVIDEK | 0.819 | 0.024 | 0.000 | 0.067 | 0.000 | 0.090 | 0.000 | 0.000 | ||
| 19 spectra, WEGVNMER | 0.738 | 0.046 | 0.000 | 0.010 | 0.206 | 0.000 | 0.000 | 0.000 | ||
| 29 spectra, IAYGAR | 0.780 | 0.063 | 0.000 | 0.004 | 0.000 | 0.153 | 0.000 | 0.000 | ||
| 1 spectrum, LTFPGGLLIGCSPGFMNVPK | 0.535 | 0.000 | 0.103 | 0.000 | 0.000 | 0.000 | 0.327 | 0.036 | ||
| 11 spectra, ELFPDWK | 0.801 | 0.010 | 0.000 | 0.047 | 0.000 | 0.142 | 0.000 | 0.000 | ||
| 1 spectrum, FAEEADVVIVGAGPAGLSAAIR | 0.932 | 0.000 | 0.000 | 0.000 | 0.000 | 0.068 | 0.000 | 0.000 | ||
| 6 spectra, SGSLAAEAIFK | 0.828 | 0.034 | 0.000 | 0.000 | 0.000 | 0.138 | 0.000 | 0.000 | ||
| 4 spectra, QLTSENLQSK | 0.898 | 0.000 | 0.000 | 0.056 | 0.000 | 0.046 | 0.000 | 0.000 | ||
| 1 spectrum, FCPAGVYEFVPLEQGDGFR | 0.998 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 | ||
| 13 spectra, GMEPWTLK | 0.716 | 0.111 | 0.000 | 0.000 | 0.000 | 0.173 | 0.000 | 0.000 | ||
| 17 spectra, GAPLNTPVTEDR | 0.863 | 0.000 | 0.000 | 0.038 | 0.000 | 0.099 | 0.000 | 0.000 | ||
| 3 spectra, FAILTEK | 0.934 | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, TAGLHVTEYEDNLK | 0.724 | 0.005 | 0.097 | 0.174 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
97 spectra |
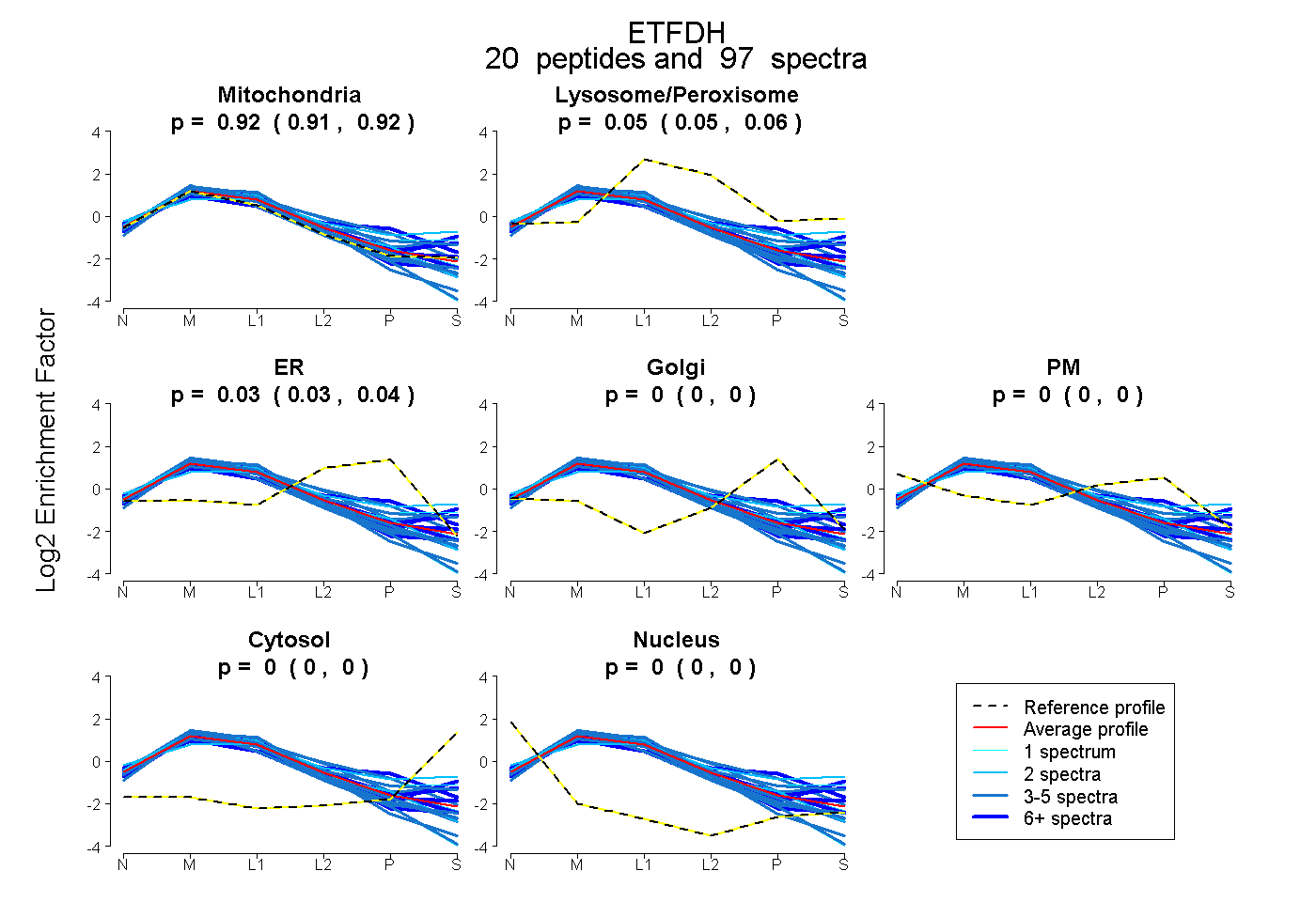 |
0.915 0.911 | 0.919 |
0.053 0.048 | 0.057 |
0.032 0.026 | 0.036 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
976 spectra |
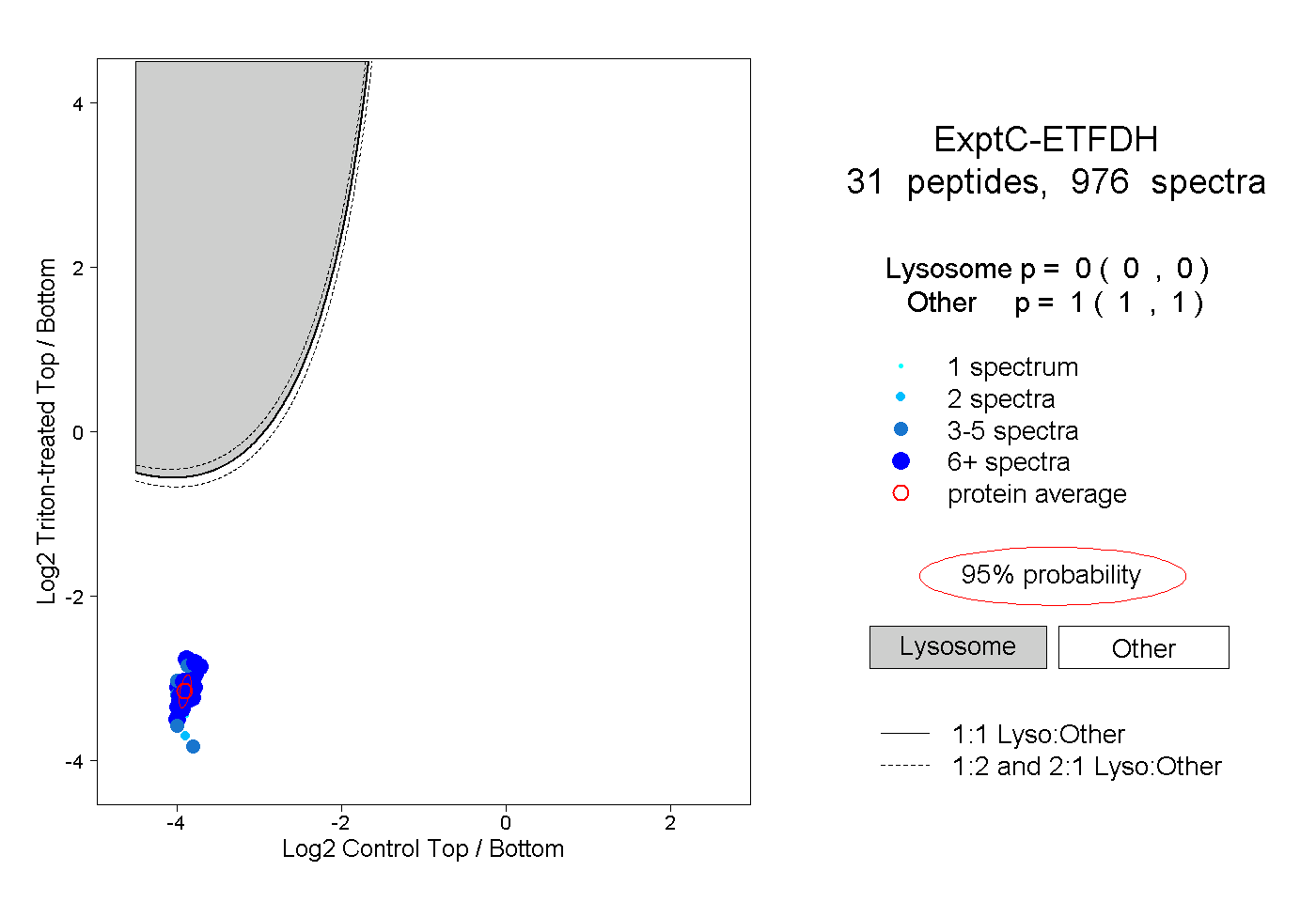 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
84 spectra |
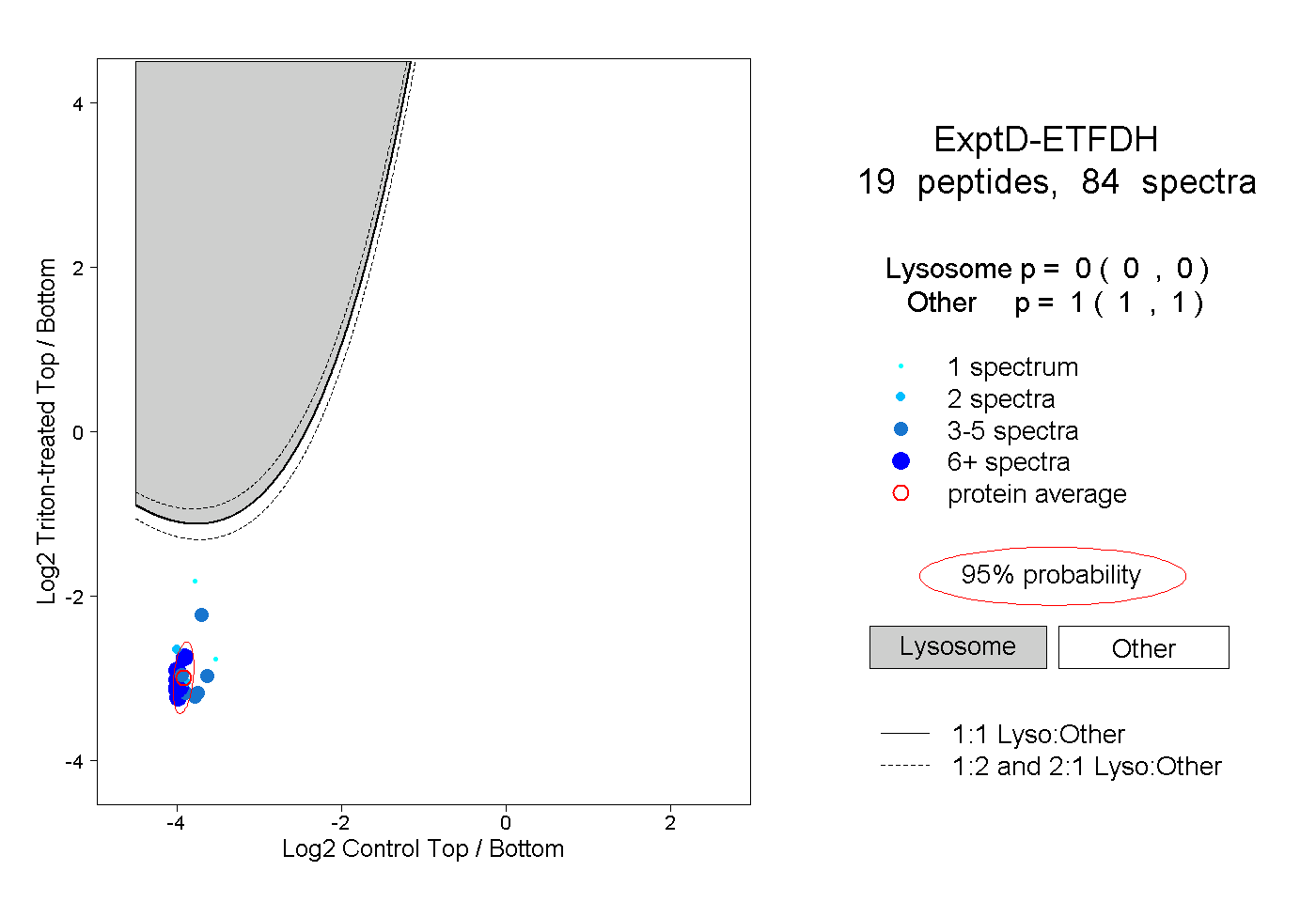 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |