peptides
spectra
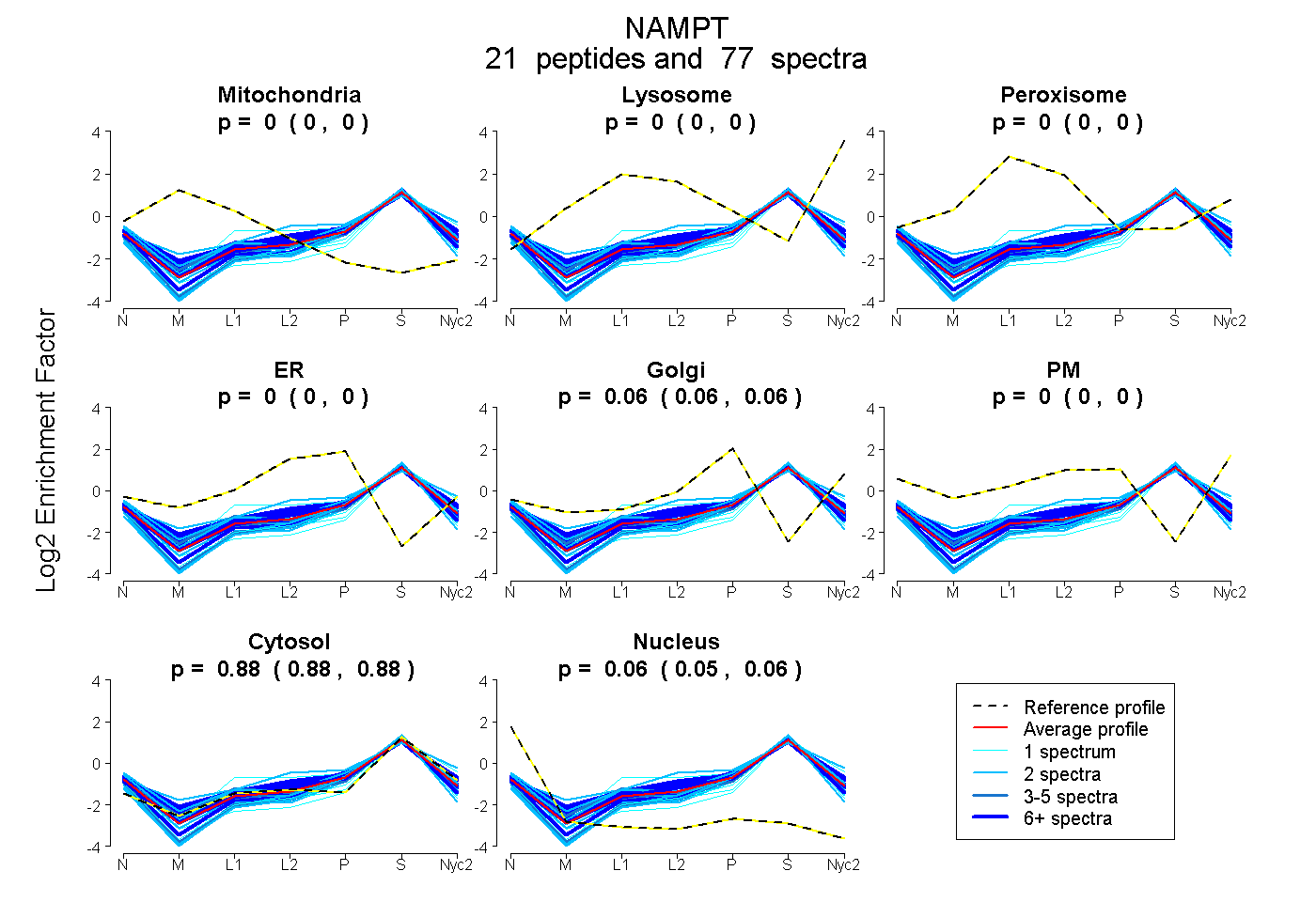
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.058 | 0.062
0.000 | 0.000
0.882 | 0.885
0.055 | 0.058
peptides
spectra
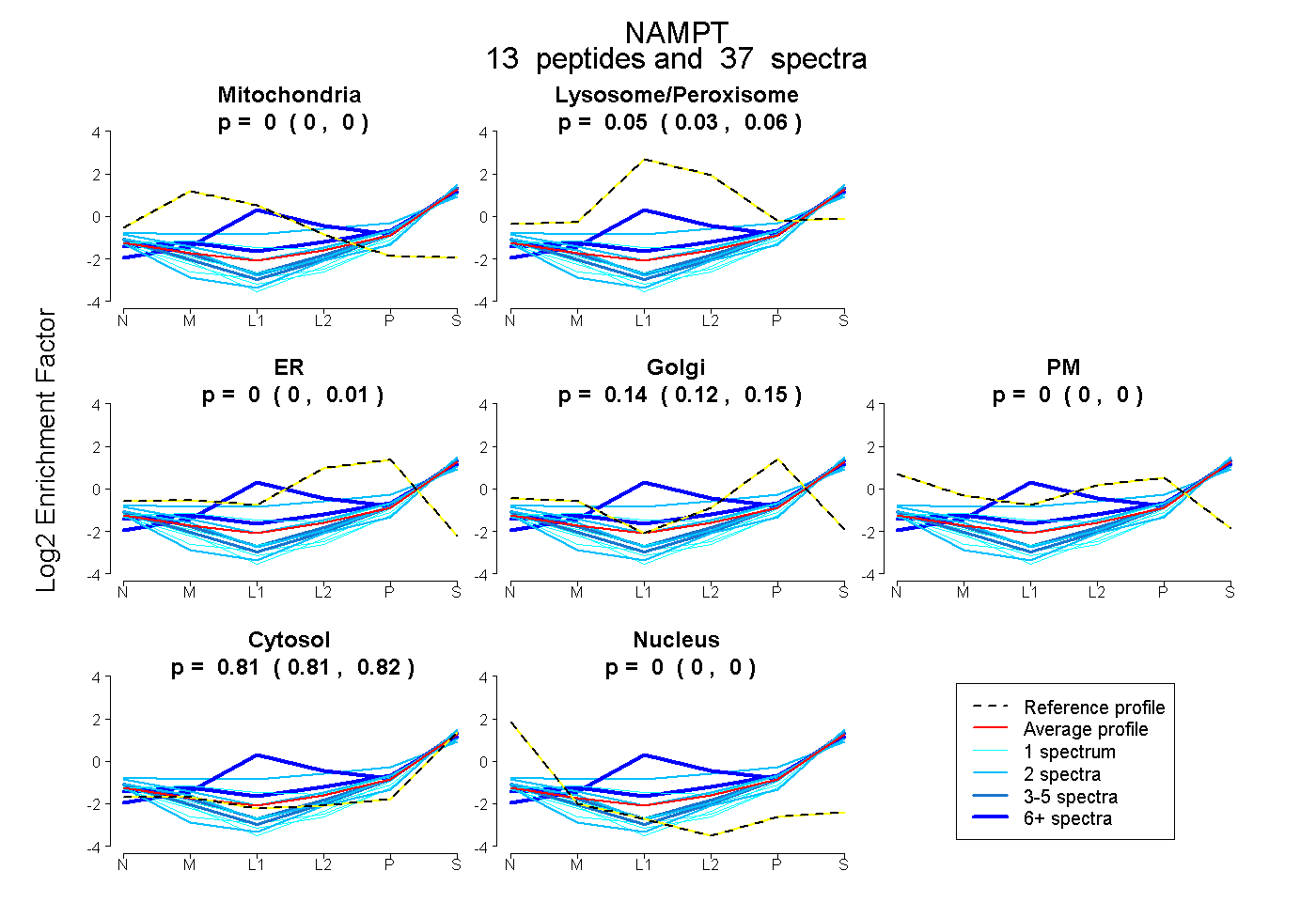
0.000 | 0.000
0.025 | 0.063
0.000 | 0.010
0.121 | 0.148
0.000 | 0.000
0.806 | 0.823
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.060 0.058 | 0.062 |
0.000 0.000 | 0.000 |
0.883 0.882 | 0.885 |
0.056 0.055 | 0.058 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
37 spectra |
 |
0.000 0.000 | 0.000 |
0.047 0.025 | 0.063 |
0.000 0.000 | 0.010 |
0.138 0.121 | 0.148 |
0.000 0.000 | 0.000 |
0.815 0.806 | 0.823 |
0.000 0.000 | 0.000 |
| 3 spectra, AVPEGSVIPR | 0.000 | 0.000 | 0.000 | 0.160 | 0.000 | 0.840 | 0.000 | |||
| 2 spectra, VYSYFECR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.944 | 0.056 | |||
| 8 spectra, EHFQDDVFNER | 0.000 | 0.138 | 0.000 | 0.143 | 0.000 | 0.719 | 0.000 | |||
| 1 spectrum, VLDILGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.932 | 0.068 | |||
| 2 spectra, STEAPLIIRPDSGNPLDTVLK | 0.000 | 0.000 | 0.000 | 0.172 | 0.000 | 0.828 | 0.000 | |||
| 2 spectra, GWNYILEK | 0.000 | 0.302 | 0.000 | 0.184 | 0.000 | 0.514 | 0.000 | |||
| 1 spectrum, IWGEDLR | 0.000 | 0.000 | 0.000 | 0.091 | 0.000 | 0.903 | 0.006 | |||
| 10 spectra, LHDFGYR | 0.000 | 0.420 | 0.000 | 0.000 | 0.000 | 0.580 | 0.000 | |||
| 1 spectrum, SYSFDEVR | 0.000 | 0.139 | 0.000 | 0.123 | 0.000 | 0.738 | 0.000 | |||
| 1 spectrum, HLIVSR | 0.000 | 0.000 | 0.000 | 0.065 | 0.000 | 0.885 | 0.050 | |||
| 2 spectra, YLLETSGNLDGLEYK | 0.000 | 0.009 | 0.000 | 0.105 | 0.153 | 0.734 | 0.000 | |||
| 1 spectrum, GTDTVAGIALIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.928 | 0.072 | |||
| 3 spectra, LLPPYLR | 0.000 | 0.000 | 0.000 | 0.129 | 0.000 | 0.864 | 0.007 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
142 spectra |
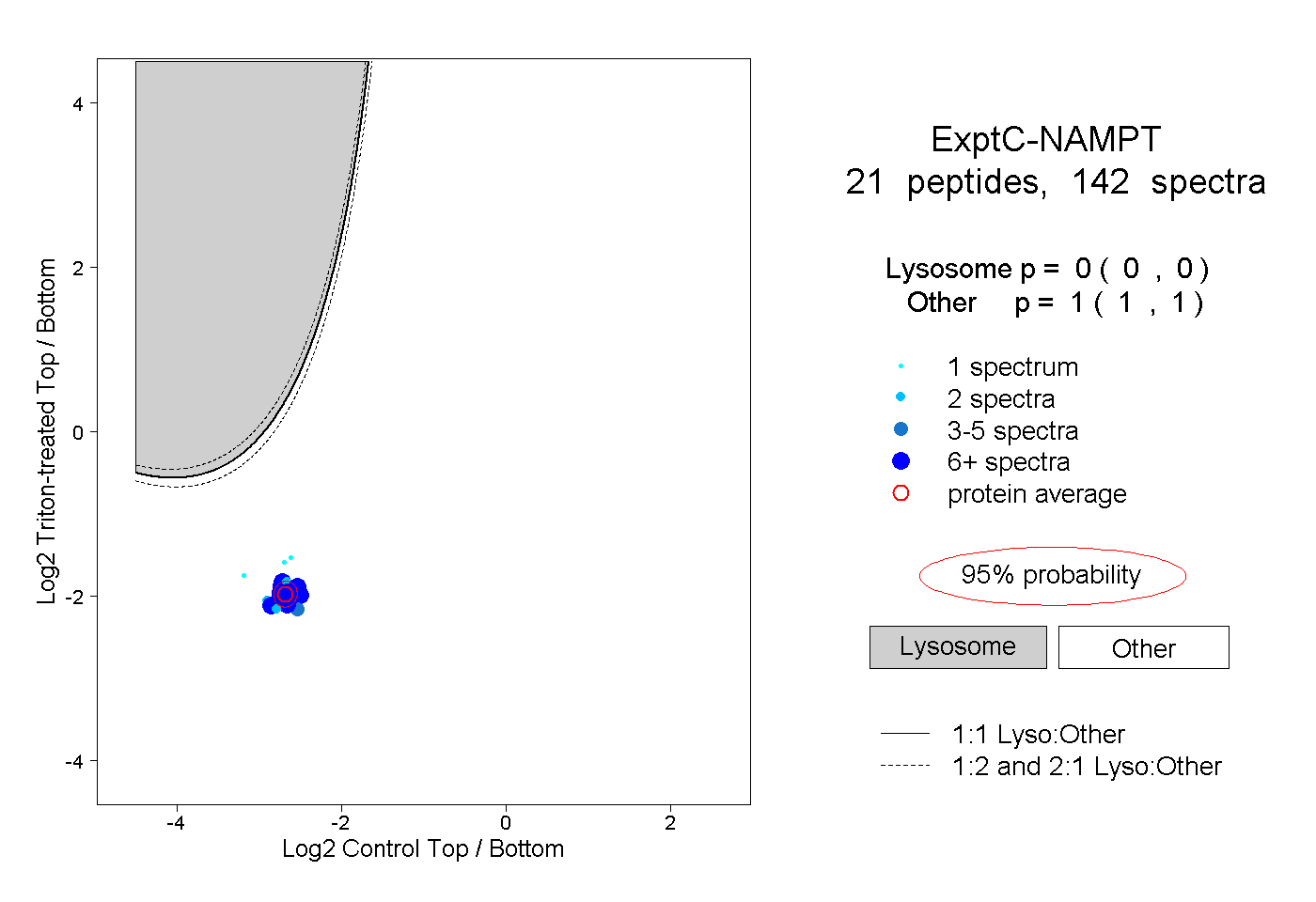 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
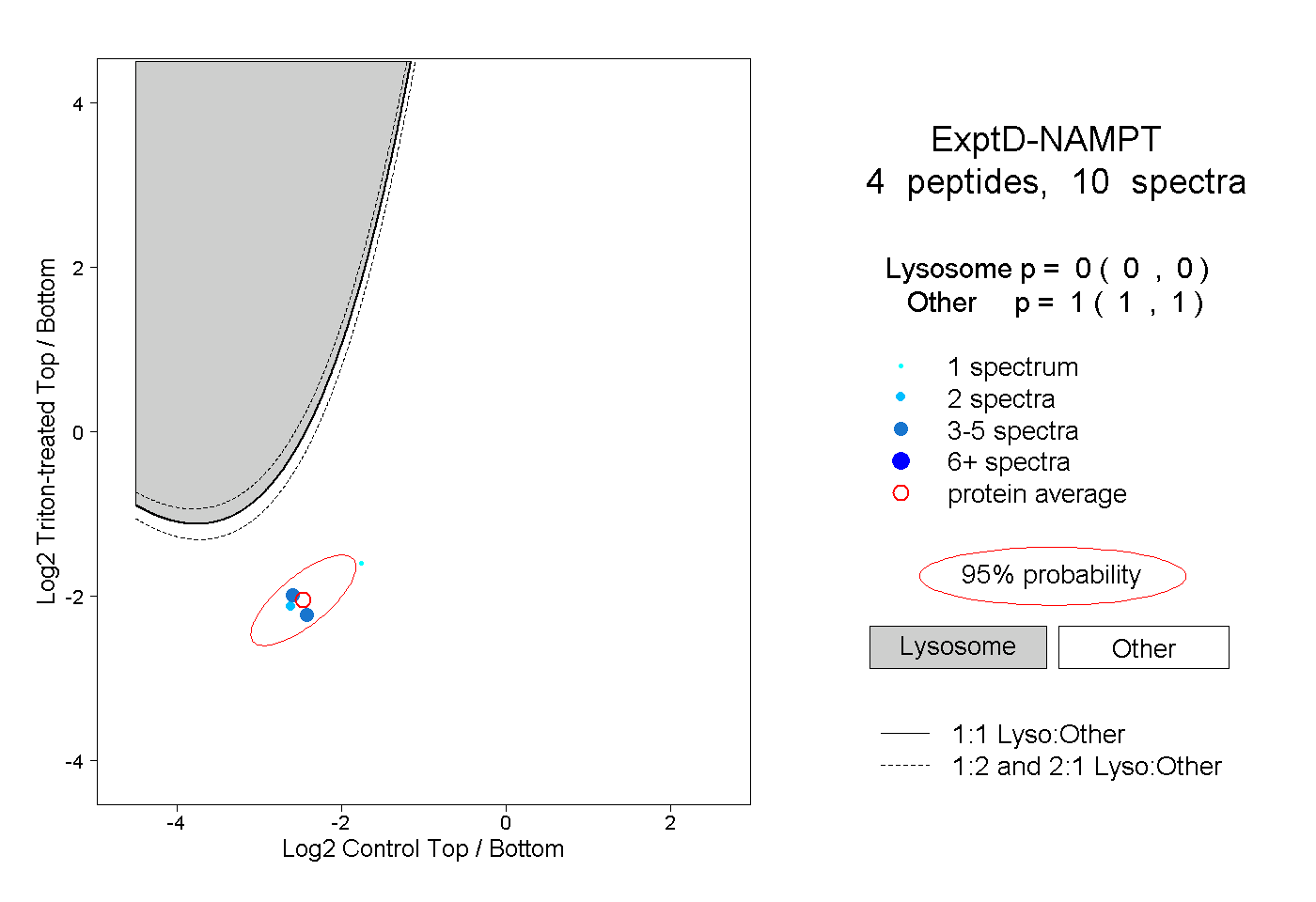 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |