peptides
spectra
0.004 | 0.018
0.000 | 0.000
0.000 | 0.000
0.908 | 0.919
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.069 | 0.078
peptides
spectra
0.000 | 0.000
0.000 | 0.020
0.800 | 0.866
0.089 | 0.141
0.007 | 0.054
0.000 | 0.017
0.000 | 0.001
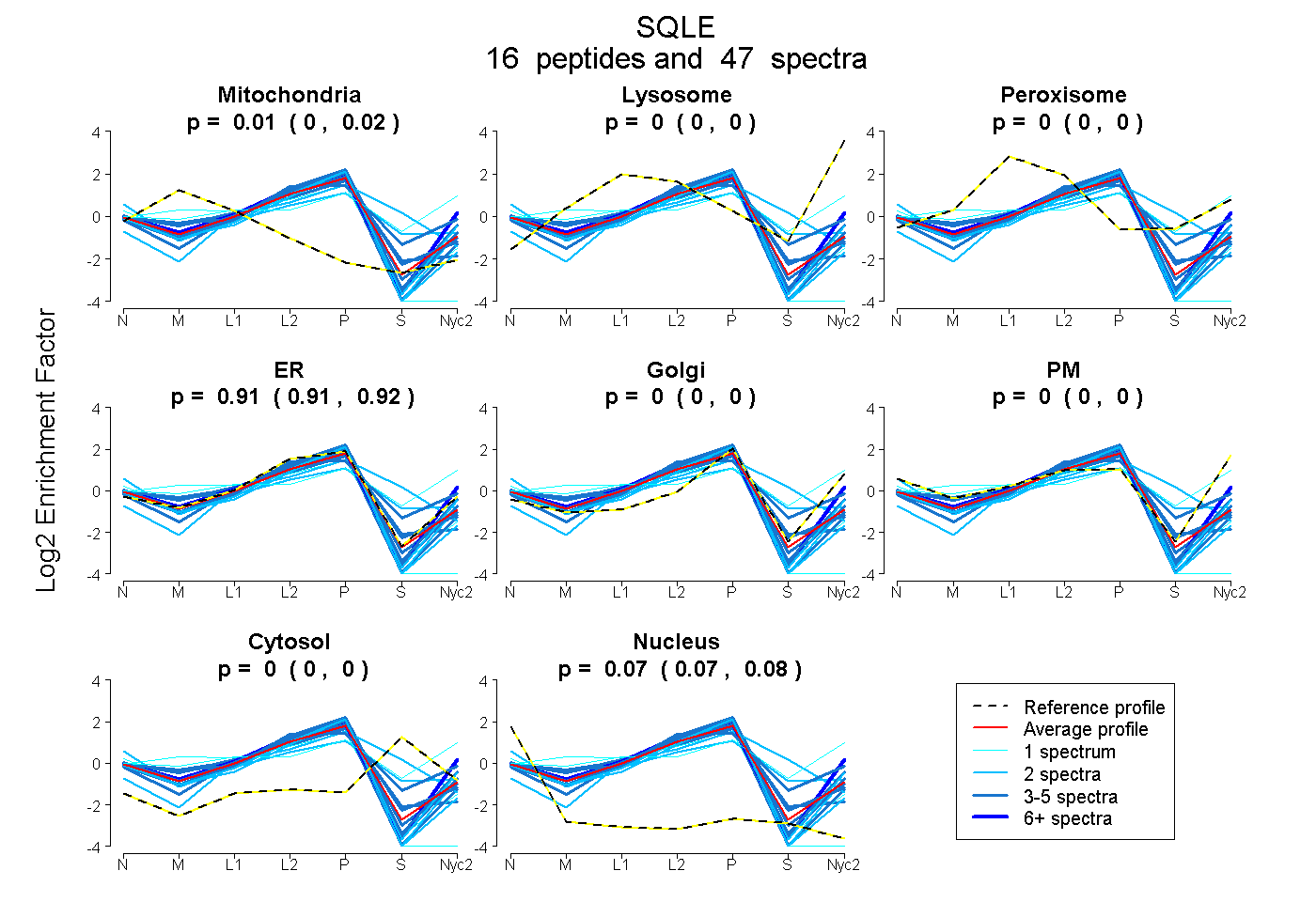
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
47 spectra |
 |
0.012 0.004 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.914 0.908 | 0.919 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.074 0.069 | 0.078 |
||
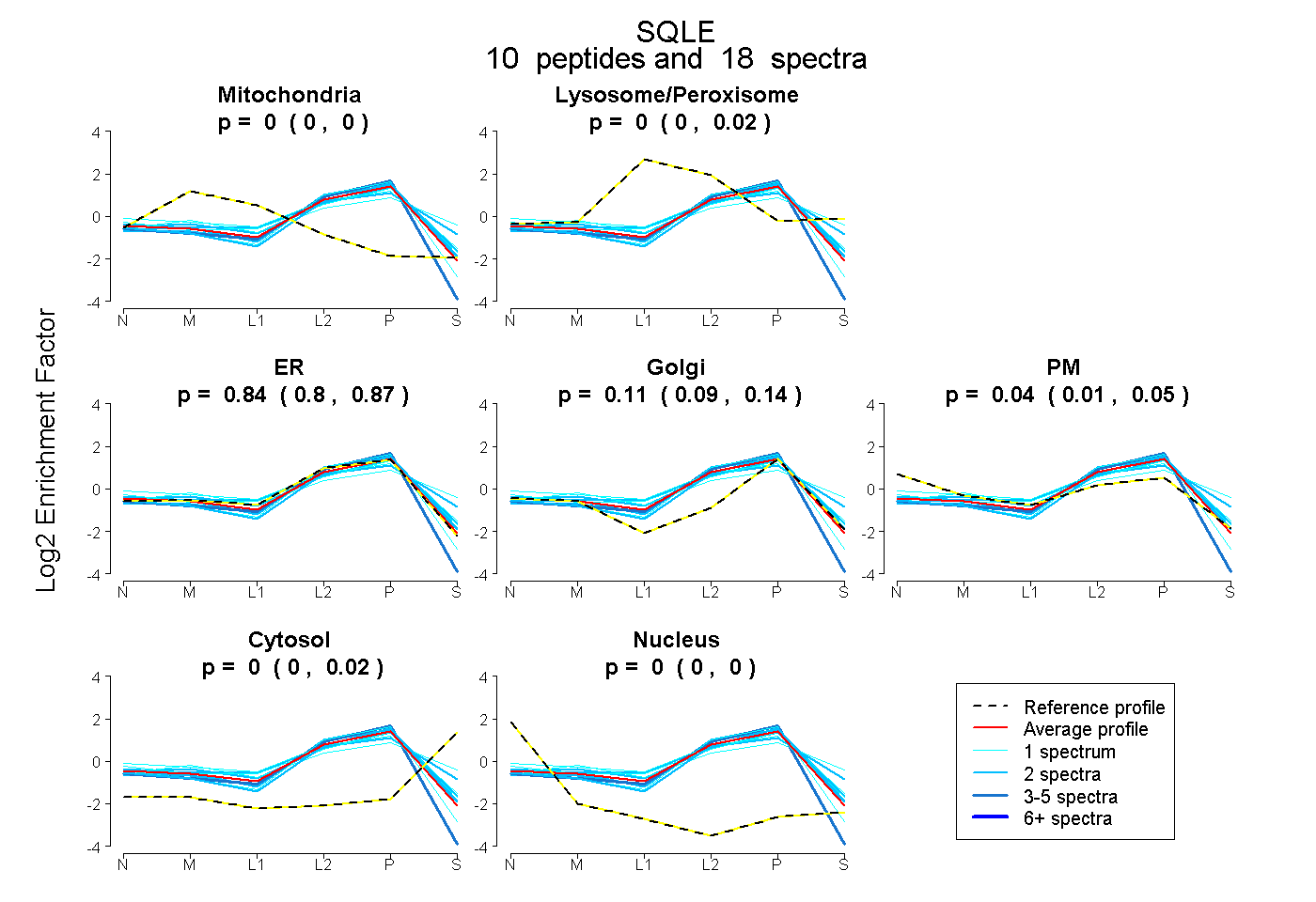
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.020 |
0.843 0.800 | 0.866 |
0.112 0.089 | 0.141 |
0.043 0.007 | 0.054 |
0.002 0.000 | 0.017 |
0.000 0.000 | 0.001 |
| 2 spectra, ACSIIFPLIYSEMK | 0.000 | 0.000 | 0.921 | 0.017 | 0.000 | 0.062 | 0.000 | |||
| 1 spectrum, NGGLLGR | 0.000 | 0.177 | 0.455 | 0.322 | 0.046 | 0.000 | 0.000 | |||
| 1 spectrum, GVLLLGDAYNLR | 0.000 | 0.121 | 0.521 | 0.093 | 0.265 | 0.000 | 0.000 | |||
| 1 spectrum, ILGECLQPGGYR | 0.000 | 0.000 | 0.894 | 0.106 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ACFLYFK | 0.000 | 0.283 | 0.326 | 0.337 | 0.000 | 0.054 | 0.000 | |||
| 2 spectra, SFFWSR | 0.000 | 0.000 | 0.744 | 0.241 | 0.000 | 0.015 | 0.000 | |||
| 2 spectra, ALFSSGAILYK | 0.000 | 0.079 | 0.678 | 0.229 | 0.015 | 0.000 | 0.000 | |||
| 1 spectrum, ELHAPLTVVADGLFSK | 0.000 | 0.318 | 0.108 | 0.459 | 0.000 | 0.116 | 0.000 | |||
| 2 spectra, ESFLEACQNAR | 0.000 | 0.000 | 0.985 | 0.015 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, FIEGVVLR | 0.000 | 0.000 | 0.993 | 0.000 | 0.000 | 0.000 | 0.007 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
38 spectra |
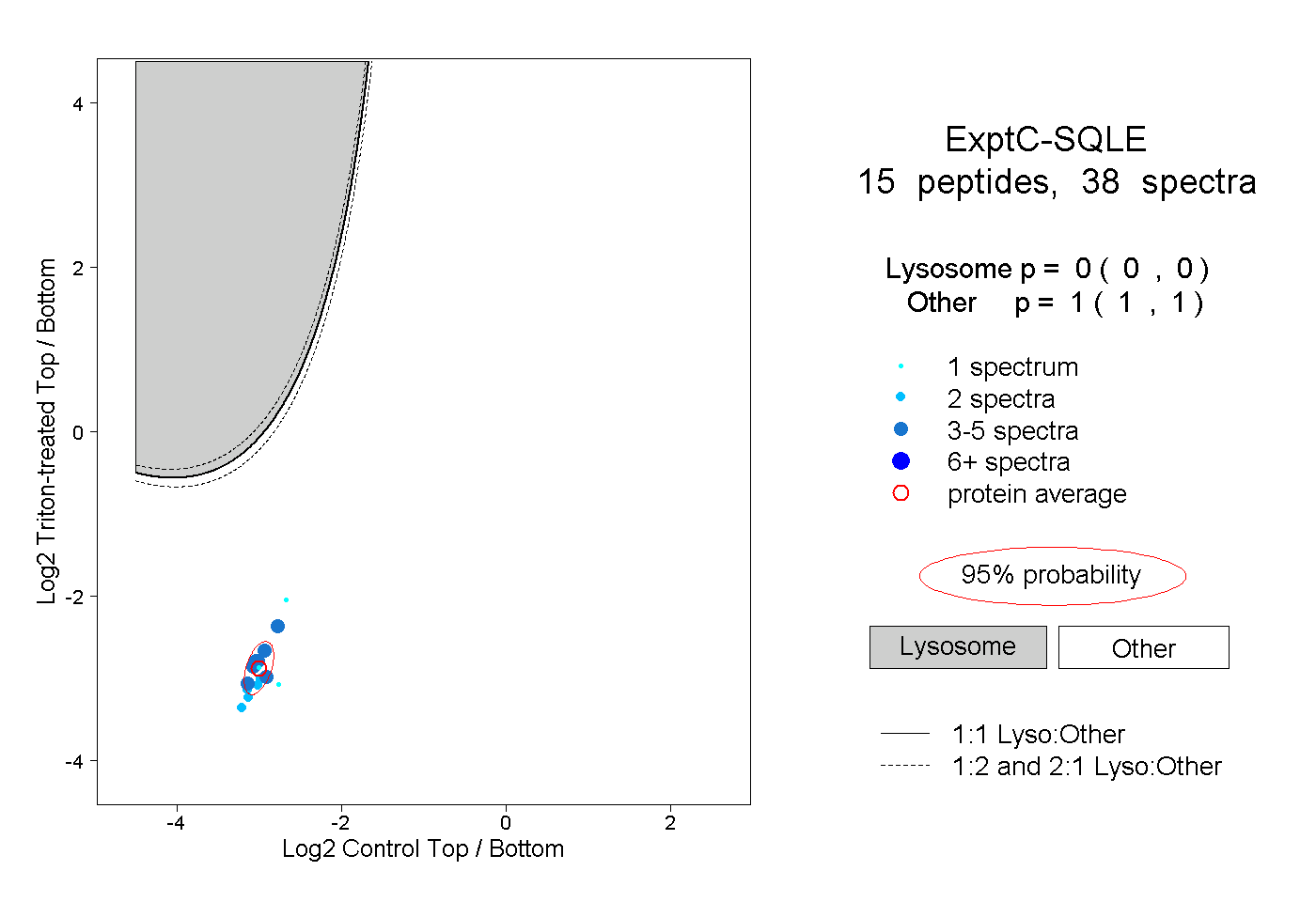 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
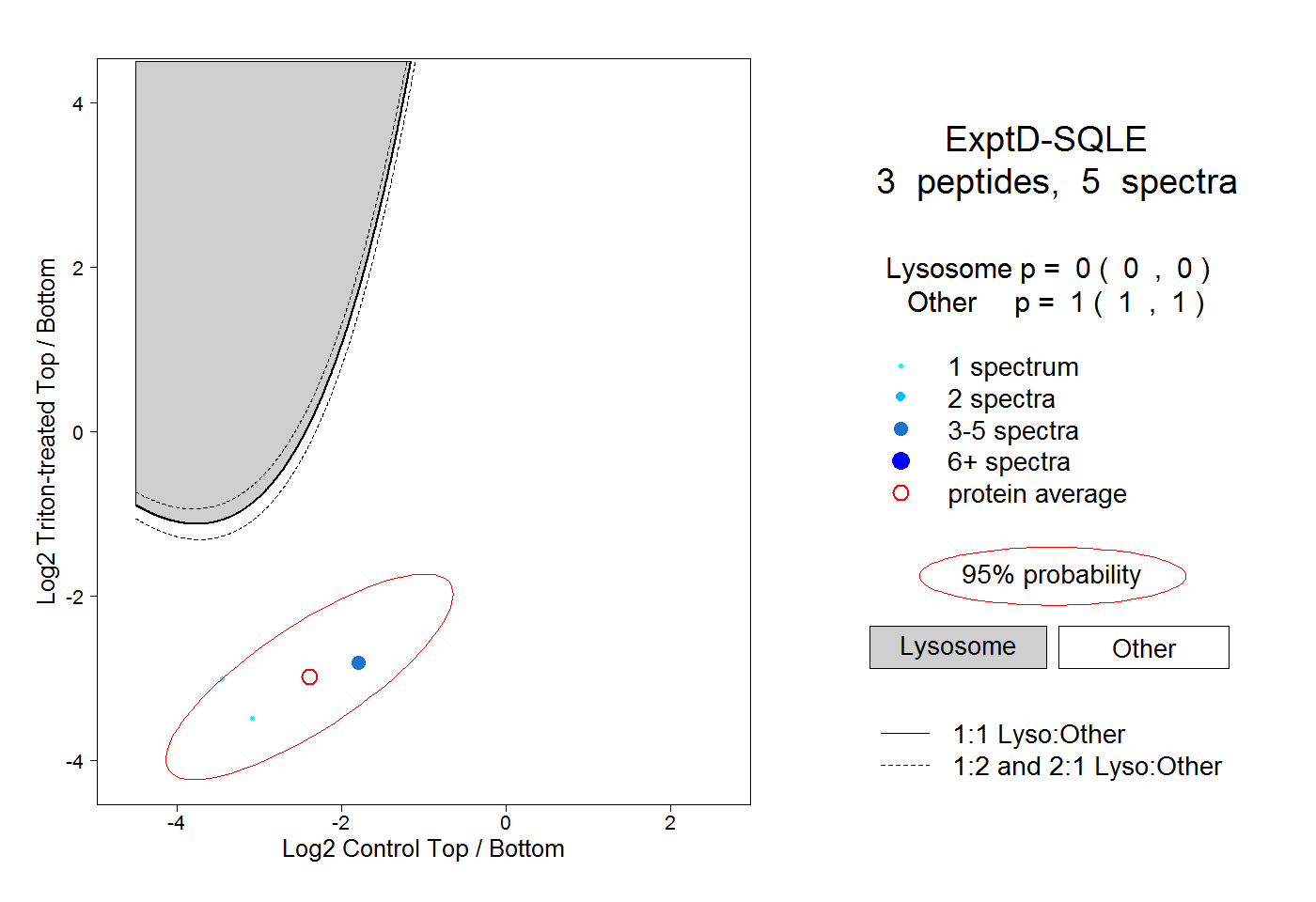 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |