peptides
spectra
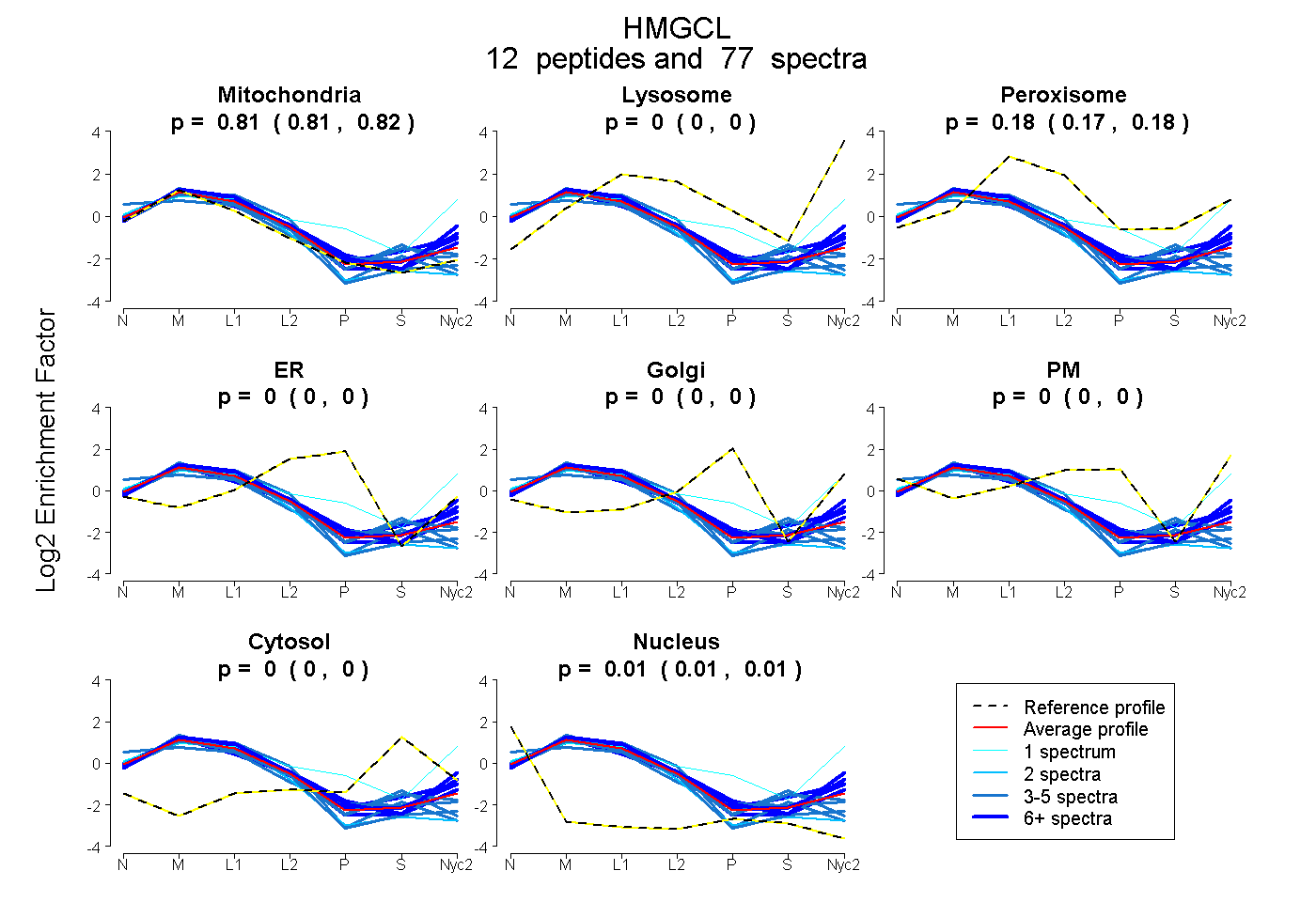
0.807 | 0.819
0.000 | 0.000
0.171 | 0.183
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.007 | 0.011
peptides
spectra
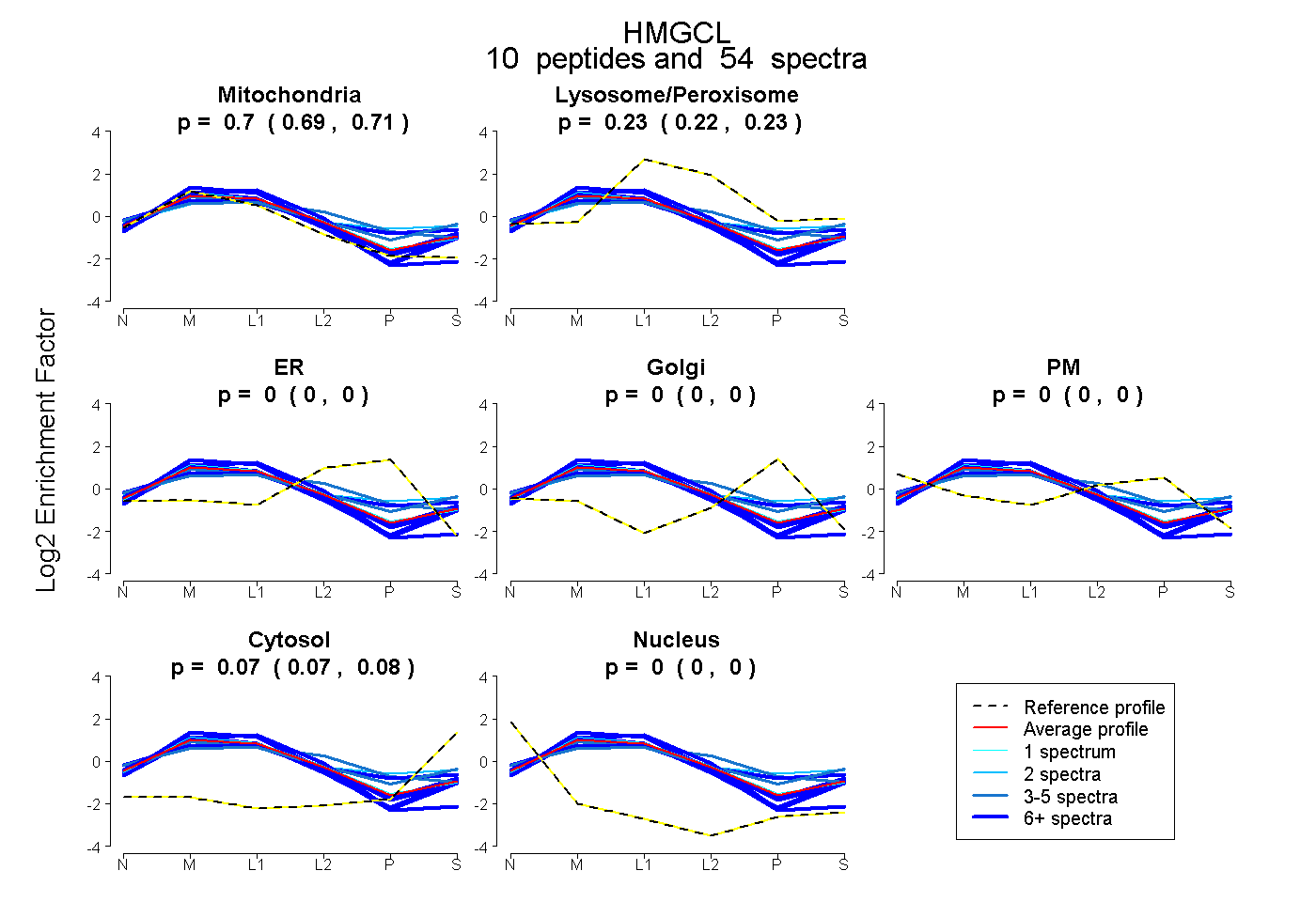
0.689 | 0.707
0.222 | 0.235
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.066 | 0.077
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.813 0.807 | 0.819 |
0.000 0.000 | 0.000 |
0.177 0.171 | 0.183 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.009 0.007 | 0.011 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
54 spectra |
 |
0.699 0.689 | 0.707 |
0.229 0.222 | 0.235 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.072 0.066 | 0.077 |
0.000 0.000 | 0.000 |
| 6 spectra, GFEEAVAAGAK | 0.478 | 0.272 | 0.000 | 0.000 | 0.137 | 0.113 | 0.000 | |||
| 1 spectrum, NVNCSIEESFQR | 0.732 | 0.221 | 0.000 | 0.000 | 0.000 | 0.047 | 0.000 | |||
| 3 spectra, FPGINYPVLTPNMK | 0.518 | 0.334 | 0.000 | 0.145 | 0.000 | 0.003 | 0.000 | |||
| 8 spectra, FDGVMQAAR | 0.761 | 0.175 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | |||
| 4 spectra, GYVSCALGCPYEGK | 0.460 | 0.315 | 0.000 | 0.000 | 0.058 | 0.167 | 0.000 | |||
| 7 spectra, AASISVR | 0.782 | 0.141 | 0.000 | 0.000 | 0.000 | 0.078 | 0.000 | |||
| 2 spectra, DGLQNEK | 0.394 | 0.348 | 0.000 | 0.080 | 0.054 | 0.124 | 0.000 | |||
| 9 spectra, LLEAGDFICQALNR | 0.770 | 0.226 | 0.000 | 0.000 | 0.000 | 0.004 | 0.000 | |||
| 7 spectra, EVSIFGAASELFTR | 0.688 | 0.200 | 0.000 | 0.000 | 0.000 | 0.112 | 0.000 | |||
| 7 spectra, IVEVGPR | 0.948 | 0.052 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
502 spectra |
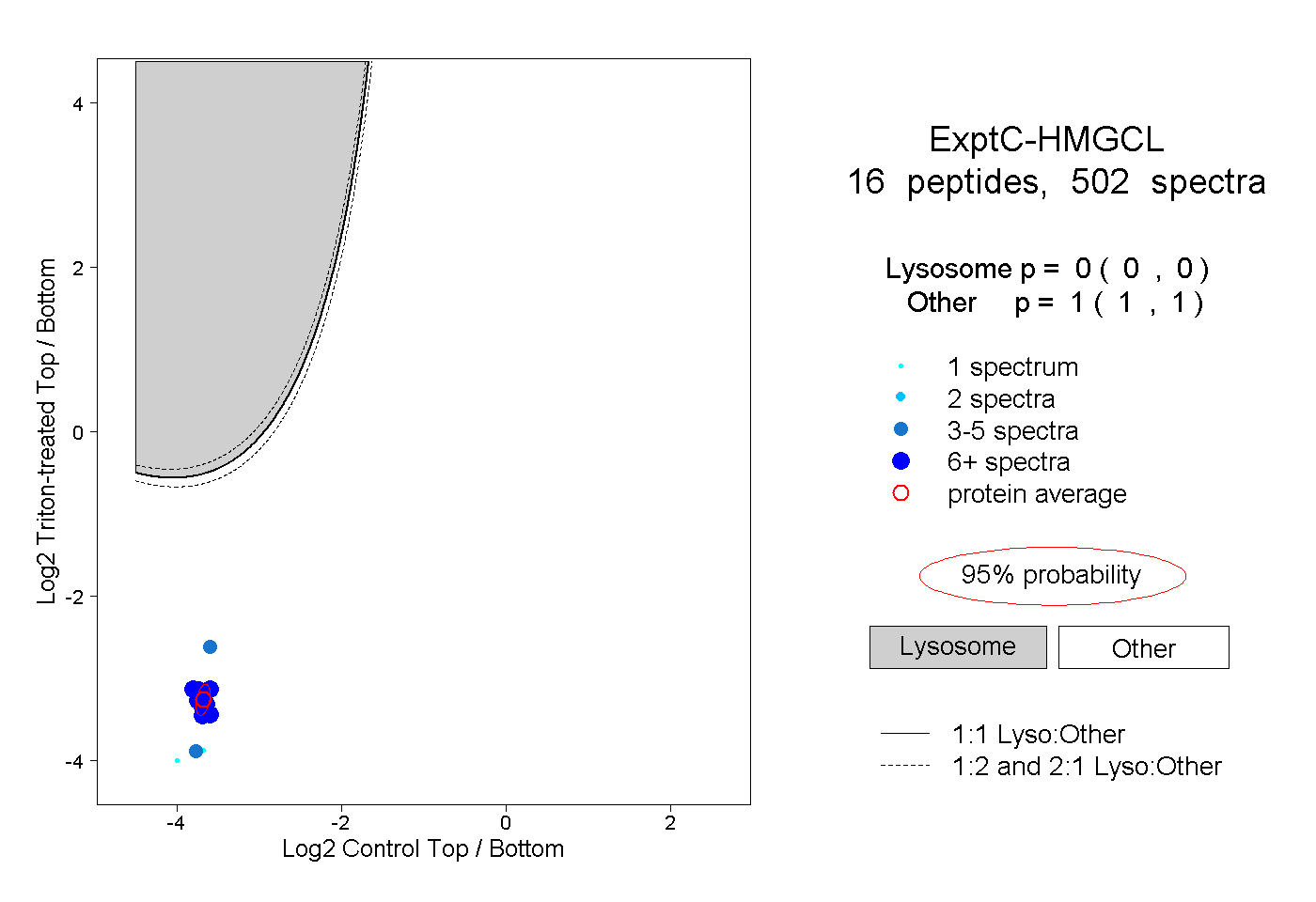 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
46 spectra |
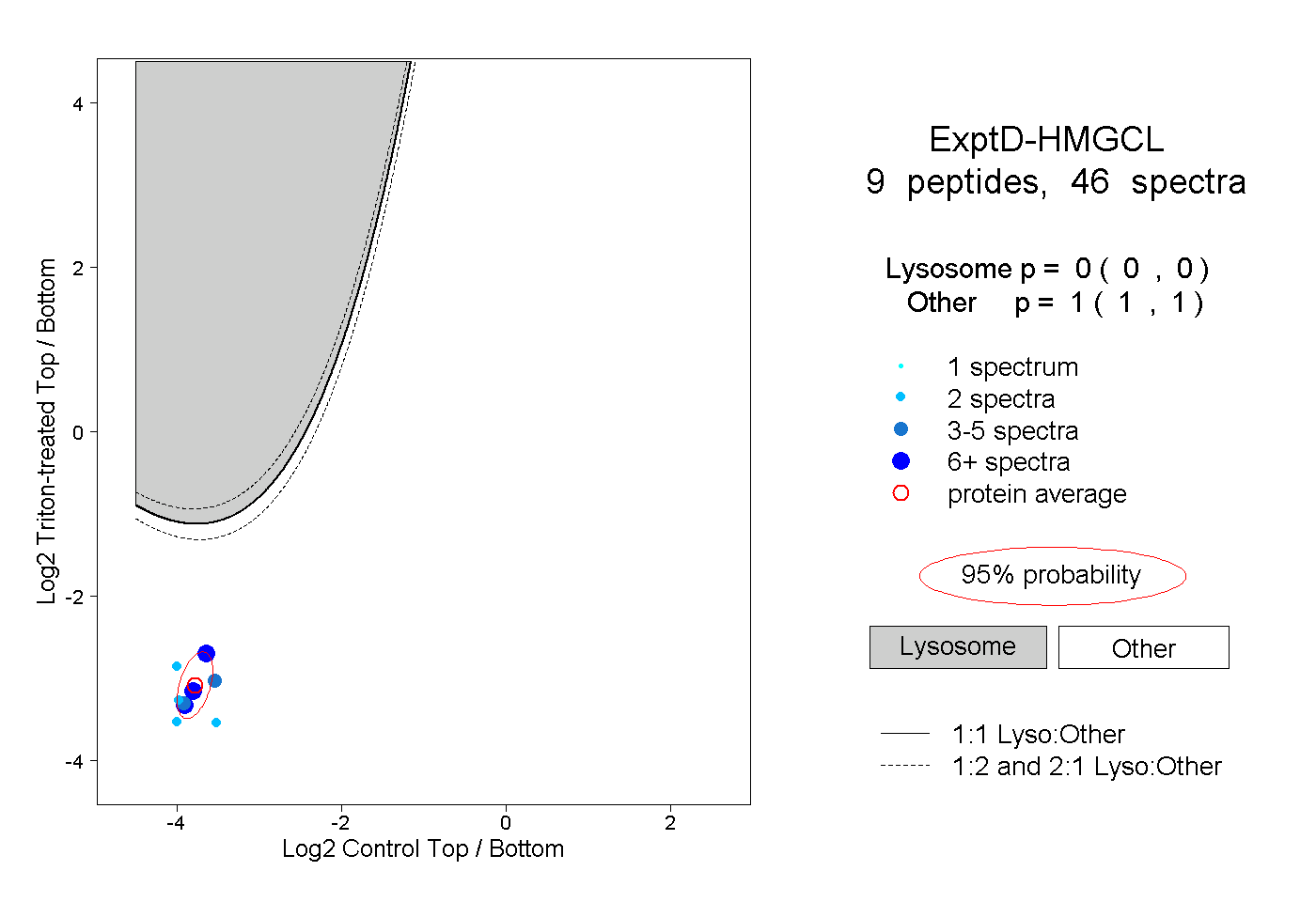 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |