peptides
spectra
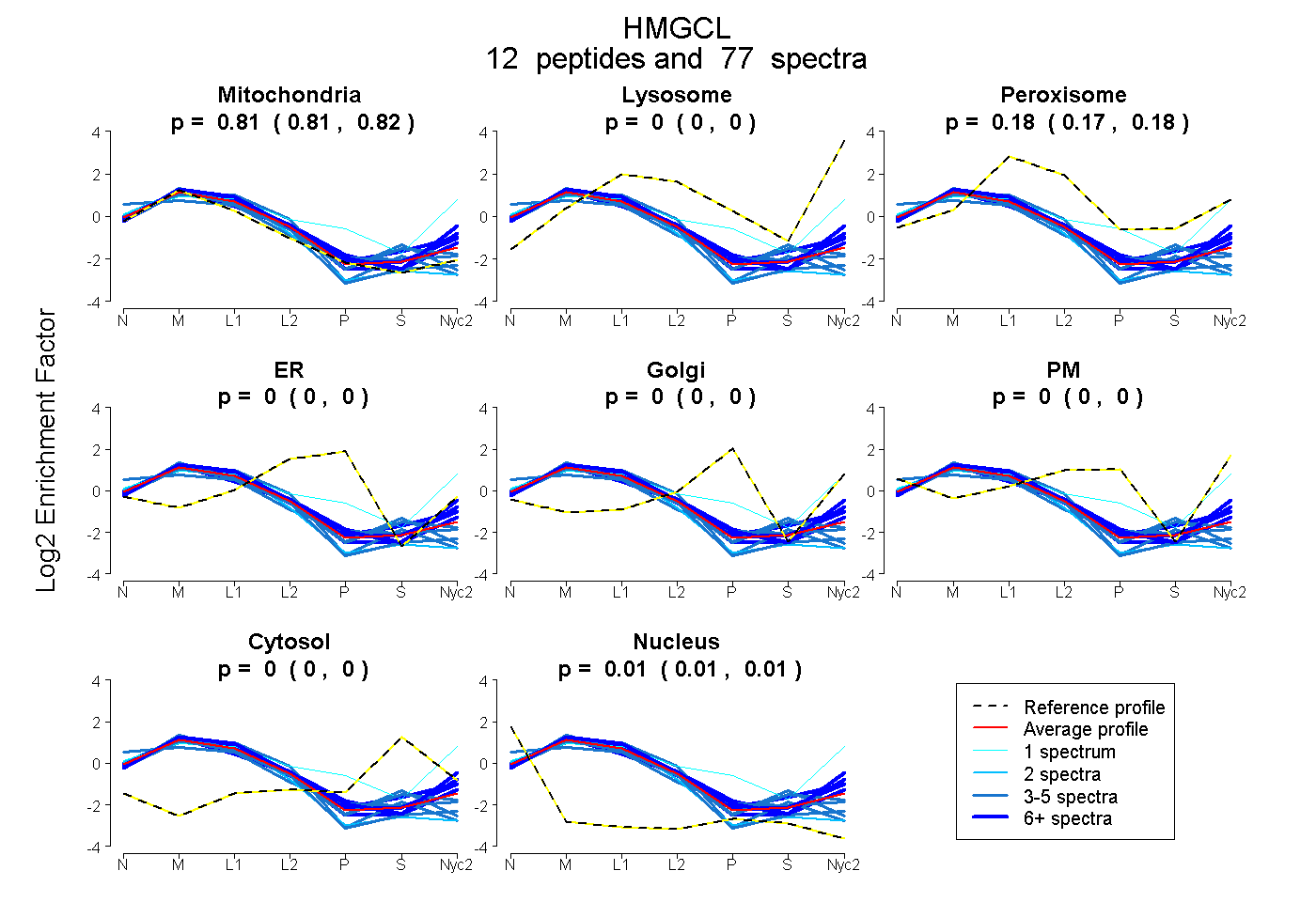
0.807 | 0.819
0.000 | 0.000
0.171 | 0.183
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.007 | 0.011
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.813 0.807 | 0.819 |
0.000 0.000 | 0.000 |
0.177 0.171 | 0.183 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.009 0.007 | 0.011 |
| 4 spectra, GFEEAVAAGAK | 0.690 | 0.000 | 0.182 | 0.000 | 0.000 | 0.000 | 0.000 | 0.128 | ||
| 4 spectra, NVNCSIEESFQR | 0.998 | 0.000 | 0.002 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, VAEVAK | 0.448 | 0.289 | 0.000 | 0.000 | 0.000 | 0.263 | 0.000 | 0.000 | ||
| 3 spectra, FPGINYPVLTPNMK | 0.897 | 0.000 | 0.096 | 0.000 | 0.000 | 0.000 | 0.000 | 0.008 | ||
| 4 spectra, VAQATCK | 0.788 | 0.000 | 0.133 | 0.000 | 0.000 | 0.000 | 0.079 | 0.000 | ||
| 12 spectra, FDGVMQAAR | 0.839 | 0.156 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.005 | ||
| 8 spectra, WVPQMADHSDVLK | 0.763 | 0.233 | 0.004 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, GYVSCALGCPYEGK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, AASISVR | 0.718 | 0.005 | 0.235 | 0.000 | 0.000 | 0.000 | 0.042 | 0.000 | ||
| 3 spectra, LLEAGDFICQALNR | 0.835 | 0.000 | 0.080 | 0.000 | 0.000 | 0.000 | 0.085 | 0.000 | ||
| 11 spectra, EVSIFGAASELFTR | 0.785 | 0.000 | 0.130 | 0.000 | 0.000 | 0.085 | 0.000 | 0.000 | ||
| 12 spectra, IVEVGPR | 0.784 | 0.061 | 0.155 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
54 spectra |
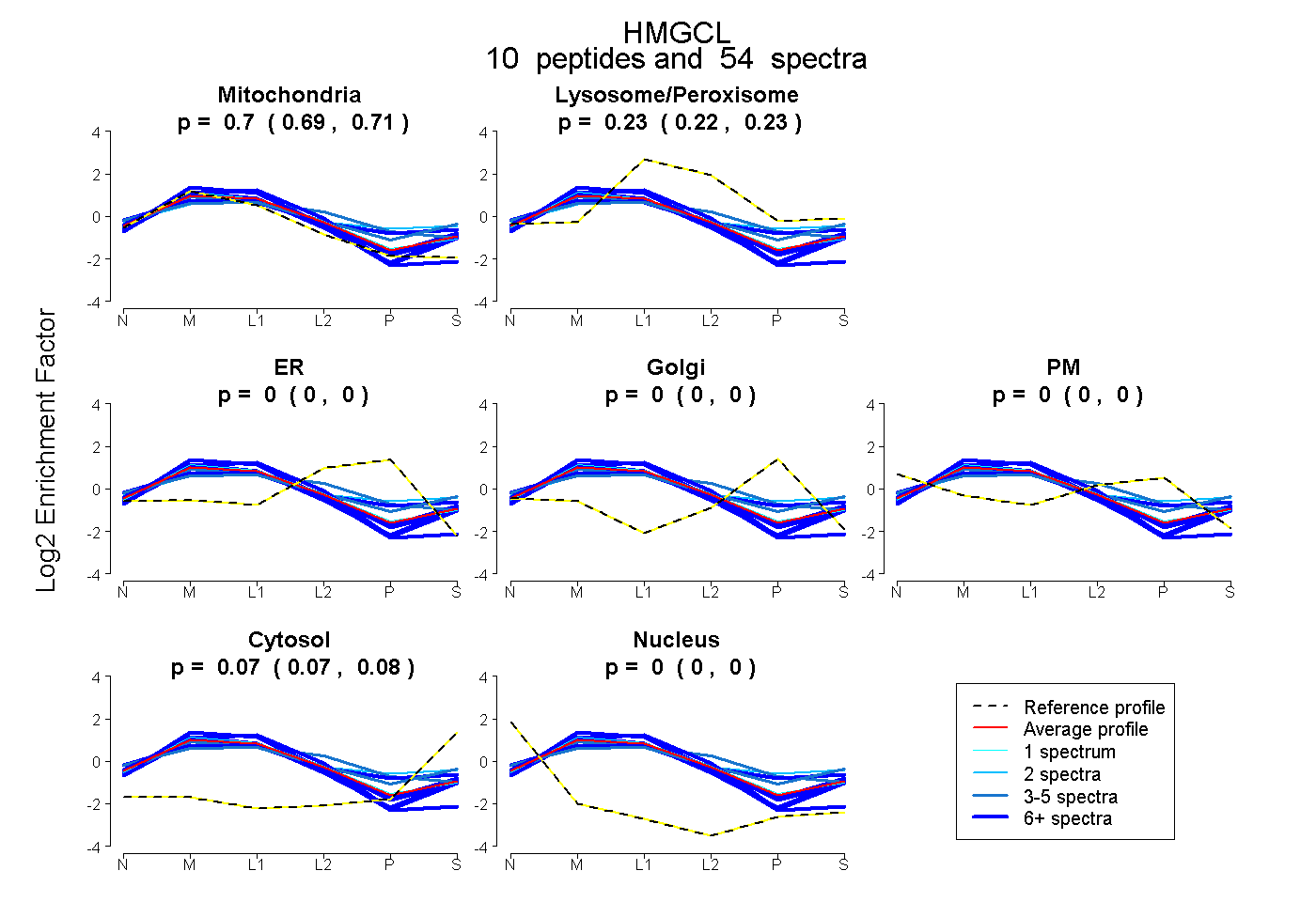 |
0.699 0.689 | 0.707 |
0.229 0.222 | 0.235 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.072 0.066 | 0.077 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
502 spectra |
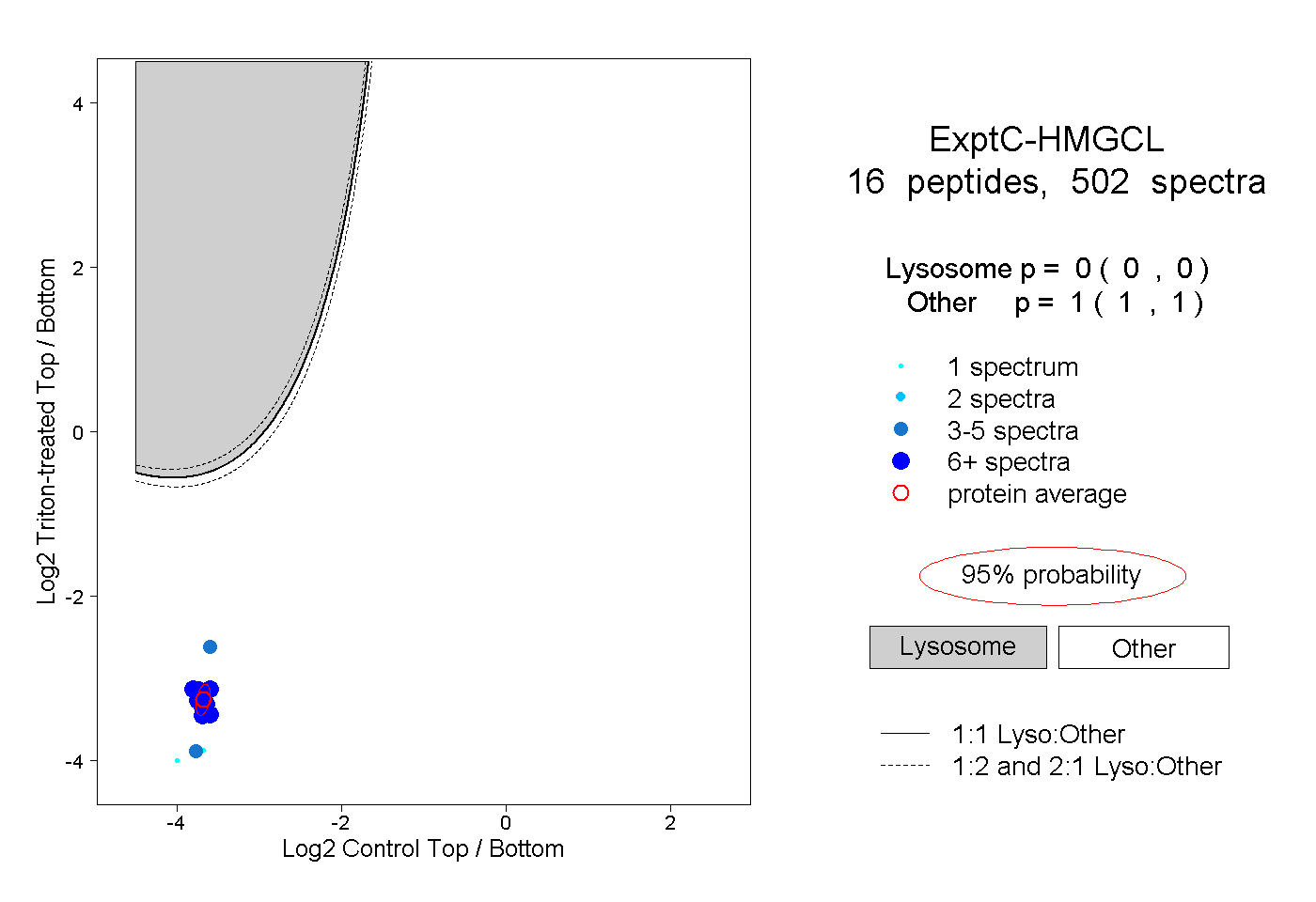 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
46 spectra |
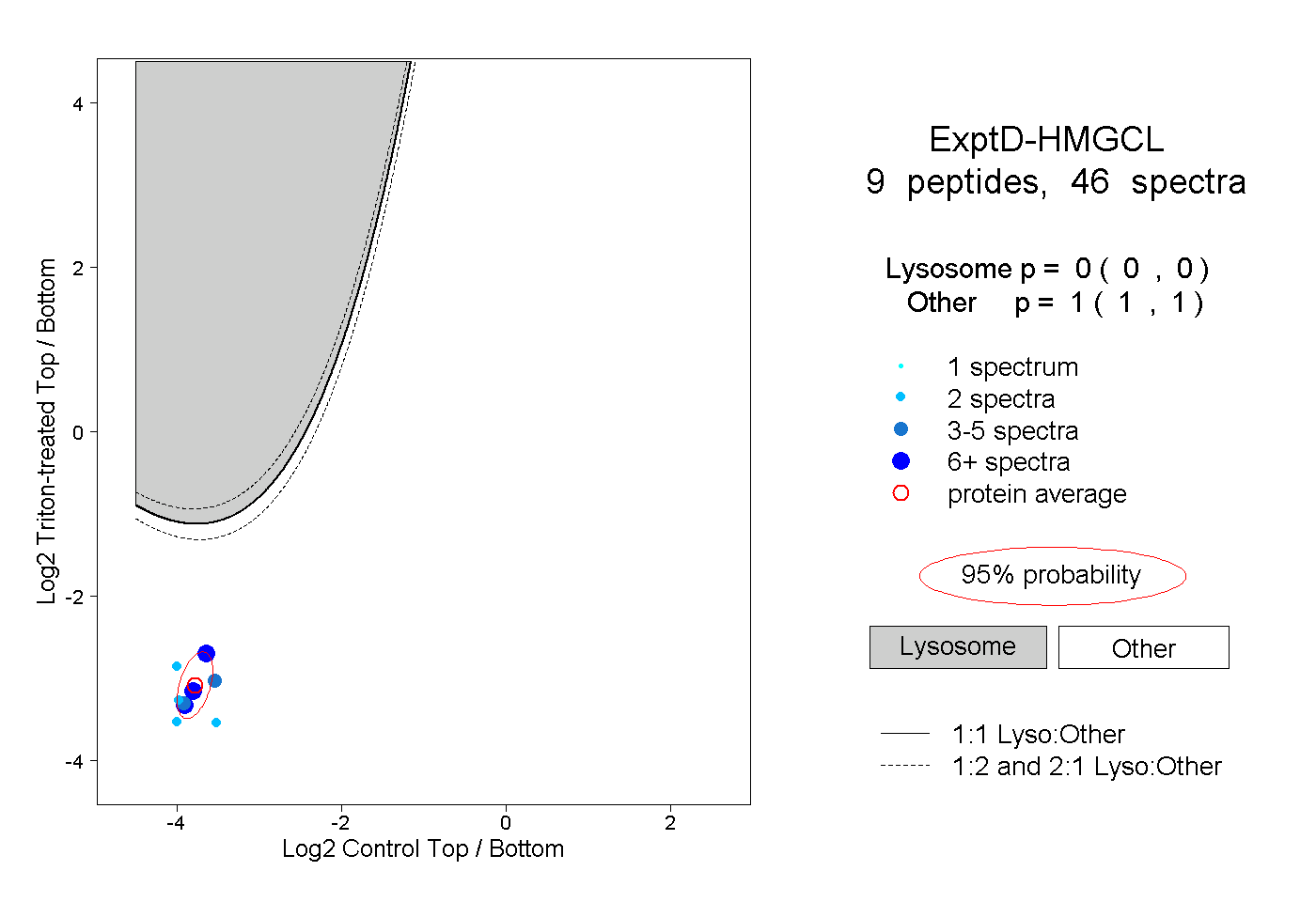 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |