peptides
spectra
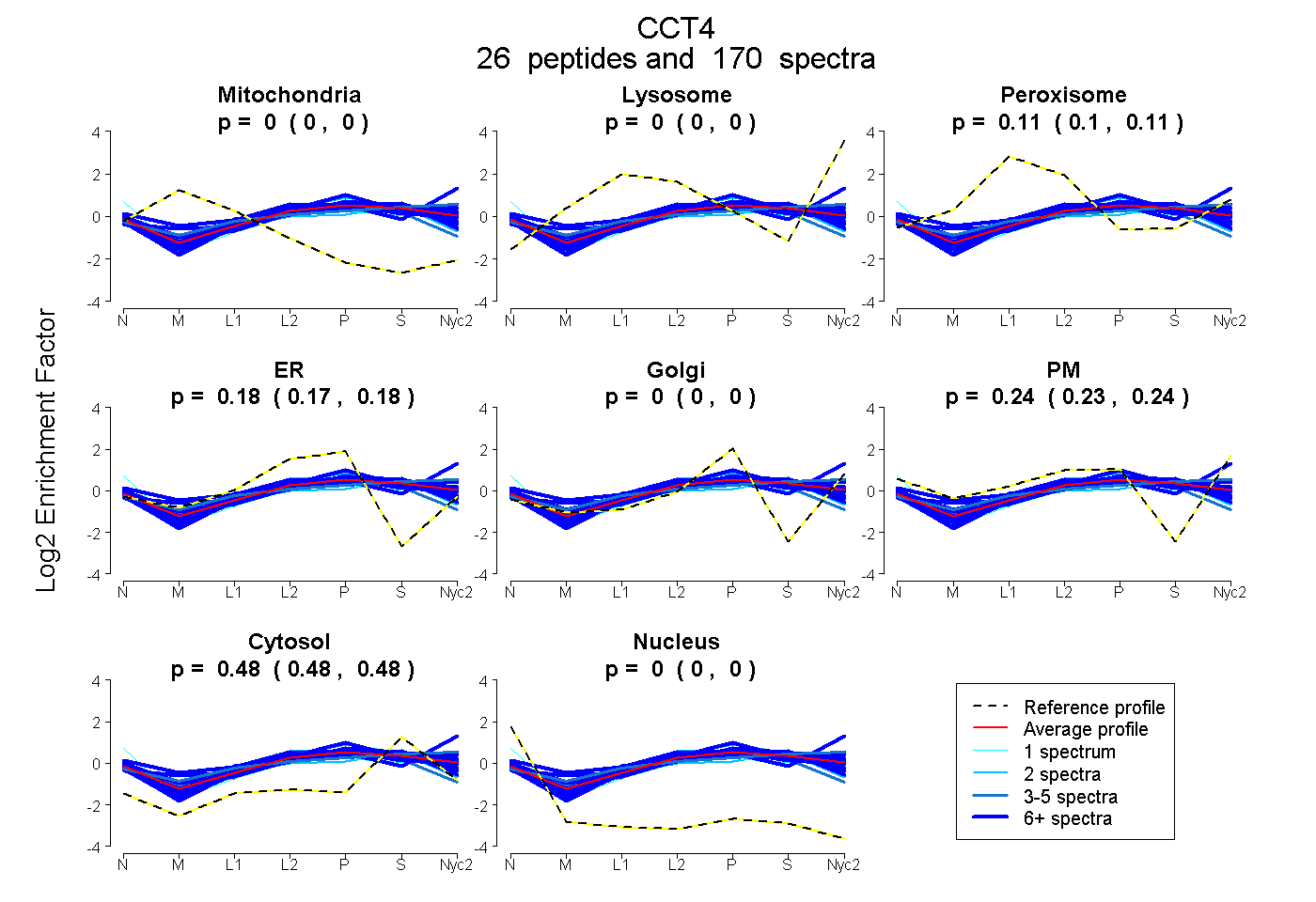
0.000 | 0.000
0.000 | 0.000
0.104 | 0.107
0.171 | 0.179
0.000 | 0.000
0.232 | 0.242
0.480 | 0.482
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
170 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.106 0.104 | 0.107 |
0.175 0.171 | 0.179 |
0.000 0.000 | 0.000 |
0.238 0.232 | 0.242 |
0.481 0.480 | 0.482 |
0.000 0.000 | 0.000 |
| 6 spectra, TVTIVVR | 0.000 | 0.019 | 0.075 | 0.087 | 0.000 | 0.349 | 0.470 | 0.000 | ||
| 11 spectra, SGPPAAGPGNR | 0.000 | 0.000 | 0.063 | 0.223 | 0.131 | 0.142 | 0.442 | 0.000 | ||
| 3 spectra, ITGCTSPGK | 0.000 | 0.000 | 0.112 | 0.434 | 0.000 | 0.000 | 0.454 | 0.000 | ||
| 10 spectra, TLSGMESYCVR | 0.000 | 0.000 | 0.124 | 0.323 | 0.021 | 0.000 | 0.532 | 0.000 | ||
| 8 spectra, SLHDALCVIR | 0.000 | 0.000 | 0.132 | 0.237 | 0.000 | 0.141 | 0.490 | 0.000 | ||
| 7 spectra, MLVELSK | 0.000 | 0.000 | 0.132 | 0.188 | 0.095 | 0.083 | 0.502 | 0.000 | ||
| 2 spectra, GDVTITNDGATILK | 0.000 | 0.000 | 0.183 | 0.026 | 0.078 | 0.196 | 0.516 | 0.000 | ||
| 11 spectra, EDIEFICK | 0.000 | 0.000 | 0.136 | 0.317 | 0.000 | 0.000 | 0.547 | 0.000 | ||
| 6 spectra, DKPAQIR | 0.000 | 0.000 | 0.115 | 0.284 | 0.000 | 0.101 | 0.500 | 0.000 | ||
| 7 spectra, VIDPATATSVDLR | 0.000 | 0.000 | 0.094 | 0.144 | 0.000 | 0.241 | 0.521 | 0.000 | ||
| 12 spectra, QMQVLHPAAR | 0.000 | 0.000 | 0.166 | 0.000 | 0.107 | 0.350 | 0.377 | 0.000 | ||
| 7 spectra, ITEYSR | 0.000 | 0.000 | 0.099 | 0.216 | 0.000 | 0.255 | 0.430 | 0.000 | ||
| 6 spectra, PENVASR | 0.000 | 0.145 | 0.046 | 0.000 | 0.000 | 0.498 | 0.310 | 0.000 | ||
| 1 spectrum, ALIAGGGAPEIELALR | 0.000 | 0.000 | 0.173 | 0.146 | 0.000 | 0.232 | 0.449 | 0.000 | ||
| 4 spectra, GLEILTDMSRPVQLSDR | 0.000 | 0.000 | 0.114 | 0.150 | 0.000 | 0.249 | 0.487 | 0.000 | ||
| 1 spectrum, MIQDGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.520 | 0.479 | 0.001 | ||
| 6 spectra, TDMDNQIVVSDYAQMDR | 0.000 | 0.000 | 0.073 | 0.293 | 0.000 | 0.102 | 0.532 | 0.000 | ||
| 7 spectra, TTGINVR | 0.000 | 0.000 | 0.230 | 0.003 | 0.185 | 0.158 | 0.424 | 0.000 | ||
| 4 spectra, IDDVVNTR | 0.000 | 0.000 | 0.074 | 0.249 | 0.000 | 0.162 | 0.515 | 0.000 | ||
| 2 spectra, FSNISAAK | 0.000 | 0.000 | 0.081 | 0.160 | 0.000 | 0.322 | 0.438 | 0.000 | ||
| 16 spectra, LVIEEAER | 0.000 | 0.000 | 0.130 | 0.113 | 0.000 | 0.286 | 0.472 | 0.000 | ||
| 2 spectra, GAYQDR | 0.000 | 0.000 | 0.044 | 0.432 | 0.000 | 0.000 | 0.524 | 0.000 | ||
| 4 spectra, VVSQYSSLLSPMSVNAVMK | 0.000 | 0.061 | 0.142 | 0.000 | 0.040 | 0.294 | 0.463 | 0.000 | ||
| 7 spectra, DALSDLALHFLNK | 0.000 | 0.000 | 0.150 | 0.128 | 0.052 | 0.200 | 0.471 | 0.000 | ||
| 10 spectra, AYILNLVK | 0.000 | 0.020 | 0.084 | 0.025 | 0.187 | 0.201 | 0.483 | 0.000 | ||
| 10 spectra, VANSGITR | 0.000 | 0.000 | 0.081 | 0.078 | 0.044 | 0.317 | 0.480 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
64 spectra |
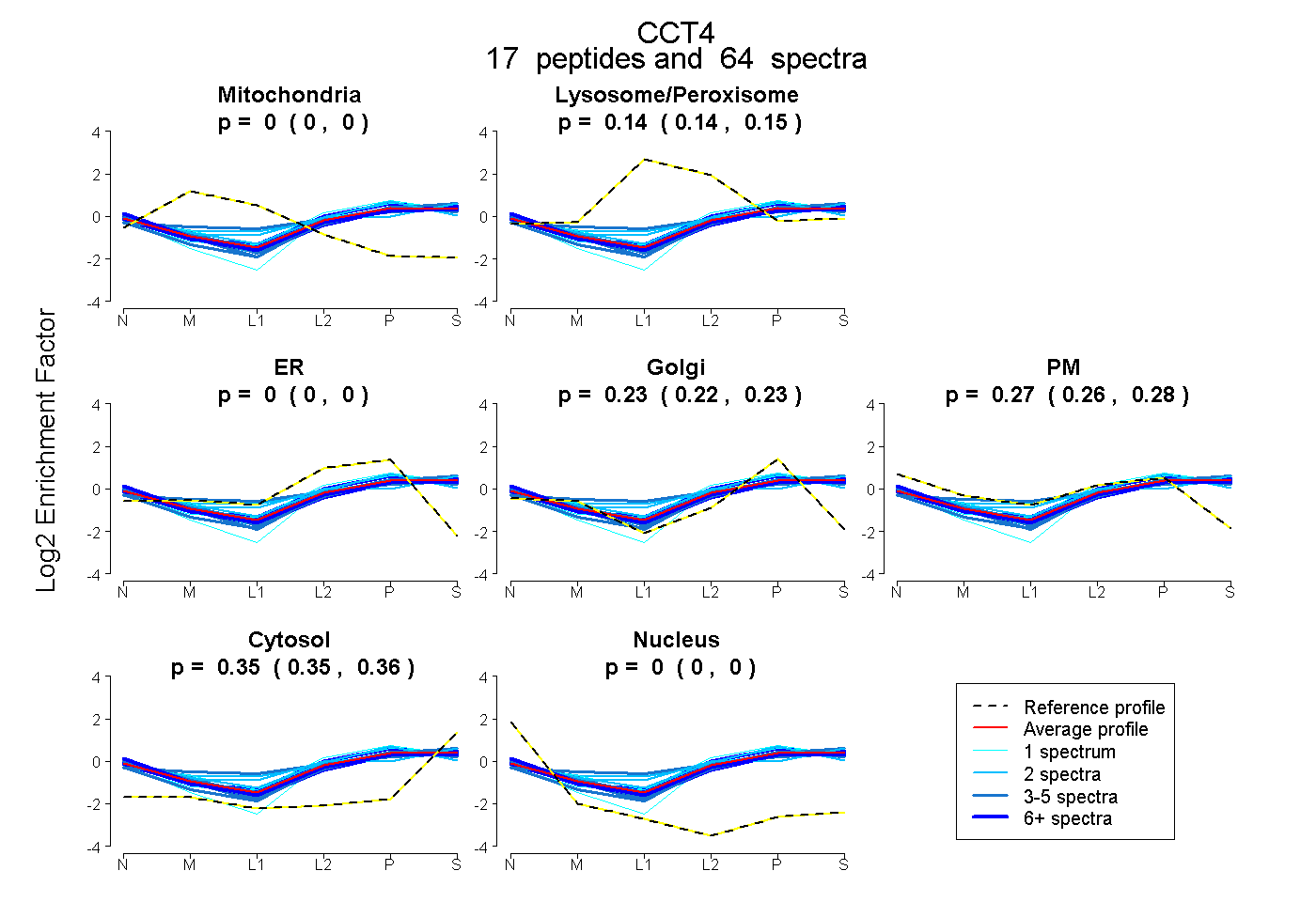 |
0.000 0.000 | 0.000 |
0.143 0.139 | 0.148 |
0.000 0.000 | 0.000 |
0.229 0.223 | 0.235 |
0.272 0.264 | 0.279 |
0.355 0.352 | 0.357 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
223 spectra |
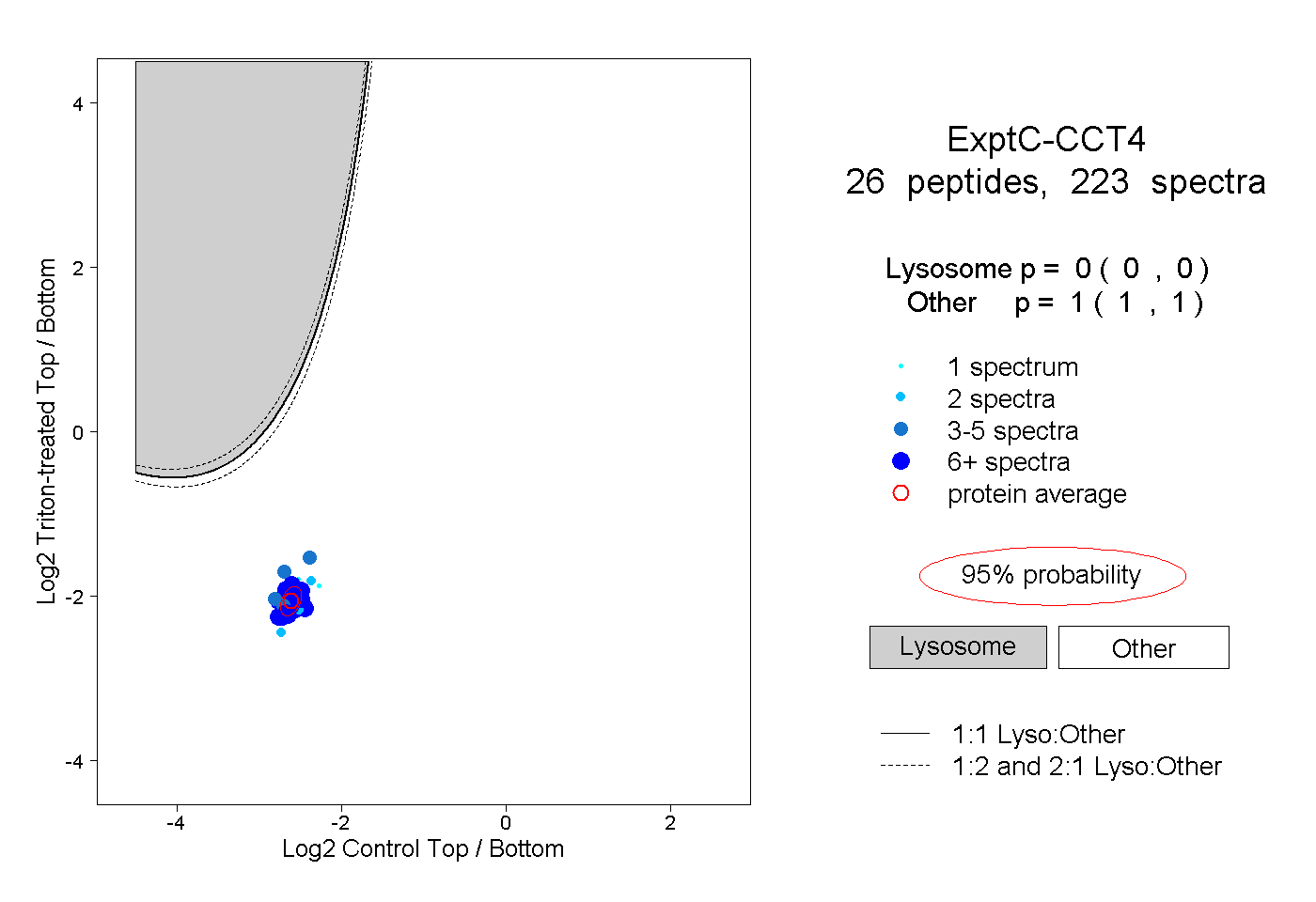 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
34 spectra |
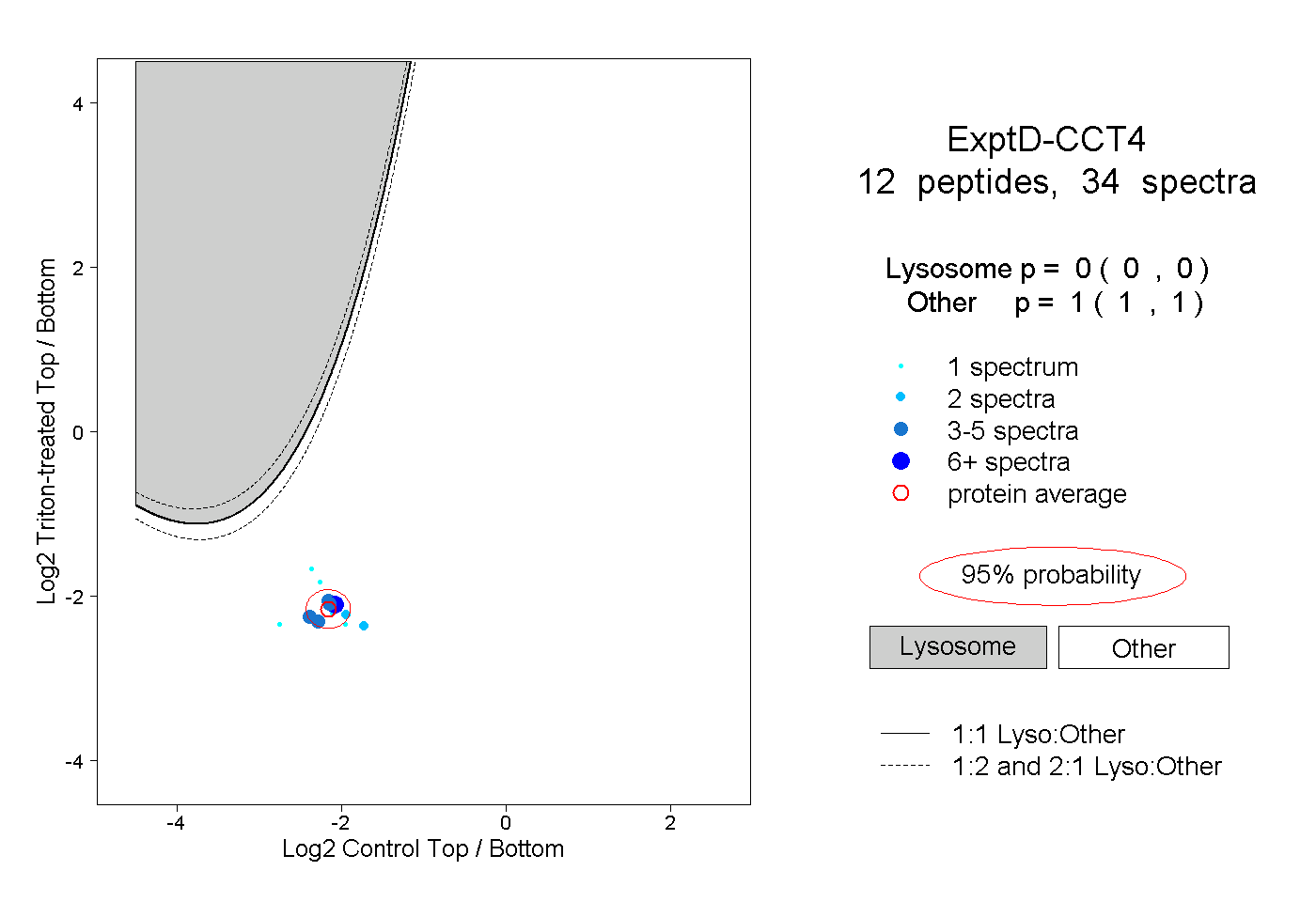 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |