peptides
spectra
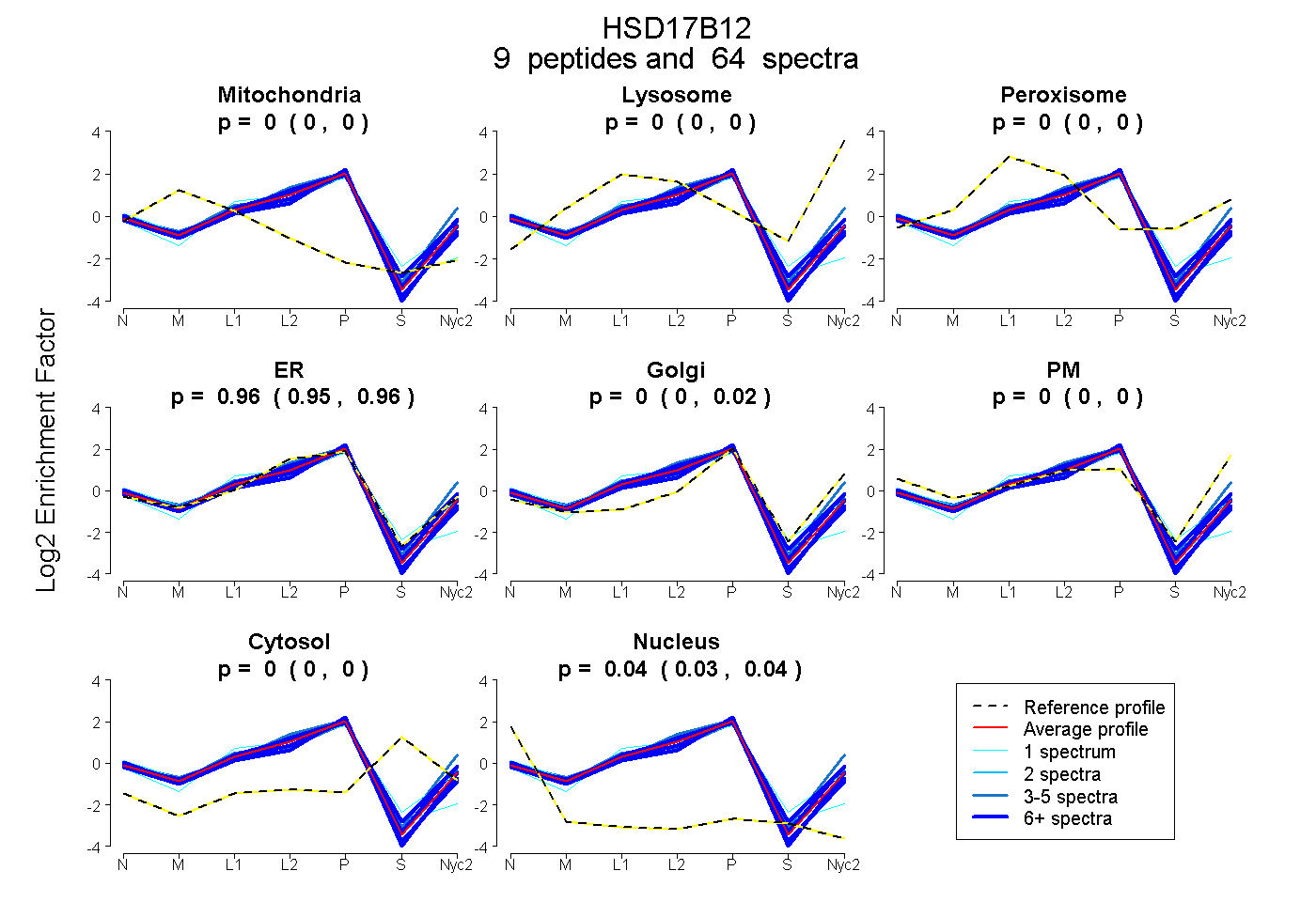
0.000 | 0.002
0.000 | 0.000
0.000 | 0.000
0.947 | 0.965
0.000 | 0.017
0.000 | 0.000
0.000 | 0.000
0.032 | 0.038
peptides
spectra
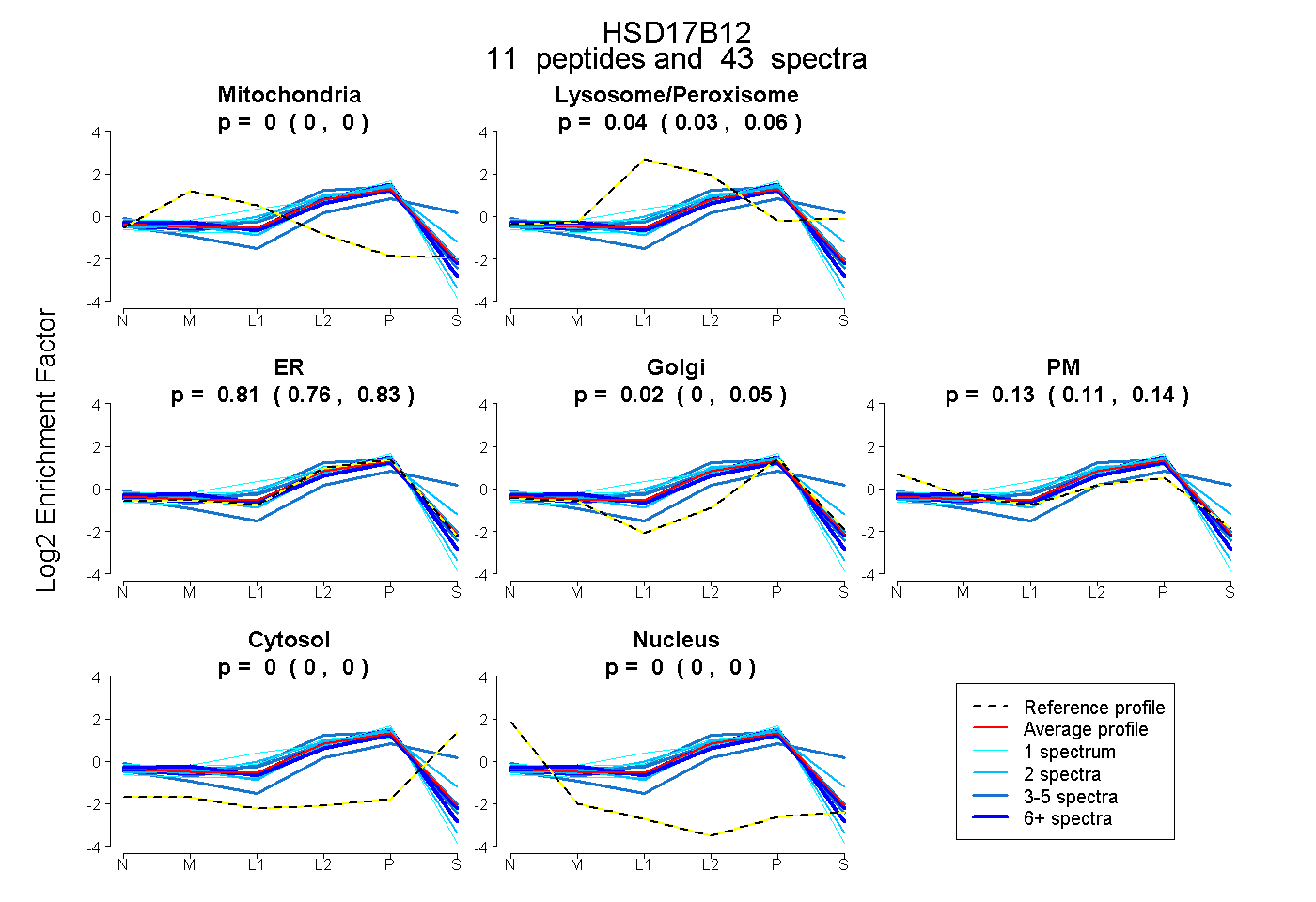
0.000 | 0.000
0.025 | 0.064
0.764 | 0.833
0.000 | 0.052
0.105 | 0.144
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
64 spectra |
 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.960 0.947 | 0.965 |
0.004 0.000 | 0.017 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.035 0.032 | 0.038 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
43 spectra |
 |
0.000 0.000 | 0.000 |
0.044 0.025 | 0.064 |
0.805 0.764 | 0.833 |
0.020 0.000 | 0.052 |
0.130 0.105 | 0.144 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 11 spectra, IVLISR | 0.000 | 0.000 | 0.993 | 0.000 | 0.000 | 0.000 | 0.007 | |||
| 3 spectra, GIFVQSVLPFFVATK | 0.000 | 0.124 | 0.319 | 0.241 | 0.000 | 0.316 | 0.000 | |||
| 1 spectrum, LVLPGMVER | 0.000 | 0.000 | 0.996 | 0.000 | 0.000 | 0.000 | 0.004 | |||
| 2 spectra, LGEWAVVTGGTDGIGK | 0.000 | 0.140 | 0.804 | 0.000 | 0.056 | 0.000 | 0.000 | |||
| 5 spectra, ASYSLFR | 0.017 | 0.048 | 0.802 | 0.000 | 0.133 | 0.000 | 0.000 | |||
| 1 spectrum, LININVLSICK | 0.000 | 0.102 | 0.753 | 0.000 | 0.145 | 0.000 | 0.000 | |||
| 3 spectra, AFVDFFSQCLHEEYK | 0.000 | 0.126 | 0.797 | 0.000 | 0.076 | 0.000 | 0.000 | |||
| 2 spectra, SYAEELAK | 0.000 | 0.000 | 0.963 | 0.024 | 0.000 | 0.000 | 0.013 | |||
| 1 spectrum, FNVETR | 0.000 | 0.413 | 0.286 | 0.300 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, TVGLQTR | 0.048 | 0.000 | 0.751 | 0.037 | 0.164 | 0.000 | 0.000 | |||
| 2 spectra, TIMGFNK | 0.000 | 0.082 | 0.813 | 0.000 | 0.000 | 0.105 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
87 spectra |
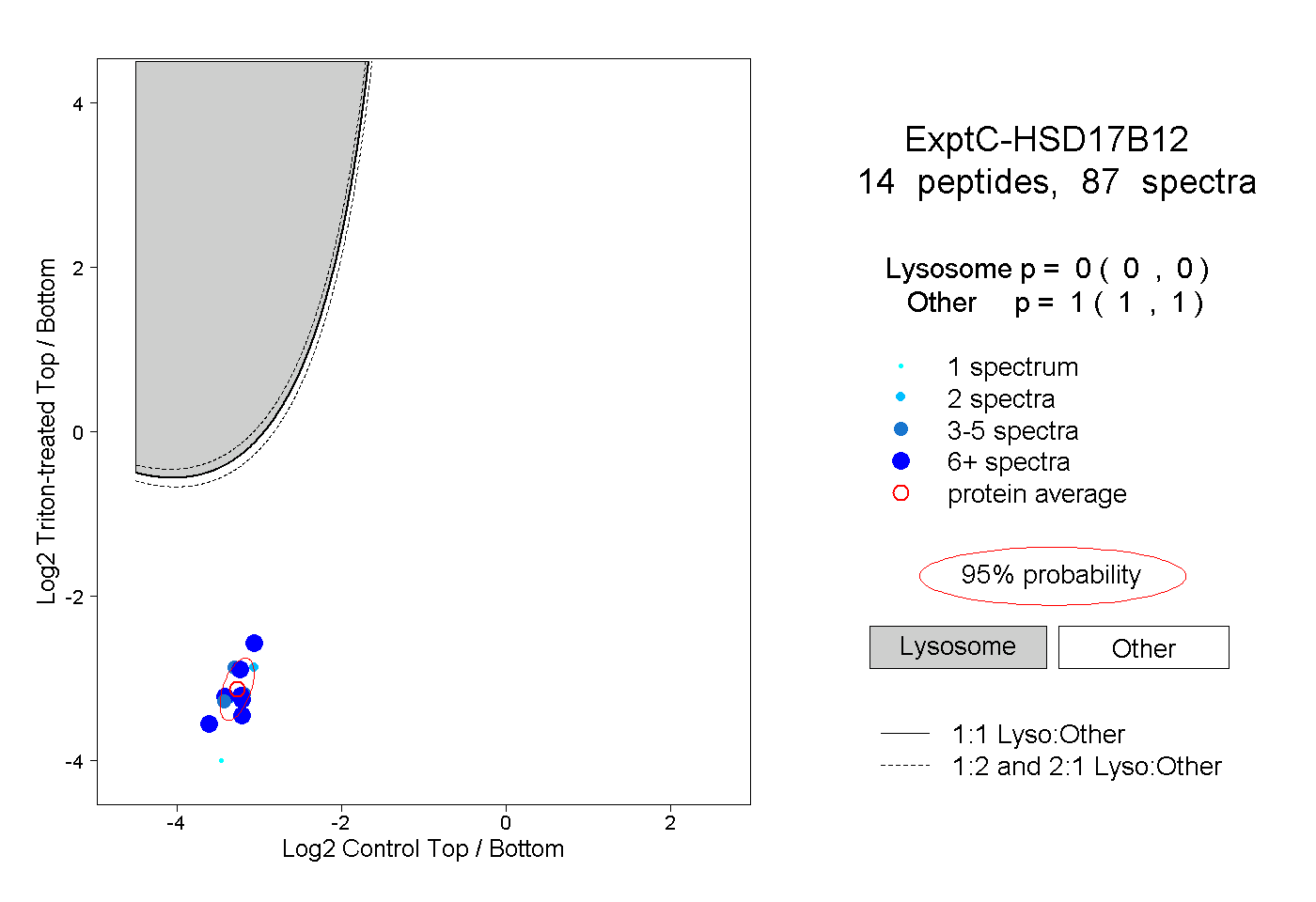 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
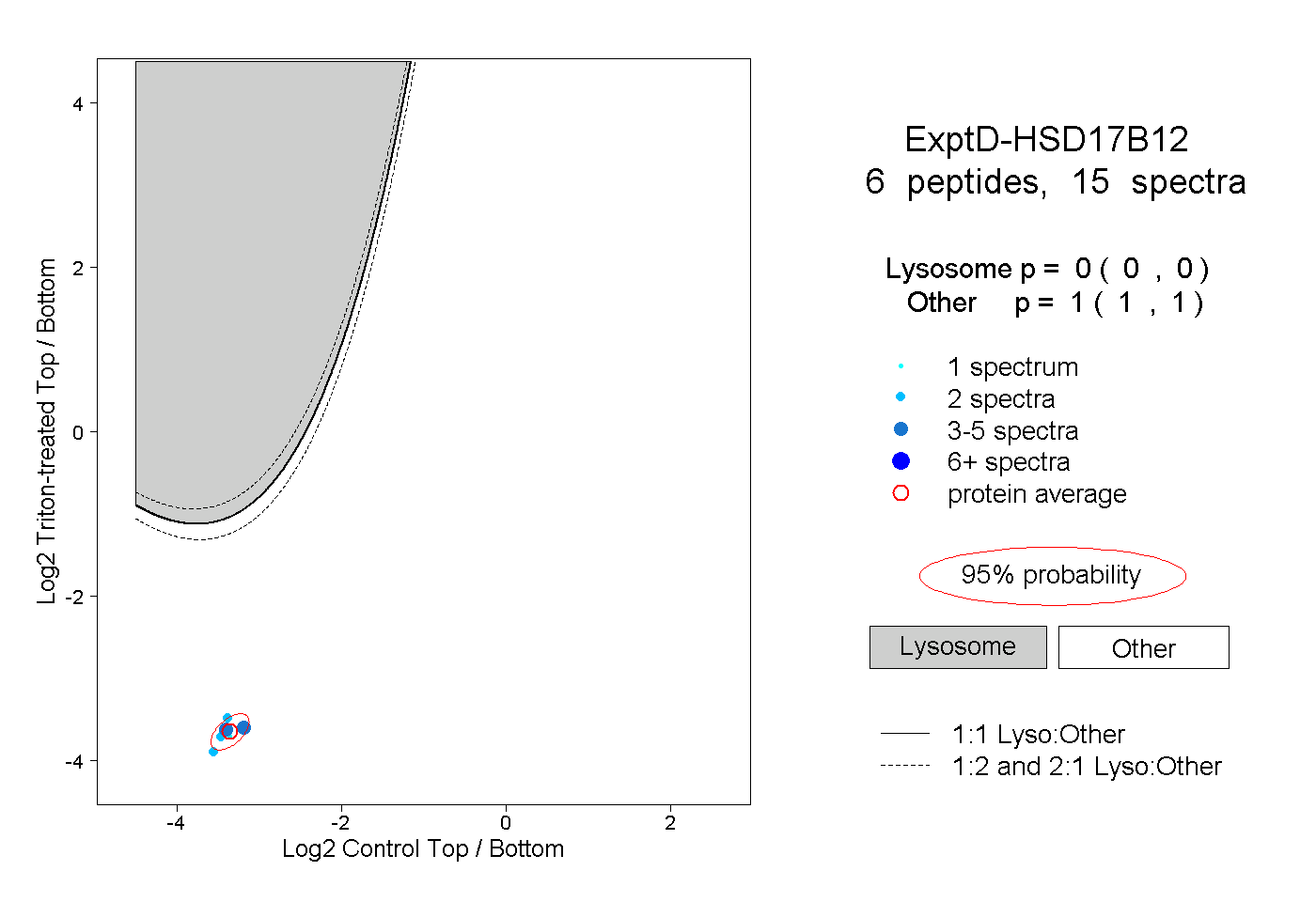 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |