peptides
spectra
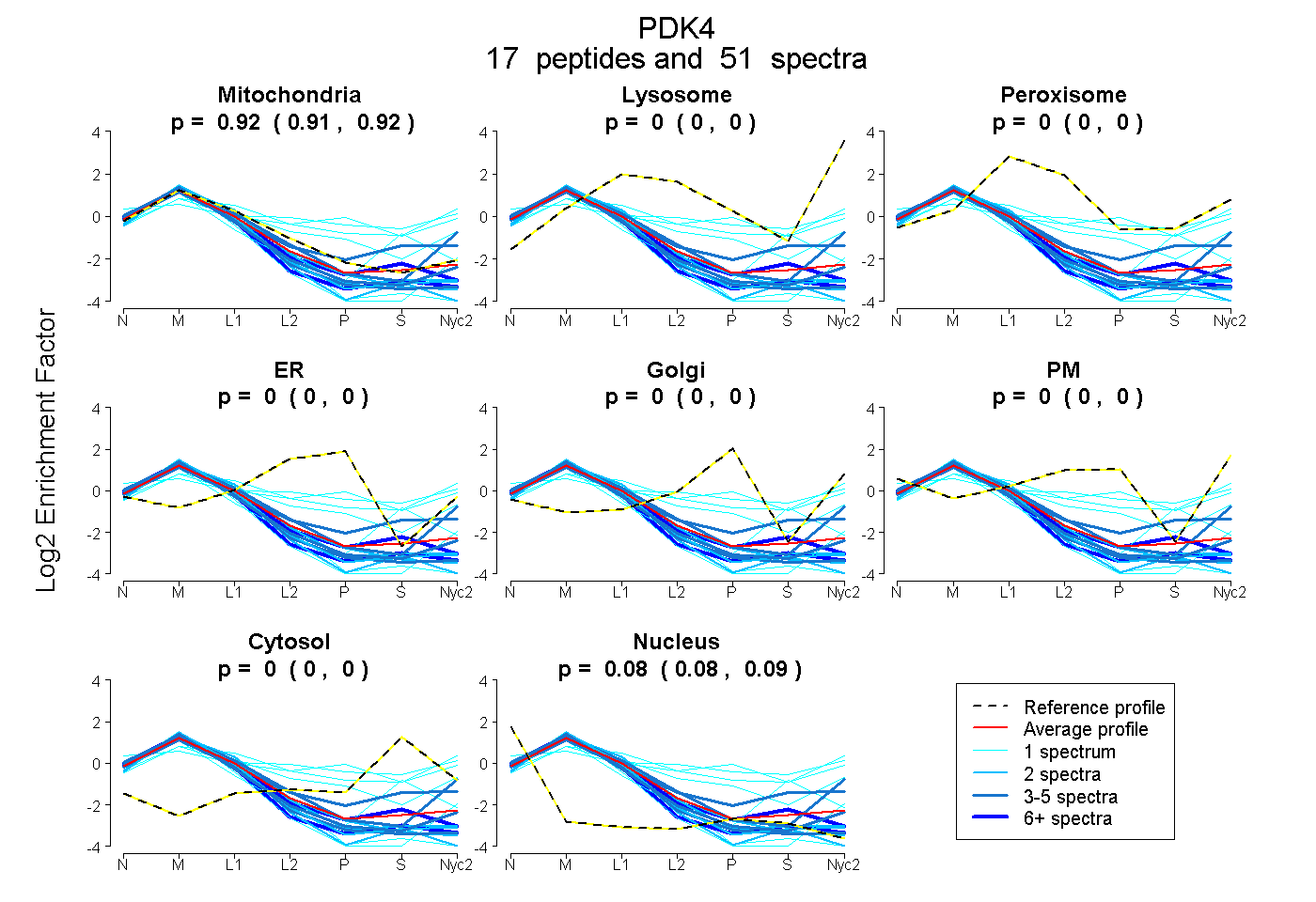
0.913 | 0.922
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.077 | 0.086
peptides
spectra
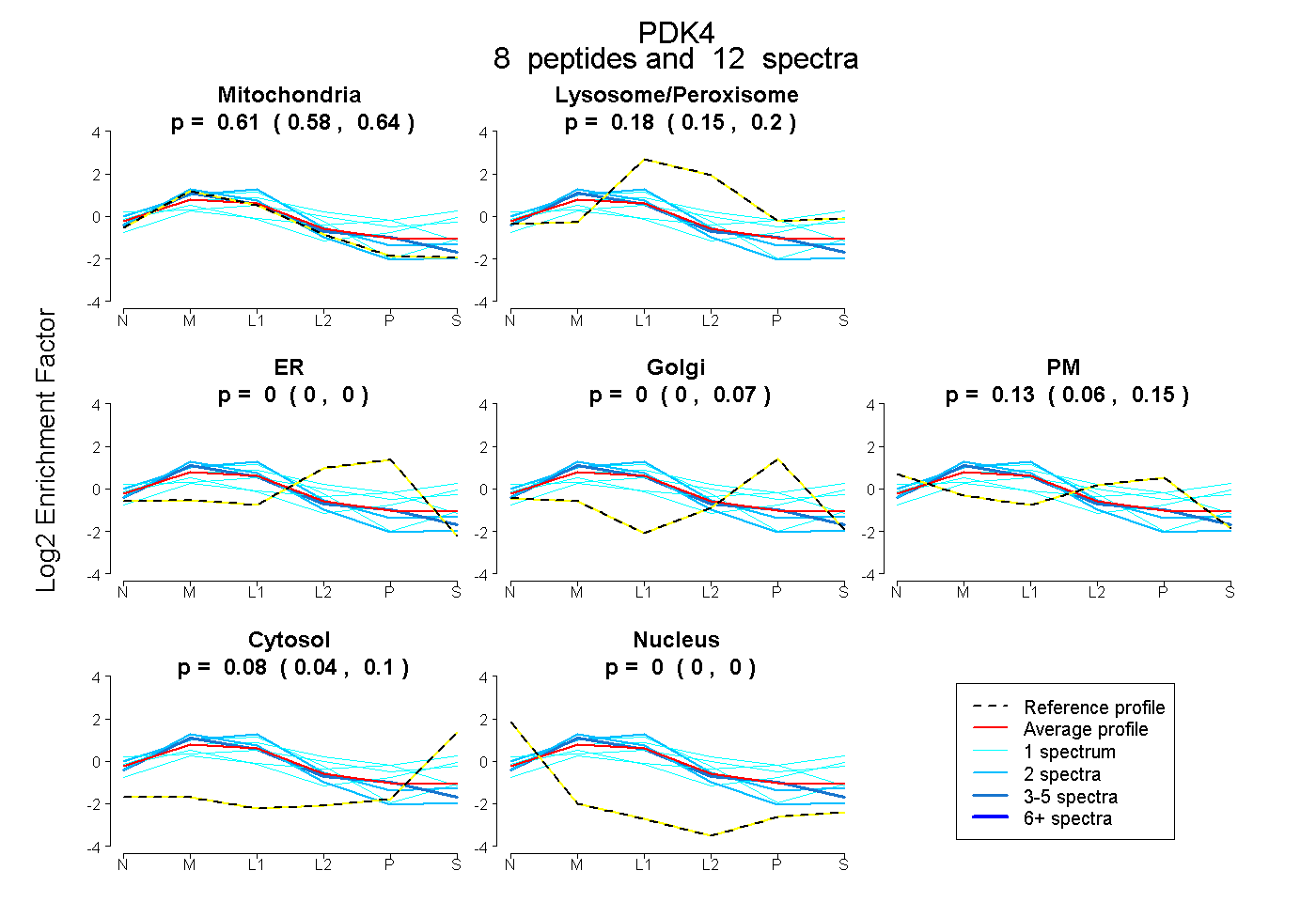
0.577 | 0.645
0.150 | 0.204
0.000 | 0.000
0.000 | 0.067
0.060 | 0.150
0.044 | 0.097
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
51 spectra |
 |
0.918 0.913 | 0.922 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.082 0.077 | 0.086 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
12 spectra |
 |
0.610 0.577 | 0.645 |
0.178 0.150 | 0.204 |
0.000 0.000 | 0.000 |
0.005 0.000 | 0.067 |
0.130 0.060 | 0.150 |
0.077 0.044 | 0.097 |
0.000 0.000 | 0.000 |
| 1 spectrum, LVNTPSVQLVK | 0.383 | 0.126 | 0.000 | 0.000 | 0.187 | 0.304 | 0.000 | |||
| 1 spectrum, TSFSFLR | 0.230 | 0.348 | 0.000 | 0.000 | 0.270 | 0.152 | 0.000 | |||
| 1 spectrum, EVELFSR | 0.379 | 0.351 | 0.000 | 0.110 | 0.160 | 0.000 | 0.000 | |||
| 1 spectrum, ALSDFVDTLVK | 0.734 | 0.244 | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | |||
| 1 spectrum, SASSLGNAGLVPR | 0.153 | 0.352 | 0.000 | 0.207 | 0.000 | 0.288 | 0.000 | |||
| 2 spectra, EIDILPER | 0.738 | 0.241 | 0.000 | 0.000 | 0.000 | 0.000 | 0.020 | |||
| 3 spectra, GGGVPLR | 0.758 | 0.108 | 0.000 | 0.134 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QELPVR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
154 spectra |
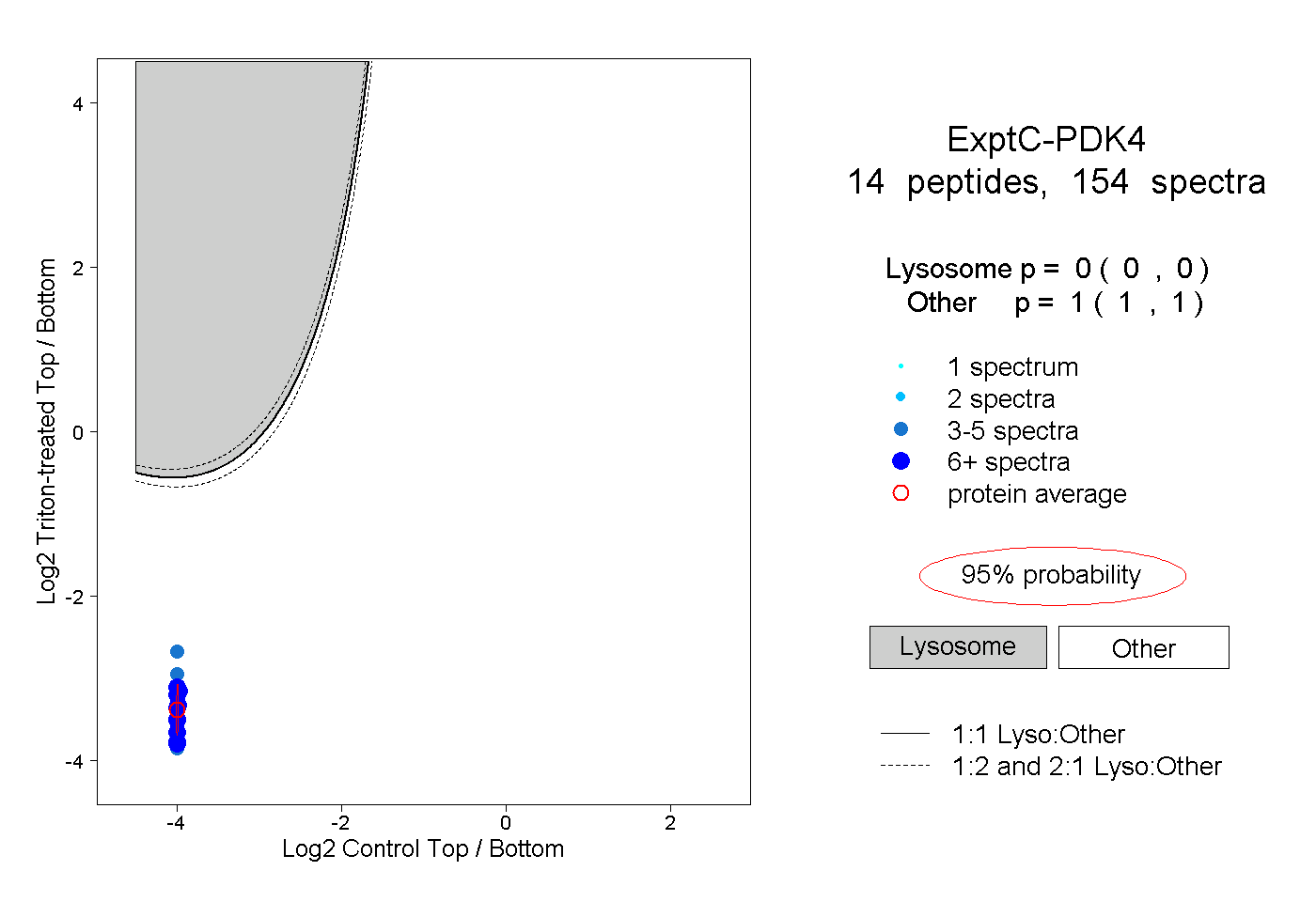 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
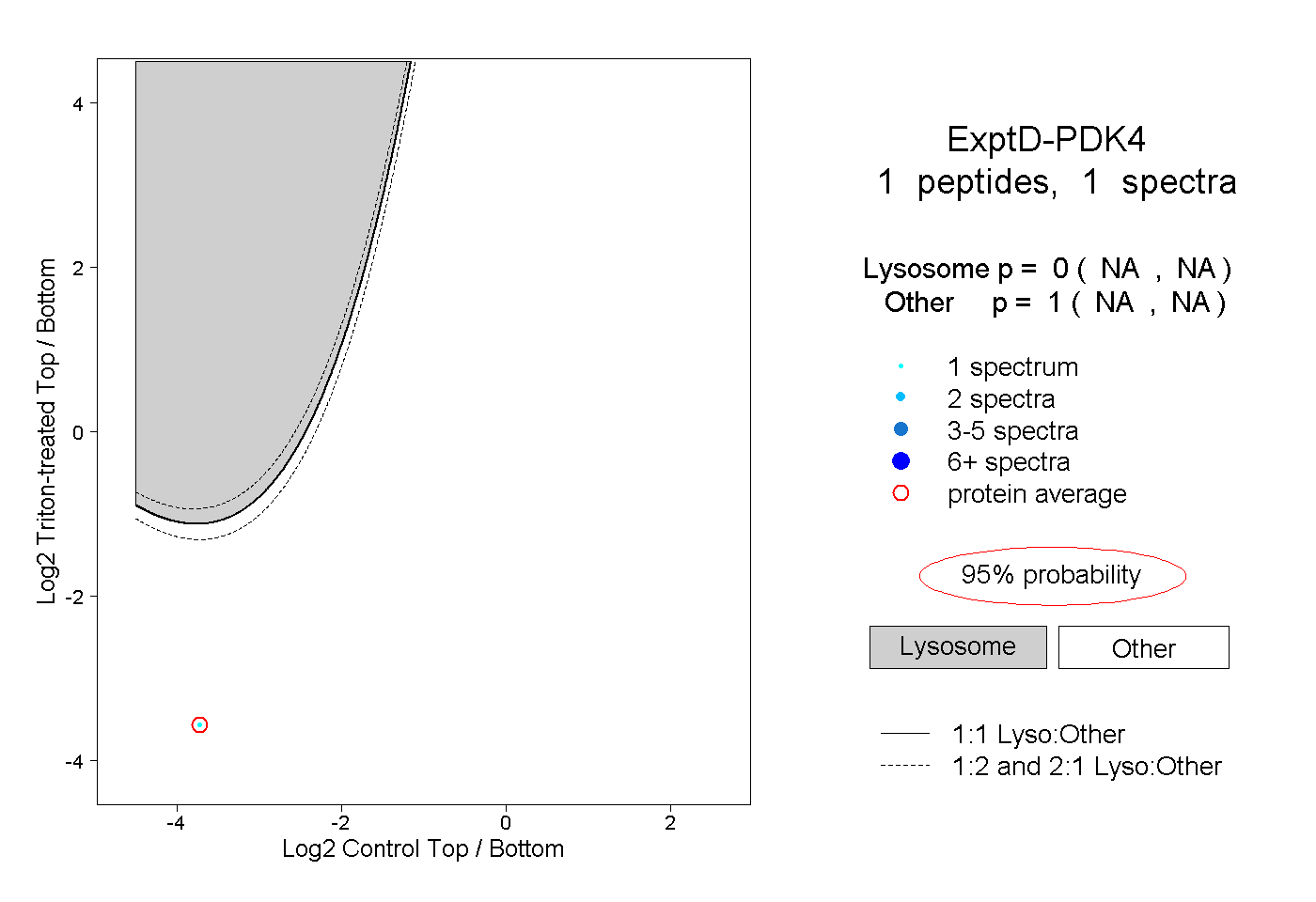 |
0.000 NA | NA |
1.000 NA | NA |