peptides
spectra
0.015 | 0.092
0.000 | 0.064
0.000 | 0.048
0.000 | 0.000
0.000 | 0.016
0.000 | 0.061
0.845 | 0.898
0.000 | 0.000
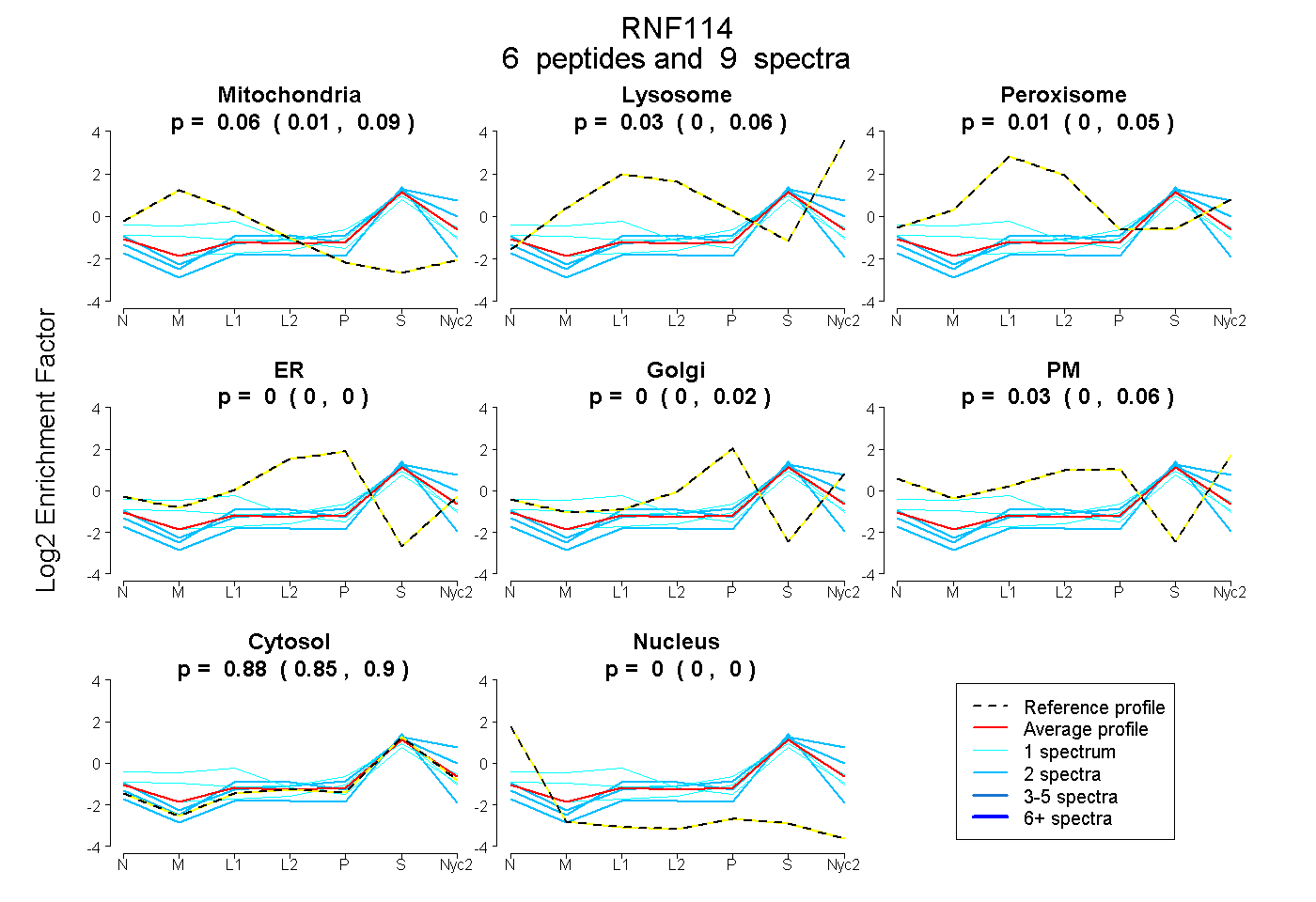
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.059 0.015 | 0.092 |
0.028 0.000 | 0.064 |
0.008 0.000 | 0.048 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.016 |
0.030 0.000 | 0.061 |
0.875 0.845 | 0.898 |
0.000 0.000 | 0.000 |
| 2 spectra, NFDQEGLVEHCK | 0.000 | 0.180 | 0.000 | 0.000 | 0.000 | 0.000 | 0.820 | 0.000 | ||
| 1 spectrum, SALAPGVR | 0.273 | 0.000 | 0.143 | 0.000 | 0.000 | 0.000 | 0.583 | 0.000 | ||
| 1 spectrum, SANFMEHIQR | 0.114 | 0.058 | 0.018 | 0.000 | 0.098 | 0.000 | 0.711 | 0.000 | ||
| 2 spectra, KPVCGVCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.909 | 0.091 | ||
| 2 spectra, DFVLSK | 0.000 | 0.047 | 0.000 | 0.000 | 0.000 | 0.090 | 0.863 | 0.000 | ||
| 1 spectrum, DASLQQR | 0.040 | 0.000 | 0.000 | 0.000 | 0.031 | 0.000 | 0.891 | 0.037 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
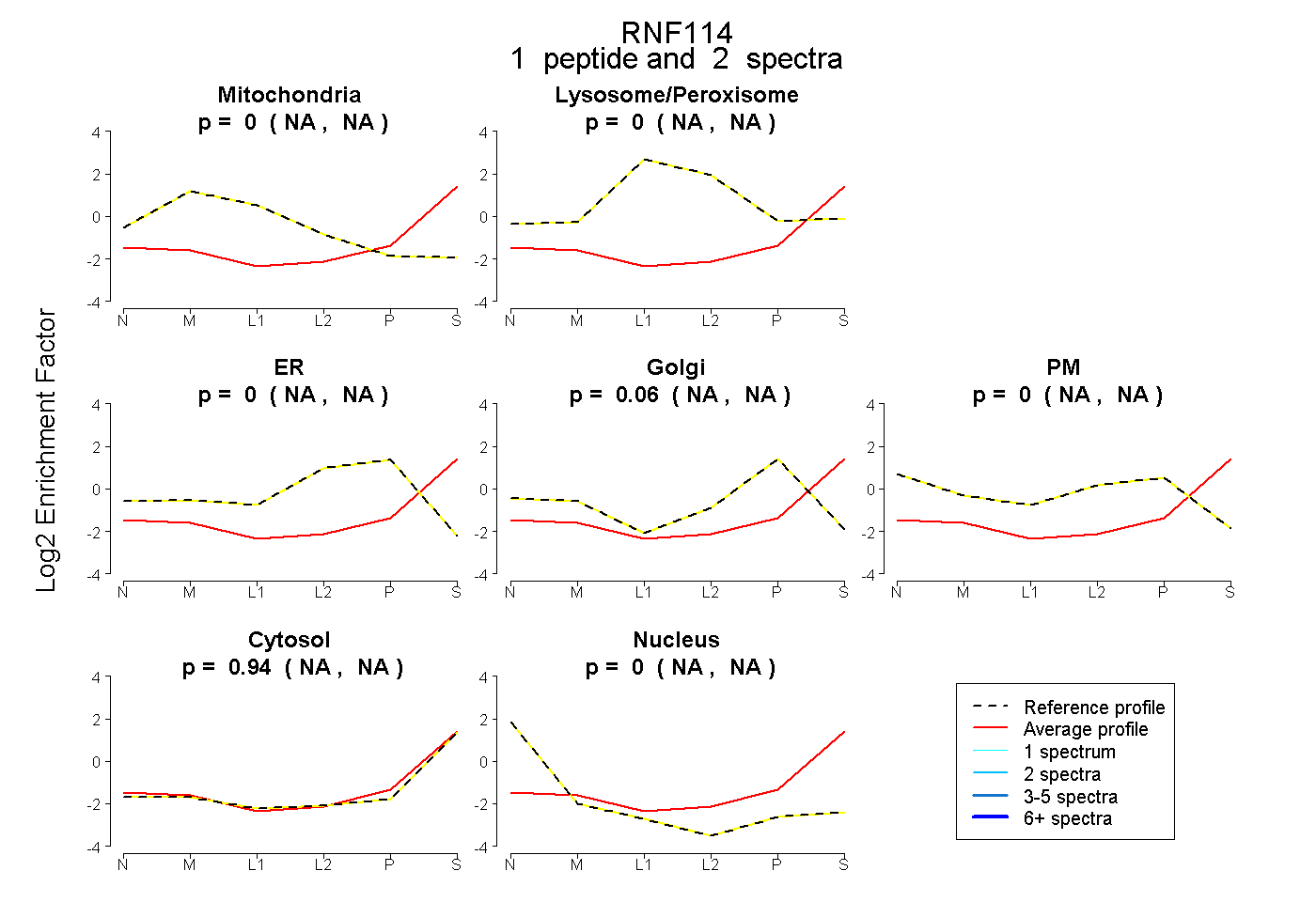 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.058 NA | NA |
0.000 NA | NA |
0.942 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
8 spectra |
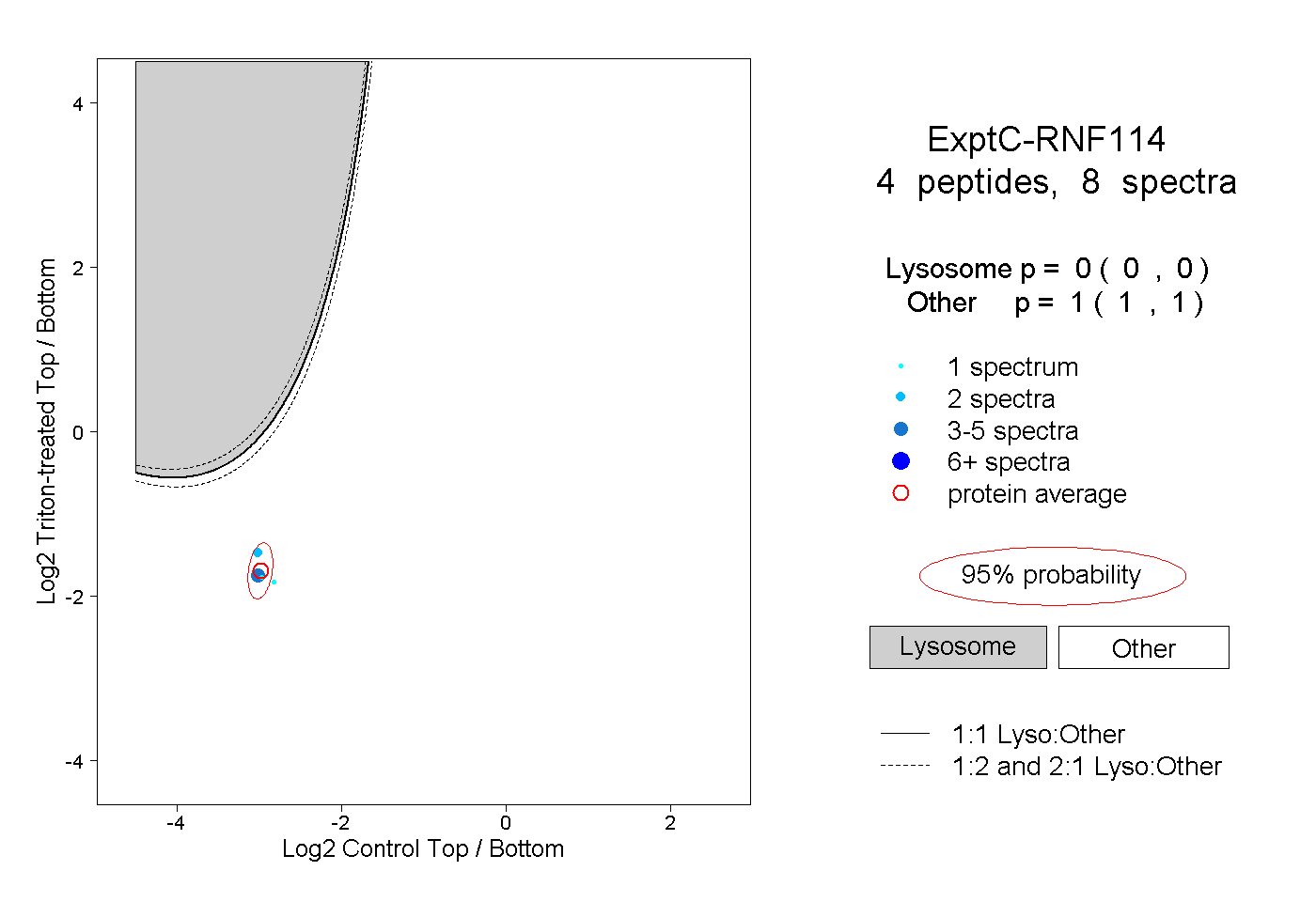 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |