peptides
spectra
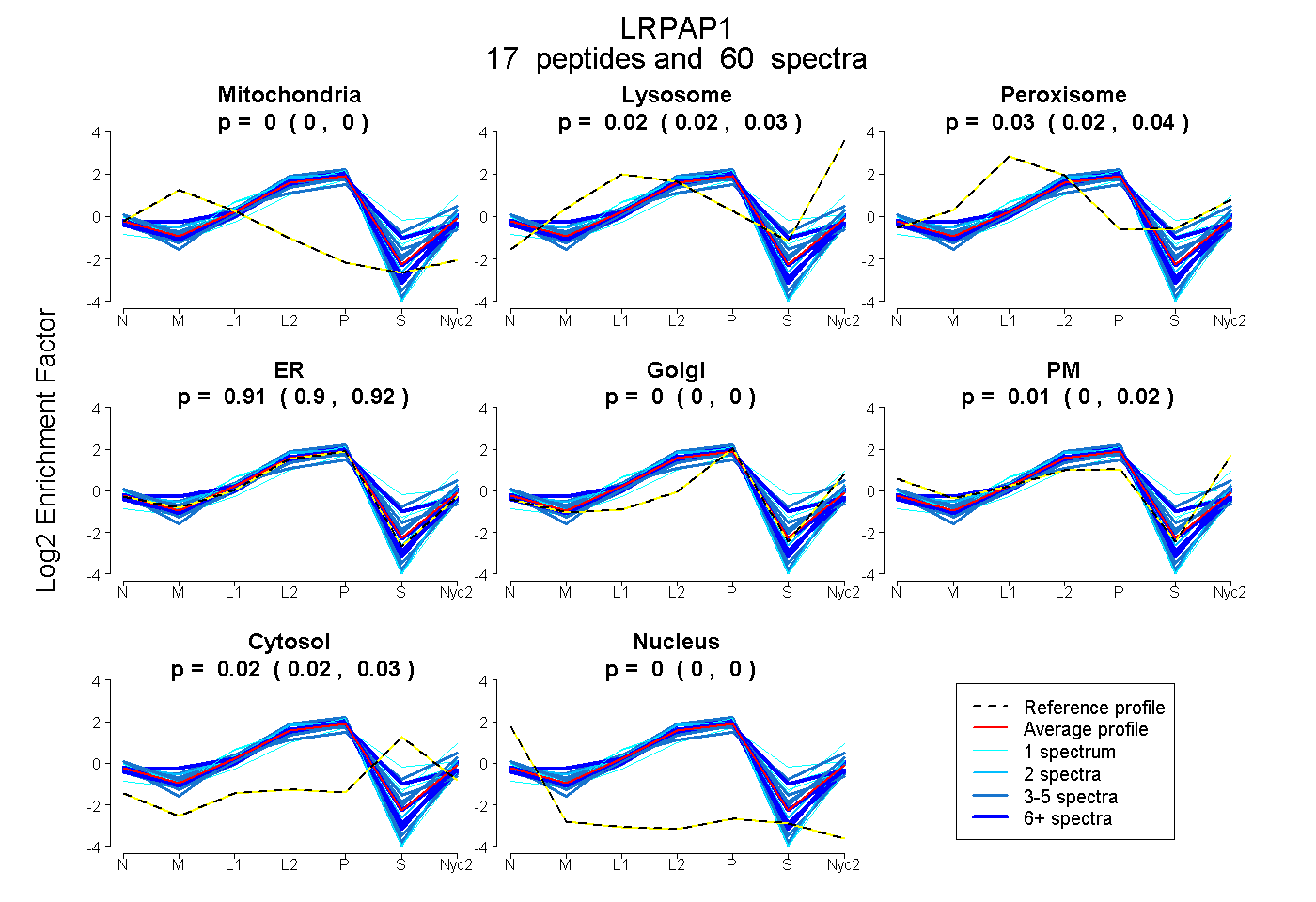
0.000 | 0.000
0.017 | 0.030
0.024 | 0.038
0.901 | 0.917
0.000 | 0.000
0.001 | 0.020
0.017 | 0.028
0.000 | 0.000
peptides
spectra
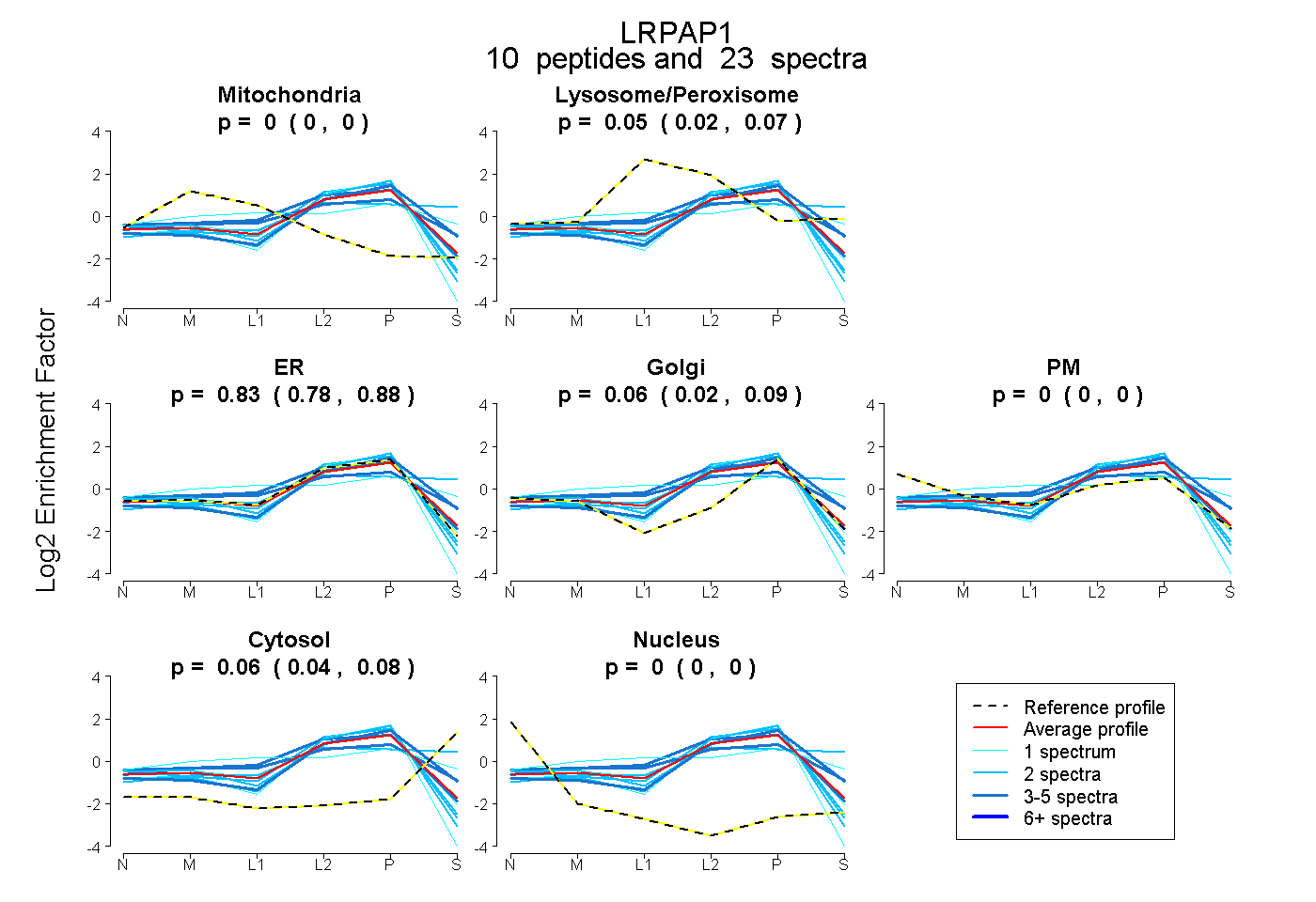
0.000 | 0.000
0.023 | 0.071
0.778 | 0.877
0.023 | 0.090
0.000 | 0.000
0.039 | 0.075
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
60 spectra |
 |
0.000 0.000 | 0.000 |
0.024 0.017 | 0.030 |
0.032 0.024 | 0.038 |
0.910 0.901 | 0.917 |
0.000 0.000 | 0.000 |
0.011 0.001 | 0.020 |
0.023 0.017 | 0.028 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.049 0.023 | 0.071 |
0.832 0.778 | 0.877 |
0.061 0.023 | 0.090 |
0.000 0.000 | 0.000 |
0.059 0.039 | 0.075 |
0.000 0.000 | 0.000 |
| 1 spectrum, ESGEEFR | 0.000 | 0.000 | 0.935 | 0.065 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EFLHYK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SINQGLDR | 0.000 | 0.000 | 0.863 | 0.137 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YVLLEEK | 0.000 | 0.000 | 0.829 | 0.000 | 0.000 | 0.171 | 0.000 | |||
| 2 spectra, IHEYNVLLDTLSR | 0.000 | 0.268 | 0.393 | 0.000 | 0.000 | 0.339 | 0.000 | |||
| 5 spectra, LNQLWEK | 0.000 | 0.313 | 0.299 | 0.302 | 0.000 | 0.087 | 0.000 | |||
| 2 spectra, LAELHSDLK | 0.000 | 0.000 | 0.899 | 0.101 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VSHQGYGPATEFEEPR | 0.005 | 0.468 | 0.000 | 0.436 | 0.000 | 0.090 | 0.000 | |||
| 1 spectrum, DTQTVHSNALNEDTQDELGDPR | 0.000 | 0.028 | 0.856 | 0.077 | 0.039 | 0.000 | 0.000 | |||
| 3 spectra, HIQDLSSR | 0.000 | 0.146 | 0.791 | 0.000 | 0.063 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
99 spectra |
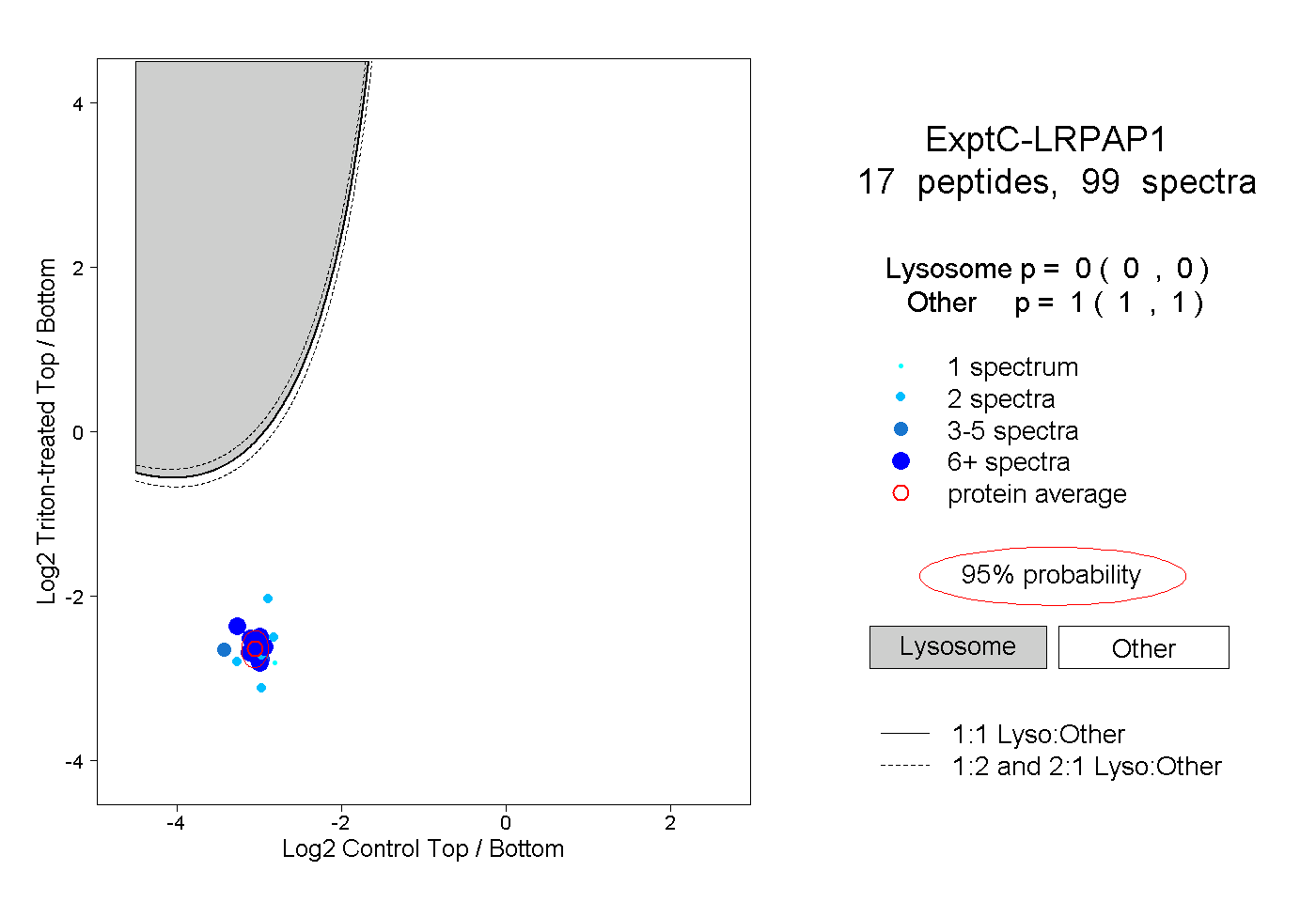 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
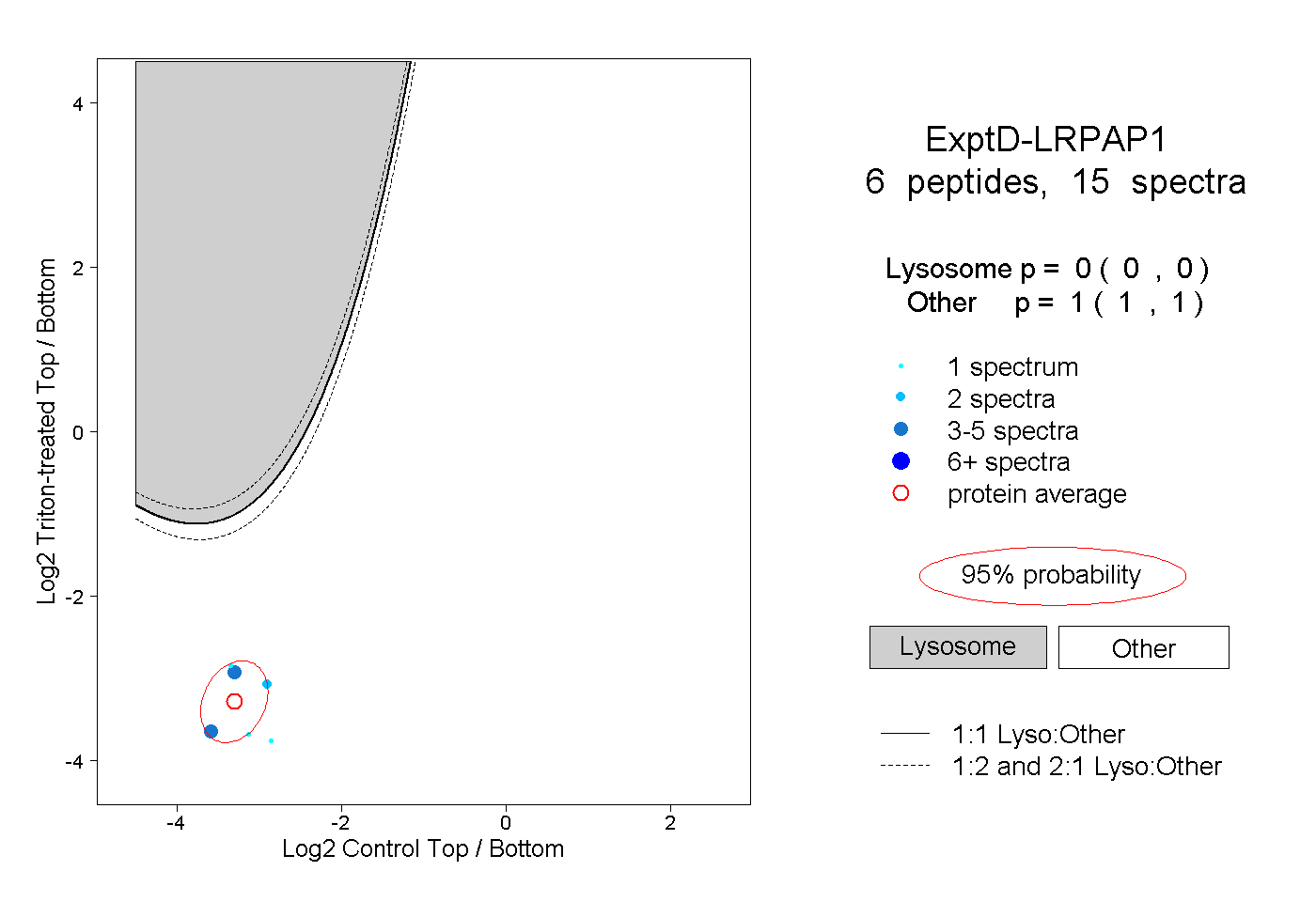 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |