peptides
spectra
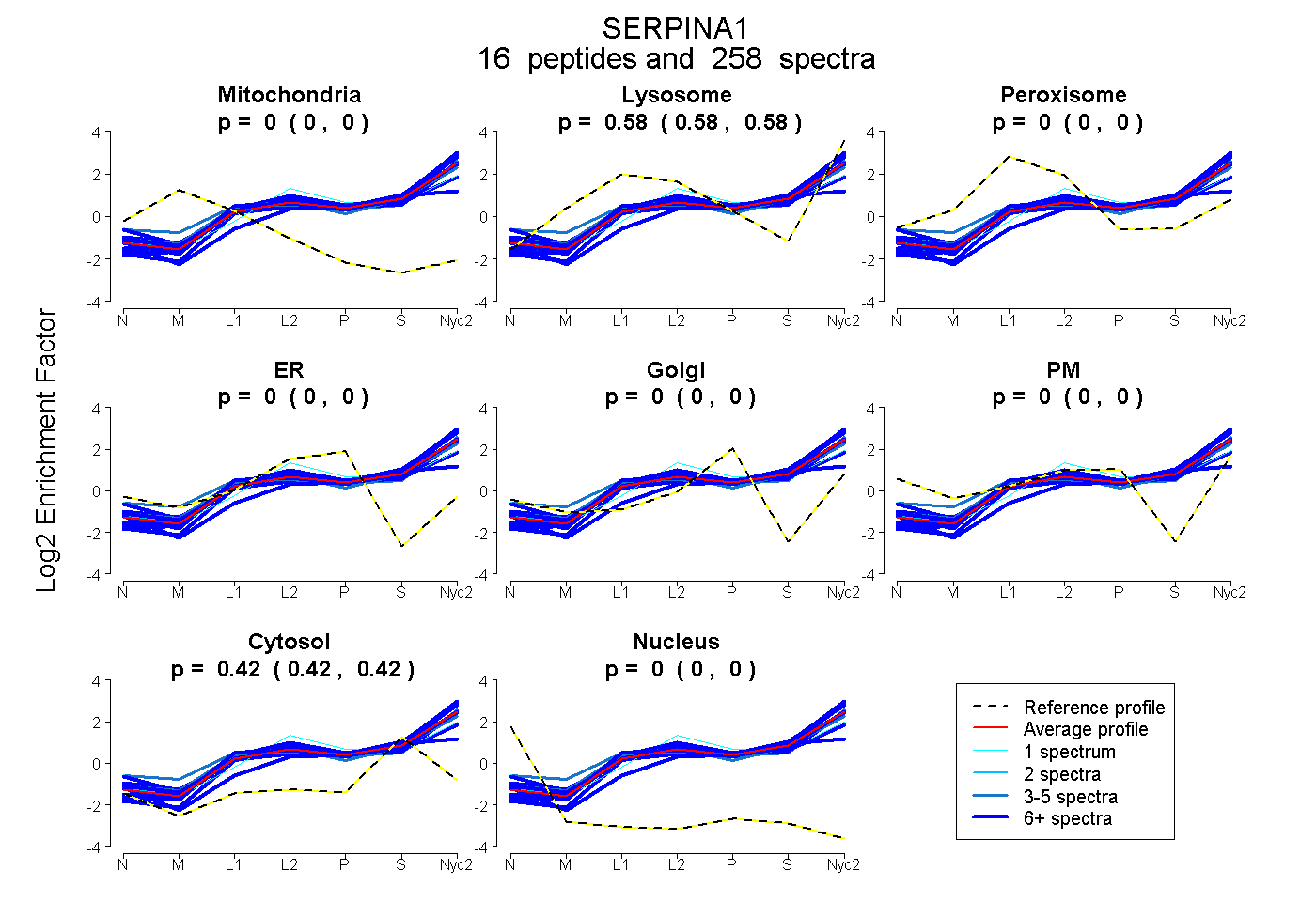
0.000 | 0.000
0.579 | 0.581
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.419 | 0.421
0.000 | 0.000
peptides
spectra
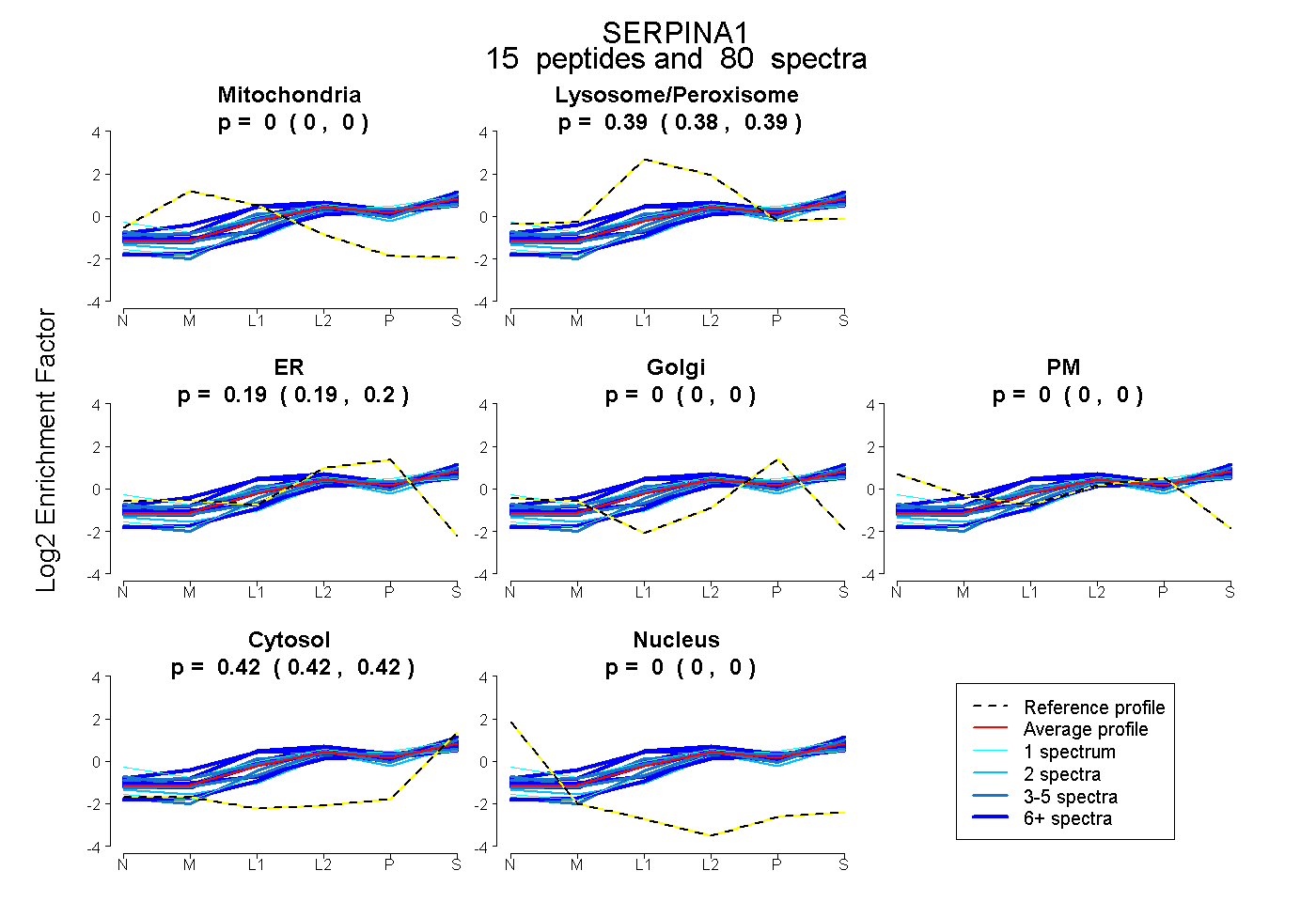
0.000 | 0.000
0.383 | 0.393
0.188 | 0.196
0.000 | 0.000
0.000 | 0.000
0.417 | 0.421
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
258 spectra |
 |
0.000 0.000 | 0.000 |
0.580 0.579 | 0.581 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.420 0.419 | 0.421 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
80 spectra |
 |
0.000 0.000 | 0.000 |
0.388 0.383 | 0.393 |
0.193 0.188 | 0.196 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.419 0.417 | 0.421 |
0.000 0.000 | 0.000 |
| 13 spectra, DADFHVDK | 0.000 | 0.528 | 0.127 | 0.052 | 0.000 | 0.293 | 0.000 | |||
| 2 spectra, MQHLEQTLTK | 0.000 | 0.555 | 0.000 | 0.091 | 0.000 | 0.354 | 0.000 | |||
| 3 spectra, VINDYVEK | 0.000 | 0.420 | 0.125 | 0.133 | 0.000 | 0.322 | 0.000 | |||
| 3 spectra, SAILYFPK | 0.000 | 0.494 | 0.000 | 0.139 | 0.000 | 0.367 | 0.000 | |||
| 7 spectra, LSQAVHK | 0.000 | 0.447 | 0.154 | 0.000 | 0.000 | 0.399 | 0.000 | |||
| 6 spectra, VIDPTR | 0.000 | 0.264 | 0.277 | 0.000 | 0.000 | 0.459 | 0.000 | |||
| 3 spectra, FLEEVK | 0.000 | 0.351 | 0.162 | 0.000 | 0.000 | 0.488 | 0.000 | |||
| 3 spectra, VPMMNR | 0.000 | 0.330 | 0.188 | 0.000 | 0.000 | 0.482 | 0.000 | |||
| 8 spectra, AVLTLDER | 0.000 | 0.415 | 0.166 | 0.015 | 0.000 | 0.405 | 0.000 | |||
| 2 spectra, ISSNLADFAFSLYR | 0.000 | 0.242 | 0.221 | 0.000 | 0.000 | 0.537 | 0.000 | |||
| 1 spectrum, VFNNDADLSGITEDAPLK | 0.000 | 0.499 | 0.000 | 0.235 | 0.022 | 0.245 | 0.000 | |||
| 8 spectra, RPFNPEHTR | 0.000 | 0.564 | 0.000 | 0.181 | 0.000 | 0.255 | 0.000 | |||
| 7 spectra, IVDLMK | 0.000 | 0.268 | 0.182 | 0.000 | 0.000 | 0.550 | 0.000 | |||
| 1 spectrum, LSISGTYNLK | 0.000 | 0.263 | 0.258 | 0.000 | 0.000 | 0.478 | 0.000 | |||
| 13 spectra, TLLSSLGITR | 0.000 | 0.402 | 0.162 | 0.000 | 0.000 | 0.436 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
611 spectra |
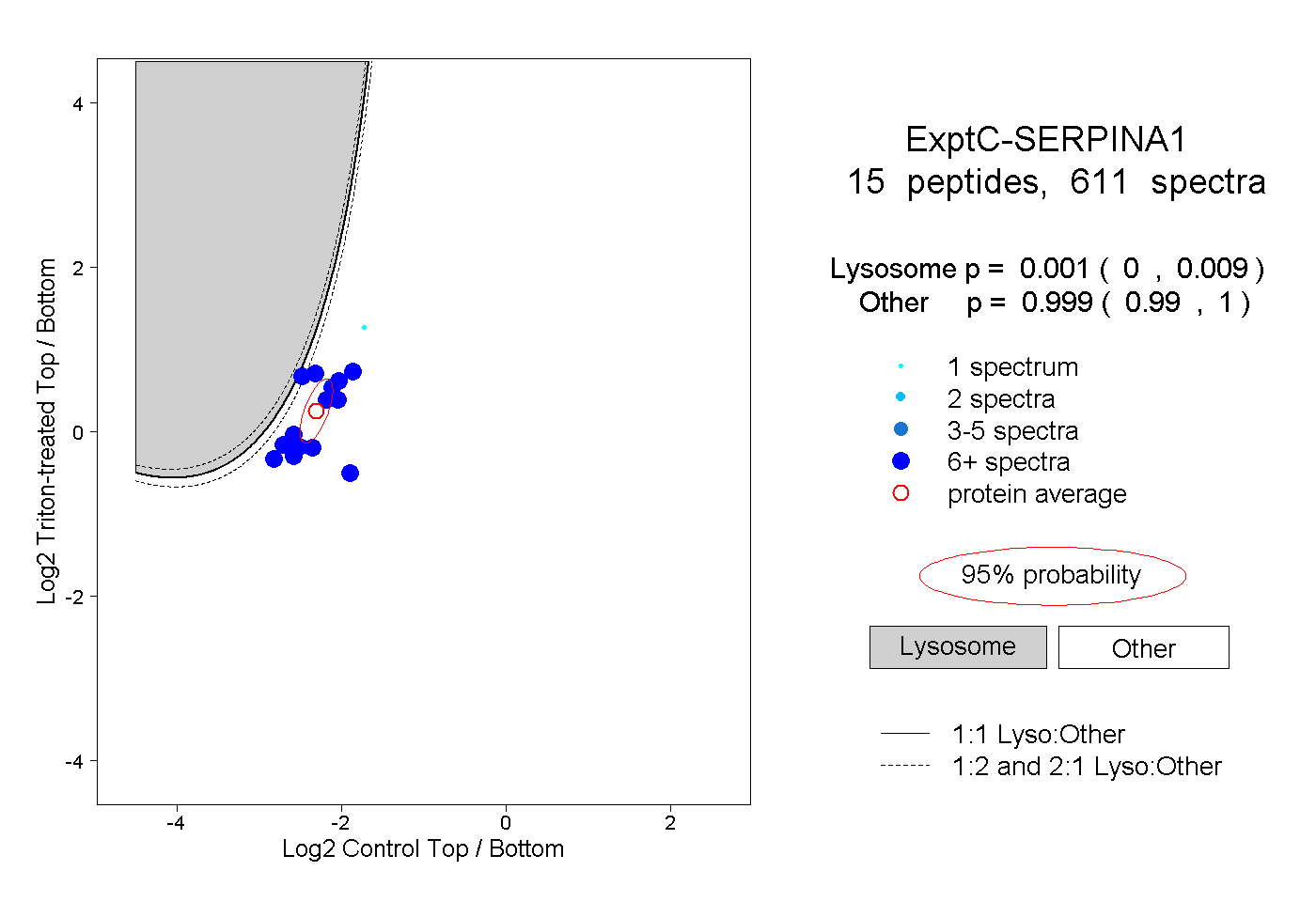 |
0.001 0.000 | 0.009 |
0.999 0.990 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
59 spectra |
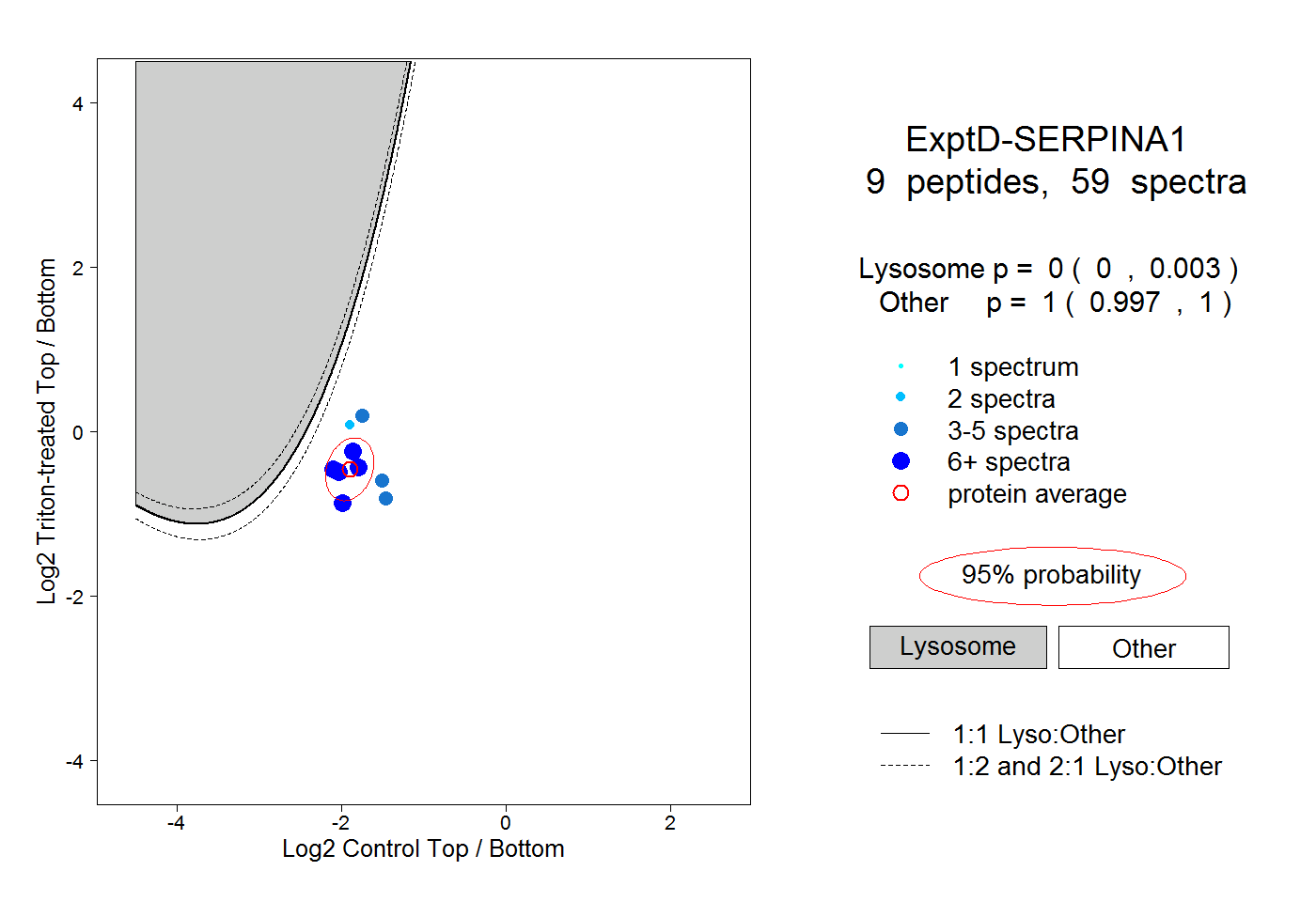 |
0.000 0.000 | 0.003 |
1.000 0.997 | 1.000 |