peptides
spectra
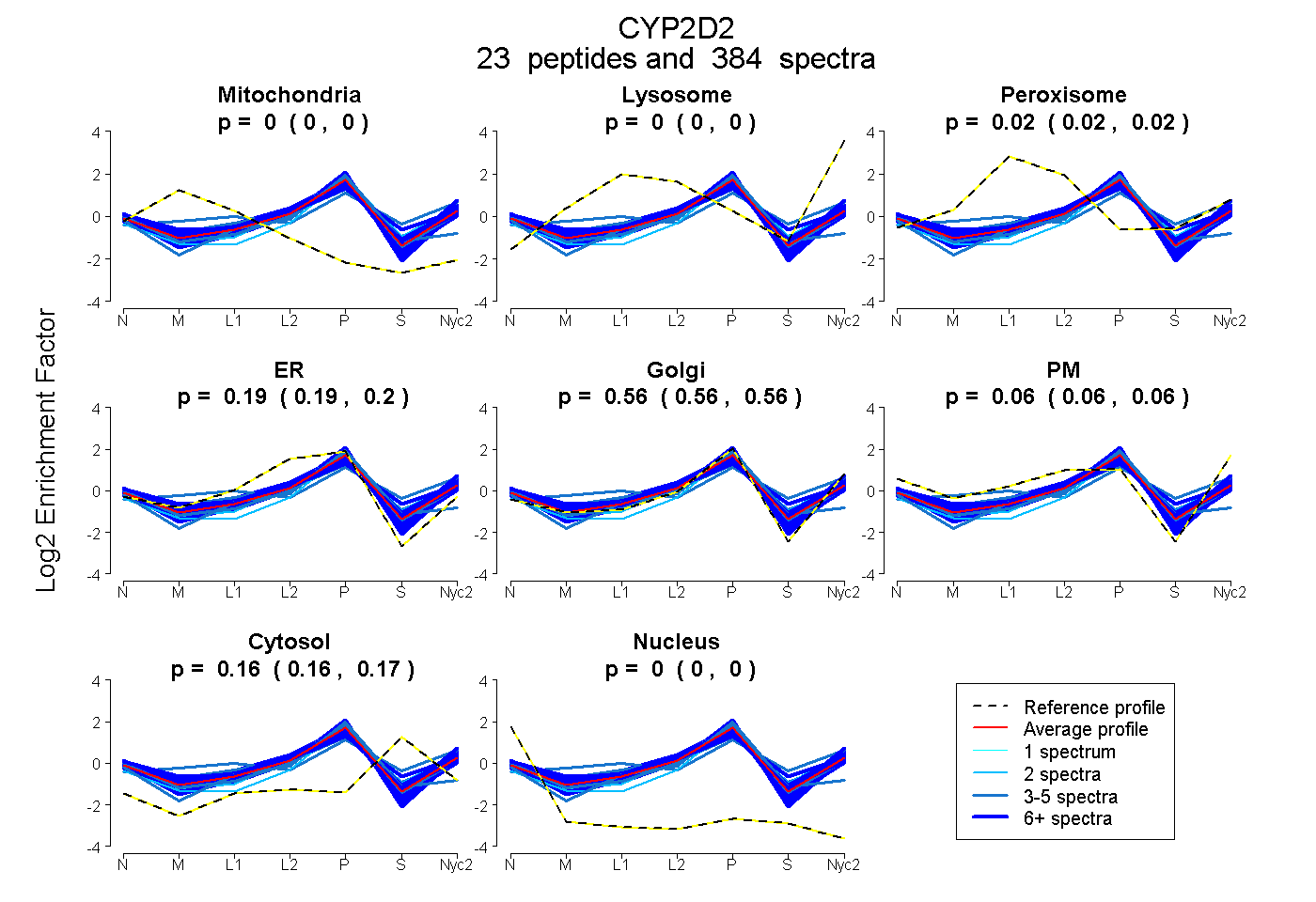
0.000 | 0.000
0.000 | 0.000
0.019 | 0.022
0.191 | 0.195
0.556 | 0.564
0.059 | 0.064
0.163 | 0.165
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
384 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.021 0.019 | 0.022 |
0.193 0.191 | 0.195 |
0.560 0.556 | 0.564 |
0.061 0.059 | 0.064 |
0.164 0.163 | 0.165 |
0.000 0.000 | 0.000 |
| 14 spectra, VHEEIDEVIGQVR | 0.021 | 0.000 | 0.025 | 0.218 | 0.371 | 0.166 | 0.198 | 0.000 | ||
| 31 spectra, HEAFMPFSAGR | 0.000 | 0.000 | 0.085 | 0.127 | 0.386 | 0.141 | 0.260 | 0.000 | ||
| 10 spectra, FHPEHFLDAQGNFVK | 0.000 | 0.000 | 0.035 | 0.295 | 0.519 | 0.025 | 0.102 | 0.023 | ||
| 4 spectra, FADIVPTNIPHMTSR | 0.000 | 0.071 | 0.211 | 0.000 | 0.488 | 0.000 | 0.229 | 0.000 | ||
| 57 spectra, RPEMADQAR | 0.000 | 0.000 | 0.038 | 0.218 | 0.338 | 0.205 | 0.202 | 0.000 | ||
| 12 spectra, DFGVGK | 0.000 | 0.000 | 0.014 | 0.270 | 0.423 | 0.195 | 0.098 | 0.000 | ||
| 11 spectra, DETVWEKPLR | 0.000 | 0.000 | 0.061 | 0.047 | 0.697 | 0.042 | 0.153 | 0.000 | ||
| 35 spectra, DMTDAFLAEMQK | 0.000 | 0.000 | 0.051 | 0.157 | 0.625 | 0.000 | 0.167 | 0.000 | ||
| 11 spectra, MLIEHK | 0.000 | 0.000 | 0.000 | 0.170 | 0.693 | 0.000 | 0.137 | 0.000 | ||
| 8 spectra, LNSFIALVDK | 0.000 | 0.000 | 0.085 | 0.035 | 0.619 | 0.170 | 0.091 | 0.000 | ||
| 17 spectra, GVVLAPYGPEWR | 0.000 | 0.000 | 0.000 | 0.233 | 0.555 | 0.060 | 0.152 | 0.000 | ||
| 40 spectra, FSVSTLR | 0.000 | 0.000 | 0.000 | 0.173 | 0.729 | 0.000 | 0.082 | 0.015 | ||
| 2 spectra, FQGFLIPK | 0.000 | 0.000 | 0.000 | 0.162 | 0.681 | 0.013 | 0.144 | 0.000 | ||
| 3 spectra, SLEQWVTEEAGHLCDTFAK | 0.000 | 0.000 | 0.000 | 0.405 | 0.312 | 0.000 | 0.246 | 0.037 | ||
| 25 spectra, ACLGEPLAR | 0.000 | 0.000 | 0.028 | 0.277 | 0.501 | 0.000 | 0.194 | 0.000 | ||
| 23 spectra, GNPESSFNDENLR | 0.000 | 0.000 | 0.000 | 0.216 | 0.647 | 0.000 | 0.113 | 0.024 | ||
| 2 spectra, GTTLIPNLSSVLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.770 | 0.000 | 0.230 | 0.000 | ||
| 7 spectra, DETVWEKPHR | 0.000 | 0.000 | 0.000 | 0.216 | 0.473 | 0.123 | 0.188 | 0.000 | ||
| 11 spectra, FEYEDPFFNR | 0.000 | 0.000 | 0.000 | 0.160 | 0.722 | 0.000 | 0.115 | 0.003 | ||
| 41 spectra, MPFTNAVIHEVQR | 0.000 | 0.000 | 0.064 | 0.129 | 0.623 | 0.045 | 0.139 | 0.000 | ||
| 4 spectra, EAEHPFNPSILLSK | 0.000 | 0.000 | 0.149 | 0.127 | 0.484 | 0.034 | 0.205 | 0.000 | ||
| 4 spectra, SWDPAQPPR | 0.000 | 0.000 | 0.000 | 0.189 | 0.645 | 0.000 | 0.164 | 0.001 | ||
| 12 spectra, AVSNVIASLVYAR | 0.000 | 0.000 | 0.000 | 0.151 | 0.773 | 0.000 | 0.040 | 0.036 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
204 spectra |
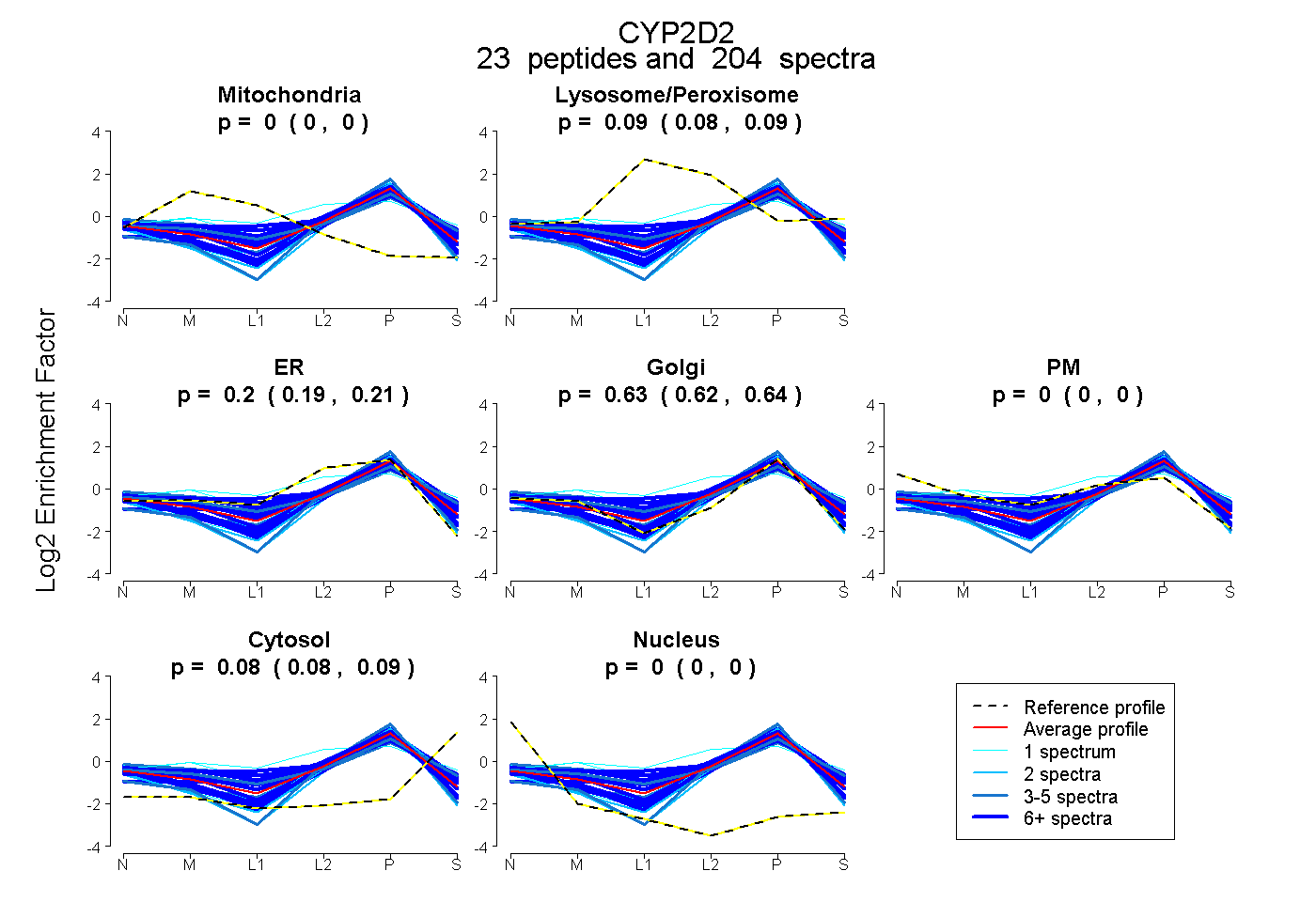 |
0.000 0.000 | 0.000 |
0.088 0.082 | 0.093 |
0.197 0.186 | 0.205 |
0.632 0.625 | 0.639 |
0.000 0.000 | 0.000 |
0.083 0.080 | 0.086 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
500 spectra |
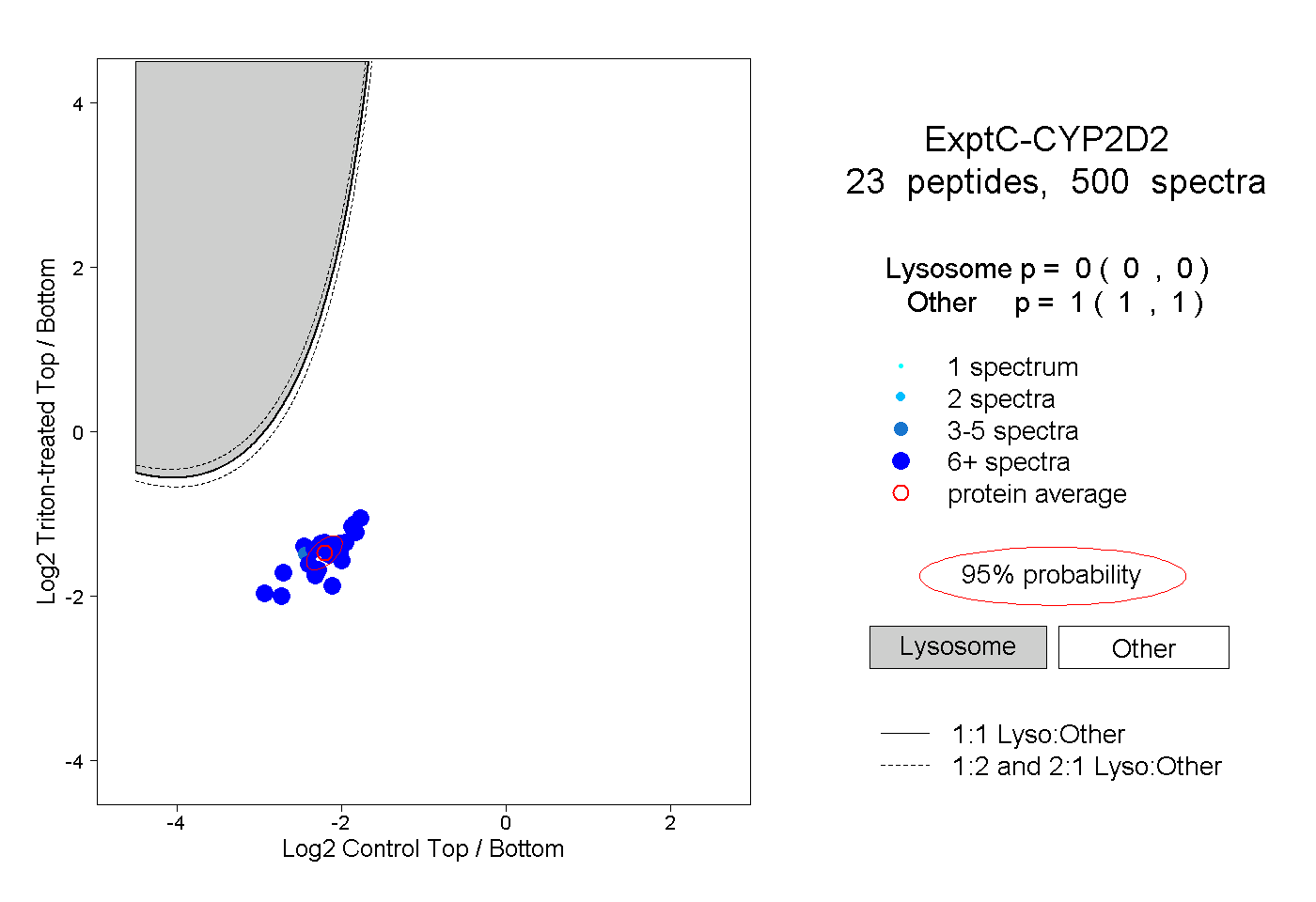 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
35 spectra |
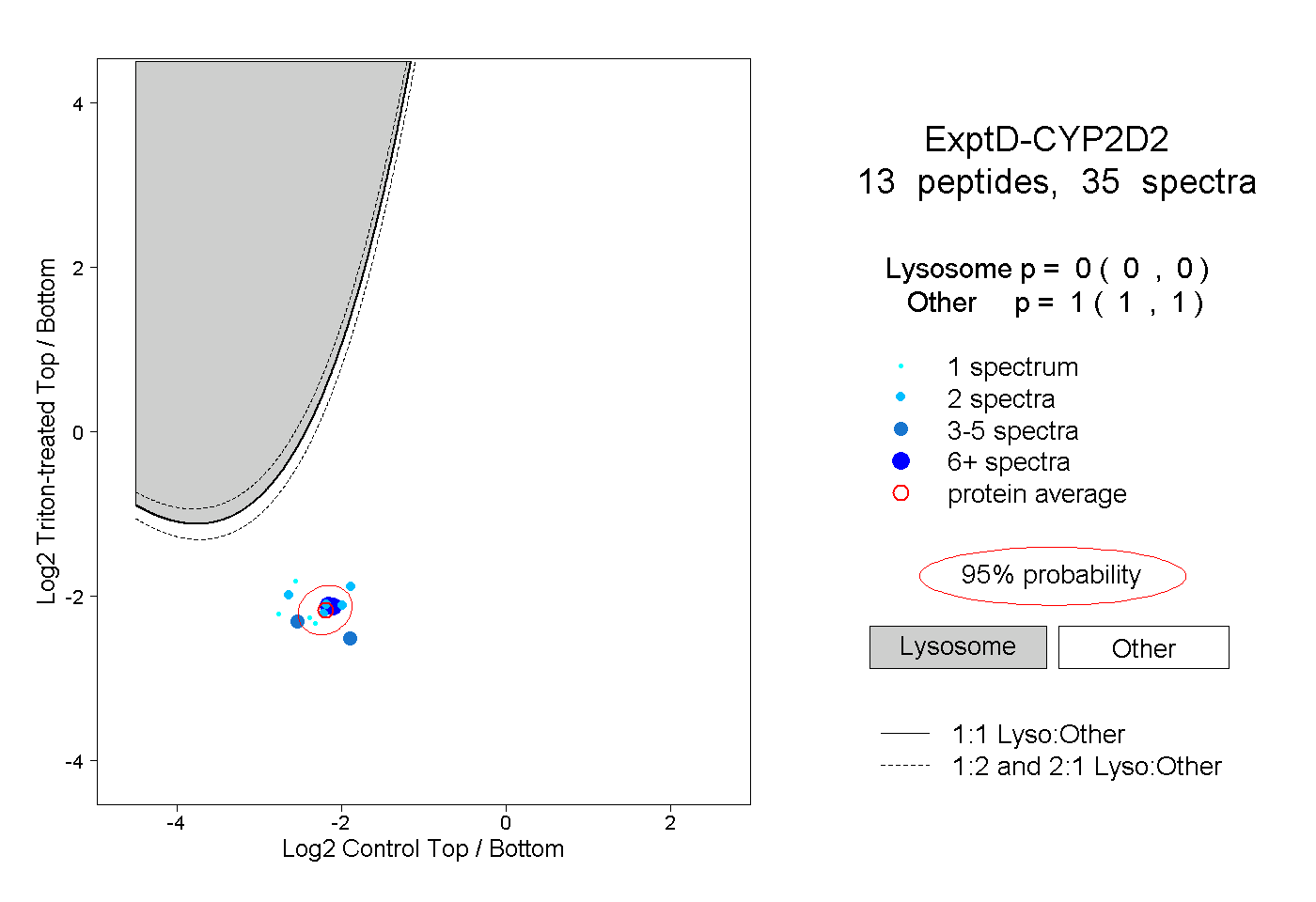 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |