peptides
spectra
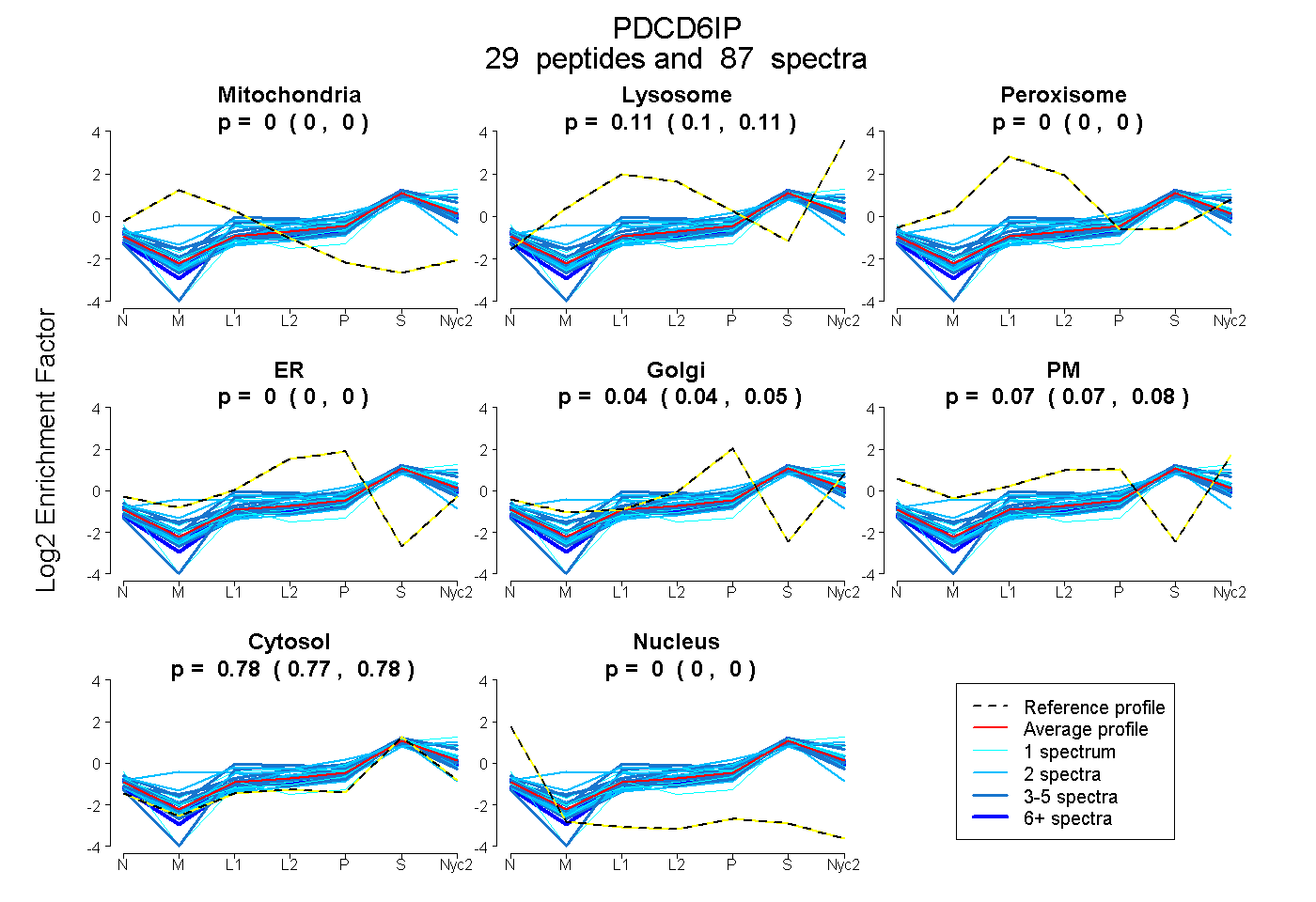
0.000 | 0.000
0.102 | 0.109
0.000 | 0.000
0.000 | 0.000
0.039 | 0.049
0.067 | 0.078
0.774 | 0.778
0.000 | 0.000
peptides
spectra
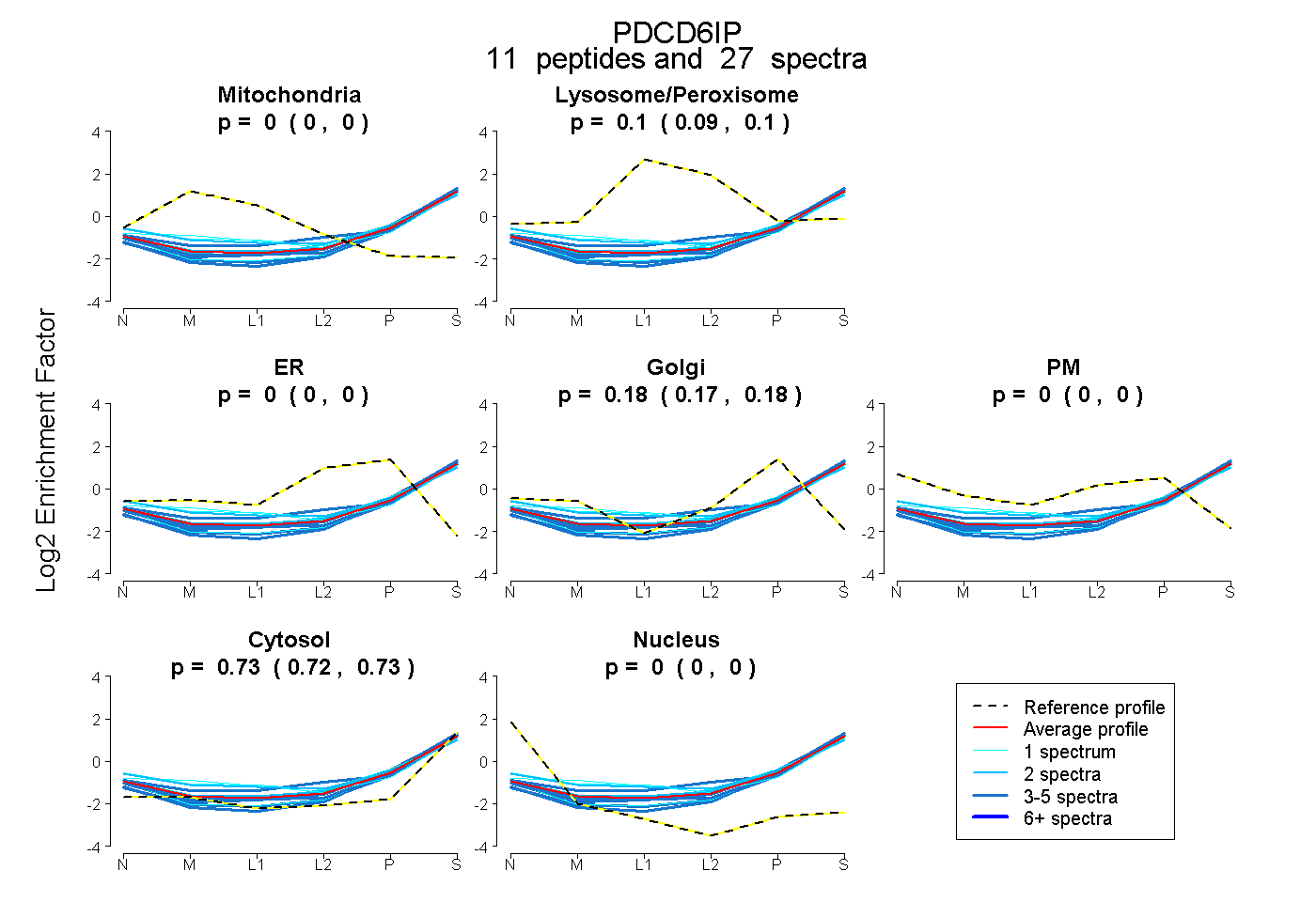
0.000 | 0.000
0.090 | 0.103
0.000 | 0.000
0.172 | 0.181
0.000 | 0.000
0.722 | 0.730
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
87 spectra |
 |
0.000 0.000 | 0.000 |
0.106 0.102 | 0.109 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.045 0.039 | 0.049 |
0.073 0.067 | 0.078 |
0.776 0.774 | 0.778 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.097 0.090 | 0.103 |
0.000 0.000 | 0.000 |
0.177 0.172 | 0.181 |
0.000 0.000 | 0.000 |
0.726 0.722 | 0.730 |
0.000 0.000 | 0.000 |
| 1 spectrum, LALASLGYEK | 0.000 | 0.161 | 0.000 | 0.053 | 0.107 | 0.679 | 0.000 | |||
| 4 spectra, DTVLSALSR | 0.000 | 0.005 | 0.000 | 0.159 | 0.000 | 0.836 | 0.000 | |||
| 2 spectra, YYDQICSIEPK | 0.000 | 0.150 | 0.000 | 0.077 | 0.144 | 0.630 | 0.000 | |||
| 3 spectra, FTDLFEK | 0.000 | 0.069 | 0.000 | 0.163 | 0.000 | 0.768 | 0.000 | |||
| 2 spectra, FYNELTEILVR | 0.000 | 0.114 | 0.000 | 0.167 | 0.000 | 0.718 | 0.000 | |||
| 1 spectrum, TMQGSEVVNVLK | 0.000 | 0.160 | 0.000 | 0.112 | 0.128 | 0.600 | 0.000 | |||
| 1 spectrum, ELPELLQR | 0.000 | 0.018 | 0.000 | 0.184 | 0.000 | 0.798 | 0.000 | |||
| 3 spectra, DNDFIYHDR | 0.000 | 0.195 | 0.000 | 0.120 | 0.015 | 0.670 | 0.000 | |||
| 4 spectra, EILEESLR | 0.000 | 0.000 | 0.000 | 0.181 | 0.000 | 0.819 | 0.000 | |||
| 2 spectra, CSDIVFAR | 0.000 | 0.088 | 0.000 | 0.208 | 0.000 | 0.704 | 0.000 | |||
| 4 spectra, DLQQSIAR | 0.000 | 0.075 | 0.000 | 0.189 | 0.000 | 0.736 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
204 spectra |
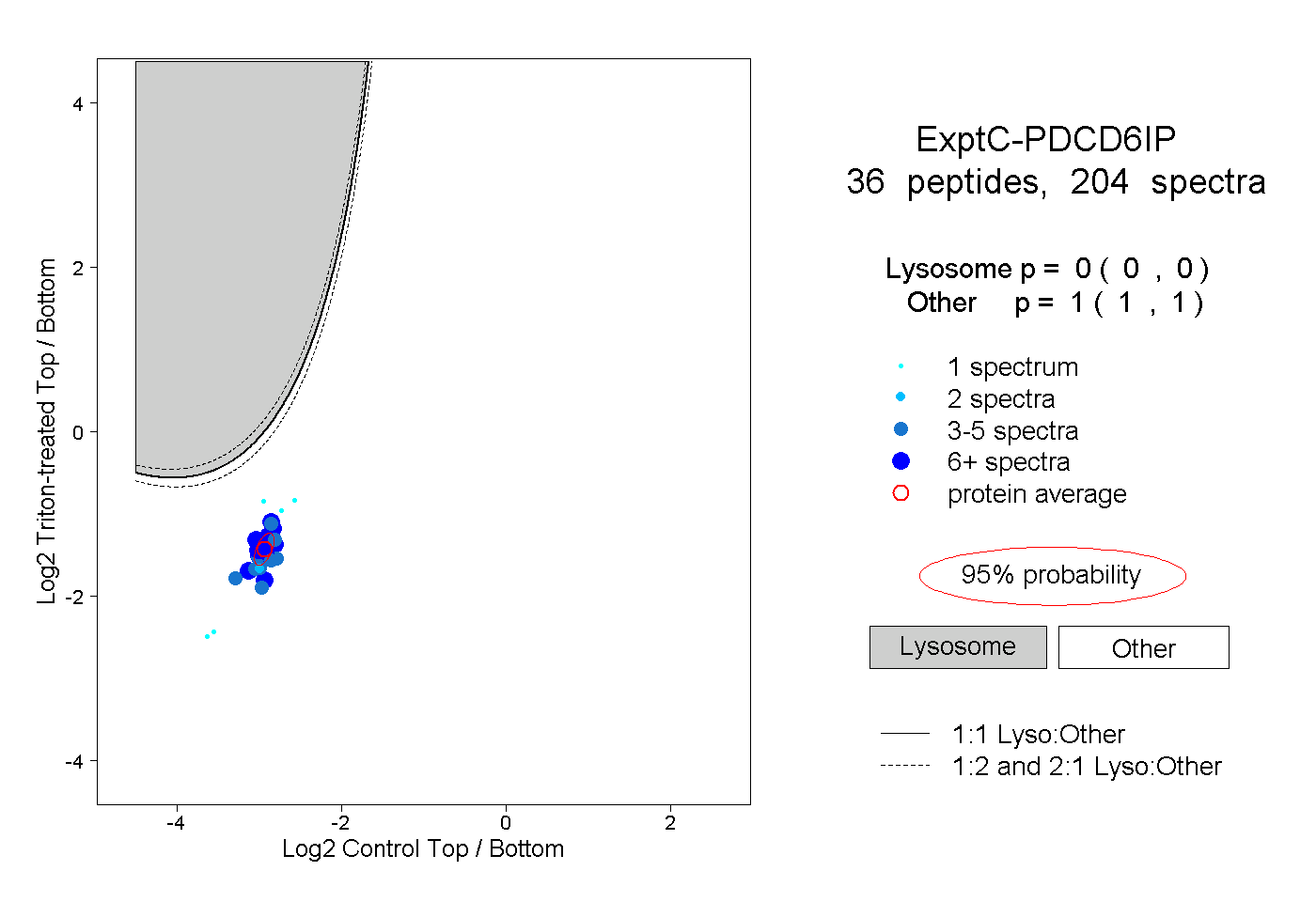 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
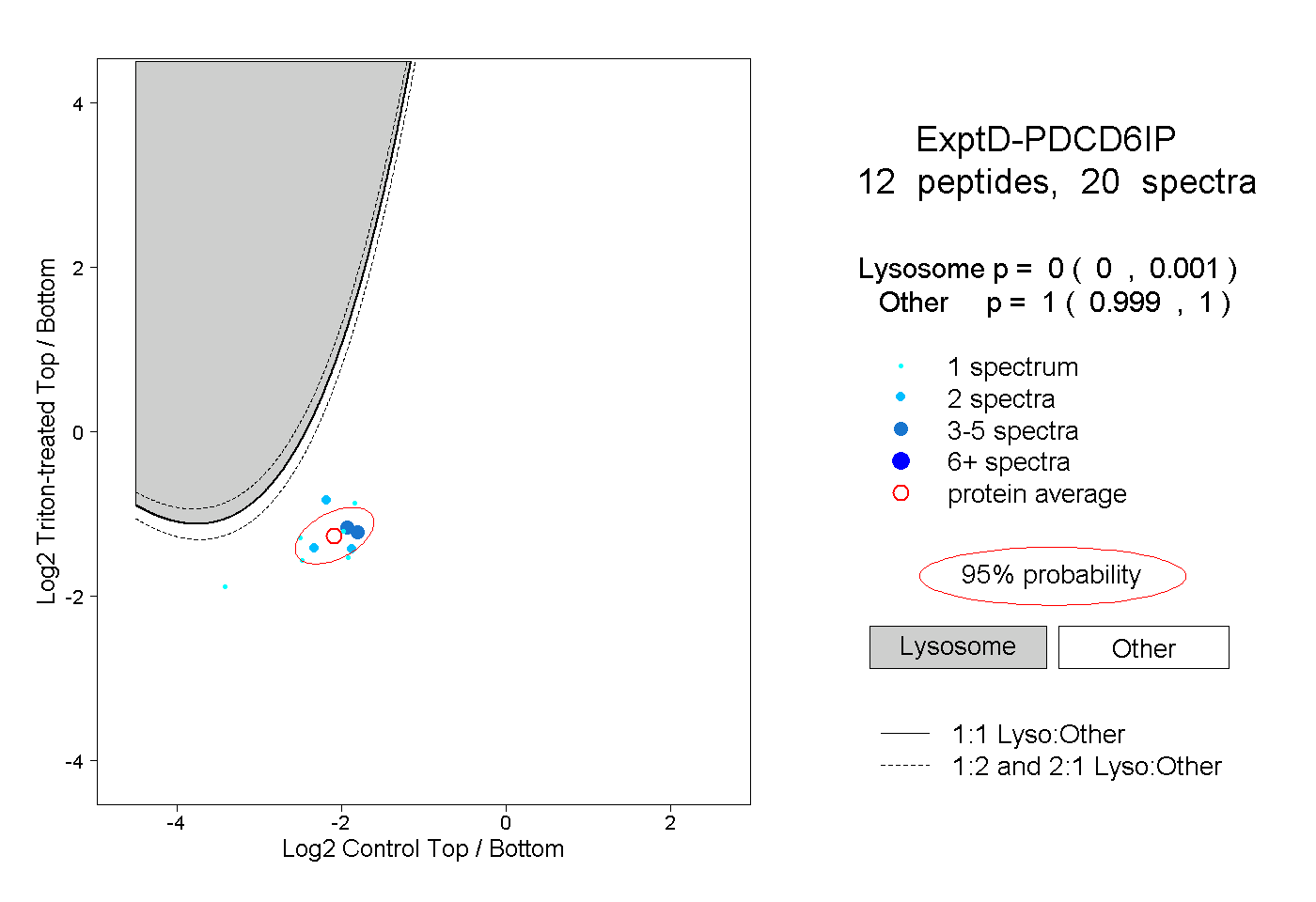 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |