peptides
spectra
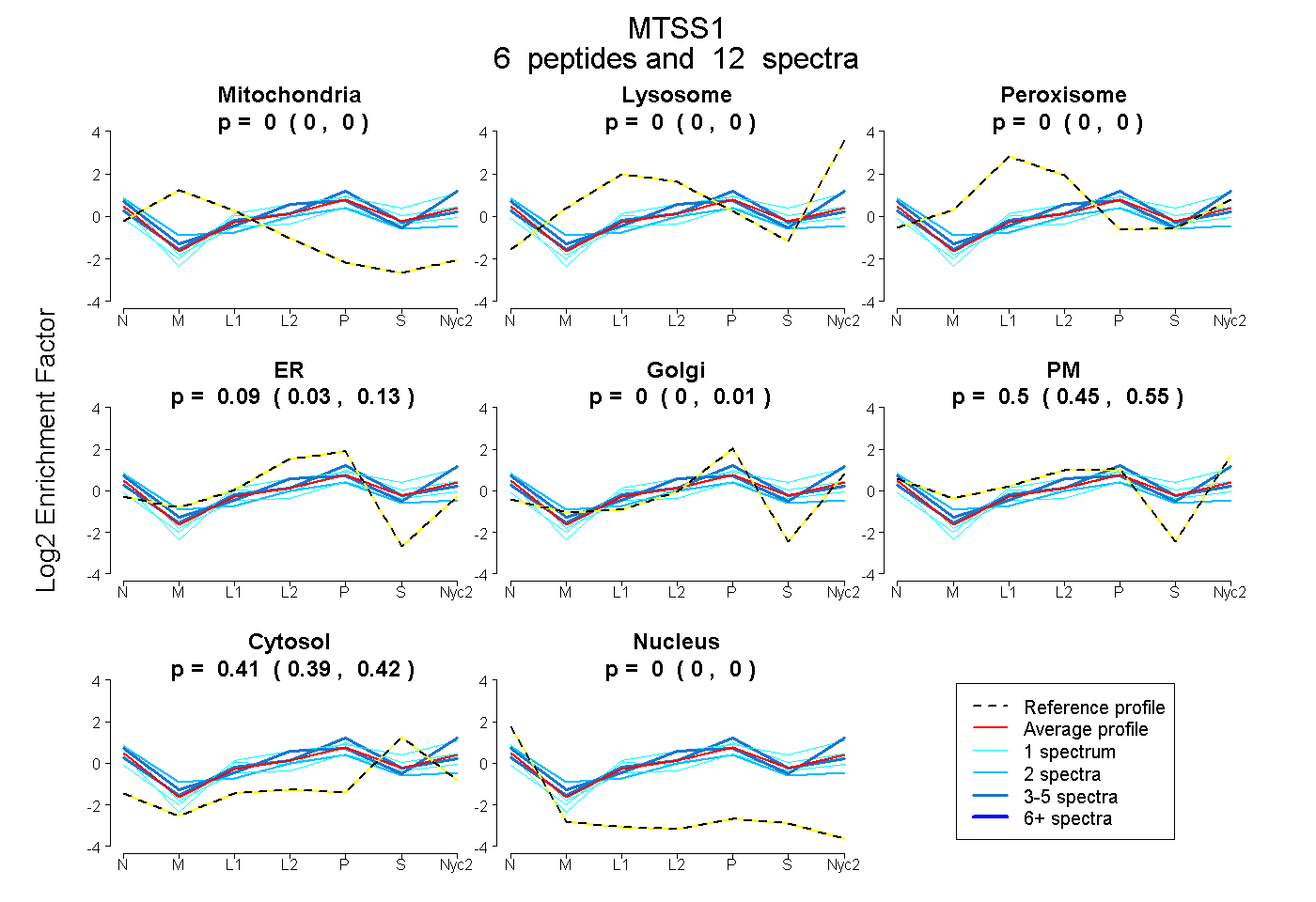
0.000 | 0.000
0.000 | 0.000
0.000 | 0.001
0.034 | 0.133
0.000 | 0.012
0.448 | 0.546
0.393 | 0.419
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
12 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.090 0.034 | 0.133 |
0.000 0.000 | 0.012 |
0.503 0.448 | 0.546 |
0.407 0.393 | 0.419 |
0.000 0.000 | 0.000 |
| 1 spectrum, TPVIPVK | 0.000 | 0.178 | 0.003 | 0.083 | 0.000 | 0.314 | 0.422 | 0.000 | ||
| 1 spectrum, GSYPVWEDFINK | 0.000 | 0.000 | 0.000 | 0.040 | 0.000 | 0.478 | 0.388 | 0.093 | ||
| 4 spectra, VADMATNTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.696 | 0.304 | 0.000 | ||
| 3 spectra, SSNLAQQAPVR | 0.000 | 0.000 | 0.050 | 0.166 | 0.169 | 0.264 | 0.351 | 0.000 | ||
| 2 spectra, EIGSALTR | 0.000 | 0.000 | 0.051 | 0.177 | 0.000 | 0.353 | 0.290 | 0.128 | ||
| 1 spectrum, EADSSGGGPTATAGPPAAAEEAQRPR | 0.000 | 0.000 | 0.001 | 0.089 | 0.034 | 0.421 | 0.454 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
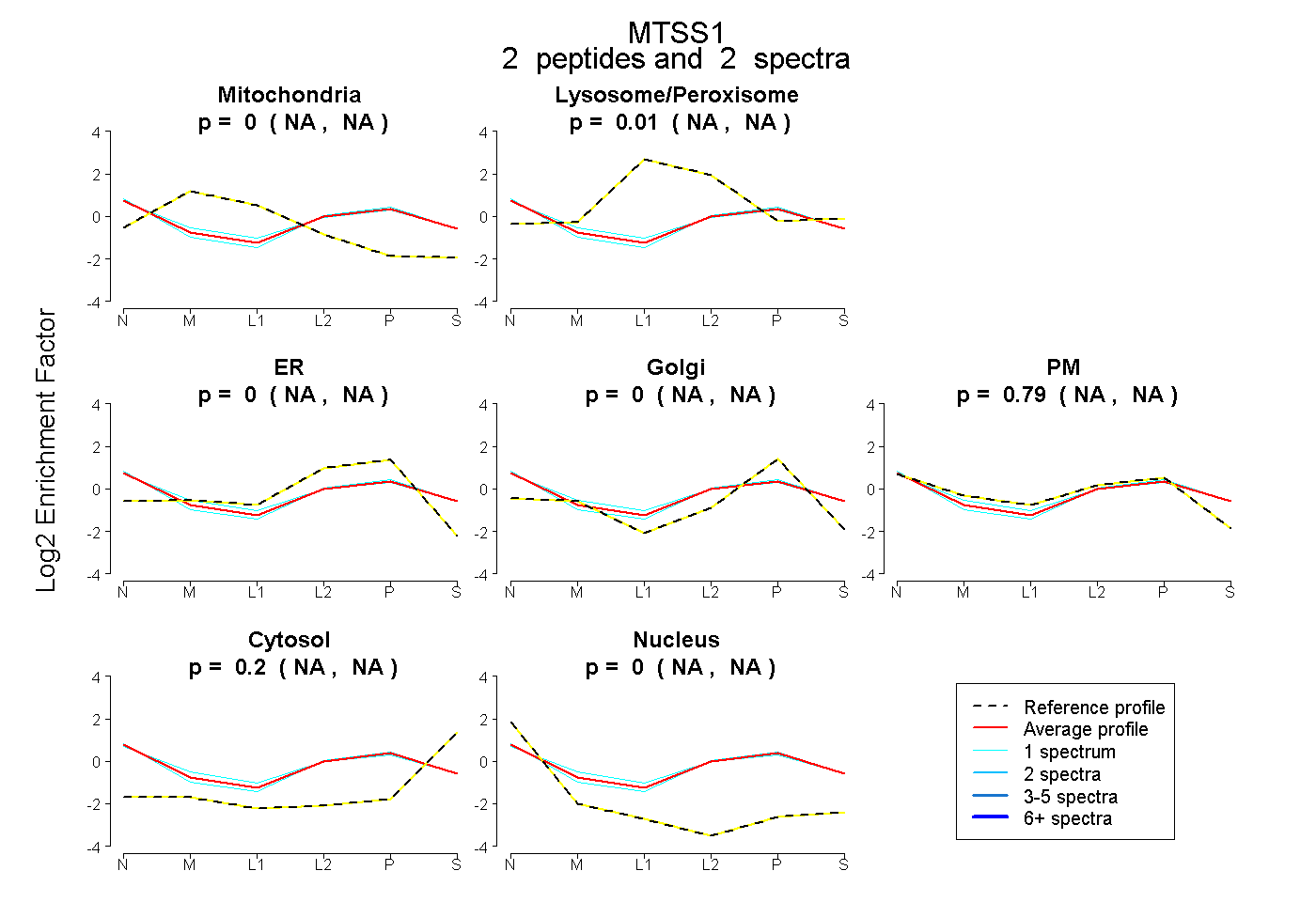 |
0.000 NA | NA |
0.015 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.786 NA | NA |
0.199 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
20 spectra |
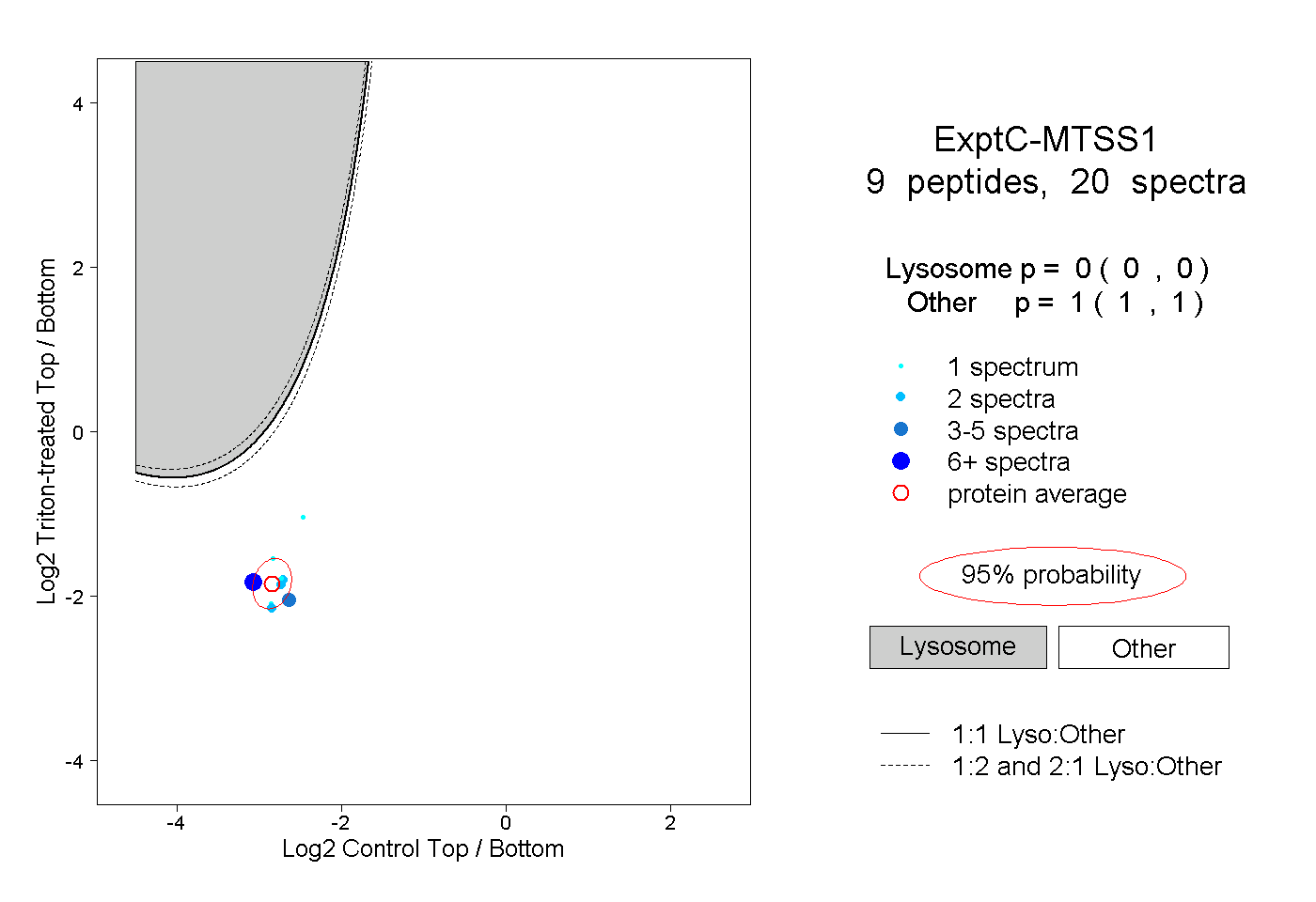 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
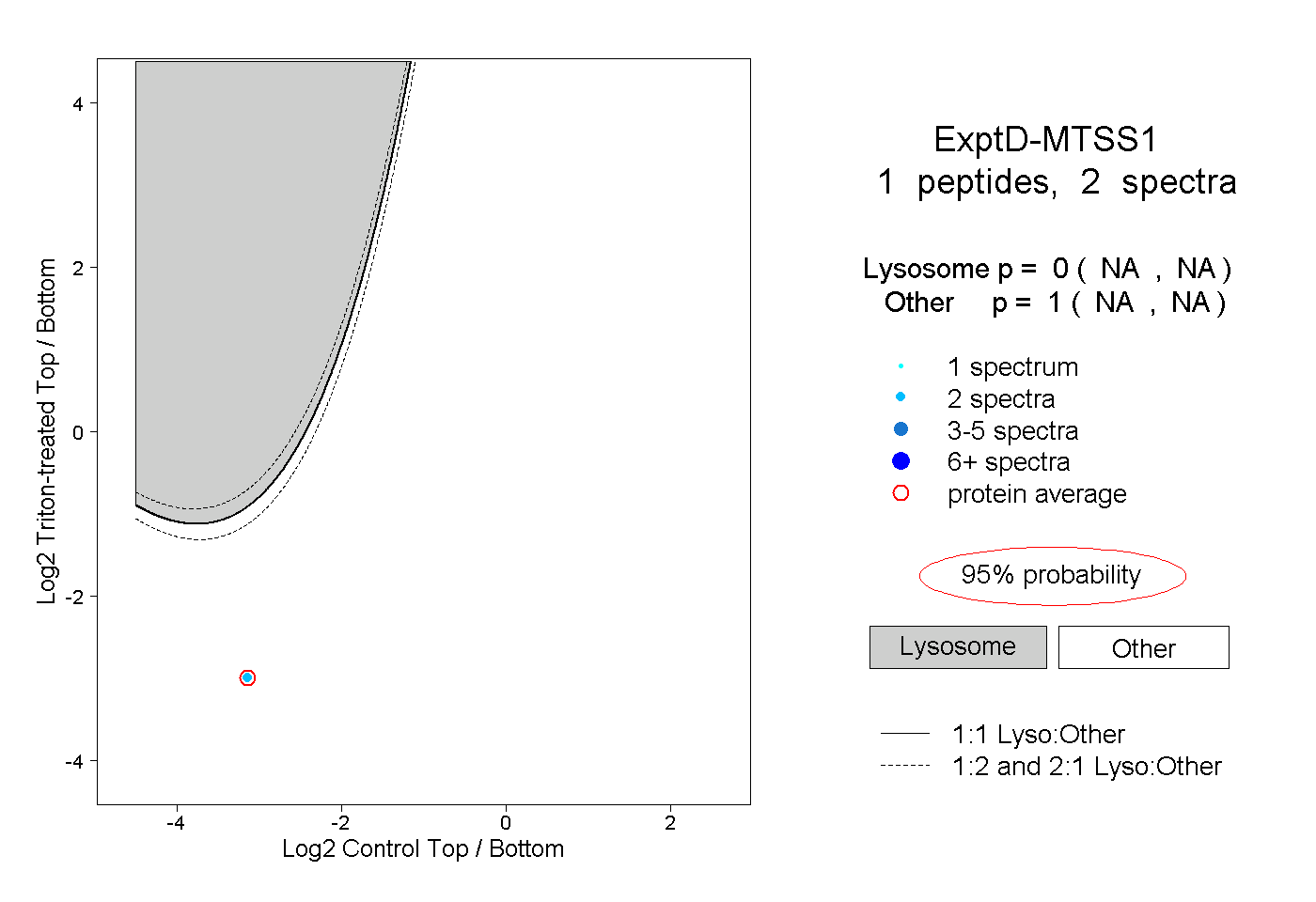 |
0.000 NA | NA |
1.000 NA | NA |