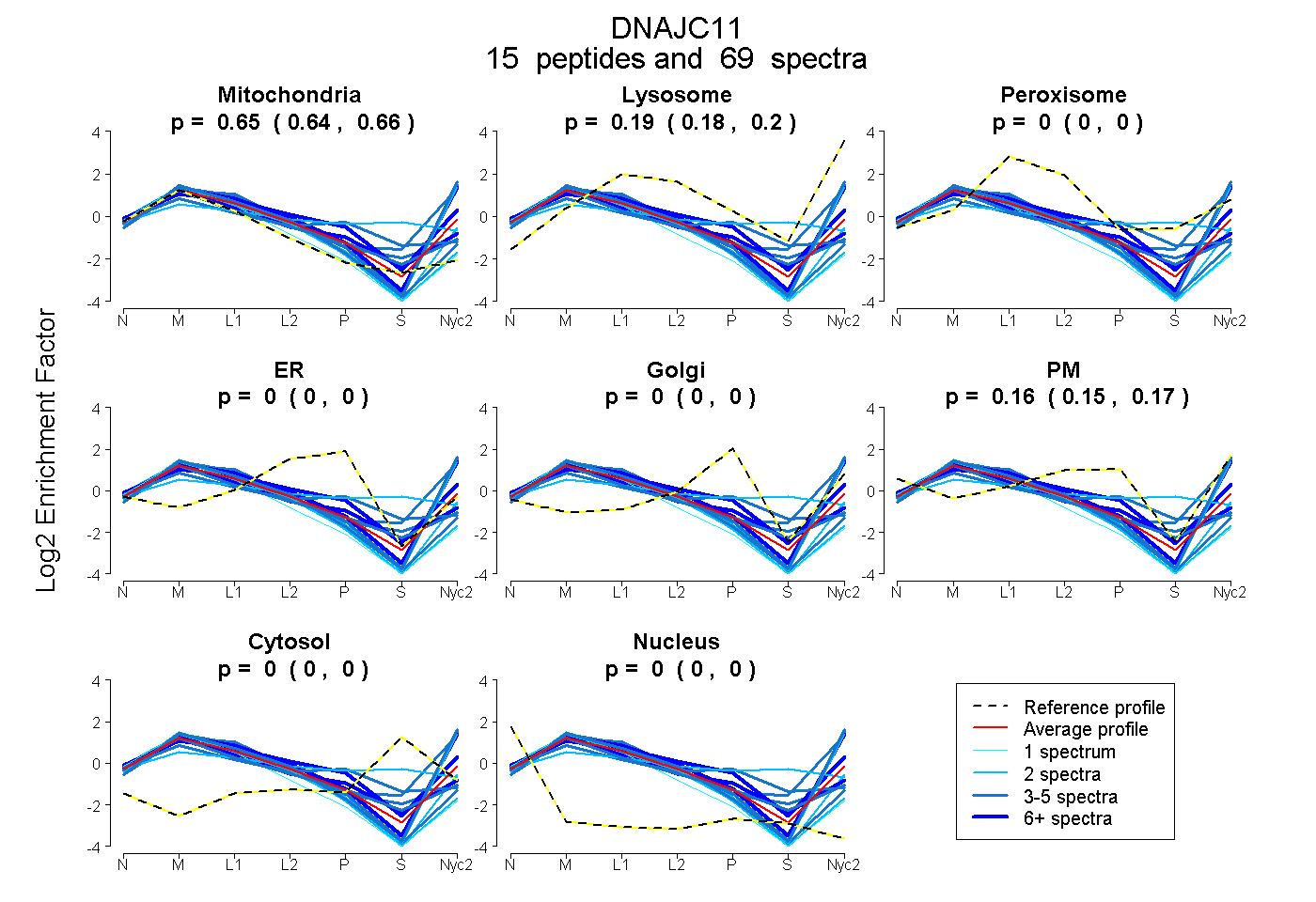
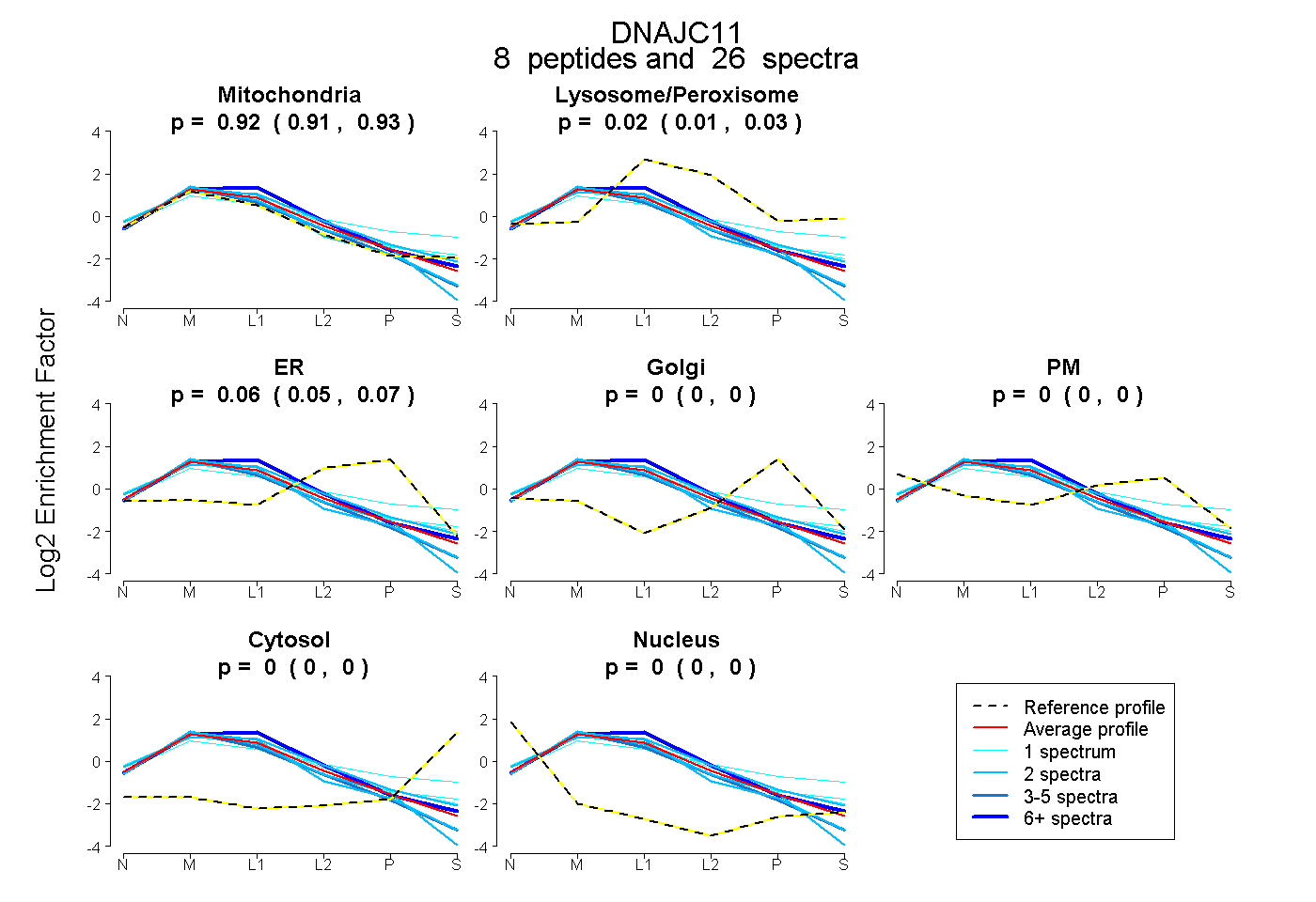
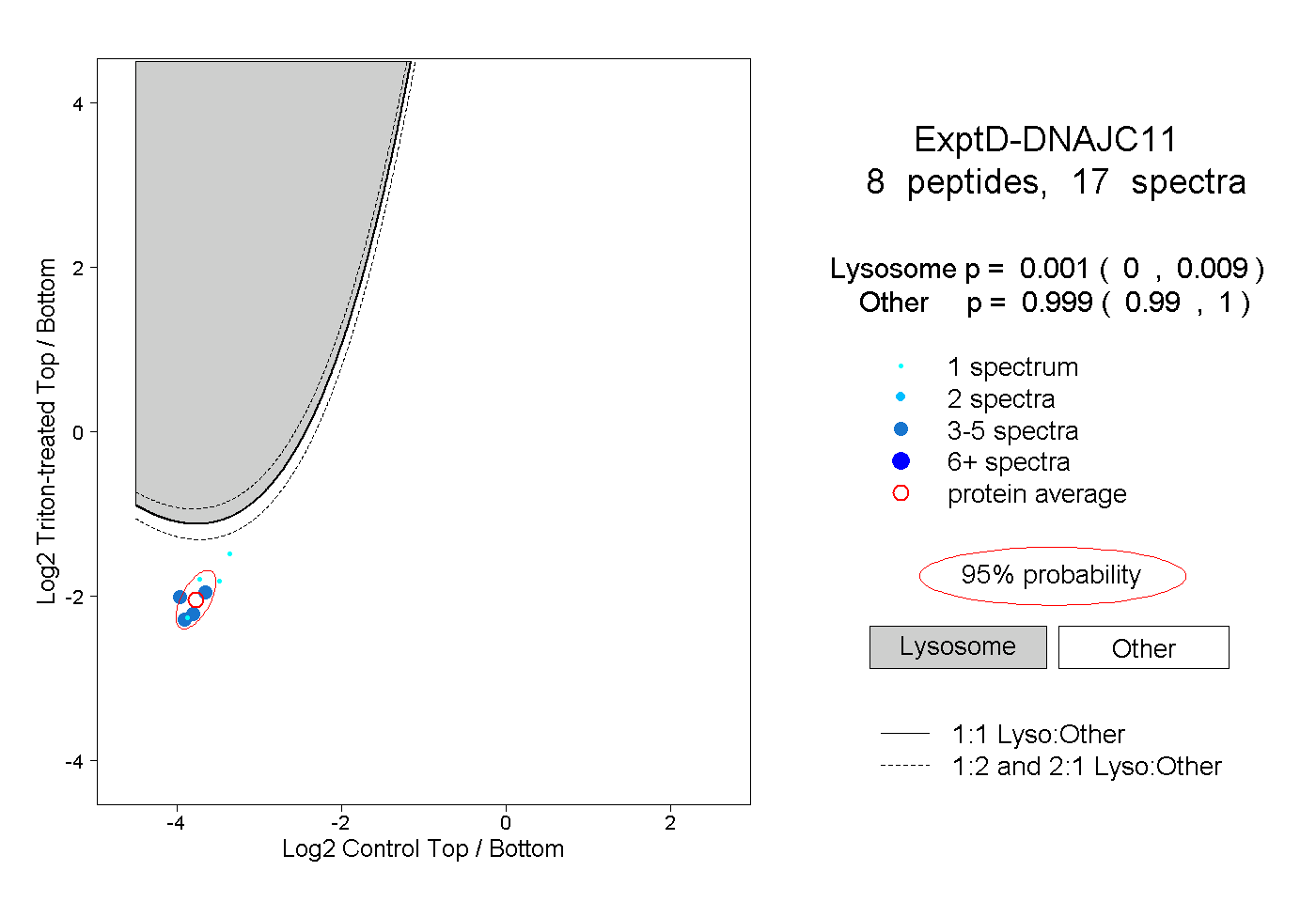
| 18 spectra, GVLHQVMMPDSEALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, LILTEASK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, FQDDDQTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, WGIQSAMNTSIVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, LMQESVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, AIYDIYGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, VLYQFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TPAEIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LCMLYHPDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AGLPGFYDPCVGEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, ENTASDILQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, GIRPGLTTVLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, EASAEELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LFNLVHQAYEVLSDPQTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AGFFGTIVEYGAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GLEMEGWEVVER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LIIRPYLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NTVGYLQWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GWGELEFGAGDLQGPLFGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, IIEAEESR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |