peptides
spectra
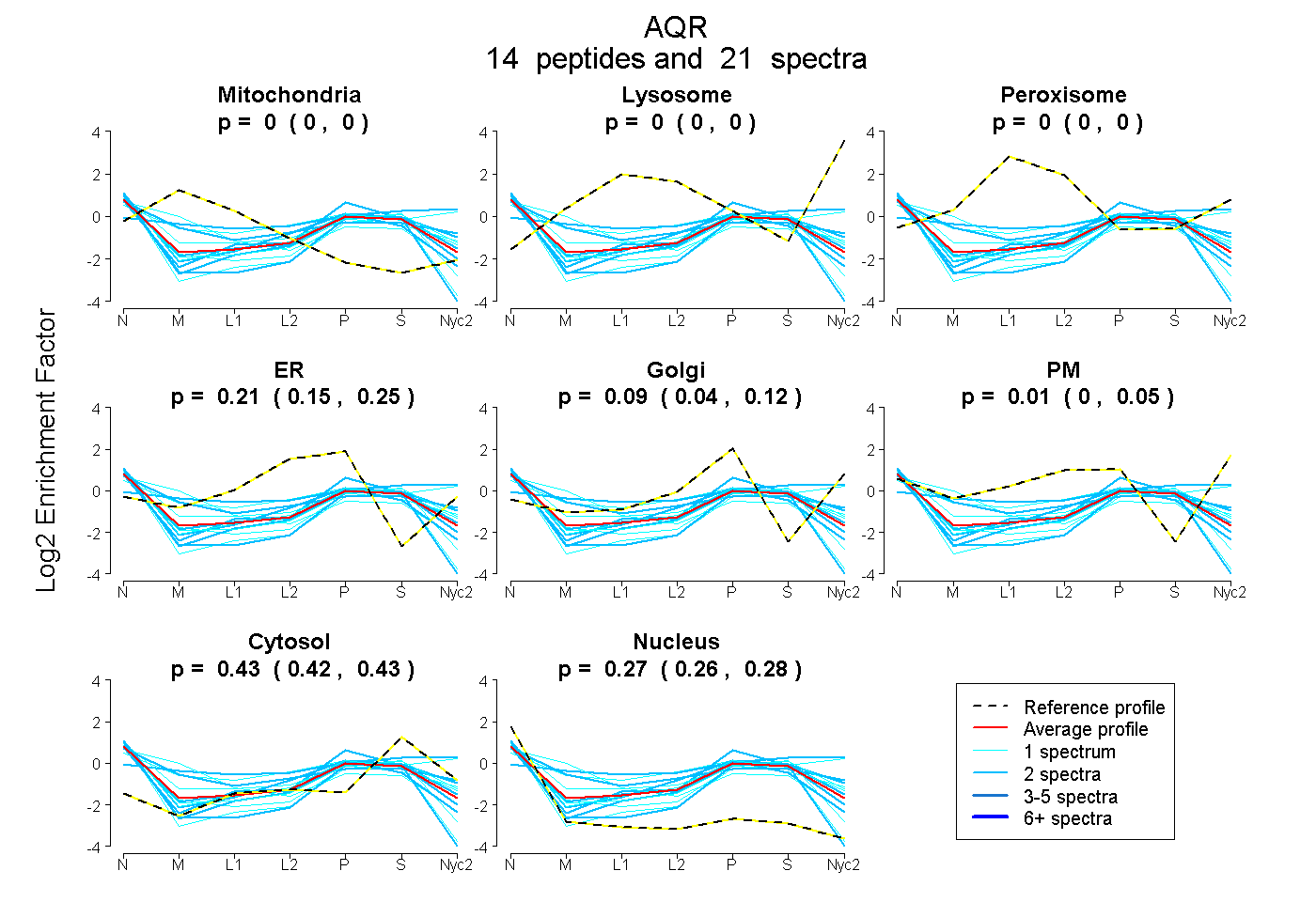
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.151 | 0.247
0.039 | 0.118
0.000 | 0.047
0.420 | 0.433
0.260 | 0.281
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.205 0.151 | 0.247 |
0.087 0.039 | 0.118 |
0.011 0.000 | 0.047 |
0.427 0.420 | 0.433 |
0.271 0.260 | 0.281 |
| 2 spectra, QDIEDSVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.258 | 0.036 | 0.454 | 0.253 | ||
| 2 spectra, TLIVEPHVIPNR | 0.142 | 0.000 | 0.000 | 0.000 | 0.000 | 0.353 | 0.379 | 0.127 | ||
| 2 spectra, RPFIEQVGLVYVR | 0.000 | 0.000 | 0.000 | 0.133 | 0.169 | 0.011 | 0.436 | 0.251 | ||
| 1 spectrum, IELEIK | 0.000 | 0.000 | 0.000 | 0.155 | 0.000 | 0.000 | 0.459 | 0.386 | ||
| 1 spectrum, DEWEGLR | 0.050 | 0.000 | 0.000 | 0.000 | 0.000 | 0.500 | 0.432 | 0.018 | ||
| 1 spectrum, AVLETIR | 0.000 | 0.000 | 0.000 | 0.060 | 0.000 | 0.000 | 0.402 | 0.538 | ||
| 1 spectrum, SIPLSEPVTMDK | 0.000 | 0.000 | 0.000 | 0.090 | 0.185 | 0.059 | 0.410 | 0.256 | ||
| 1 spectrum, LTFPVR | 0.392 | 0.000 | 0.000 | 0.041 | 0.112 | 0.000 | 0.268 | 0.188 | ||
| 2 spectra, DFDLFR | 0.046 | 0.010 | 0.071 | 0.000 | 0.000 | 0.395 | 0.477 | 0.000 | ||
| 2 spectra, EQAYQER | 0.000 | 0.000 | 0.000 | 0.258 | 0.065 | 0.000 | 0.419 | 0.259 | ||
| 2 spectra, NFNLFR | 0.000 | 0.000 | 0.000 | 0.326 | 0.000 | 0.000 | 0.330 | 0.344 | ||
| 1 spectrum, WEEYMSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.223 | 0.059 | 0.467 | 0.251 | ||
| 2 spectra, VIEEIYEK | 0.000 | 0.000 | 0.000 | 0.073 | 0.000 | 0.000 | 0.375 | 0.552 | ||
| 1 spectrum, IFTQLEEFR | 0.000 | 0.000 | 0.013 | 0.081 | 0.000 | 0.289 | 0.357 | 0.260 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
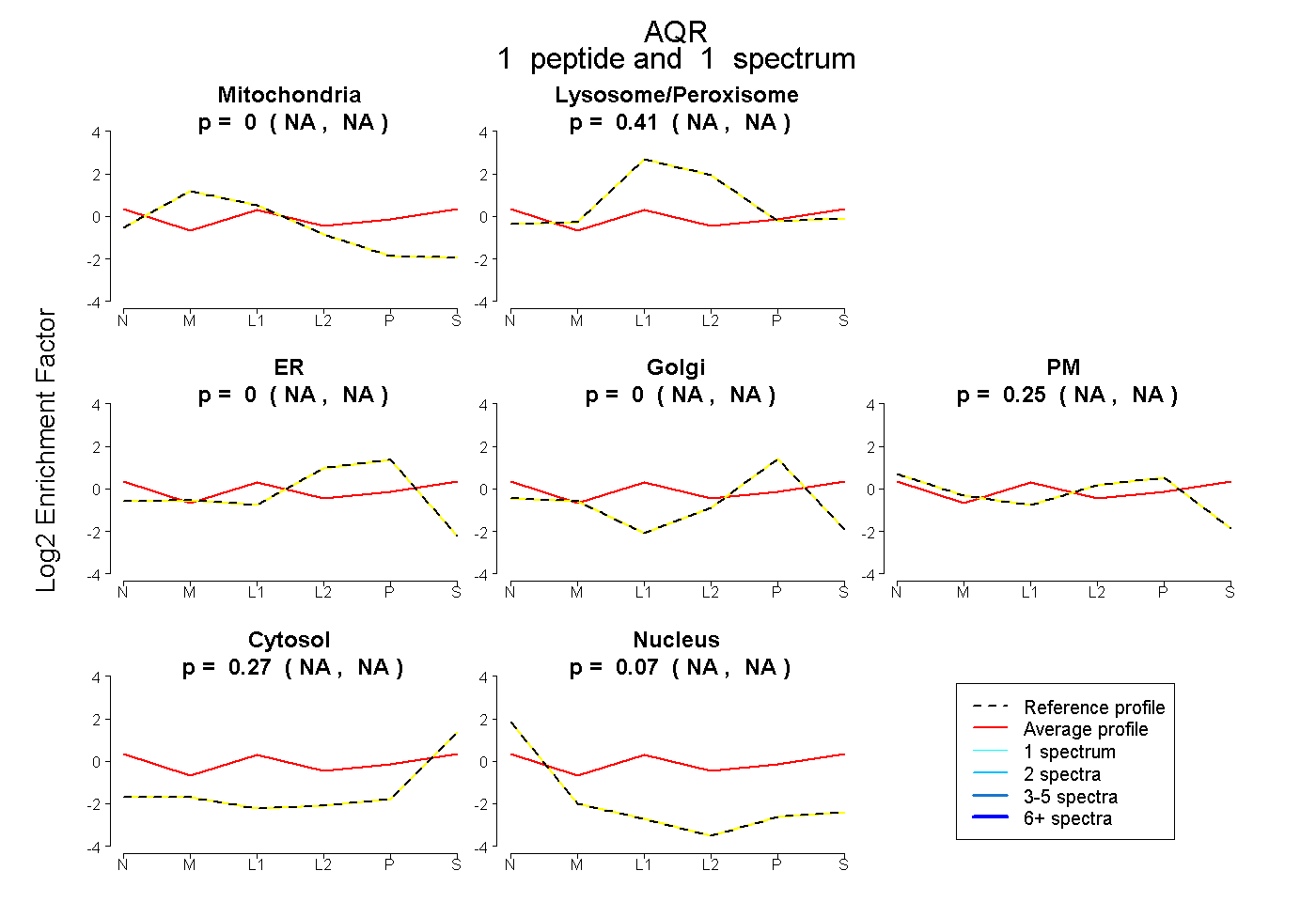 |
0.000 NA | NA |
0.407 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.249 NA | NA |
0.273 NA | NA |
0.072 NA | NA |