peptides
spectra
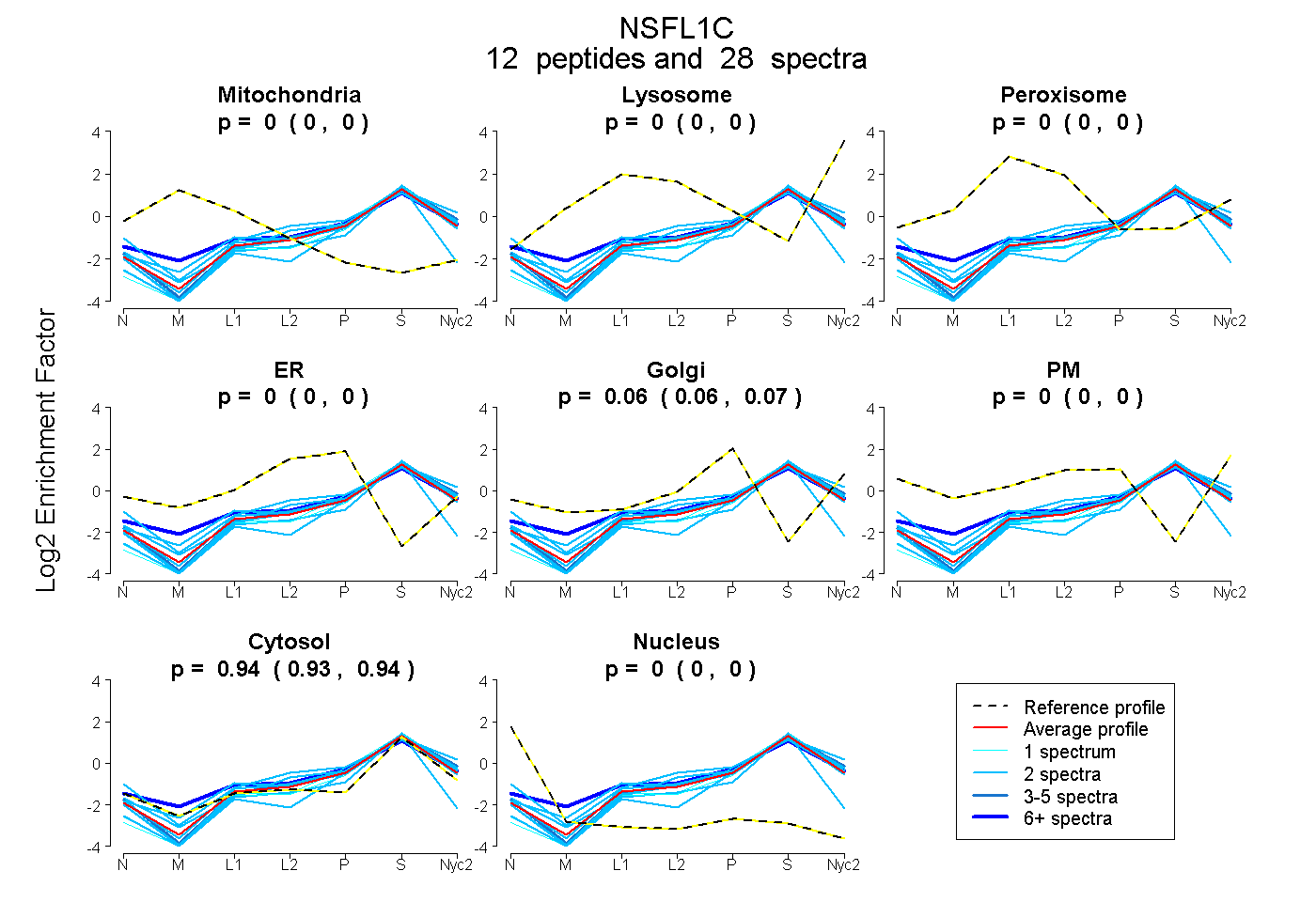
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.058 | 0.070
0.000 | 0.000
0.929 | 0.941
0.000 | 0.000
peptides
spectra
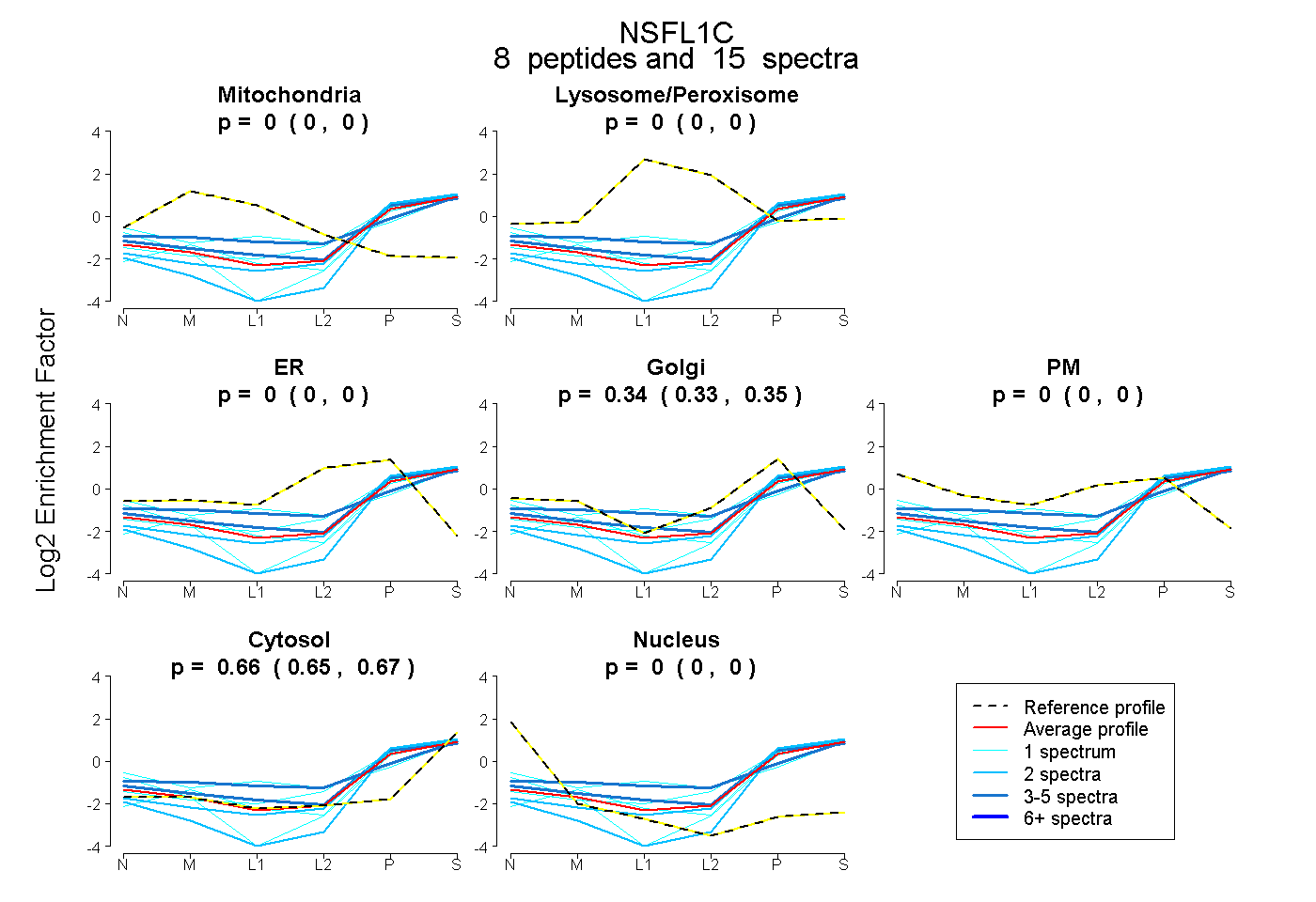
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.327 | 0.350
0.000 | 0.000
0.648 | 0.671
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.065 0.058 | 0.070 |
0.000 0.000 | 0.000 |
0.935 0.929 | 0.941 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
15 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.340 0.327 | 0.350 |
0.000 0.000 | 0.000 |
0.660 0.648 | 0.671 |
0.000 0.000 | 0.000 |
| 2 spectra, SPNELVDDLFK | 0.000 | 0.000 | 0.000 | 0.215 | 0.000 | 0.785 | 0.000 | |||
| 1 spectrum, SGQQIVGPPR | 0.000 | 0.000 | 0.000 | 0.311 | 0.000 | 0.689 | 0.000 | |||
| 3 spectra, TGFSLDNGDLR | 0.000 | 0.187 | 0.000 | 0.249 | 0.000 | 0.564 | 0.000 | |||
| 4 spectra, SPGETSKPRPFAGGGYR | 0.000 | 0.002 | 0.000 | 0.400 | 0.000 | 0.598 | 0.000 | |||
| 1 spectrum, DLIHDQDEEEEEEEGQR | 0.000 | 0.029 | 0.000 | 0.348 | 0.000 | 0.623 | 0.000 | |||
| 1 spectrum, AFTGEGQK | 0.000 | 0.213 | 0.000 | 0.149 | 0.061 | 0.578 | 0.000 | |||
| 2 spectra, SYQDPSNAQFLESIR | 0.000 | 0.000 | 0.000 | 0.324 | 0.000 | 0.676 | 0.000 | |||
| 1 spectrum, EHGAVAVER | 0.000 | 0.000 | 0.000 | 0.314 | 0.000 | 0.651 | 0.035 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
29 spectra |
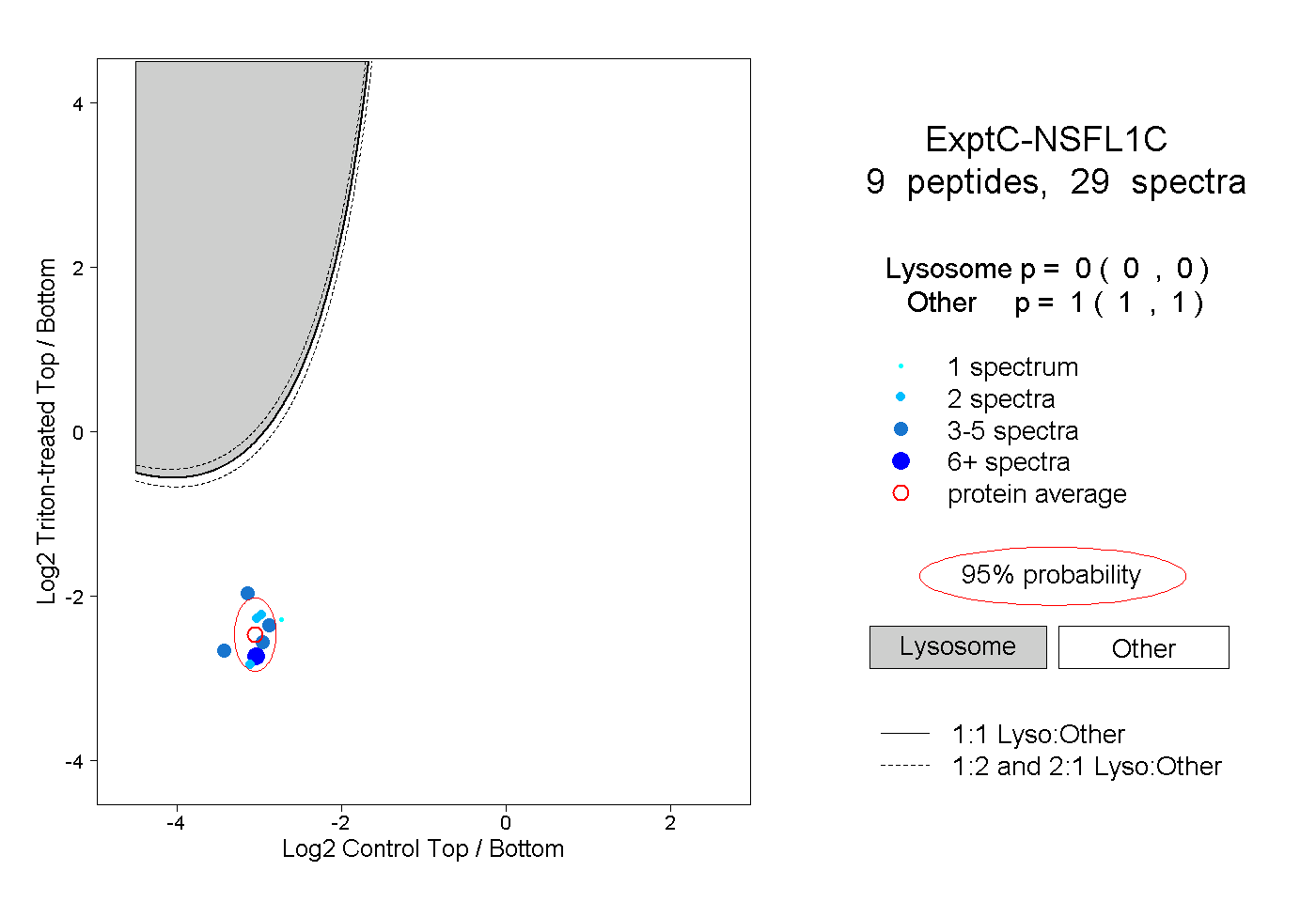 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
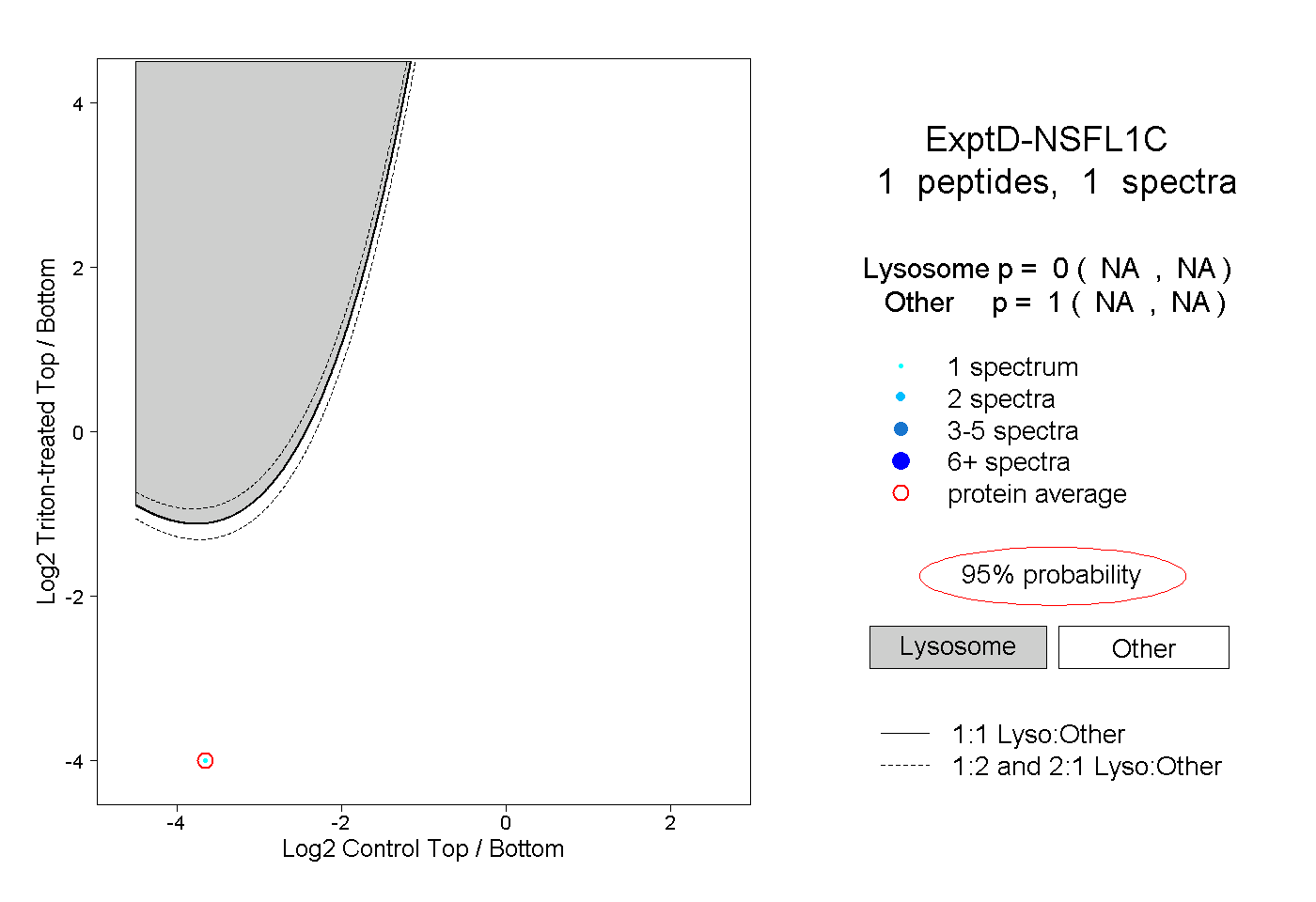 |
0.000 NA | NA |
1.000 NA | NA |