peptides
spectra
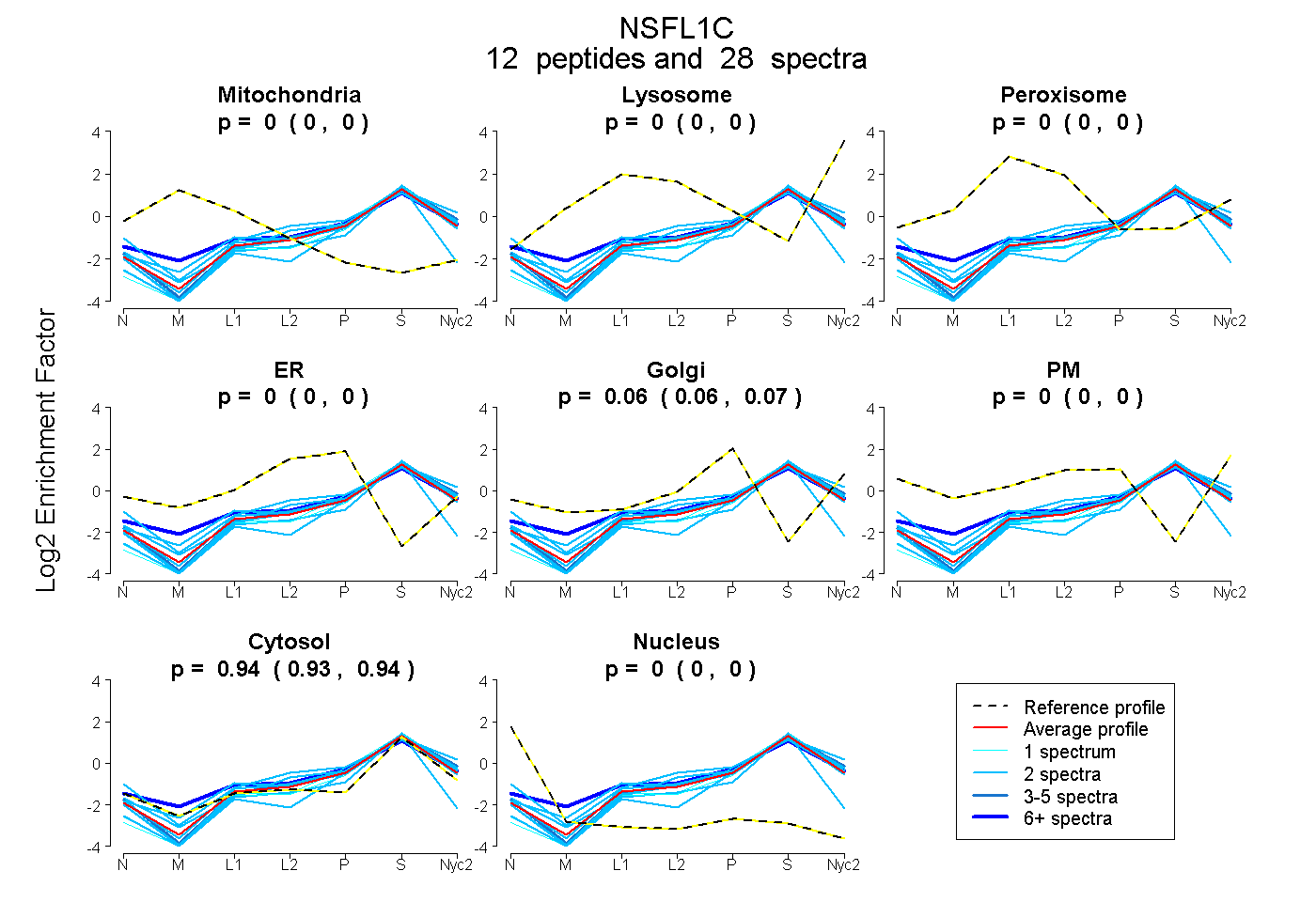
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.058 | 0.070
0.000 | 0.000
0.929 | 0.941
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.065 0.058 | 0.070 |
0.000 0.000 | 0.000 |
0.935 0.929 | 0.941 |
0.000 0.000 | 0.000 |
| 2 spectra, SPNELVDDLFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | 0.000 | 0.978 | 0.000 | ||
| 1 spectrum, GTAPSDNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, EFVAVTGAEEDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, SGQQIVGPPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.979 | 0.021 | ||
| 2 spectra, TGFSLDNGDLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.036 | 0.000 | 0.964 | 0.000 | ||
| 6 spectra, AFTGEGQK | 0.000 | 0.067 | 0.000 | 0.000 | 0.131 | 0.000 | 0.802 | 0.000 | ||
| 2 spectra, SYQDPSNAQFLESIR | 0.000 | 0.127 | 0.000 | 0.000 | 0.024 | 0.000 | 0.848 | 0.000 | ||
| 4 spectra, ELADENQTLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.057 | 0.000 | 0.943 | 0.000 | ||
| 2 spectra, LGAAPEEESAYVAGER | 0.000 | 0.001 | 0.000 | 0.124 | 0.062 | 0.000 | 0.813 | 0.000 | ||
| 1 spectrum, ASSSILINEAEPTTNIQIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | 0.000 | 0.994 | 0.000 | ||
| 2 spectra, FYAGGSER | 0.000 | 0.000 | 0.000 | 0.000 | 0.084 | 0.000 | 0.916 | 0.000 | ||
| 2 spectra, EHGAVAVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.108 | 0.000 | 0.892 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
15 spectra |
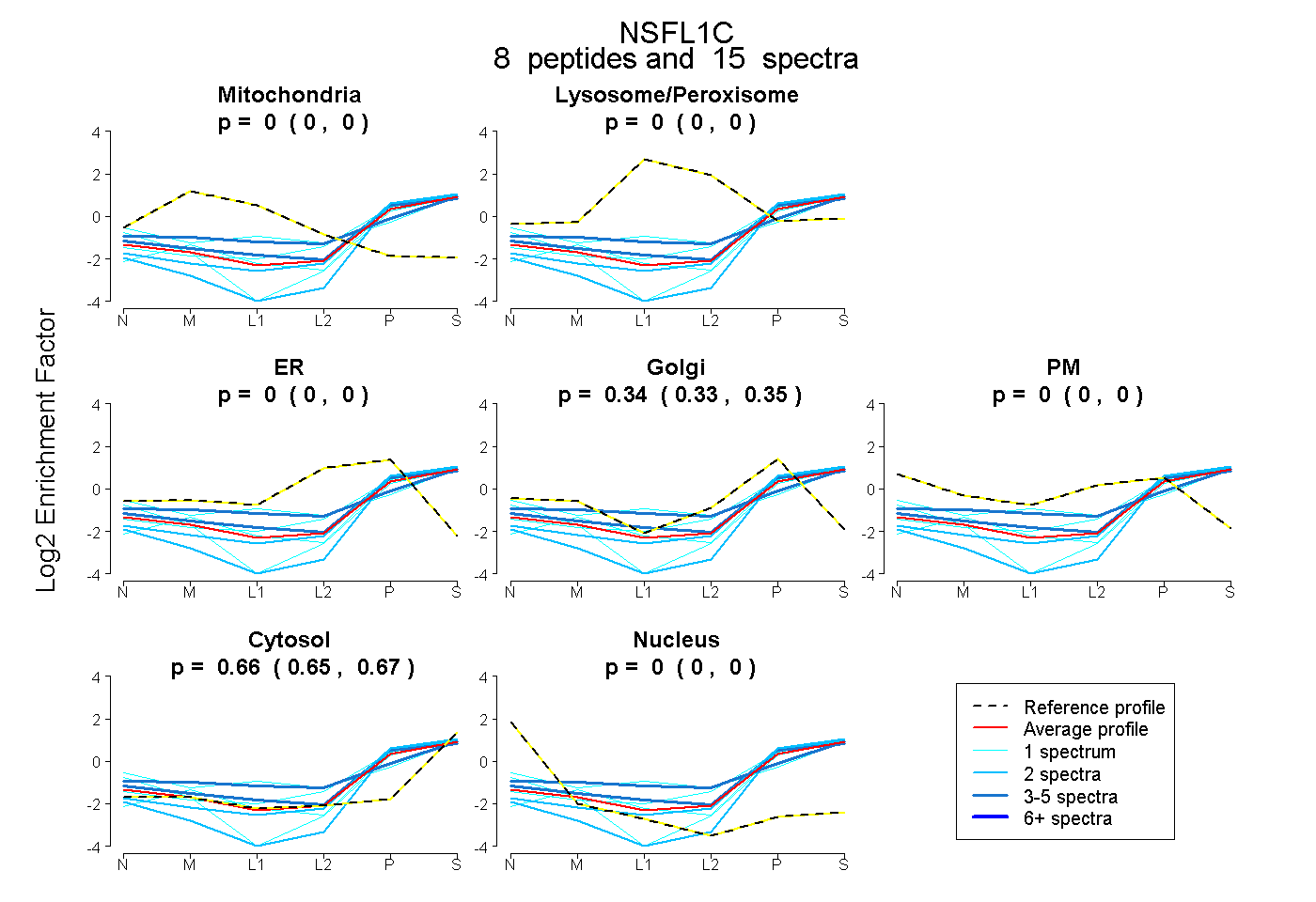 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.340 0.327 | 0.350 |
0.000 0.000 | 0.000 |
0.660 0.648 | 0.671 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
29 spectra |
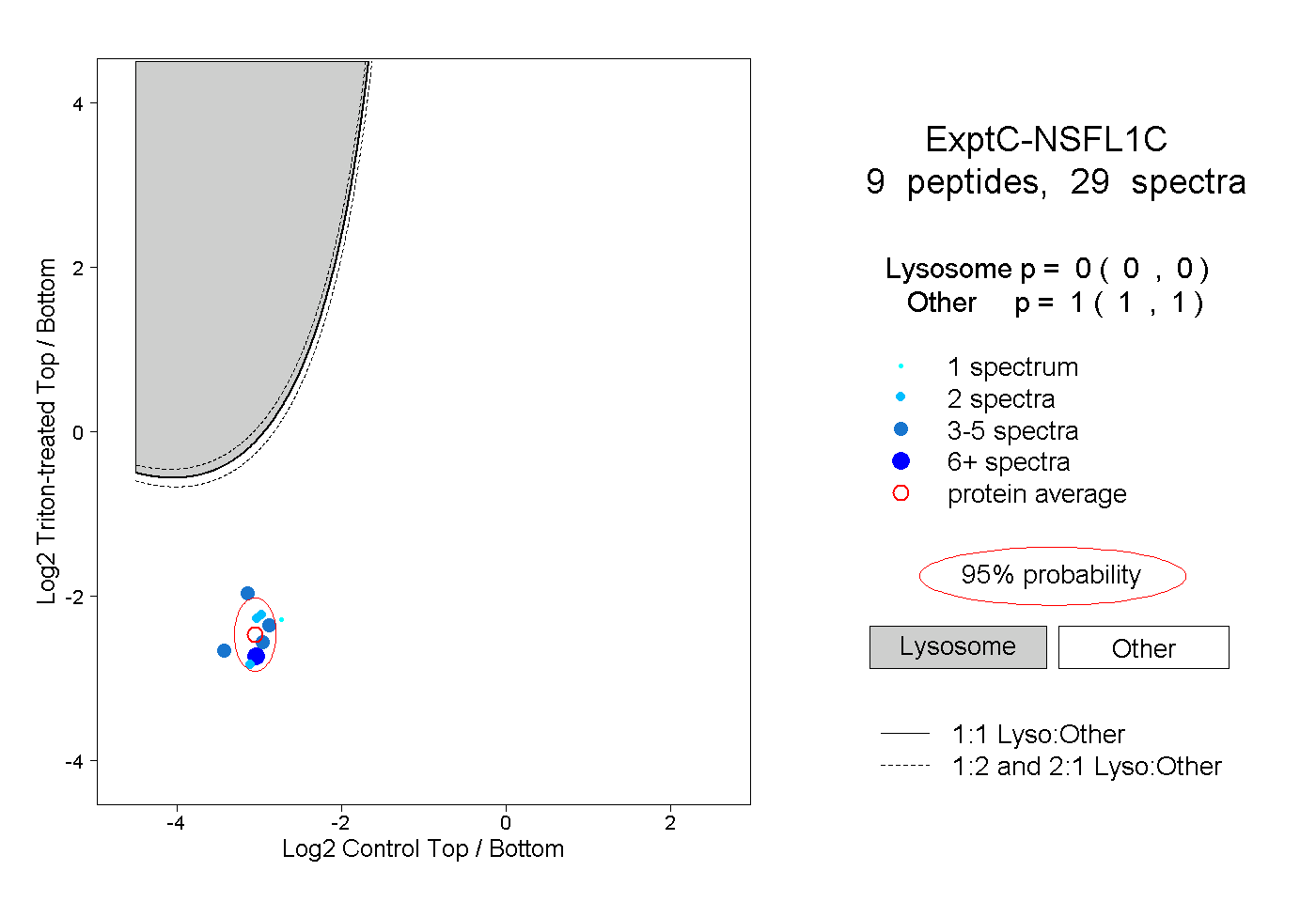 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
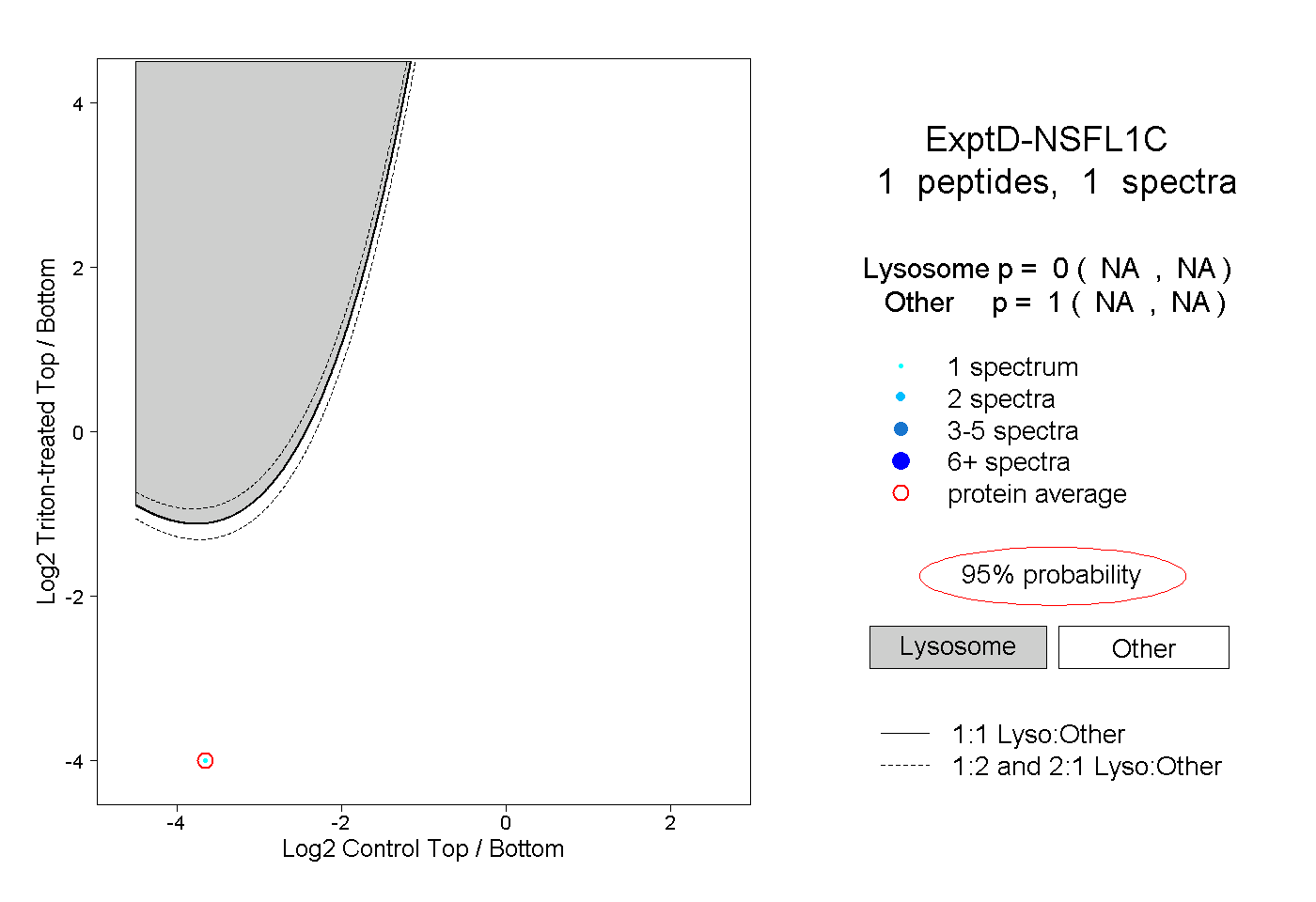 |
0.000 NA | NA |
1.000 NA | NA |