peptides
spectra
0.000 | 0.000
0.207 | 0.364
0.000 | 0.143
0.000 | 0.000
0.000 | 0.000
0.227 | 0.333
0.318 | 0.376
0.000 | 0.000
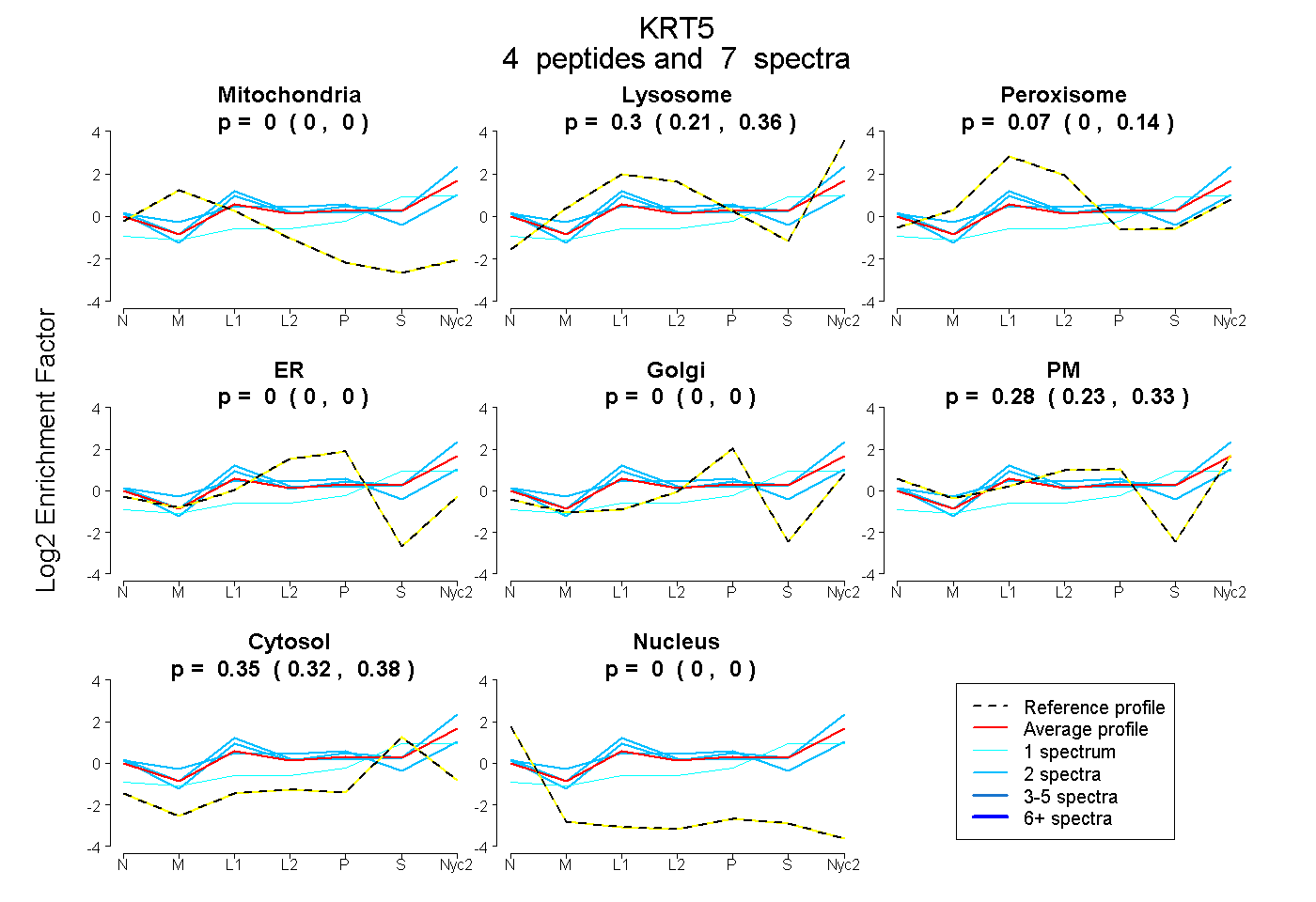
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
7 spectra |
 |
0.000 0.000 | 0.000 |
0.295 0.207 | 0.364 |
0.071 0.000 | 0.143 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.285 0.227 | 0.333 |
0.349 0.318 | 0.376 |
0.000 0.000 | 0.000 |
| 1 spectrum, WTLLQEQGTK | 0.000 | 0.296 | 0.000 | 0.000 | 0.055 | 0.028 | 0.621 | 0.000 | ||
| 2 spectra, TTAENEFVMLK | 0.000 | 0.427 | 0.000 | 0.000 | 0.000 | 0.260 | 0.314 | 0.000 | ||
| 2 spectra, VDALMDEINFMK | 0.000 | 0.039 | 0.244 | 0.000 | 0.030 | 0.455 | 0.233 | 0.000 | ||
| 2 spectra, YEELQQTAGR | 0.000 | 0.439 | 0.087 | 0.000 | 0.000 | 0.198 | 0.276 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
7 spectra |
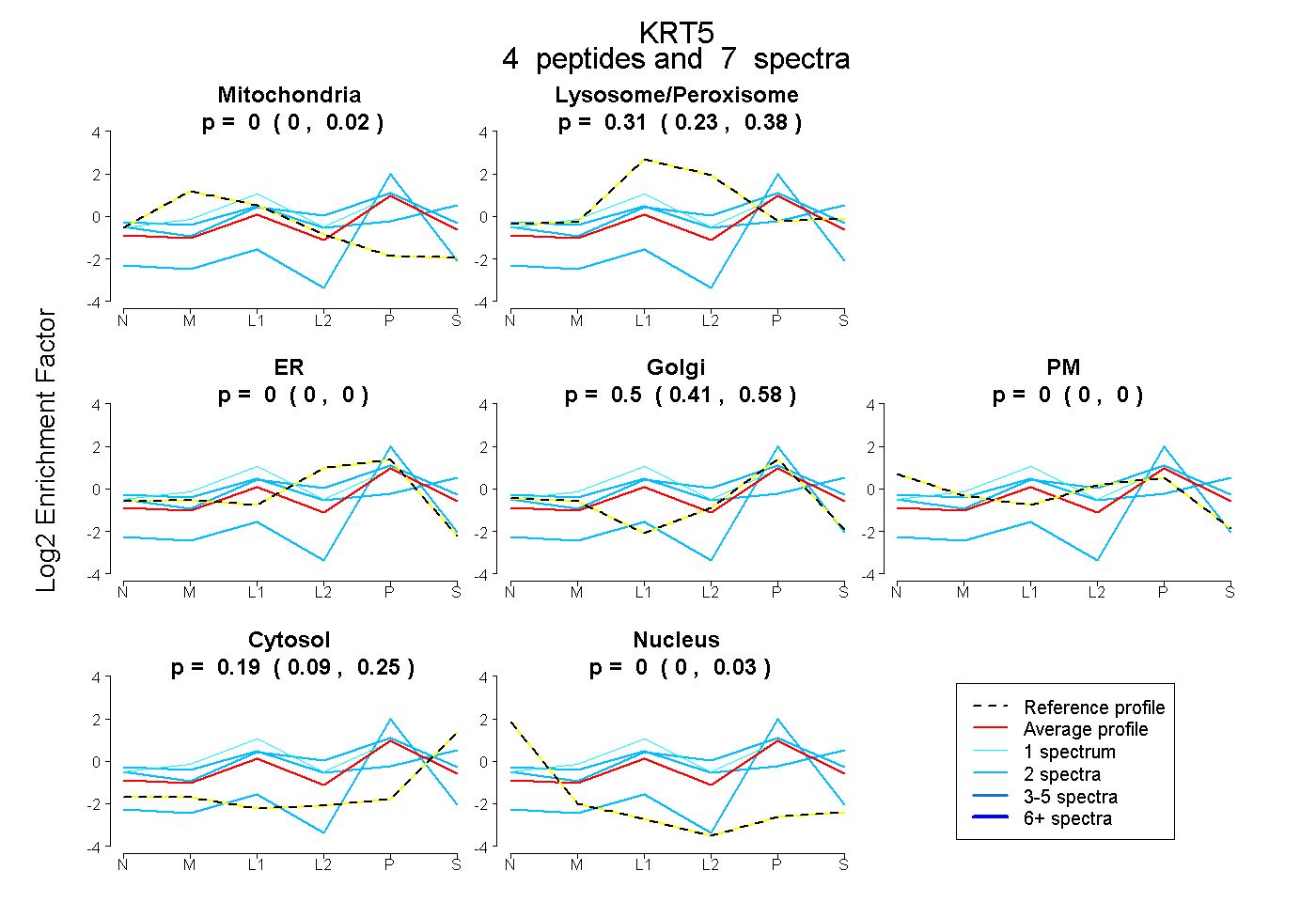 |
0.000 0.000 | 0.020 |
0.313 0.229 | 0.376 |
0.000 0.000 | 0.000 |
0.502 0.408 | 0.579 |
0.000 0.000 | 0.000 |
0.185 0.095 | 0.254 |
0.000 0.000 | 0.027 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
47 spectra |
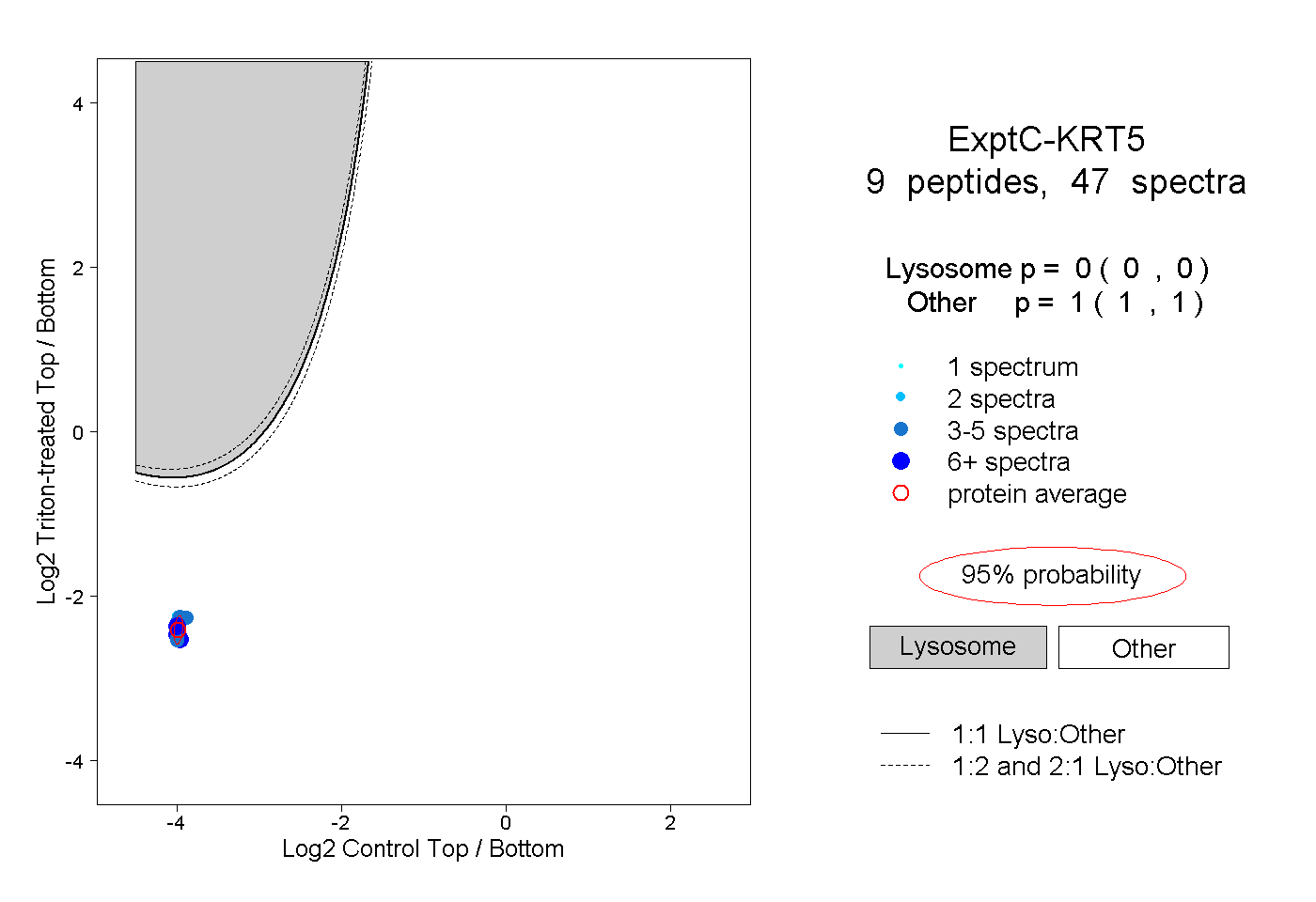 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
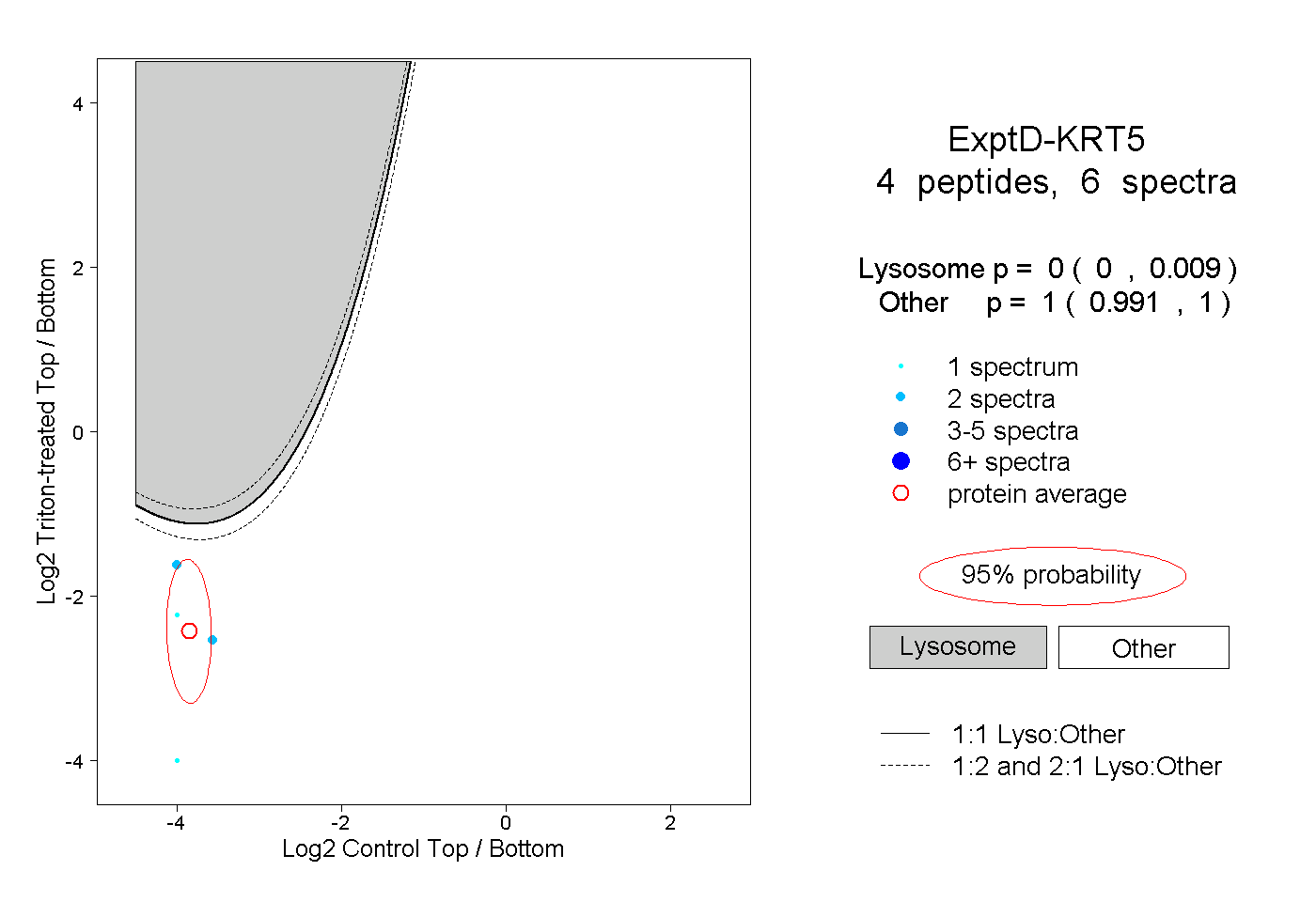 |
0.000 0.000 | 0.009 |
1.000 0.991 | 1.000 |