peptides
spectra
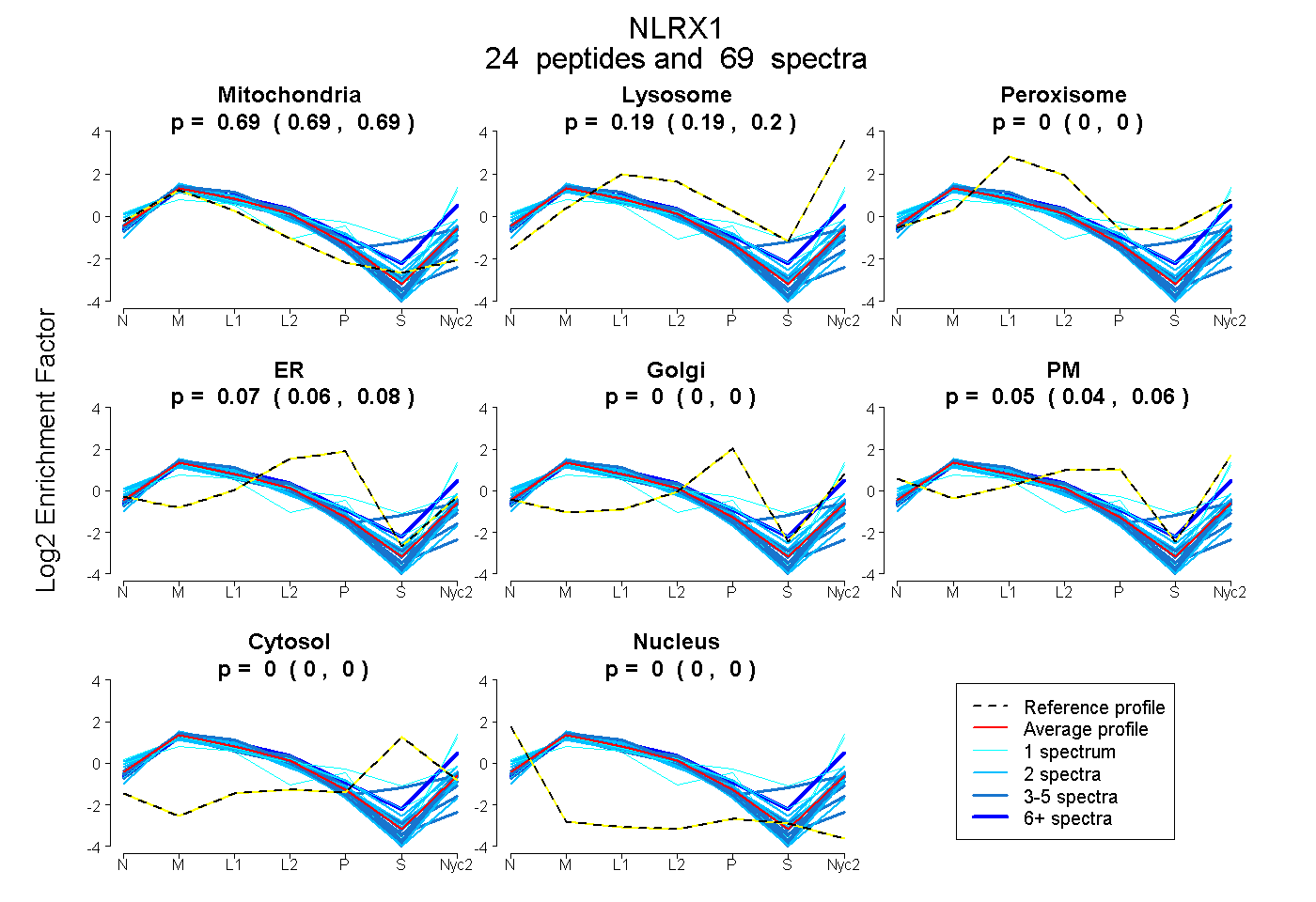
0.686 | 0.693
0.187 | 0.197
0.000 | 0.000
0.055 | 0.075
0.000 | 0.000
0.039 | 0.063
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
69 spectra |
 |
0.690 0.686 | 0.693 |
0.192 0.187 | 0.197 |
0.000 0.000 | 0.000 |
0.066 0.055 | 0.075 |
0.000 0.000 | 0.000 |
0.051 0.039 | 0.063 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, AVLAQLGCPIK | 0.427 | 0.075 | 0.000 | 0.000 | 0.000 | 0.498 | 0.000 | 0.000 | ||
| 1 spectrum, VQTVVLYGTVGTGK | 0.350 | 0.000 | 0.301 | 0.000 | 0.143 | 0.131 | 0.075 | 0.000 | ||
| 4 spectra, NLNSWDPVR | 0.695 | 0.191 | 0.000 | 0.101 | 0.000 | 0.013 | 0.000 | 0.000 | ||
| 4 spectra, YMLPEASILVTTRPSAIGR | 0.725 | 0.200 | 0.000 | 0.000 | 0.000 | 0.075 | 0.000 | 0.000 | ||
| 4 spectra, EVFEFVGR | 0.722 | 0.168 | 0.000 | 0.005 | 0.000 | 0.105 | 0.000 | 0.000 | ||
| 2 spectra, MVLDWCYGR | 0.837 | 0.048 | 0.000 | 0.115 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, TEEEFQLLQIFR | 0.702 | 0.184 | 0.000 | 0.073 | 0.000 | 0.041 | 0.000 | 0.000 | ||
| 4 spectra, NLTEWFSR | 0.660 | 0.186 | 0.000 | 0.081 | 0.000 | 0.073 | 0.000 | 0.000 | ||
| 2 spectra, DLGGSGEGGAR | 0.725 | 0.155 | 0.000 | 0.092 | 0.000 | 0.028 | 0.000 | 0.000 | ||
| 3 spectra, QFGPTFALDTVHVDPVIR | 0.640 | 0.190 | 0.000 | 0.108 | 0.000 | 0.062 | 0.000 | 0.000 | ||
| 3 spectra, DNLIQMLSR | 0.718 | 0.158 | 0.000 | 0.124 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TYFSEEDVR | 0.594 | 0.142 | 0.029 | 0.050 | 0.000 | 0.186 | 0.000 | 0.000 | ||
| 10 spectra, GATLNPWR | 0.532 | 0.405 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | 0.000 | ||
| 3 spectra, FSAEVLGSLR | 0.576 | 0.140 | 0.190 | 0.000 | 0.000 | 0.000 | 0.095 | 0.000 | ||
| 1 spectrum, YGEICGFSDTNLQK | 0.615 | 0.167 | 0.088 | 0.130 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TLLEQLGGSGH | 0.674 | 0.108 | 0.000 | 0.000 | 0.000 | 0.219 | 0.000 | 0.000 | ||
| 2 spectra, SISATEAIQR | 0.765 | 0.140 | 0.000 | 0.025 | 0.000 | 0.071 | 0.000 | 0.000 | ||
| 1 spectrum, LNLDFR | 0.536 | 0.369 | 0.000 | 0.000 | 0.000 | 0.094 | 0.000 | 0.000 | ||
| 2 spectra, LYFQLR | 0.655 | 0.000 | 0.096 | 0.046 | 0.000 | 0.203 | 0.000 | 0.000 | ||
| 3 spectra, NLDALENAQAIK | 0.726 | 0.123 | 0.048 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, CTVVASVLGSGR | 0.810 | 0.000 | 0.014 | 0.176 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, EVLPLMNAAGSR | 0.608 | 0.206 | 0.040 | 0.000 | 0.000 | 0.147 | 0.000 | 0.000 | ||
| 2 spectra, LAYEGVSSR | 0.740 | 0.154 | 0.000 | 0.066 | 0.000 | 0.039 | 0.000 | 0.000 | ||
| 4 spectra, DLLLHDQCQITTLR | 0.750 | 0.000 | 0.123 | 0.127 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
29 spectra |
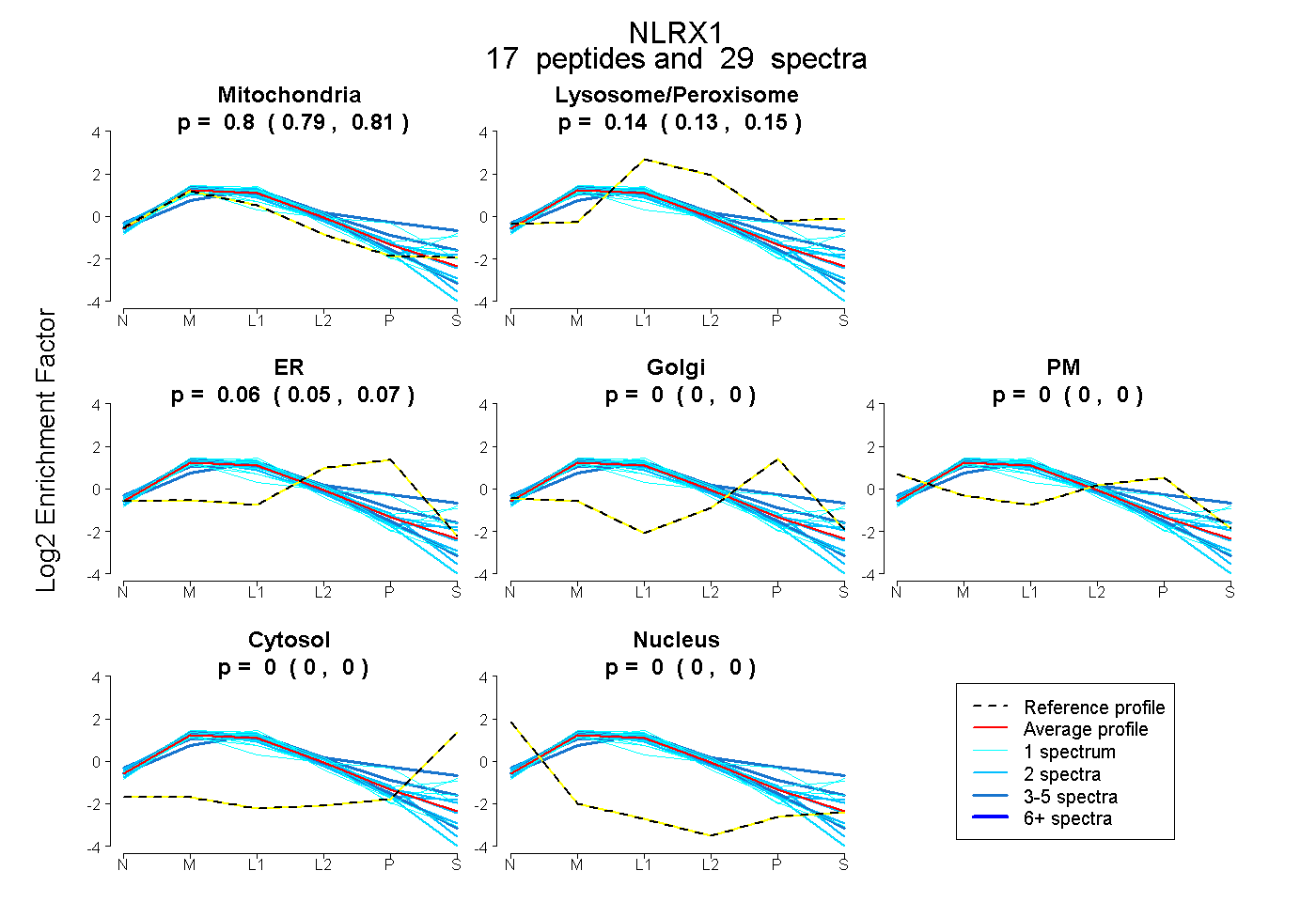 |
0.802 0.793 | 0.810 |
0.139 0.127 | 0.149 |
0.059 0.048 | 0.069 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
157 spectra |
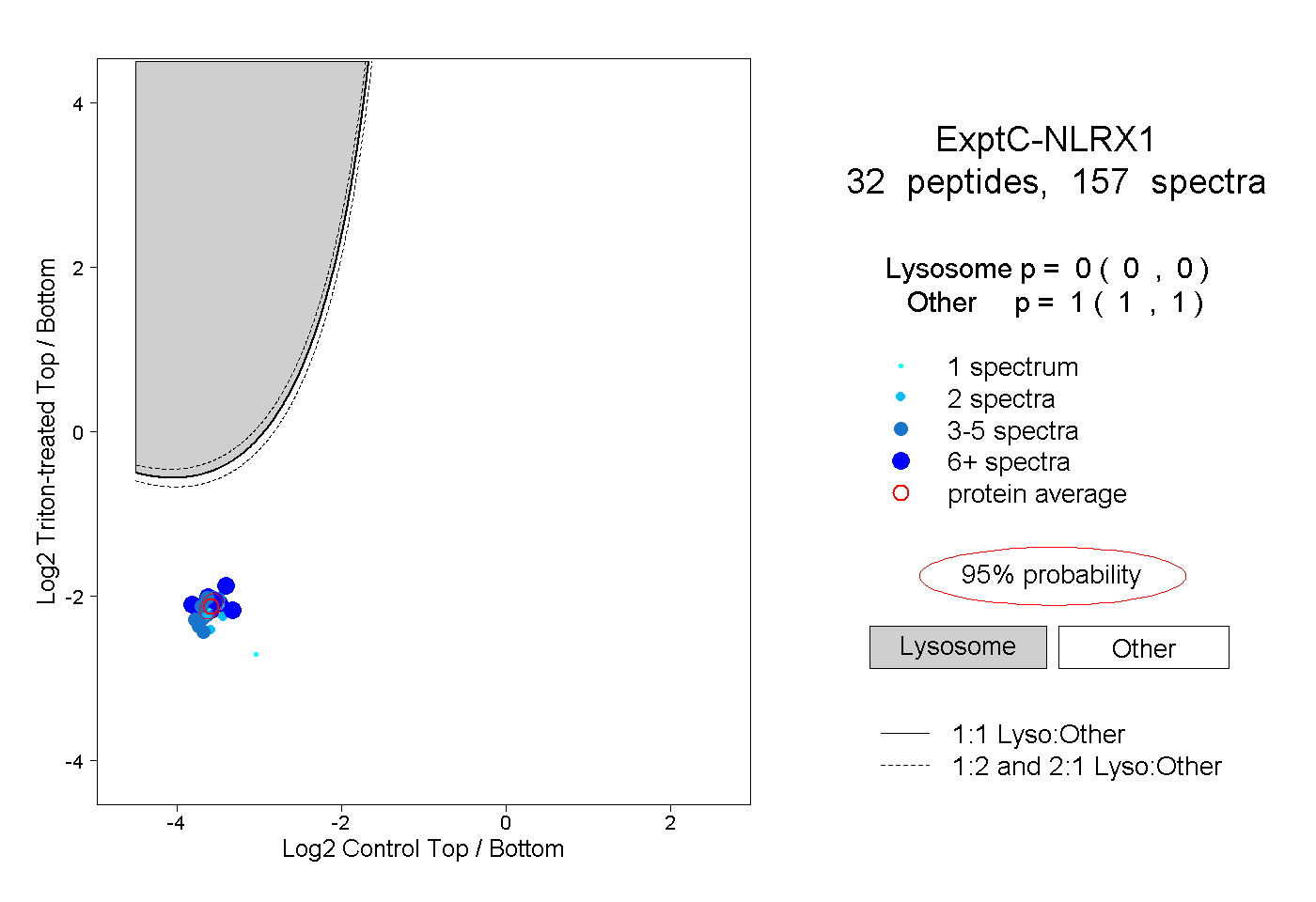 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
27 spectra |
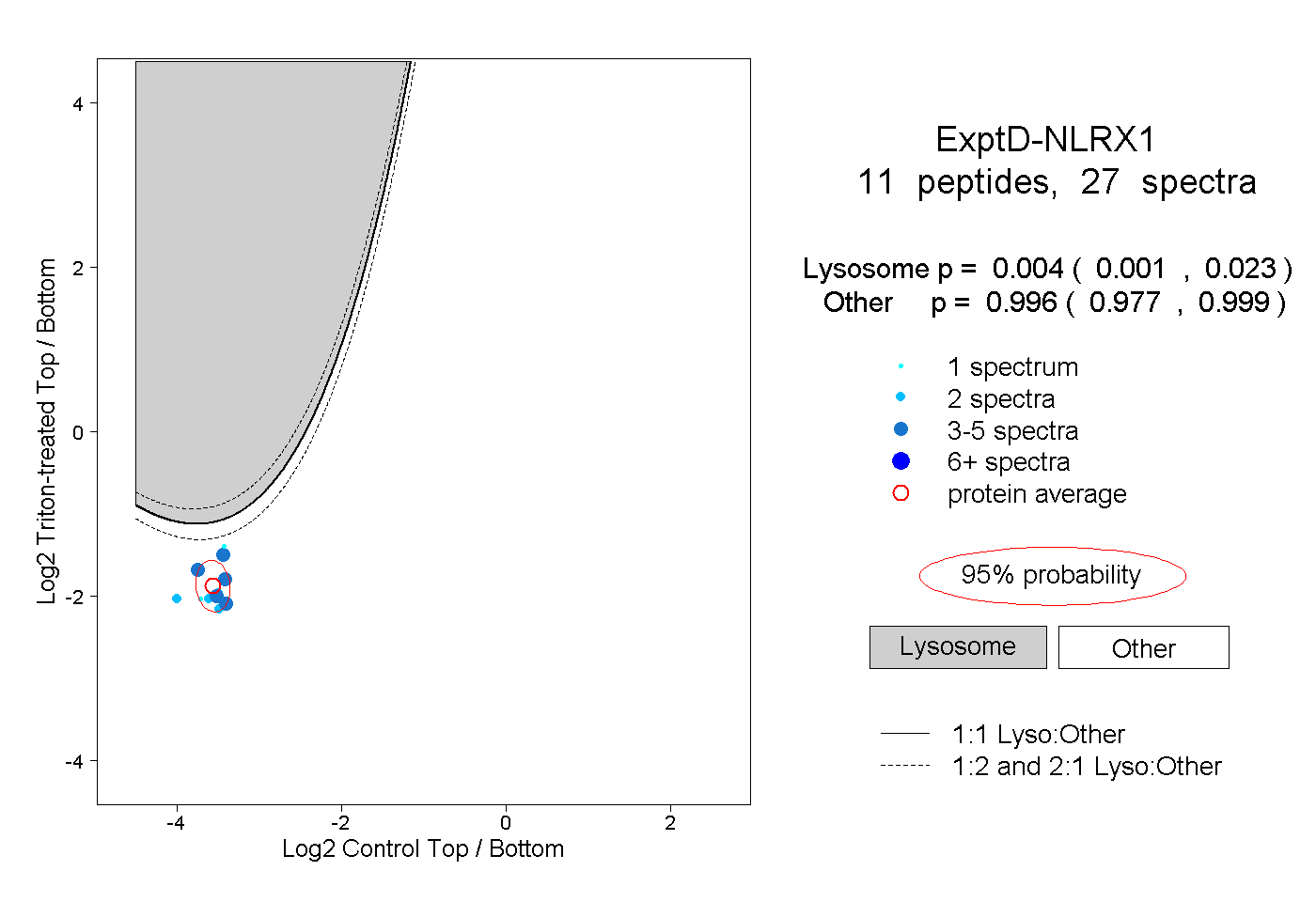 |
0.004 0.001 | 0.023 |
0.996 0.977 | 0.999 |