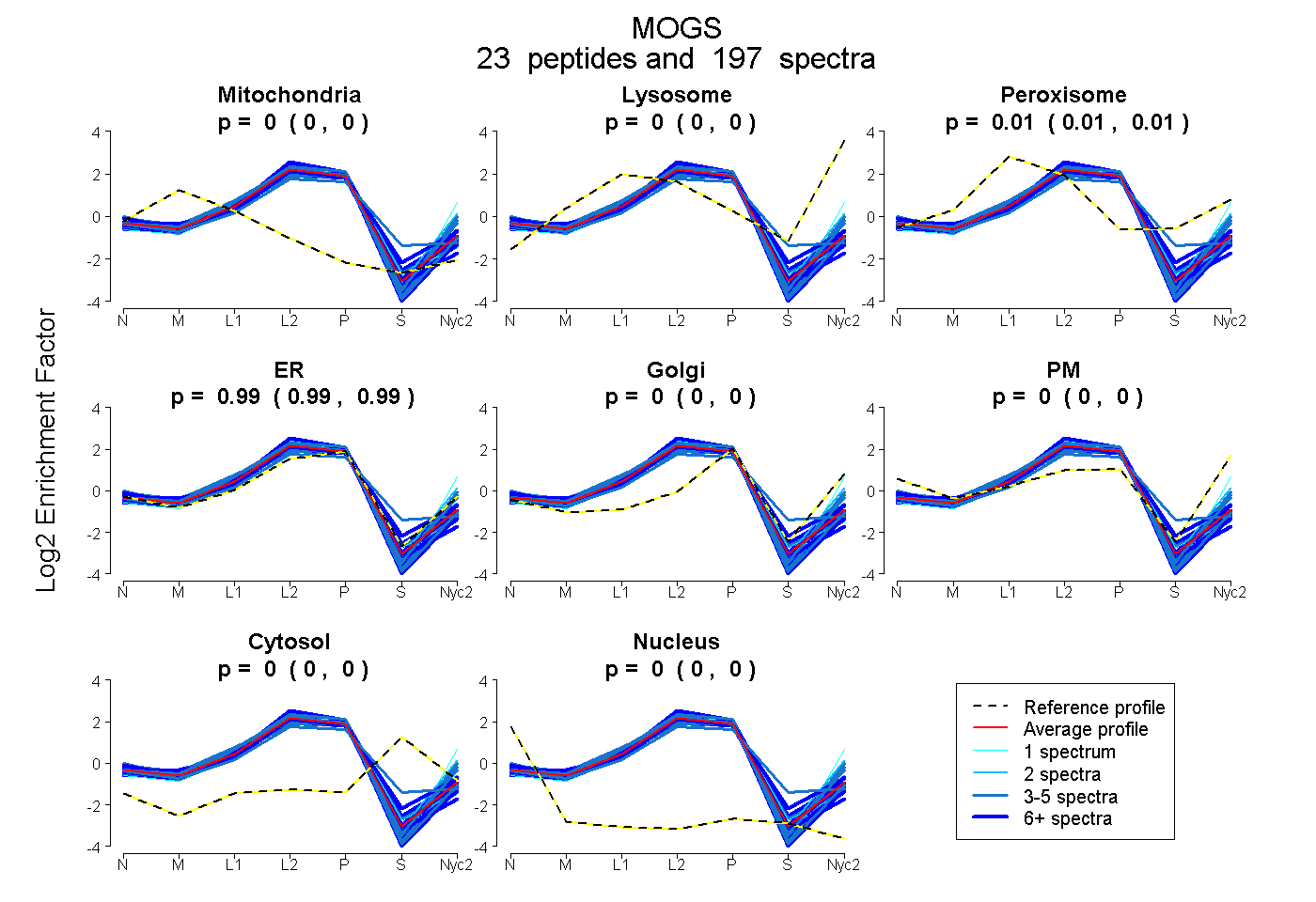
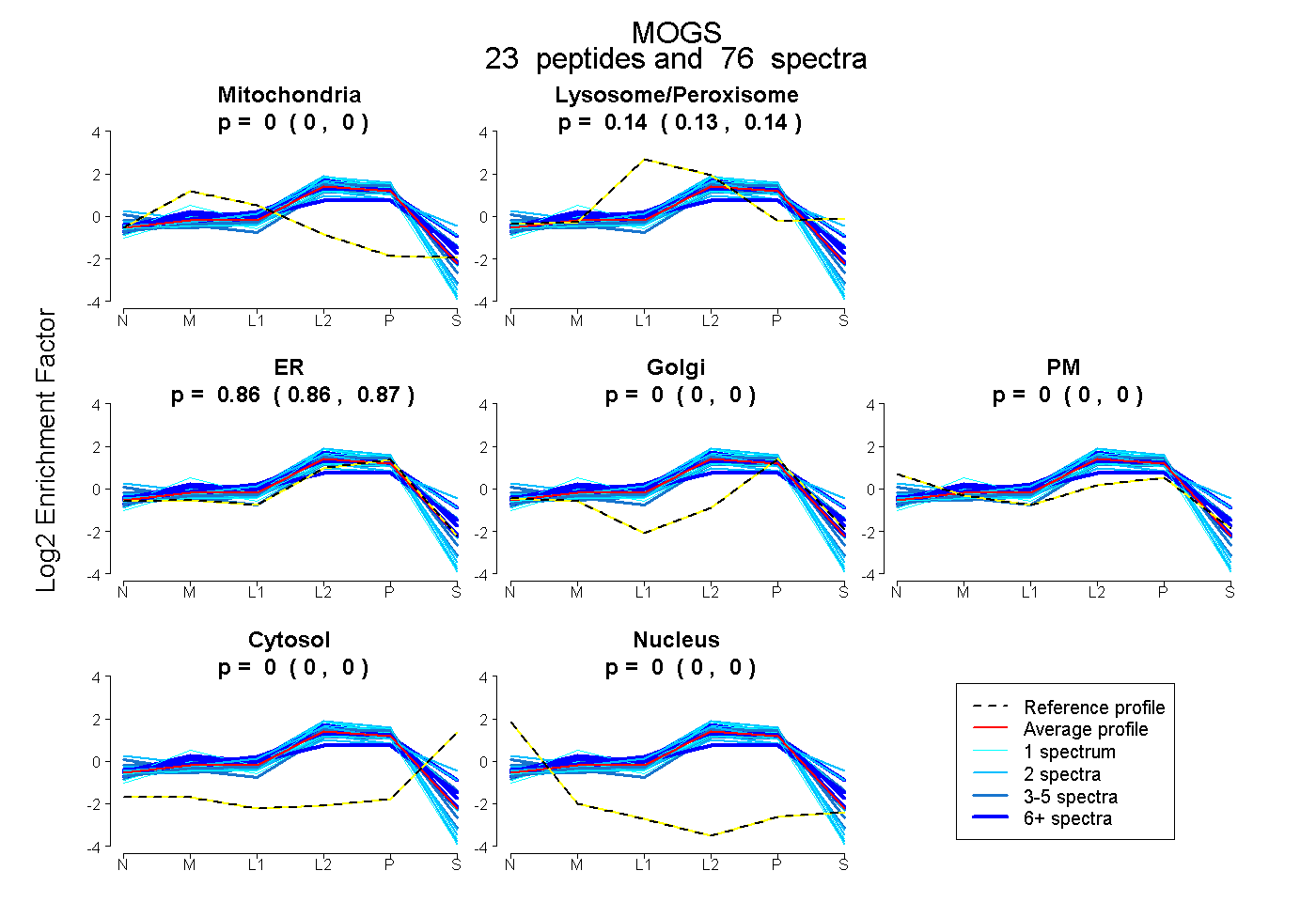
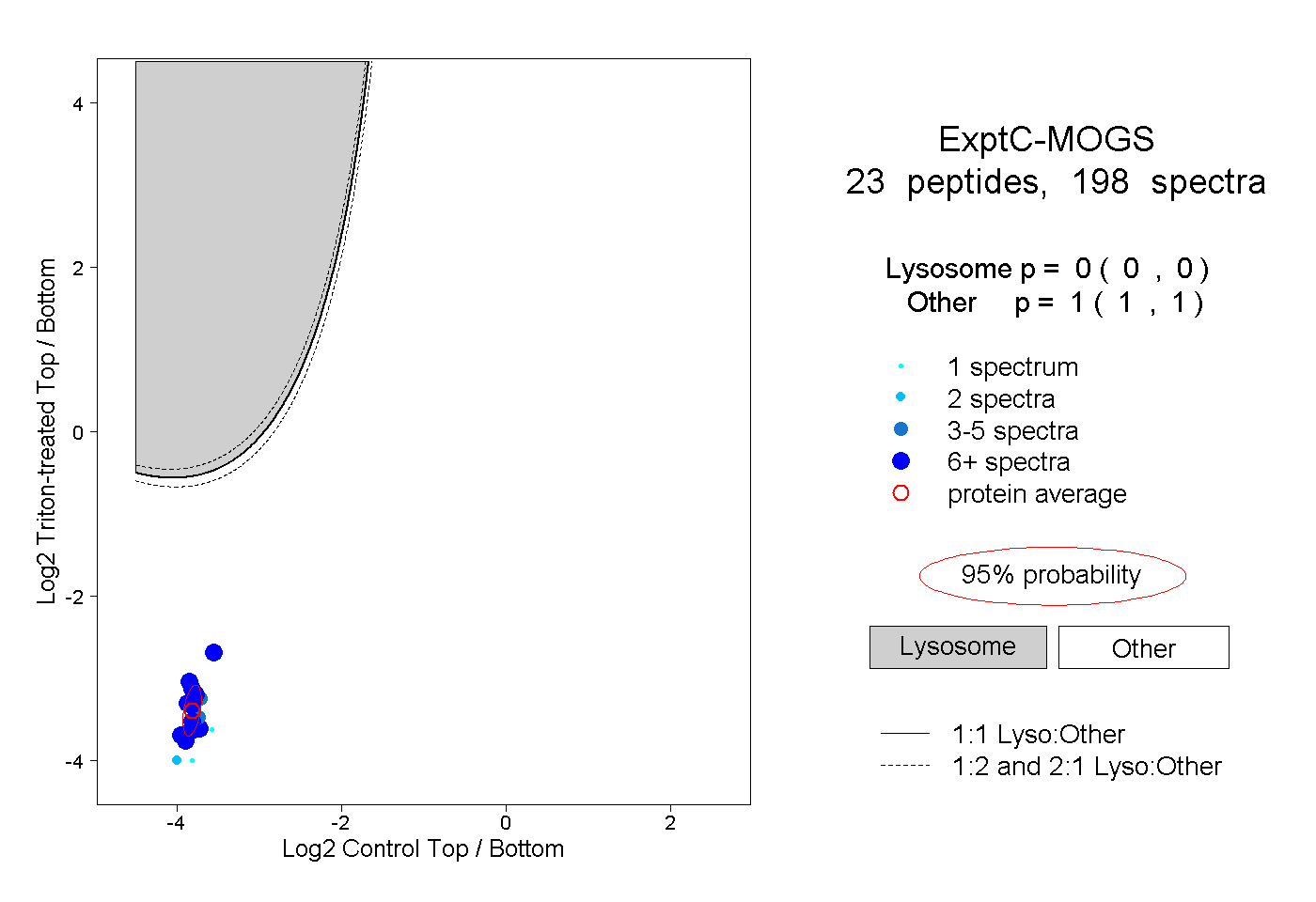
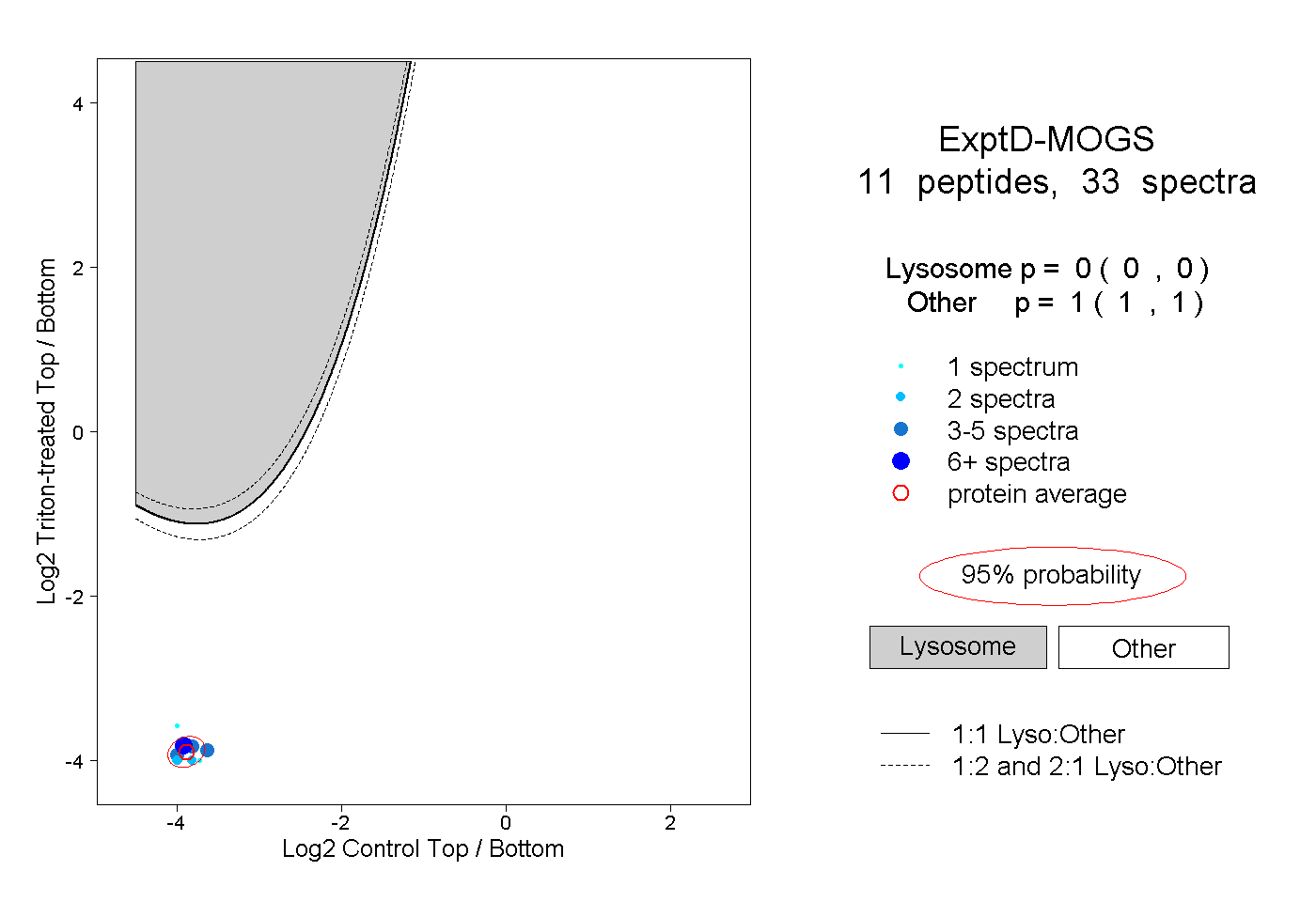
| 13 spectra, VVGRPPPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LTTEFVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, GFLWDEGFHQLVVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VEGPHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, APEDLAFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, CWVTLGAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, YLGLPGSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, TLPSGLDDYPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, ANVVSNVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, ALESHAAAFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, QHIYDGALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, LGPLLDVLADSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, VPPEFLVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AAAAEGARPLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, EQILGDEAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, SRPPQGLVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HLWSPFGLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, APFSVEFVFESGSAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NTEHDPPYWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DQASEQLVGGQLTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GPSGQGQFLVQQVTLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, MDPSLFPPVPLFSGVPSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, SLSASSLFYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |