peptides
spectra
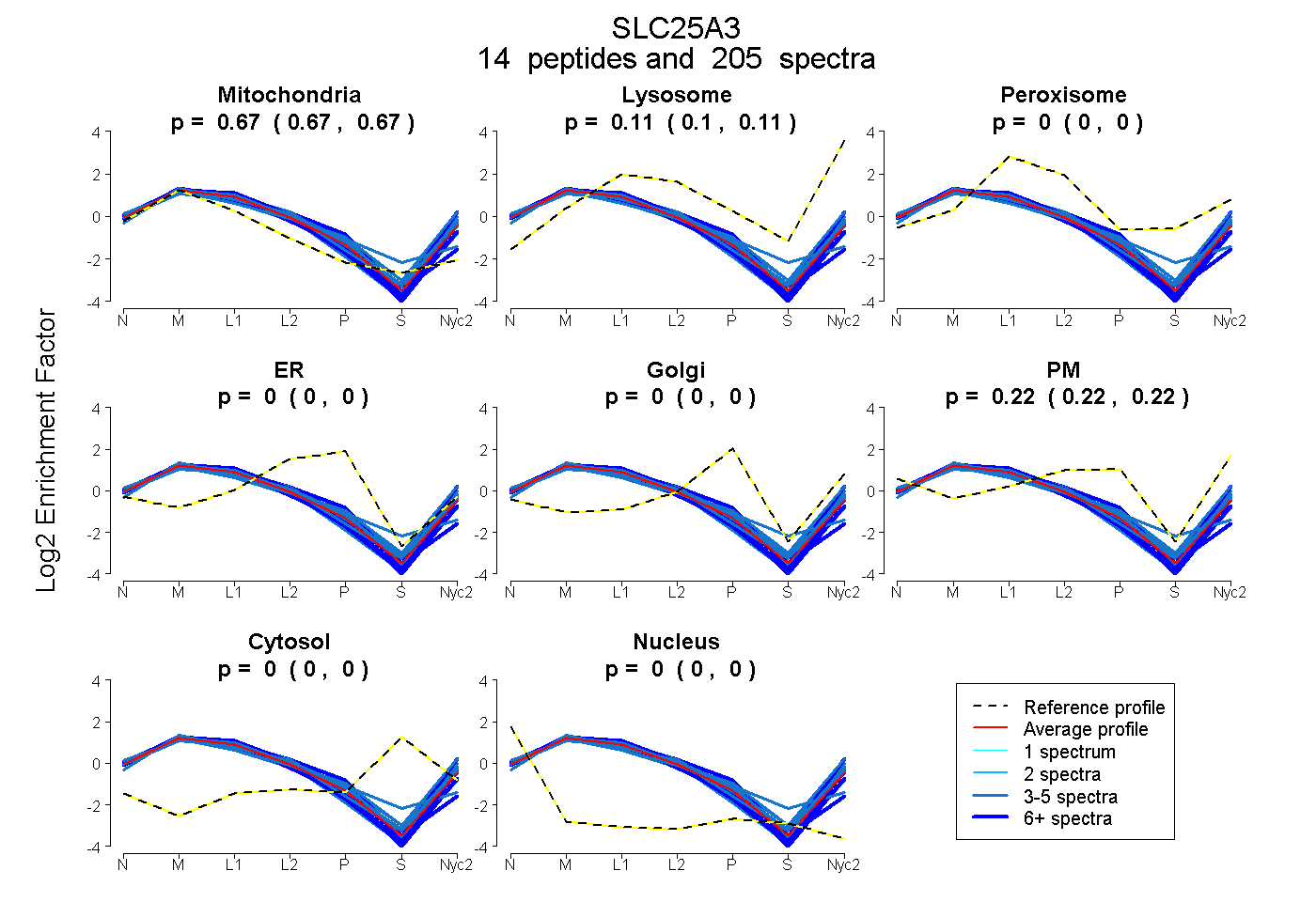
0.670 | 0.675
0.104 | 0.109
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.218 | 0.223
0.000 | 0.000
0.000 | 0.000
peptides
spectra
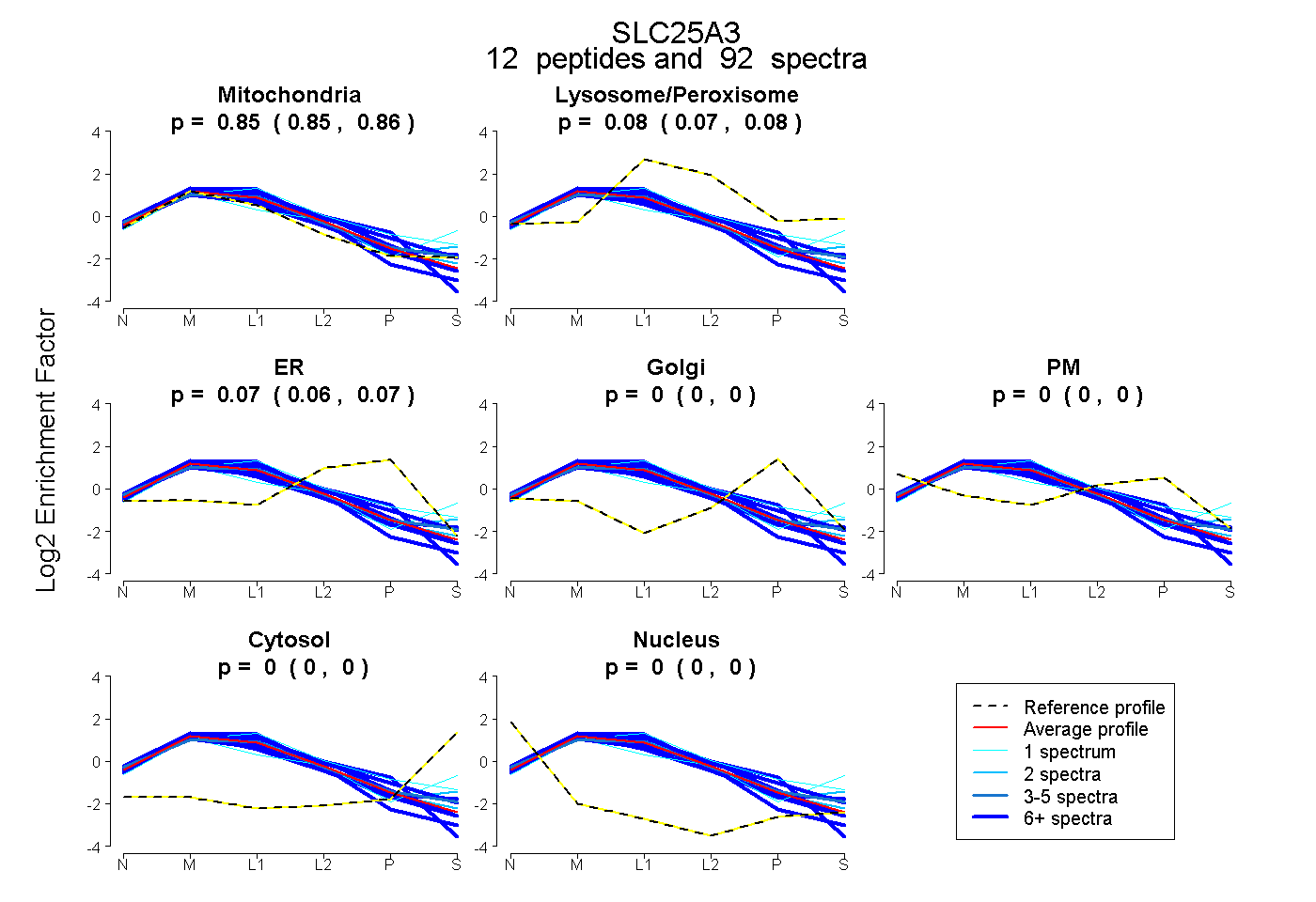
0.849 | 0.859
0.072 | 0.083
0.061 | 0.073
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
205 spectra |
 |
0.672 0.670 | 0.675 |
0.107 0.104 | 0.109 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.221 0.218 | 0.223 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
92 spectra |
 |
0.854 0.849 | 0.859 |
0.078 0.072 | 0.083 |
0.068 0.061 | 0.073 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, TVEALYK | 0.800 | 0.145 | 0.000 | 0.000 | 0.055 | 0.000 | 0.000 | |||
| 6 spectra, MQVDPQK | 0.710 | 0.112 | 0.134 | 0.000 | 0.044 | 0.000 | 0.000 | |||
| 1 spectrum, GWAPTLIGYSMQGLCK | 0.619 | 0.332 | 0.000 | 0.008 | 0.041 | 0.000 | 0.000 | |||
| 2 spectra, GIFNGFSITLK | 0.871 | 0.110 | 0.019 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 16 spectra, FVVPKPR | 0.736 | 0.000 | 0.264 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LPRPPPPEMPESLK | 0.686 | 0.170 | 0.000 | 0.000 | 0.000 | 0.143 | 0.000 | |||
| 12 spectra, GVAPLWMR | 0.823 | 0.048 | 0.128 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, FACFER | 0.978 | 0.022 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, GSTASQVLQR | 0.919 | 0.000 | 0.081 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, IQTQPGYANTLR | 0.932 | 0.041 | 0.027 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EEGLNAFYK | 0.841 | 0.138 | 0.000 | 0.000 | 0.000 | 0.021 | 0.000 | |||
| 11 spectra, FGFYEVFK | 0.812 | 0.188 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
901 spectra |
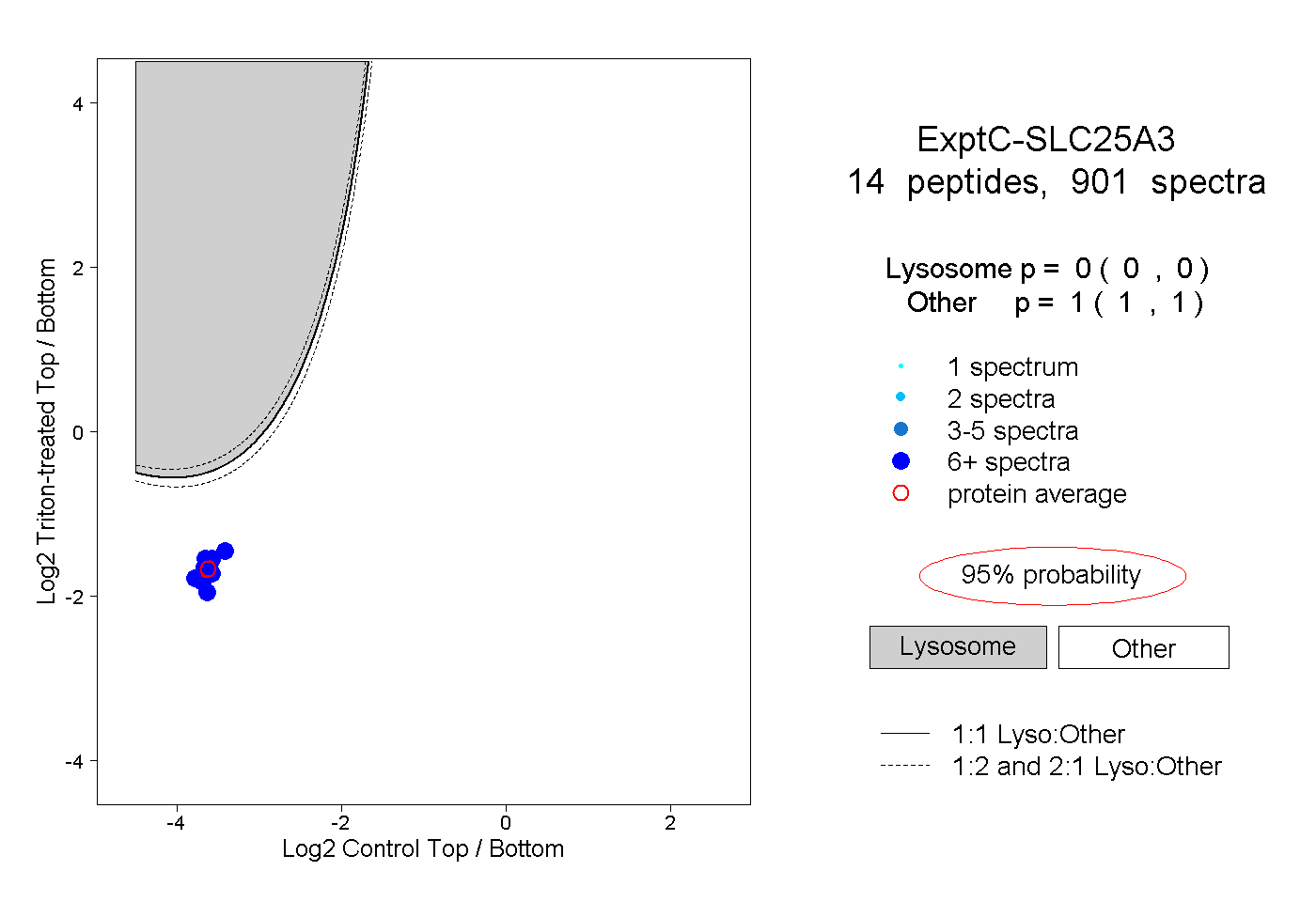 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
66 spectra |
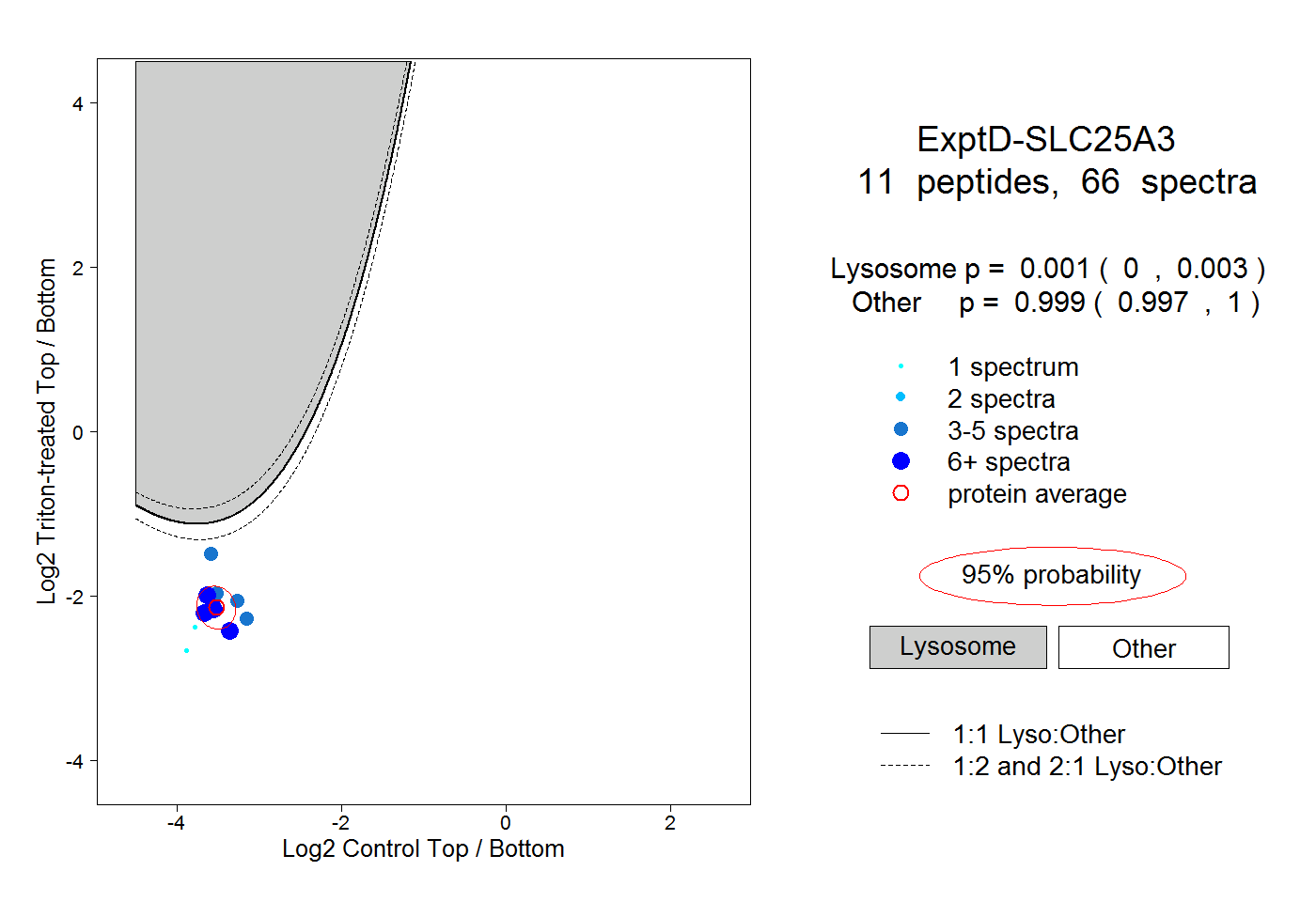 |
0.001 0.000 | 0.003 |
0.999 0.997 | 1.000 |